Evolución

A evolución é o cambio nas características herdadas das poboacións biolóxicas co paso das xeracións. Os procesos evolutivos dan lugar a diversidade en todos os niveis biolóxicos de organización, como as especies, os organismos individuais e as moléculas como o ADN e proteínas.[2] Todos os seres vivos da Terra descenden dun antepasado común (LUCA) que viviu hai entre 3 500 e 3 800 millóns de anos.[3] En xullo de 2016, os científicos informaron da identificación dun conxunto de 355 xenes procedentes de LUCA en todos os organismos vivos da Terra.[4] Os repetidos eventos de especiación e de diverxencia dos seres vivos poden inferirse do conxunto de trazos bioquímicos e morfolóxicos compartidos, ou das secuencias de ADN compartidas.[5] Estes trazos e secuencias homólogas son moi similares entre as especies que comparten un antepasado común máis recente, e poden utilizarse para reconstruír as historias evolutivas, utilizando tanto as especies existentes coma o rexistro fósil. Os padróns existentes de biodiversidade foron modelados pola especiación e pola extinción.[6]
Charles Darwin foi o primeiro que formulou un argumento científico para a teoría da evolución por selección natural e selección sexual. A evolución por selección natural é un proceso que se pode inferir de tres feitos sobre as poboacións: primeiro, prodúcese máis descendencia da que é posible que sobreviva; segundo, os trazos varían entre os individuos, o que orixina diferentes taxas de supervivencia e reprodución; e terceiro, as diferenzas nos trazos son herdables.[7] Así, cando morren os membros dunha poboación son substituídos pola proxenie dos pais que estaban mellor adaptados para sobrevivir e reproducirse no medio ambiente no cal ten lugar a selección natural. Este proceso crea e preserva trazos que son aparentemente axeitados para o seu papel funcional.[8] A selección natural é a única causa coñecida da adaptación biolóxica, pero non a única causa da evolución. Outras causas non adaptativas da evolución son a mutación e a deriva xenética.[9]
A inicios do século XX, os coñecementos da xenética clásica foron integrados coa teoría de Darwin da evolución por selección natural coa creación da disciplina da xenética de poboacións. A importancia da selección natural como causa da evolución foi aceptada noutras ramas da bioloxía. Ademais, as nocións que se mantiñan anteriormente sobre evolución, como a ortoxénese e o "progreso" quedaron obsoletas.[10] Os científicos continúan estudando varios aspectos da evolución formulando e poñendo a proba hipóteses, construíndo teorías, usando datos observacionais, e realizando experimentos de campo e de laboratorio. Os biólogos están de acordo en que a descendencia con modificacións é un dos feitos científicos establecidos con máis fiabilidade.[11] En termos de aplicacións prácticas, a comprensión da evolución foi instrumental para os desenvolvementos de varios campos científicos e industriais, incluíndo a agricultura, medicina, veterinaria e a bioloxía en xeral.[11][12][13] Os descubrimentos feitos na bioloxía evolutiva tiveron un impacto significativo non só nas áreas tradicionais da bioloxía senón tamén noutras disciplinas académicas, incluíndo a antropoloxía e a psicoloxía.[14][15]
Historia do pensamento evolucionista[editar | editar a fonte]
- Artigo principal: Historia do pensamento evolucionista.
A idea de que un tipo de animal podía descender doutro tipo de animal remóntase aos primeiros filósofos gregos presocráticos, como Anaximandro e Empédocles.[17] A diferenza destas visións materialistas, Aristóteles consideraba todas as cousas naturais, non só as viventes, como concrecións (entelequias) imperfectas de diferentes posibilidades naturais fixadas, o que se coñece como "formas", "ideas" ou (nas traducións latinas) "especies".[18][19] Isto formaba parte do coñecemento teleolóxico da natureza na cal todas as cousas estaban destinadas a xogar un papel na orde cósmica divina. O poeta e filósofo romano Lucrecio propuxo a posibilidade de que existisen cambios evolutivos nos organismos, na súa obra De rerum natura.[20][21] Variacións desta idea fixéronse comúns na Idade Media, e foron integradas dentro das ensinanzas cristiáns, pero Aristóteles non esixía que cada tipo real de animal correspondese a unha forma metafísica exacta, e deu exemplos específicos de como se podían chegar a formar novos tipos de seres vivos.[22]
No século XVII o novo método da ciencia moderna rexeitaba o enfoque de Aristóteles, e procuraba as explicacións dos fenómenos naturais nas leis da natureza, que eran as mesmas para todas as cousas visibles, e non necesitaba asumir ningunha categoría natural fixada, nin ningunha orde cósmica divina. Pero este novo enfoque tardou moito en aplicarse ás ciencias biolóxicas, que se converteron no último bastión do concepto de tipos naturais fixos. John Ray usou un dos termos anteriormente máis xerais para os tipos naturais fixos, "especies", para aplicalo aos tipos de animais e plantas, pero a diferenza de Aristóteles el identificou estritamente cada tipo de cousa viva como unha especie, e propuxo que cada especie podía definirse por características que se perpetuaban en cada xeración.[23] A clasificación biolóxica introducida por Carl von Linné en 1735 tamén consideraba que as especies eran fixas segundo os plans divinos.[24]
Outros naturalistas do seu tempo especularon sobre o cambio evolutivo das especies ao longo do tempo de acordo coas leis naturais. Maupertuis escribiu en 1751 sobre as modificacións naturais que ocorrían durante a reprodución e que se acumulaban ao longo de moitas xeracións para producir novas especies.[25] Buffon suxeriu que as especies podían dexenerar orixinando diferentes organismos, e Erasmus Darwin propuxo que todos os animais de sangue quente puideron descender dun só microorganismo (ou "filamento").[26] O primeiro esquema propiamente evolucionista foi a teoría da "transmutación" de Lamarck de 1809.[27] Esta teoría consideraba que a xeración espontánea producía continuamente formas de vida simples e orixinábase unha maior complexidade en liñaxes paralelas cunha tendencia inherente a progresar, e que a nivel local estas liñaxes se adaptaban ao medio ambiente ao herdaren cambios causados polo uso ou desuso de órganos feito polos seus pais.[28][29] Este último proceso denominouse despois "lamarckismo".[28][30][31][32] Estas ideas foron condenadas polos naturalistas establecidos como especulacións carentes de apoio empírico. En particular Georges Cuvier insistía en que as especies non estaban relacionadas entre si e eran fixas, as súas semellanzas reflectían o deseño divino para satisfacer as súas necesidades funcionais. Mentres tanto, William Paley desenvolveu as ideas de Ray do deseño benevolente no seu libro de 1802 Natural Theology or Evidences of the Existence and Attributes of the Deity (Teoloxía natural ou probas da existencia e atributos da deidade), que propoñía que as complexas adaptacións observadas eran evidencia do deseño divino, o cal Charles Darwin ao principio admiraba, pero despois acabou criticando.[33][34][35]
A ruptura fundamental co concepto de especie fixa (fixismo) en bioloxía empezou coa teoría da evolución por selección natural, que formulou Charles Darwin. Darwin, en parte influenciado polo An Essay on the Principle of Population (Ensaio sobre o principio da poboación) de Thomas Robert Malthus, fixo notar que o crecemento da poboación dos distintos seres vivos leva a unha "loita pola existencia" na cal as variacións favorables poderían prevalecer mentres que outras perecerían. En cada xeración, moitos dos descendentes non conseguen sobrevivir ata a idade reprodutiva debido á limitación dos recursos do seu medio. Isto podía explicar a formación dunha diversidade de animais e plantas a partir dun antepasado común por medio do funcionamento das leis naturais, que funcionaban igual para todo tipo de cousas.[36][37][38][39] Darwin estivo desenvolvendo a súa teoría da "selección natural" desde 1838 en adiante ata que Alfred Russel Wallace lle enviou unha teoría semellante en 1858. Ambos os dous presentaron documentos por separado á Sociedade linneana de Londres.[40] A finais de 1859, o libro publicado por Darwin A orixe das especies explicou a selección natural en detalle e dun modo que fixo que se producise unha crecente aceptación da evolución darwinista. Thomas Henry Huxley aplicou as ideas de Darwin aos humanos, usando a paleontoloxía e a anatomía comparada para proporcionar evidencias de que os homes e os simios compartían un antepasado común. Na súa época a algúns lles molestou esta idea, xa que implicaba que os humanos non ocupaban un sitio especial no Universo.[41]
Os mecanismos precisos da herdanza reprodutiva e da orixe dos novos trazos seguía sendo un enigma. Ao final da súa vida Darwin desenvolveu a súa teoría provisional da panxénese.[42] En 1865 Gregor Mendel informou que as características xenéticas se herdaban dunha maneira predicible por medio da distribución independente e a segregación de "elementos" (máis tarde chamados xenes). As leis de Mendel da herdanza finalmente substituirían á teoría da panxénese de Darwin.[43] Despois, August Weismann fixo a importante distinción entre as células da liña xerminal (liña dos espermatozoides e óvulos) e as células somáticas do corpo, demostrando que a herdanza se transmite só a través da liña xerminal (barreira de Weismann). Hugo de Vries conectou a teoría da panxénese de Darwin coa distinción de Weismann entre células xerminais e somáticas e propuxo que os panxenes de Darwin estaban concentrados no núcleo celular e cando se expresaban podían moverse ao citoplasma para cambiar a estrutura celular (o que hoxe sabemos que non é exactamente así). De Vries foi tamén un dos investigadores que fixo que se coñecesen os traballos de Mendel, e cría que os trazos mendelianos se debían á transferencia de variacións herdables na liña xerminal.[44] Para explicar como se orixinaban as novas variacións, De Vries desenvolveu unha teoría da mutación que orixinou unha división temporal entre os que aceptaban a evolución darwinista e os biométricos que apoiaban a de Vries.[29][45][46] Coa chegada do século XX, os pioneiros no campo da xenética de poboacións, como J. B. S. Haldane, Sewall Wright, e Ronald Fisher, estableceron os alicerces da evolución sobre unha base estatística robusta. Fíxose entón evidente a falsa contradición entre a teoría de Darwin, as mutacións xenéticas, e a herdanza mendeliana, que foron reconciliadas.[47]
Nas décadas de 1920 e 1930 a síntese evolutiva moderna conectou a selección natural, a teoría da mutación, e a herdanza mendeliana nunha teoría unificada que se aplicou de forma xeral en todas as pólas da bioloxía. A síntese moderna podía explicar os padróns observados nas especies en termos de poboacións, a través de fósiles transicionais en paleontoloxía, e por medio de complexos mecanismos celulares na bioloxía do desenvolvemento.[29][48] A publicación da estrutura do ADN por James Watson e Francis Crick en 1953 demostrou a base física da herdanza.[49] A bioloxía molecular mellorou moito a nosa comprensión das relacións entre xenotipo e fenotipo. Fixéronse tamén moitos avances en sistemática filoxenética, mapando a transición dos trazos xenéticos nun marco comparativo e comprobable que levou á publicación e uso de árbores filoxenéticas evolutivas.[50][51] En 1973, o biólogo evolucionista Theodosius Dobzhansky escribiu que "nada en bioloxía ten sentido se non está baixo a luz da evolución", porque explica as relacións do que antes parecían feitos inconexos da historia natural nun corpo de coñecementos coherente explicativo que describe e predí moitos feitos observables sobre a vida no noso planeta.[52] Desde entón, a síntese moderna ampliouse moito máis para explicar os fenómenos biolóxicos a través da escala integradora completa da xerarquía biolóxica, desde os xenes ata as especies. Esta ampliación denominouse bioloxía evolutiva do desenvolvemento.[53][54][55]
Herdanza[editar | editar a fonte]
- Véxase tamén: Xenética e Leis de Mendel.

A evolución nos organismos ocorre por medio de cambios nos trazos herdables (as características particulares dun organismo). Nos humanos, por exemplo, a cor dos ollos é unha característica herdada e un individuo pode herdar o "trazo ollos castaños" dun dos seus proxenitores.[56] Os trazos ou caracteres herdados están controlados por xenes e o conxunto completo de xenes do xenoma dun organismo coas variantes concretas que este posúe son o xenotipo dese organismo.[57]
O conxunto completo de trazos observables ou detectables que forman a estrutura e comportamento dun organismo denomínase fenotipo. Estes trazos orixínanse pola interacción do seu xenotipo co ambiente.[58] Como resultado, moitos aspectos do fenotipo dun organismo non se herdan. Por exemplo, o bronceado da pel depende da interacción entre o xenotipo dunha persoa e a luz do sol, polo que o bronceado non se transmite de pais a fillos. Porén, algunhas persoas póñense morenas con máis facilidade que outras, debido a diferenzas nos seus xenotipos; un exemplo extremo é o das persoas que herdan o carácter albinismo, que teñen falta do pigmento da pel melanina, non se poden poñer morenos e son moi propensos ás queimaduras solares.[59]
Os trazos herdables pasan dunha xeración á seguinte por medio do ADN cromosómico, unha molécula que codifica a información xenética.[57] O ADN é un longo polímero composto por catro tipo de bases. A secuencia de bases dunha determinada molécula de ADN especifica a información xenética, de maneira similar a como unha secuencia de letras serve para escribir unha frase. Antes de que a célula se divida, o ADN é copiado, para que cada unha das células fillas resultantes herde a secuencia de ADN. As porcións dunha molécula de ADN que especifican unha soa unidade funcional denomínanse xenes, e os diferentes xenes teñen diferentes secuencias de bases. Nas células, as longas fibras de ADN asociadas con proteínas forman estruturas condensadas chamadas cromosomas. A localización específica dunha secuencia de ADN nun cromosoma denomínase locus. Se a secuencia de ADN nun locus varía entre individuos, as diferentes formas desta secuencia denomínanse alelos. Polo tanto, un xene dunha especie pode ter varios alelos na poboación. As secuencias de ADN poden cambiar por medio de mutacións, orixinando novos alelos. Se ten lugar unha mutación nun xene, o novo alelo pode afectar o trazo que ese xene controla (ou sobre o que inflúe), alterando o fenotipo do organismo.[60] Porén, aínda que esta simple correspondencia entre alelo e trazo (ou carácter) funciona nalgúns casos, a maioría dos trazos son máis complexos e están controlados por varios xenes que interaccionan (hai moitas posibilidades como os caracteres cuantitativos, epistase etc.).[61][62]
Descubrimentos máis recentes confirmaron importantes exemplos de cambios herdables que non se poden explicar por cambios na secuencia de nucleótidos do ADN, que se clasifican como sistemas de herdanza epixenéticos.[63] A metilación do ADN que marca a cromatina, os bucles metabólicos autosostibles, o silenciamento de xenes por interferencia de ARN e a conformación tridimensional de certas proteínas (como os prións) son áreas onde se descubriron sistemas de herdanza epixenética a nivel de organismo.[64][65] Os biólogos do desenvolvemento suxiren que as complexas interaccións nas redes xenéticas e a comunicación entre as células poden orixinar variacións herdables que poden subxacer na mecánica da plasticidade do desenvolvemento e a canalización.[66] A heredabilidade pode tamén ocorrer a grandes escalas, como pode ser, por exemplo, a herdanza ecolóxica polo proceso de construción de nicho, que se define polas actividades regulares e repetidas dos organismos no seu ambiente. Isto xera un legado de efectos que modifica e retroalimenta o réxime de selección de subseguintes xeracións. Os descendentes herdan xenes xunto coas características ambientais xeradas polas accións ecolóxicas dos seus devanceiros.[67] Outros exemplos de heredabilidade na evolución que non están baixo o control directo dos xenes son a herdanza de trazos culturais e a simbioxénese.[68][69]
Variabilidade[editar | editar a fonte]


- Véxase tamén: Xenética de poboacións.
O fenotipo de cada organismo individual depende do seu xenotipo e da influencia do ambiente no que vive. Unha parte substancial da variación nos fenotipos dunha poboación débese á diferenza nos seus xenotipos.[62] A síntese evolutiva moderna define evolución como o cambio co paso do tempo nesta variabilidade xenética. A frecuencia dun determinado alelo faise máis ou menos prevalente en relación con outras formas dese xene. A variabilidade desaparece cando un novo alelo chega ao punto en que se fixa, é dicir, cando desaparece totalmente da poboación ou substitúe por completo o alelo ancestral.[70]
A selección natural só causa evolución se hai variabilidade xenética dabondo nunha poboación. Antes do descubrimento da xenética mendeliana, unha hipótese habitual era a herdanza mesturada. Pero con este tipo de herdanza, as variacións xenéticas perderíanse rapidamente, facendo imposible a evolución por selección natural. A lei ou principio de Hardy-Weinberg é unha solución para explicar como se mantén a variabilidade nunha poboación con herdanza mendeliana. As frecuencias dos alelos (variacións nun xene) permanecen constantes en ausencia de selección, mutación, migración e deriva xenética (véxase máis abaixo).[71]
A variabilidade procede das mutacións que experimenta o material xenético, da redistribución dos xenes por medio da reprodución sexual e da migración entre poboacións (fluxo xénico). Malia a constante introdución de novas variacións polas mutacións e o fluxo xénico, a maioría do xenoma dunha especie é idéntico en todos os individuos desa especie.[72][73] Porén, mesmo se hai só relativamente poucas diferenzas no xenotipo isto pode producir grandes diferenzas no fenotipo: por exemplo, os chimpancés e os humanos difiren en só un 5% dos seus xenomas.[74]
Mutación[editar | editar a fonte]
- Artigo principal: Mutación.

As mutacións son cambios na secuencia de ADN do xenoma dunha célula. Cando ocorre unha mutación, pode non ter efecto, alterar o produto dun xene ou impedir que o xene funcione. Baseándose nos estudos realizados na mosca Drosophila melanogaster, suxeriuse que se unha mutación cambia a proteína producida por un xene, isto seguramente será prexudicial, xa que aproximadamente o 70% destas mutacións teñen efectos daniños, e o resto en canto aos seus efectos son neutras ou lixeiramente beneficiosas.[75]
As mutacións poden afectar a grandes seccións dun cromosoma, que se poden duplicar (xeralmente por recombinación xenética), o cal pode introducir copias extra dun xene nun xenoma.[76] As copias extra dos xenes son unha fonte importante da materia prima necesaria para que evolucionen novos xenes.[77] Isto é importante porque a maioría dos novos xenes evolucionan dentro de familias xénicas a partir de xenes preexistentes que comparten antepasados comúns.[78] Por exemplo, o ollo humano utiliza catro xenes para construír estruturas que captan a luz: tres son para a visión da cor (conos) e unha para a visión nocturna (bastón), pero os catro descenden dun só xene ancestral.[79]
Os novos xenes poden xerarse a partir dun xene ancestral se unha copia orixinada por duplicación muta e adquire unha nova función. Este proceso é máis fácil unha vez que o xene se duplicou porque iso incrementa a redundancia do sistema (a mesma cousa fana dous xenes); un xene dese par pode adquirir unha nova función mentres que a outra copia continúa realizando a súa función orixinal.[80][81] Outros tipos de mutacións poden mesmo xerar xenes completamente novos a partir de ADN que previamente era non codificante.[82][83]
A xeración de novos xenes pode tamén implicar a duplicación de pequenas partes de varios xenes, e estes fragmentos despois poden recombinarse para formar novas combinacións con novas funcións.[84][85] Cando os novos xenes se ensamblan a partir do rearranxo de partes preexistentes, os dominios proteicos actúan como módulos con funcións independentes simples, que se poden mesturar e unir para producir novas combinacións con novas e complexas funcións.[86] Por exemplo, as policétido sintases son grandes encimas que producen antibióticos; estes encimas conteñen ata cen dominios independentes, cada un dos cales cataliza un paso do proceso xeral da síntese, como un paso nunha cadea de montaxe.[87]
Sexo e recombinación[editar | editar a fonte]
- Véxase tamén: Reprodución sexual e Recombinación xenética.
Nos organismos asexuais, os xenes hérdanse todos xuntos, ou ligados, xa que non se poden mesturar con outros xenes doutros individuos durante a reprodución. Polo contrario, a descendencia dos organismos sexuais contén mesturas aleatorias dos cromosomas dos seus proxenitores que se formaron por distribución independente (tipicamente a metade dos cromosomas procede da nai e o outra metade do pai). Nun proceso relacionado chamado recombinación homóloga, os organismos sexuais intercambian ADN entre dous cromosomas que se corresponden (os chamados pares de cromosomas homólogos).[88] A recombinación e a distribución independente non alteran as frecuencias dos alelos, pero si crean novas combinacións de alelos que levará o individuo, producindo unha descendencia con novas combinacións de alelos, que non van ser iguais ás dos seus pais.[89] O sexo xeralmente incrementa a variabilidade xenética e pode incrementar a taxa de evolución.[90][91]
Fluxo xénico[editar | editar a fonte]
- Artigos principais: Fluxo xénico, Transferencia horizontal de xenes e Híbrido (bioloxía).
O fluxo xénico ou xenético é o intercambio de xenes entre as poboacións dunha especie e entre especies.[92] Xa que logo, pode ser unha fonte de variabilidade nova para unha poboación ou especie. O fluxo xénico pode ser causado polo movemento de individuos entre poboacións separadas dunha especie, como pode ser o movemento de ratos de poboacións do interior do continente cara ás poboacións costeiras, ou o movemento de pole entre plantas herbáceas tolerantes a metais pesados (que viven en áreas contaminadas con eses metais) e outras sensibles a eses metais.
A transferencia de xenes entre especies distintas inclúe a formación de organismos híbridos e o transferencia horizontal de xenes. A transferencia horizontal de xenes é a transferencia de material xenético dun organismo a outro que non forma parte da súa proxenie, e é máis común entre as bacterias.[93] En medicina, isto contribúe ao espallamento da resistencia a antibióticos, que ocorre cando unha bacteria adquire xenes de resistencia transferidos doutra especie (ou cepa) coa que convive.[94] A transferencia horizontal de xenes desde as bacterias aos eucariotas tamén ocorreu, como nos lévedos Saccharomyces cerevisiae e no escaravello Callosobruchus chinensis.[95][96] Un exemplo de transferencia a grande escala son os eucariotas rotíferos bdeloideos, que recibiron todo un conxunto de xenes das bacterias, fungos e plantas.[97] Os virus poden tamén transferir ADN dun organismo a outro, mesmo de distintos dominios dos seres vivos.[98]
A transferencia de xenes a grande escala ocorreu tamén entre os antepasados das células eucariotas e as bacteria, durante a adquisición dos cloroplastos e mitocondrias mediante un proceso de endosimbiose. É posible que os eucariotas como tales se orixinasen por transferencia horizontal de xenes entre as bacterias e as arqueas.[99]
Mecanismos[editar | editar a fonte]

Desde unha perspectiva neodarwinista, a evolución ocorre cando se producen cambios na frecuencia dos alelos nunha poboación de organismos que se poden aparear entre si.[71] Por exemplo, se o alelo para a cor negra nunha poboación de avelaíñas (lepidópteros) se fai máis común, iso supón un cambio evolutivo. Os mecanismos que poden orixinar estes cambios nas frecuencias dos alelos son a selección natural, a deriva xenética, o autostop xenético, a mutación e o fluxo xénico.
Selección natural[editar | editar a fonte]
- Artigos principais: Selección natural e Fitness (bioloxía).
A evolución por medio da selección natural é o proceso polo cal as mutacións xenéticas que melloran a reprodución (posibilidade de deixar fillos) fanse máis comúns e mantéñense en sucesivas xeracións dunha poboación. A miúdo tense considerado como un mecanismo "evidente" porque se segue necesariamente de tres simples feitos:
- A variación herdable existe nas poboacións de organismos.
- Os organismos producen máis proxenie da que pode sobrevivir.
- Esta descendencia varía na súa capacidade de sobrevivir e reproducirse.
Estas condicións producen unha competición entre os organismos por sobrevivir e reproducirse. En consecuencia, os organismos con trazos ou características que lles dan vantaxe sobre os seus competidores transmiten eses trazos vantaxosos aos seus fillos, mentres que os trazos que non confiren vantaxe non se transmiten á seguinte xeración na mesma proporción.[100]
O concepto central de selección natural é a chamada eficacia biolóxica, aptitude biolóxica ou fitness evolutiva dun organismo.[101] A fitness mídese pola capacidade dun organismo de sobrevivir e reproducirse, o cal determina a magnitude da súa contribución xenética á seguinte xeración.[101] Porén, a fitness dun organismo non é o mesmo que o seu número total de fillos, senón que vén indicada pola proporción de xeracións seguintes que levan os xenes dese organismo .[102] Por exemplo, se un organismo puido sobrevivir ben e reproducirse rapidamente, pero a súa descendencia estaba formada por individuos que eran todos demasiado pequenos e febles como para sobrevivir, este organismo vai facer finalmente unha contribución xenética pequena ás futuras xeracións (haberá poucos xenes procedentes del nas seguintes xeracións) e entón habería que considerar que tiña unha baixa fitness.[101]
Se un alelo incrementa a fitness máis que outros alelos dun determinado xene, entón con cada xeración ese alelo farase máis común na poboación. Estes trazos dise que son "seleccionados favorablemente". Exemplos de trazos que poden incrementar a fitness son os que melloran a supervivencia e incrementan a fecundidade. Inversamente, a diminución da fitness causada por ter alelos menos beneficiosos ou deletéreos fai que eses alelos se fagan máis raros (son "seleccionados en contra").[103] É importante subliñar que a fitness dun alelo non é unha característica fixada; porque se se producen cambios no ambiente, trazos que eran previamente neutrais ou daniños poden pasar a ser beneficiosos, e outros que previamente eran beneficiosos poden pasar a ser prexudiciais.[60] Porén, mesmo se a dirección da selección se inverte deste modo, os trazos que se perderon no pasado poden non reevolucionar de forma idéntica (ver lei de Dollo).[104][105]

A selección natural nunha poboación dun trazo que pode variar nun rango de valores, como a altura, pode clasificarse en tres tipos. O primeiro é a selección direccional, que é un cambio no valor medio dun trazo co tempo (por exemplo, organismos que se van facendo pouco a pouco máis altos).[106] Outro tipo é a selección disruptiva, que é a selección en favor dos valores extremos do trazo, que con frecuencia dá lugar a que se fagan máis comúns dous valores diferentes moi separados, e haxa unha selección en contra dos valores medios. Isto ocorre, por exemplo, cando tanto os organismos altos coma os baixos teñen unha vantaxe, pero non os de tamaños medios. Finalmente, na selección estabilizante hai selección en contra dos trazos extremos tanto os moi elevados como os moi pequenos, o que fai que diminúa a varianza arredor do valor medio e haxa menos diversidade.[100][107] Isto faría, por exemplo, que os organismos se fixeran pouco a pouco todos da mesma altura.
Un caso especial de selección natural é a selección sexual, que é a selección a favor de calquera trazo que incremente o éxito no apareamento ao incrementar o atractivo dun organismo para conseguir potenciais parellas.[108] Os trazos que evolucionaron por medio da selección sexual son particularmente salientables nos machos dalgunhas especies animais. A pesar de que características como ter cornamentas incómodas, chamadas de apareamento ou brillantes cores que poden atraer a atención dos depredadores, fan decrecer a supervivencia dos machos,[109] esta desvantaxe compénsase co seu maior éxito reprodutivo.[110]
A selección natural na maior parte dos casos fai da "natureza" o árbitro que determina que individuos ou trazos individuais é máis probable que sobrevivan. A "natureza" neste sentido significa un ecosistema, que é o sistema no cal os organismos interaccionan con todos os demais elementos que os rodean, tanto abióticos (físicos, químicos) coma bióticos (seres vivos), no seu medio ambiente local. Eugene Odum, fundador da ecoloxía, definiu ecosistema como: "Calquera unidade que inclúa todos os organismos...dunha determinada área que interaccionan co ambiente físico para que un fluxo de enerxía leve a definir claramente estruturas tróficas, diversidade biótica e ciclos materiais (por exemplo, o intercambio de materiais entre as partes vivas e non vivas) nese ecosistema."[111] Cada poboación nun ecosistema ocupa un diferente nicho ecolóxico ou posición, establecendo distintas relacións con outras partes do sistema. Estas relacións implican a historia da vida do organismo, a súa posición na cadea trófica e a súa distribución xeográfica. Esta comprensión ampla da natureza permite aos científicos delinear forzas específicas que, en conxunto, comprenden a selección natural.
A selección natural pode actuar en diferentes niveis de organización, como os xenes, células, individuos, grupos de individuos e especies.[112][113][114] A selección pode actuar a múltiples niveis simultaneamente.[115] Un exemplo de selección que ocorre a un nivel inferior ao de individuo é a dos xenes chamados transposóns, que poden replicarse e espallarse por todo o xenoma.[116] A selección a nivel superior ao de individuo, como a selección de grupo, pode permitir a evolución da cooperación, como se discutiu antes.[117]
Mutación nesgada[editar | editar a fonte]
Ademais de ser unha das fontes principais de variabilidade, a mutación pode tamén funcionar como un mecanismo evolutivo cando hai diferentes probabilidades a nivel molecular de que ocorran as mutacións, un proceso que se coñece como nesgo na mutación.[118] Se temos dous xenotipos, por exemplo un co nucleótido G e outro co nucleótido A na mesma posición, que teñen a mesma fitness, pero a mutación de G a A ocorre con máis frecuencia que a mutación de A a G, entón os xenotipos con A tenderán a evolucionar.[119] Diferentes nesgos nas mutacións de inserción fronte a deleción en distintos taxons poden causar a evolución de diferentes tamaños xenómicos.[120][121] O nesgo mutacional ou de desenvolvemento foi tamén observado na evolución morfolóxica.[122][123] Por exemplo, segundo a teoría da evolución de fenotipo primeiro, as mutacións poden causar eventualmente a asimilación xenética de trazos que eran previamente inducidos polo ambiente.[124][125]
Os efectos do nesgo mutacional superpóñense a outros procesos. Se a selección favorece unha das dúas mutacións, pero non hai vantaxe extra de telas as dúas á vez, entón a mutación que ocorre con maior frecuencia é a que máis probablemente quedará fixada na poboación.[126][127] As mutacións que orixinan a perda da función dun xene son moito máis comúns que as mutacións que producen un novo xene completamente funcional. A maioría das mutacións de perda de función sofren unha selección en contra. Pero cando a selección é feble, o nesgo mutacional cara á perda de función pode afectar á evolución.[128] Por exemplo, os pigmentos xa nos son útiles cando os animais viven en covas, e tenden a perderse.[129] Este tipo de perda de función pode ocorrer a causa do nesgo mutacional, e/ou porque a función ten un custo, e unha vez que desaparece o beneficio que proporcionaba a función, a selección natural leva á súa perda. A perda da capacidade de esporulación con nesgo mutacional en certas bacterias durante a súa evolución no laboratorio parece que é causada polo nesgo na mutación, máis que por selección natural contra o custo de manter a capacidade de esporulación.[130] Cando non hai selección a favor da perda de función, a velocidade á cal evoluciona a perda depende máis do grao de mutación que do tamaño efectivo de poboación,[131] indicando que foi dirixida máis polo nesgo na mutación que pola deriva xenética.
Deriva xenética[editar | editar a fonte]
- Artigos principais: Deriva xenética e Tamaño efectivo de poboación.

A deriva xenética é o cambio na frecuencia dos alelos dunha xeración á seguinte que se produce debido a que os alelos están suxeitos a erros de mostraxe.[132] Como resultado, cando están ausentes forzas selectivas ou estas son relativamente febles, as frecuencias alélicas tenden a "derivar" subindo ou baixando aleatoriamente. Esta deriva detense cando un alelo finalmente queda fixado, ou desaparece da poboación, ou substitúe completamente os outros alelos. A deriva xenética pode eliminar algúns alelos da poboación debido só á sorte. Mesmo en ausencia de forzas selectivas, a deriva xenética pode orixinar dúas poboacións separadas que empezaron tendo a mesma estrutura xenética pero que derivaron separándose en dúas poboacións diverxentes con diferentes conxuntos de alelos.[133]
É xeralmente difícil medir a importancia relativa dos procesos de selección e os neutros, incluíndo a deriva.[134] A importancia comparativa das forzas adaptativas e non adaptativas na dirección do cambio evolutivo é unha área na que se está a investigar dende comezos do século XX.[135]
A teoría neutralista da evolución molecular propón que a maioría dos cambios evolutivos son o resultado da fixación de mutacións neutras por deriva xenética.[9] Polo tanto, neste modelo a maioría dos cambios xenéticos na poboación son o resultado da presión de mutación constante e a deriva xenética.[136] Esta forma da teoría neutralista foi en gran medida abandonada, xa que non parece cadrar coa variabilidade xenética observada na natureza.[137][138] Porén, unha versión deste modelo máis recente e con mellores apoios é a teoría case neutralista da evolución molecular, na que unha mutación que sería neutra nunha pequena poboación non é necesariamente neutra nunha poboación grande.[100] Outras teorías alternativas propoñen que a deriva xenética queda empequenecida por outras forzas estocásticas que operan na evolución, como o arrastre por ligamento ou efecto autostop, tamén chamado genetic draft.[132][139][140]
O tempo que tarda un alelo en fixarse por deriva xenética depende do tamaño de poboación, e a fixación ocorre máis rapidamente en poboacións pequenas.[141] O número de individuos dunha poboación non é o fundamental, senón un valor coñecido como tamaño efectivo de poboación.[142] A poboación efectiva é xeralmente menor que a poboación total, xa que para calculala hai que ter en conta factores como o nivel de endogamia e o estado do ciclo vital no cal a poboación é menor.[142] O tamaño efectivo de poboación pode non ser o mesmo para todos os xenes dunha mesma poboación.[143]
Arrastre por ligamento[editar | editar a fonte]
- Artigo principal: Arrastre por ligamento.
A recombinación permite que os alelos da mesma fibra dun ADN acaben separados (doutro modo herdaríanse xuntos, xa que as cromátides dos cromosomas se distribúen enteiras nas células fillas). Porén, o grao de recombinación é baixo (aproximadamente hai dous eventos de recombinación por cromosoma e por xeración). Como resultado, os xenes que están próximos entre si nun cromosoma poucas veces serán redistribuídos separándose un do outro e tenden a herdarse xuntos, un fenómeno que se denomina ligamento xenético.[144] Esta tendencia mídese calculando a frecuencia con que dous alelos aparecen xuntos nun cromosoma comparada co esperado, o que se denomina desequilibrio de ligamento. Un conxunto de alelos que xeralmente se herda nun grupo denomínase haplotipo. Isto pode ser importante cando un alelo dun determinado haplotipo é moi beneficioso, xa que a selección natural pode impulsar un varrido selectivo que tamén causará que outros alelos do haplotipo se fagan máis comúns na poboación; este efecto denomínase arrastre por ligamento ou efecto autostop (genetic hitchhiking ou genetic draft).[145] Este efecto causado polo feito de que algúns xenes neutros están ligados xeneticamente a outros que están baixo selección pode ser parcialmente capturado por un tamaño efectivo de poboación apropiado.[139]
Fluxo xénico[editar | editar a fonte]
- Artigos principais: Fluxo xénico, Híbrido (bioloxía) e Transferencia horizontal de xenes.
O fluxo xénico ou fluxo xenético é o intercambio de xenes entre poboacións e entre especies.[92] A presenza ou ausencia de fluxo xénico supón un cambio fundamental no curso da evolución. Debido á complexidade dos organismos, dúas poboacións completamente illadas desenvolverán co tempo incompatibilidades xenéticas por medio de procesos neutros, como no modelo de Bateson-Dobzhansky-Muller, mesmo se ambas as poboacións permanecen esencialmente idénticas en canto á súa adaptación ao ambiente.
Se se produce a diferenciación xenética entre as poboacións, o fluxo xénico entre as poboacións pode introducir trazos ou alelos que son desvantaxosos para a poboación local e isto pode facer que os organismos desa poboación evolucionen producindo mecanismos que impiden o apareamento con poboacións xeneticamente afastadas, e finalmente isto dá lugar á aparición de novas especies. Así, o intercambio de información xenética entre individuos ten unha importancia fundamental para o desenvolvemento do concepto de especie biolóxica.
Durante o desenvolvemento da síntese evolutiva moderna, Sewall Wright desenvolveu a súa teoría do equilibrio cambiante na que o fluxo xénico entre poboacións parcialmente illadas era un aspecto importante da evolución adaptativa.[146] Porén, recentemente houbo críticas substanciais sobre a importancia que realmente ten esta teoría.[147]
Resultados da evolución[editar | editar a fonte]
A evolución inflúe en todos os aspectos que afectan á forma e comportamento dos organismos. Os máis salientables son o comportamento específico e a adaptación física que son o resultado da selección natural. Estas adaptacións incrementan a aptitude biolóxica ou fitness ao engadir cambios en actividades como a procura de alimentos, evitación de depredadores ou a atracción de parellas. Os organismos poden tamén responder á selección cooperando uns cos outros, xeralmente axudando os seus parentes ou establecendo simbioses mutuamente beneficiosas. A longo prazo, a evolución produce novas especies ao dividir as poboacións ancestrais de organismos en novos grupos que non poden ou acabarán por non poder cruzarse.
Estes resultados da evolución divídense ás veces en dous niveis de evolución: macroevolución e microevolución. A macroevolución é a evolución que ocorre ao nivel ou por encima do nivel de especie, como a extinción e a especiación. A microevolución son os cambios evolutivos pequenos, como as adaptacións dentro dunha especie ou poboación.[148] En xeral, a macroevolución considérase como o resultado de longos períodos de microevolución.[149] Deste xeito, a distinción entre micro e macroevolución non é fundamental, xa que a diferenza é simplemente a cantidade de tempo implicado.[150] Porén, en macroevolución, os trazos da especie enteira poden ser importantes. Por exemplo, a existencia dunha gran cantidade da variación entre os individuos é característica dunha especie que se adapta rapidamente a novos hábitats, diminuíndo así a posibilidade de extinguirse, mentres que ter unha área de distribución xeográfica ampla incrementa a posibilidade de especiación ao facer máis probable que parte da poboación quede illada. Neste sentido, a microevolución e a macroevolución poderían implicar unha selección a diferentes niveis; a microevolución actuaría sobre os xenes e organismos, e os procesos macroevolutivos como a selección de especies actuarían sobre a especie enteira e afectarían ás súas taxas de especiación e extinción.[151][152][153]
Un erro de concepto común é pensar que a evolución ten obxectivos ou plans a longo prazo; porén, en realidade, a evolución non ten obxectivos a longo prazo e non necesariamente vai producir unha maior complexidade.[154] Aínda que na evolución se orixinaron especies complexas, estas apareceron como un efecto lateral do crecente número total de organismos e as formas simples de vida seguen sendo as máis comúns na biosfera.[155] Por exemplo, a inmensa maioría das especies son procariotas microscópicos, os cales forman aproximadamente a metade da biomasa do planeta malia o seu pequeno tamaño,[156] e constitúen a gran maioría da biodiversidade de Terra.[157] Os organismos simples foron as formas de vida dominantes en toda a historia de Terra e continúan séndoo, mentres que as formas complexas de vida nos parecen máis diversas só porque destacan máis nun exame superficial.[158] de feito, a evolución dos microorganismos é especialmente importante na investigación evolutiva moderna, xa que a súa rápida reprodución permite o estudo da evolución experimental e a observación da evolución e a adaptación en tempo real.[159][160]
Adaptación[editar | editar a fonte]
- Artigo principal: Adaptación biolóxica.

A adaptación é o proceso que fai que os organismos adquiran as características máis axeitadas para vivir no seu hábitat.[161][162] O termo tamén se pode referir aos trazos que son importantes para a supervivencia dun organismo. Por exemplo, a adaptación dos dentes dos cabalos para triturar a herba. Podemos distinguir os dous sentidos da palabra usando os termos adaptación para o proceso evolutivo e trazo adaptativo para o produto (a parte do corpo ou función). As adaptacións prodúcense por selección natural.[163] As seguintes definicións débense a Theodosius Dobzhansky.
- Adaptación (adaptation) é o proceso evolutivo polo que un organismo mellora a súa capacidade de vivir no seu hábitat ou hábitats.[164]
- Idoneidade (adaptedness) é o estado de estar adaptado: o grao no cal un organismo pode vivir e reproducirse nun determinado conxunto de hábitats.[165]
- Un trazo adaptativo ou carácter adaptativo é un aspecto do padrón de desenvolvemento dun organismo que permite ou aumenta a probabilidade de que un organismo sobreviva e se reproduza.[166]
A adaptación pode facer que se adquira unha nova característica ou que se perda unha característica ancestral. Un exemplo que mostra os dous tipos de cambio é a adaptación bacteriana aos antibióticos, na que cambios xenéticos orixinan resistencia a antibióticos ao modificaren a diana sobre a que actuaba o antibiótico ou incrementaren a actividade dos transportadores que bombean o antibiótico fóra da célula.[167] Outros exemplos notables son a capacidade adquirida pola bacteria Escherichia coli de utilizar o ácido cítrico como nutriente en experimentos de laboratorio de evolución a longo prazo,[168] a adquisición polas Flavobacterium de novos encimas que permiten que estas bacterias crezan nos produtos da manufactura do nailon,[169][170] ou a evolución na bacteria do chan Sphingobium dunha vía metabólica completamente nova que degrada o pesticida sintético pentaclorofenol.[171][172] Unha interesante pero aínda controvertida idea é que algunhas adaptacións poderían incrementar a capacidade dos organismos de xerar diversidade xenética e adaptarse por selección natural (incrementando a evolucionabilidade do organismo).[173][174][175][176]
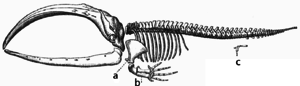
A adaptación ten lugar pola modificación gradual de estruturas existentes. Consecuentemente, as estruturas cunha organización interna similar poden ter diferentes funcións en organismos emparentados. Isto é o resultado da adaptación dunha estrutura ancestral a funcionar de diferentes modos. Os ósos das ás dos morcegos, por exemplo, son moi similares aos dos pés do rato e mans dos primates porque todas estas estruturas descenden das dun devanceiro común mamífero.[178] Porén, como todos os organismos vivos están emparentados nalgunha medida,[179] mesmo órganos que parecen ter pouca ou ningunha semellanza estrutural, como os ollos dos artrópodos, luras e vertebrados, ou as extremidades e ás de artrópodos e vertebrados, poden depender dun conxunto de xenes homólogos que controlan a súa ensamblaxe e funcionamento, o que se chama homoloxía profunda.[180][181]
Durante a evolución algunhas estruturas poden perder a súa función orixinal e converterse en estruturas vestixiais.[182] Tales estruturas poden ter nas especies actuais moi poucas ou ningunha función, pero tiñan unha clara función nas especies ancestrais, ou outras especies relacionadas. Exemplos poden ser os pseudoxenes,[183] os restos non funcionais de ollos en peixes cegos que viven en covas,[184] as ás de aves non voadoras,[185] e a presenza de ósos das cadeiras en baleas e serpes.[177] Exemplos de estruturas vestixiais en humanos son a moa do xuízo,[186] o cóccix,[182] e outros vestixios de comportamento como a pel de galiña[187][188] e os reflexos primitivos.[189][190][191]
Porén, moitos trazos que parecen ser adaptacións simples son de feito o que se chama exaptacións: estruturas adaptadas orixinalmente para unha función, pero que casualmente no proceso se fixeron útiles para algunha outra función.[192] Un exemplo é o lagarto africano Holaspis guentheri, que evolucionou adquirindo unha cabeza extremadamente plana para esconderse en gretas, como se pode comprobar observando os seus parentes próximos. Porén, nesta especie, a cabeza quedou tan aplanada que lle axuda a saltar planando dunha árbore a outra.[192] Nas células, as máquinas moleculares como o flaxelo bacteriano[193] e a maquinaria de translocación de proteínas mitocondrial[194] evolucionaron polo recrutamento de varias proteínas preexistentes que previamente tiñan diferentes funcións.[148] Outro exemplo é o recrutamento de encimas da glicólise e metabolismo xenobiótico para servir como proteínas estruturais chamadas cristalinas nas lentes do ollo (o cristalino).[195][196]
Unha área de investigación actual en bioloxía evolutiva do desenvolvemento é o estudo da base relacionada co desenvolvemento que subxace nas adaptacións e exaptacións.[197] Esta investigación está enfocada a estudar a orixe e evolución do desenvolvemento embrionario e como as modificacións do desenvolvemento e os seus procesos producen novas características.[198] Estes estudos mostran que a evolución pode alterar o desenvolvemento para producir novas estruturas, como as estruturas óseas embrionarias que se forman na mandíbula de moitos vertebrados que nos mamíferos forman parte do oído medio.[199] Tamén é posible que estruturas que se perderon na evolución reaparezan debido a cambios nos xenes do desenvolvemento, como a mutación en polos que causa que aos embrións de polo lles crezan dentes similares aos dos crocodilos.[200] Agora parece claro que a maioría das alteracións na forma dos organismos débense a cambios nun pequeno grupo de xenes conservados.[201]
Coevolución[editar | editar a fonte]

- Artigo principal: Coevolución.
As interaccións entre os organismos poden producir conflitos mais tamén cooperacións. Cando as interaccións son entre pares de especies, como entre patóxenos e hóspedes, ou predadores e presas, estas especies poden desenvolver conxuntos emparellados de adaptacións. Neste caso, a evolución dunha das especies fai que se produzan adaptacións na segunda especie. Despois, estes cambios na segunda especie causan, á súa vez, novas adaptacións na primeira especie. Este ciclo de selección e resposta denomínase coevolución.[202] Un exemplo é a produción de tetrodotoxina nos anfibios Taricha granulosa e a evolución de resistencia á tetrodotoxina no seu predador a serpe Thamnophis sirtalis sirtalis. Neste par predador-presa, produciuse unha carreira de armamentos evolutiva que orixinou a produción de altos niveis de toxina no anfibio e correspondentes altos niveis de resistencia á toxina na serpe.[203]
Cooperación[editar | editar a fonte]
- Artigo principal: Cooperación (evolución).
Non todas as interaccións que coevolucionan entre especies implican un conflito nin a toma de contramedidas.[204] Evolucionaron tamén moitos casos de interaccións mutuamente beneficiosas. Por exemplo, existe unha cooperación extrema entre as plantas e os fungos que forman micorrizas que crecen nas raíces da planta e axudan á planta a absorber nutrientes do chan.[205] Esta é unha relación recíproca, xa que a planta proporciona ao fungo azucres fabricados na fotosíntese. Aquí, o fungo medra introducíndose dentro das células da planta, o que lle permite intercambiar nutrientes co seu hóspede, á vez que envía sinais que suprimen a reacción defensiva da planta.[206]
Tamén evolucionaron coalicións entre organismos da mesma especie. Un caso extremo é a eusocialidade que se encontra nos insectos sociais, como as abellas, térmites e formigas, na que os insectos estériles alimentan e coidan a un pequeno número de individuos da colonia que poden reproducirse. A unha escala aínda menor, as células somáticas que forman o corpo dun animal limitan a súa propia reprodución para que poidan manter un organismo estable, o cal mantén un número pequeno de células xerminais, que son as que producirán a descendencia. Aquí, as células somáticas responden a sinais específicos que dan as instrucións para crecer, permanecer como están ou morrer. Se as células ignoran estes sinais e se multiplican inapropiadamente, o seu crecemento incontrolado causa un cancro.[207]
Esta cooperación entre especies pode evolucionar por un proceso de selección de parentesco, na cal un organismo actúa para axudar os descendentes emparentados con el.[208] Esta actividade é seleccionada favorablemente porque se o individuo que axuda contén alelos que promoven a actividade de axudar, é probable que os seus descendentes tamén conteñan eses alelos e os transmitan.[209] Outros procesos que poden promover a cooperación son a selección de grupo, na que a cooperación proporciona beneficios a un grupo de organismos.[210]
Especiación[editar | editar a fonte]
- Artigo principal: Especiación.

A especiación é o proceso mediante o que as especies diverxen orixinando dúas ou máis especies distintas descendentes.[211] Hai moitas formas de definir o concepto de "especie". A elección da definición depende das particularidades das especies en cuestión.[212] Por exemplo, algúns conceptos de especie aplícanse máis doadamente a organismos que se reproducen sexualmente, mentres que outros son mellores para organismos asexuais. A pesar da diversidade de conceptos de especie, estes poden adscribirse a tres posibles enfoques: de cruzamento, ecolóxicos e filoxenéticos.[213] O concepto de especie biolóxica é un exemplo clásico do enfoque centrado no cruzamento. Definido por Ernst Mayr en 1942, o concepto biolóxico de especie establece que a "especie son grupos de poboacións naturais que real ou potencialmente se poden cruzar, que están reprodutivamente illados doutros grupos".[214] Malia o amplo e duradeiro uso desta definición, o concepto biolóxico de especie non está exento de controversia, por exemplo porque este concepto non se pode aplicar aos procariotas,[215] e esta dificultade é o que se chama o problema da especie.[212] Algúns investigadores intentaron unificar a definición monística de especie, mentres que outros adoptaron unha aproximación pluralista e suxiren que podería haber diferentes modos para interpretar loxicamente a definición de especie.[212][213]
Cómpre que haxa barreiras reprodutivas entre dúas poboacións sexualmente diverxentes para que as poboacións orixinen novas especies. O fluxo xénico pode facer máis lento este proceso ao estender as novas variantes xenéticas tamén ás outras poboacións. Dependendo do moito que diverxesen entre si dúas especies desde o seu antepasado común máis recente, pode ser que aínda poidan producir descendencia por un cruzamento entre elas, como ocorre co cabalo e o burro, que se poden aparear orixinando unha mula.[216] Tales híbridos son xeralmente estériles. Neste caso, especies moi próximas poden cruzarse regularmente, pero os híbridos formados sufrirán unha selección en contra e as especies seguirán sendo distintas. Porén, poden formarse ocasionalmente híbridos viables e estas novas especies híbridas poden ou ben ter propiedades intermedias entre as dúas especies parentais, ou ben posuirán un fenotipo totalmente novo.[217] A importancia da hibridación na produción de novas especies de animais non está clara, aínda que se teñen visto casos en moitos tipos de animais,[218] como o ben estudado exemplo da ra arbórea gris (Hyla versicolor).[219]
A especiación observouse en numerosas ocasións en condicións controladas de laboratorio e na natureza.[220] Nos organismos que se reproducen sexualmente, a especiación orixínase polo illamento reprodutivo seguido dunha diverxencia xenealóxica. Hai catro mecanismos para a especiación. O máis común nos animais é a especiación alopátrica, que ten lugar en poboacións inicialmente illadas xeograficamente, como ocorre pola fragmentación do hábitat ou a migración. A selección baixo estas condicións pode producir cambios moi rápidos na aparencia e comportamento dos organismos.[221][222] Como a selección e a deriva actúan independentemente nas poboacións que están illadas do resto das súas especies, a separación pode finalmente producir organismos que non se poden cruzar.[223]
O segundo mecanismo de especiación é a especiación peripátrica, que ten lugar cando unha pequena poboación de organismos queda illada nun novo ambiente. Isto difire da especiación alopátrica en que as poboacións illadas son moito menores numericamente que a poboación parental. Aquí, o efecto fundador causa unha rápida especiación despois dun incremento de cruzamentos endogámicos que incrementa a selección sobre os homocigotos, o que produce un rápido cambio xenético.[224]
O terceiro mecanismo de especiación é a especiación parapátrica. É similar á especiación peripátrica en que tamén unha pequena poboación entra nun novo hábitat, pero difire en que non hai separación física entre estas dúas poboacións. A especiación é resultado de que evolucionan mecanismos que reducen o fluxo xénico entre as dúas poboacións.[211] Xeralmente isto ocorre cando houbo un drástico cambio no ambiente dentro do hábitat da especie parental. Un exemplo é a planta herbácea Anthoxanthum odoratum (lesta), que pode sufrir unha especiación parapátrica en resposta á contaminación da terra por metais procedentes de explotacións mineiras.[225] Aquí, as plantas evolucionan para ter resistencia aos altos niveis de metais no chan. A selección en contra do cruzamento coa poboación parental sensible aos metais produciu un cambio gradual no tempo de floración das plantas resistentes aos metais, o cal finalmente orixinou un completo illamento reprodutivo. A selección en contra dos híbridos entre as dúas poboacións pode causar un reforzamento, o cal é a evolución de trazos que promoven o apareamento dentro de cada especie, e o desprazamento de carácter, que se produce cando dúas especies se fan máis distintas en aspecto.[226]

Finalmente, na especiación simpátrica as especies diverxen sen que haxa illamento xeográfico nin cambios no hábitat. Esta forma é rara, xa que mesmo unha pequena cantidade de fluxo xénico pode eliminar as diferenzas xenéticas entre partes dunha poboación.[227] Xeralmente a especiación simpátrica nos animais require a evolución de diferenzas xenéticas e apareamento non aleatorio, para que poida evolucionar o illamento reprodutivo.[228]
Un tipo de especiación simpátrica implica a hibridación entre dúas especies relacionadas que producen unha nova especie híbrida. Isto non é común en animais, xa que os híbridos animais son xeralmente estériles, porque durante a meiose os cromosomas homólogos de cada proxenitor son de diferentes especies e non poden emparellarse con éxito. Porén, é máis común en plantas porque as plantas con frecuencia duplican o seu número de cromosomas para formar poliploides.[229] Isto permite que os cromosomas de cada especie proxenitora formen pares coincidentes (homólogos) durante a meiose, xa que cada cromosoma de cada proxenitor está xa representado por un par.[230] Un exemplo dese tipo de especiación é o cruzamento das plantas da especie Arabidopsis thaliana coas Arabidopsis arenosa, que deu lugar á nova especie Arabidopsis suecica.[231] Isto ocorreu hai uns 20 000 anos,[232] e o proceso de especiación foi repetido no laboratorio, o cal permitiu estudar os mecanismos xenéticos implicados neste proceso.[233] A duplicación cromosómica nunha especie pode ser unha causa común de illamento reprodutivo, xa que a metade dos cromosomas duplicados quedará sen emparellarse na meiose cando se crucen con organismos sen esa duplicación.[234]
Os eventos de especiación son importantes na teoría do equilibrio interrompido (ou puntuado), que intenta explicar o padrón observado no rexistro fósil de curtos períodos de "explosión" evolutiva intercalados con períodos relativamente longos de "estase", nos cales as especies permanecen relativamente sen cambiar.[235] Nesta teoría, a especiación e a rápida evolución están ligadas, e a selección natural e a deriva xenética actúan máis intensamente sobre os organismos que están sufrindo especiación en novos hábitats ou pequenas poboacións. Como resultado, os períodos de estase no rexistro fósil corresponden á poboación parental e os organismos que sofren especiación e rápida evolución encóntranse en pequenas poboacións ou hábitats xeograficamente restrinxidos e, polo tanto, raramente aparecen preservados no rexistro fósil.[236]
Extinción[editar | editar a fonte]
- Artigo principal: Extinción.

A extinción é a desaparición completa dunha especie. A extinción é un evento natural, xa que as especies aparecen regularmente por especiación e desaparecen por extinción.[237] Case todas as especies de animais e plantas que existiron sobre a Terra están agora extinguidas,[238] e a extinción parece ser o destino final de todas as especies.[239] Estas extincións ocorreron continuamente no decurso da historia da vida, aínda que a taxa de extinción se dispara en ocasionais episodios de extinción en masa.[240] O evento de extinción do Cretáceo-Paleoxeno, durante o cal se extinguiron os dinosauros non aviarios, é o mellor coñecido, pero o anterior evento de extinción do Pérmico-Triásico foi aínda máis intenso, e nel desapareceron o 96% das especies.[240] O evento de extinción do Holoceno é un episodio de extinción en masa que está en marcha na época actual asociado coa expansión da humanidade por todo o globo nos últimos miles de anos. As taxas de extinción actuais son de 100 a 1000 veces maiores que a taxa normal, e ata un 30% das especies actuais poden extinguirse a mediados do século XXI.[241] As actividades humanas son agora a causa primaria do episodio de extinción actual,[242] e o quecemento global pode acelerala no futuro.[243]
O papel da extinción na evolución non se comprende ben e pode depender de que tipo de extinción se considere.[240] As causas dos continuos episodios de extinción de "baixo nivel", que forman a maioría das extincións, poden ser o resultado da competición entre especies polos recursos limitados (exclusión competitiva).[53] Se unha especie pode deixar fóra da competencia a outra, eliminándoa, isto podería producir unha selección de especies, e a especie mellor adaptada sobrevivirá e a outra especie extinguirase.[113] As extincións en masa intermitentes son tamén importantes, pero en vez de actuaren como forza selectiva, o que fan é reduciren drasticamente a diversidade dunha maneira non específica e promoveren explosións de evolución rápida e a especiación nos sobreviventes.[244]
Falta de adaptación[editar | editar a fonte]
- Artigo principal: Hipótese da Raíña Vermella.
O ambiente que un organismo explota e co que se ten que confrontar está constantemente cambiando, e pode, ás veces, cambiar de forma rápida e drástica, ou deteriorarse. É necesaria unha constante adaptación a cambios pequenos e grandes para que un organismo continúe prosperando, ou mesmo sobreviva. Esta é a "hipótese da Raíña Vermella", chamada así pola afirmación da Raíña Vermella do libro Alicia do outro lado do espello de Lewis Carroll de que a Terra era un lugar onde, “tes que correr todo o que poidas para manterte no mesmo sitio”.[245][246]
Historia evolutiva da vida[editar | editar a fonte]
- Artigos principais: Historia evolutiva da vida e Evolución humana.
Orixe da vida[editar | editar a fonte]
- Artigos principais: Orixe da vida, Hipótese do mundo de ARN e Panspermia.
A idade da Terra estímase nuns 4 540 millóns de anos.[247][248][249] A evidencia máis antiga indiscutida de vida na Terra data de polo menos 3 500 millóns de anos,[3][250] durante a era Eoarcaica. Atopáronse restos fósiles de tapetes microbianos en rochas de 3 480 millóns de anos de antigüidade en Australia Occidental.[251][252][253] Outra evidencia física moi antiga dunha substancia bioxénica é o grafito de hai 3 700 millóns de anos descuberto en rochas de Groenlandia[254] e os "restos de vida biótica" atopados en rochas de 4 100 millóns de anos de Australia Occidental.[255][256]
Hai uns 4 mil millóns de anos crese que unhas reaccións químicas moi enerxéticas orixinaron a primeira molécula autorreplicante, e 500 millóns de anos máis tarde apareceu o último antepasado común universal de todos os seres vivos actuais.[257] O consenso científico actual é que a bioquímica complexa que conforma a vida procede de reaccións químicas máis simples.[258] O principio da vida puido comprender a formación de moléculas autorreplicantes como o ARN[259] e a ensamblaxe de células simples.[260]
Ascendencia común[editar | editar a fonte]
- Artigos principais: Antepasado común e Probas da evolución.

Todos os organismos da Terra descenden dun antepasado común ou poza xenética ancestral.[179][261] As especies actuais son un estadio no proceso evolutivo, e a súa diversidade é produto dunha longa serie de episodios de especiación e extinción.[262] O antepasado común de todos os organismos foi deducido por catro simples feitos que afectan aos organismos: Primeiro, teñen distribucións xeográficas que non poden ser explicadas por adaptacións locais. Segundo, a diversidade da vida non está formada por un conxunto de organismos únicos separados, senón que os organismos comparten semellanzas morfolóxicas. Terceiro, os trazos vestixiais que non teñen unha clara función lembran aos trazos ancestrais e, finalmente, eses organismos poden clasificarse usando estas semellanzas nunha xerarquía de grupos aniñados uns dentro doutros máis amplos, que é similar a unha árbore de familia.[263] Porén, a investigación moderna suxire que, debido á transferencia horizontal de xenes, esta "árbore da vida" pode ser máis complicada que unha simple árbore ramificada, xa que algúns xenes se difundiron independentemente entre especies afastadas.[264][265]
As especies pasadas deixaron tamén rexistro da súa historia evolutiva. Os fósiles, xunto coa anatomía comparada dos organismos actuais, constitúen un rexistro morfolóxico ou anatómico.[266] Comparando as anatomías de especies modernas e extinguidas, os paleontólogos poden inferir a liñaxe desas especies. Con todo, esta aproximación ten máis éxito para os organismos que teñen partes duras, como cunchas, ósos ou dentes. Ademais, os procariotas como as bacterias e as arqueas comparten un conxunto limitado de morfoloxías comúns, e os seus fósiles non proporcionan información sobre os seus devanceiros.
Máis recentemente, as evidencias sobre unha ascendencia común proceden dos estudos das semellanzas bioquímicas entre os organismos. Por exemplo, todas as células vivas utilizan o mesmo conxunto básico de nucleótidos e aminoácidos.[267] O desenvolvemento da xenética molecular revelou o rexistro que deixou a evolución nos xenomas dos organismos, o que permitiu facer datacións do momento en que as especies diverxeron por medio de reloxos moleculares producidos polas mutacións.[268] Por exemplo, estas comparacións das secuencias de ADN revelaron que os humanos e os chimpancés comparten o 98% dos seus xenomas, e analizando as poucas áreas nas que son diferentes pódese obter moita información de en que época existiu o antepasado común desas dúas especies.[269]
Evolución da vida[editar | editar a fonte]
- Artigo principal: Historia evolutiva da vida.
Os procariotas levan habitando na Terra desde hai aproximadamente de 3 a 4 miles de millóns de anos.[270][271] Non se produciron cambios obvios en morfoloxía ou organización celular neses organismos nos últimos miles de millóns de anos.[272] As células eucariotas apareceron hai entre 1,6 e 2,7 miles de millóns de anos. O seguinte cambio importante na estrutura celular produciuse cando certas bacterias foron fagocitadas por células eucariotas, e estableceron unha asociación cooperativa chamada endosimbiose.[273][274] Estas bacterias incluídas dentro das células eucariotas e a célula hóspede experimentaron unha coevolución, e as bacterias evolucionaron transformándose nas mitocondrias ou en hidroxenosomas.[275] Outra fagocitose similar de organismos fotosintéticos similares a cianobacterias deu orixe aos cloroplastos das algas e plantas.[276]
A historia da vida foi só a dos eucariotas, bacterias e arqueas unicelulares ata hai uns 610 millóns de anos cando empezaron a aparecer os organismos multicelulares nos océanos no período Ediacariano.[270][277] A evolución da multicelularidade tivo lugar por medio de moitos episodios independentes, en organismos tan diversos como esponxas, algas pardas, cianobacterias, mofos mucosos e mixobacterias.[278]
Pouco despois da emerxencia destes primeiros organismos pluricelulares, apareceu unha importante diversidade biolóxica en aproximadamente 10 millóns de anos, nun evento chamado explosión cámbrica. Nese momento apareceron a maioría dos filos de animais modernos no rexistro fósil, xunto con outras liñaxes que se extinguiron.[279] Propuxéronse varios factores que puideron desencadear a explosión cámbrica, como a acumulación de osíxeno na atmosfera debido á actividade fotosintética.[280]
Hai uns 500 millóns de anos, as plantas e os fungos colonizaron a terra firme e foron axiña seguidos polos artrópodos e outros animais.[281] Os insectos tiveron un especial éxito e aínda hoxe son a maioría das especies animais.[282] Os anfibios apareceron hai uns 364 millóns de anos, seguidos polos primeiros amniotas e aves hai uns 155 millóns de anos (ambos os dous da liñaxe reptiliana), os mamíferos apareceron hai arredor de 129 millóns de anos, os homininae hai arredor de 10 millóns de anos, e os humanos modernos hai uns 250 000 anos.[283][284][285] Con todo, a pesar de que evolucionaron todos eses grandes animais e plantas, os organismos máis pequenos similares aos que primeiro apareceran no inicio da evolución seguen tendo un éxito enorme e aínda dominan a Terra, de modo que a maioría da biomasa e das especies da Terra son procariotas.[157]
Aplicacións[editar | editar a fonte]
Os conceptos e modelos utilizados en bioloxía evolutiva como a selección natural, teñen moitas aplicacións.[286]
A selección artificial é a selección intencional de trazos na poboación de organismos. Isto foi utilizado desde hai miles de anos para a domesticación de animais e plantas.[287] Máis recentemente, esa selección converteuse nunha parte vital da enxeñaría xenética, e utilízanse marcadores seleccionables como xenes de resistencia a antibióticos para manipular o ADN. Poden facerse evolucionar con repetidas roldas de mutación e selección a proteínas con propiedades valiosas, por exemplo encimas modificados e novos anticorpos, nun proceso chamado evolución dirixida.[288]
Comprender os cambios que ocorreron durante a evolución dun organismo pode revelar os xenes que se necesitan para construír partes do corpo, xenes que poden estar implicados nos trastornos xenéticos humanos.[289] Por exemplo, o peixe Astyanax mexicanus é un peixe de caverna albino que perdeu a súa vista durante a evolución. Cruzando diferentes poboacións deste peixe cego nacen algúns descendentes con ollos funcionais, xa que ocorreron diferentes mutacións nas poboacións illadas que evolucionaran en diferentes cavernas e que orixinaban cada unha a cegueira.[290] Isto axudou a identificar os xenes necesarios para a visión e a pigmentación.[291]
Moitas doenzas humanas non son fenómenos estáticos, senón con capacidade de evolucionar. Virus, bacterias, fungos e os cancros evolucionan para ser resistentes ao sistema inmunitario do seu hóspede, e aos fármacos.[292][293][294] Estes mesmos problemas ocorren na agricultura coa resistencia a pesticidas[295] e herbicidas.[296] É posible que nos esteamos enfrontando ao fin da vida efectiva de moitos antibióticos[297] e para predicir a evolución e a evolucionabilidade[298] dos nosos patóxenos e idear estratexias para facelas máis lentas ou evitalas cómpre ter profundos coñecementos das complexas forzas que impulsan a evolución a nivel molecular.[299]
Na ciencia da computación, as simulacións da evolución usando algoritmos evolutivos e a vida artificial iniciáronse na década de 1960 e ampliáronse coa simulación da selección artificial.[300] A evolución artificial converteuse nun método de optimización amplamente recoñecido como resultado do traballo de Ingo Rechenberg na década de 1960. Rechenberg utilizou estratexias evolutivas para resolver complexos problemas de enxeñaría.[301] Os algoritmos xenéticos en particular fixéronse populares coas publicacións de John Holland.[302] Entre as aplicacións prácticas tamén están os programas computacionais de evolución automática.[303] Os algoritmos evolutivos son agora utilizados para resolver problemas multidimensionais máis eficientemente que o software ideado polos deseñadores humanos e tamén para optimizar o deseño de sistemas.[304]
Respostas sociais e culturais[editar | editar a fonte]
- Véxase tamén: Obxeccións á evolución.

No século XIX, particularmente despois da publicación de A orixe das especies en 1859, a idea de que a vida evolucionara era unha fonte activa de debate académico centrado nas implicacións evolutivas relixiosas, sociais e filosóficas. Hoxe, a síntese evolutiva moderna é aceptada por unha esmagadora maioría dos científicos.[53] Porén, a evolución segue sendo un concepto contencioso para algúns teístas.[306]
Aínda que varias confesións relixiosas reconciliaron as súas crenzas coa evolución por medio de conceptos como a evolución teísta, hai aínda creacionistas que cren que a evolución é contradita polos mitos da creación que forman parte das súas relixións e que presentan varias obxeccións á evolución.[148][307][308] Como xa se demostrara polas respostas á publicación do libro Vestiges of the Natural History of Creation (Vestixios da Historia Natural da Creación) en 1844, os aspectos máis controvertidos da bioloxía evolutiva son que a evolución humana implica que os humanos comparten un antepasado común cos simios e que as facultades mentais e morais da humanidade teñen o mesmo tipo de causas naturais que outros trazos herdados nos animais.[309]
En canto a Galicia, aínda que actualmente non hai polémicas significativas sobre a evolución e a súa ensinanza, que forma parte do currículo escolar, a situación foi moi distinta cando xurdiu o darwinismo no século XIX. Daquela estas novas ideas chocaban cunha sociedade dominada pola Igrexa, que mantiña aínda moitos privilexios e poder e cunha parte da burguesía conservadora e enfrontáronse ás lexislacións dese turbulento século en España. A propia Universidade de Santiago de Compostela era moi conservadora, o que se evidencia nos discursos de inauguración de curso claramente antidarwinistas e de xustificación da supeditación da Ciencia á Relixión, a prohibición de comprar libros darwinistas para a Biblioteca e da súa ensinanza. Durante o Sexenio Revolucionario os profesores da Universidade Augusto González de Linares e Laureano Calderón Arana son destituídos por defenderen ideas darwinistas e de liberdade de cátedra ao aplicárselles o decreto Orovio[310], contrario á liberdade de cátedra, que o prohibía. Outra intelectual galega da época antidarwinista foi Emilia Pardo Bazán, que escribiu Reflexiones críticas contra el darwinismo (Reflexións críticas contra o darwinismo) e incluíu referencias ao evolucionismo na novela Os pazos de Ulloa. En consecuencia, o darwinismo difundiuse moi pouco en Galicia no século XIX.[311][312]
Nalgúns países, en Occidente fundamentalmente en Estados Unidos, estas tensións entre ciencia e relixión impulsaron a actual controversia creación-evolución, un conflito relixioso centrado na política e a educación pública.[313] Aínda que outros campos científicos como a cosmoloxía[314] e as ciencias da Terra[315] tamén entran en conflito con interpretacións literais de moitos textos relixiosos, é a bioloxía evolutiva a que ten significativamente máis oposición das persoas relixiosas literalistas.
A ensinanza da evolución nas clases de bioloxía na escola secundaria norteamericana era pouco común na maior parte da primeira metade do século XX. A famosa sentenza do xuízo de Scopes de 1925 fixo que esa materia aparecese raramente nos libros de bioloxía de secundaria norteamericanos durante unha xeración, pero foi reintroducida gradualmente máis tarde e quedou legalmente protexida coa sentenza de 1968 de Epperson contra Arkansas. Desde entón, as crenzas relixiosas do creacionismo non foron recoñecidas no currículo da escola secundaria en varias decisións nas décadas de 1970 e 1980, pero regresaron en forma pseudocientífica como o deseño intelixente, para seren excluídas unha vez máis no caso de 2005 de Kitzmiller contra o Distrito Escolar da Área de Dover.[316]
Notas[editar | editar a fonte]
Todas as referencias en inglés agás cando se indique o contrario.
- ↑ Ciccarelli FD, Doerks T, von Mering C, Creevey CJ, Snel B, Bork P (2006). "Toward automatic reconstruction of a highly resolved tree of life". Science 311 (5765): 1283–87. Bibcode:2006Sci...311.1283C. PMID 16513982. doi:10.1126/science.1123061.
- ↑ Hall & Hallgrímsson 2008, pp. 3–5
- ↑ 3,0 3,1 Schopf, J. William; Kudryavtsev, Anatoliy B.; Czaja, Andrew D.; Tripathi, Abhishek B. (5 de outubro 2007). "Evidence of Archean life: Stromatolites and microfossils". Precambrian Research (Amsterdam, the Netherlands: Elsevier) 158 (3–4): 141–155. ISSN 0301-9268. doi:10.1016/j.precamres.2007.04.009.
- ↑ Wade, Nicholas (25 de xullo de 2016). "Meet Luca, the Ancestor of All Living Things". New York Times. Consultado o 25 de xullo de 2016.
- ↑ Panno, Joseph (2005). The Cell: Evolution of the First Organism. Facts on File science library. Nova York: Facts on File. pp. xv–16. ISBN 0-8160-4946-7. LCCN 2003025841. OCLC 53901436.
- ↑ Futuyma, Douglas J. (2004). "The Fruit of the Tree of Life: Insights into Evolution and Ecology". En Cracraft, Joel; Donoghue, Michael J. Assembling the Tree of Life. Nova York: Oxford University Press. p. 33. ISBN 0-19-517234-5. LCCN 2003058012. OCLC 61342697.
- ↑ Lewontin, R. C. (1970). "The units of selection". Annual Review of Ecology and Systematics 1: 1–18. ISSN 1545-2069. JSTOR 2096764. doi:10.1146/annurev.es.01.110170.000245.
- ↑ Darwin 1859, Capítulo XIV
- ↑ 9,0 9,1 Kimura, Motoo (1991). "The neutral theory of molecular evolution: a review of recent evidence". ournal of Human Genetics (Genetics Society of Japan) 66 (4): 367–386. ISSN 0021-504X. PMID 1954033. doi:10.1266/jjg.66.367.
- ↑ Provine, William B. (1988). "Progress in Evolution and Meaning in Life". En Nitecki, Matthew H. Evolutionary Progress. University of Chicago Press. pp. 49–79. ISBN 0-226-58693-6. LCCN 88020835. OCLC 18380658.
- ↑ 11,0 11,1 NAS 2008, pp. R11–R12
- ↑ Ayala, Francisco J.; Avise, John C., eds. (2014). Essential Readings in Evolutionary Biology. Baltimore: Johns Hopkins University Press. ISBN 978-1-4214-1305-1. LCCN 2013027718. OCLC 854285705.
- ↑ NAS 2008, p. 17
- ↑ Moore, Randy; Decker, Mark; Cotner, Sehoya (2010). Chronology of the Evolution-Creationism Controversy. Santa Barbara: Greenwood Press / ABC-CLIO. p. 454. ISBN 978-0-313-36287-3. LCCN 2009039784. OCLC 422757410.
- ↑ Futuyma, Douglas J., ed. (1999). "Evolution, Science, and Society: Evolutionary Biology and the National Research Agenda" (PDF). New Brunswick, NJ: Office of University Publications, Rutgers, The State University of New Jersey. OCLC 43422991. Arquivado dende o orixinal (PDF) o 31 de xaneiro de 2012. Consultado o 27 de maio de 2016.
- ↑ Darwin, Francis, ed. (1909). The foundations of The origin of species, a sketch written in 1842 (PDF). Cambridge: University Press. p. 53. LCCN 61057537. OCLC 1184581.
- ↑ Kirk, Geoffrey; Raven, John; Schofield, Malcolm (1983). The Presocratic Philosophers: A Critical History with a Selection of Texts (2ª ed.). Cambridge University Press. pp. 100–142, 280–321. ISBN 0-521-27455-9. LCCN 82023505. OCLC 9081712.
- ↑ Torrey, Harry Beal; Felin, Frances (1937). "Was Aristotle an evolutionist?". The Quarterly Review of Biology 12 (1): 1–18. JSTOR 2808399. doi:10.1086/394520.
- ↑ Hull, D. L. (1967). "The metaphysics of evolution". The British Journal for the History of Science 3 (4): 309–337. JSTOR 4024958. doi:10.1017/S0007087400002892.
- ↑ Lucrecio. "Libro V". De Rerum Natura. Perseus Digital Library. Editado e traducido por William Ellery Leonard (1916) (Tufts University). OCLC 33233743.
- ↑ Sedley, David (2003). "Lucretius and the New Empedocles" (PDF). Leeds International Classical Studies (Leeds International Classics Seminar) 2 (4). ISSN 1477-3643. Arquivado dende o orixinal (PDF) o 23 de agosto de 2014. Consultado o 07 de xuño de 2016.
- ↑ Mason, Stephen F. (1962). A History of the Sciences. Collier Books. Science Library, CS9. Nova York: Collier Books. pp. 43–44. LCCN 62003378. OCLC 568032626.
- ↑ Mayr 1982, pp. 256–257; Ray, John (1686). Historia Plantarum I. Typis Mariæ Clark. LCCN agr11000774. OCLC 2126030.
- ↑ Waggoner, Ben (7 de xullo de 2000). "Carl Linnaeus (1707-1778)". Evolution. University of California Museum of Paleontology. Consultado o 11 de febreiro de 2012.
- ↑ Bowler 2003, pp. 73–75
- ↑ "Erasmus Darwin (1731-1802)". Evolution. University of California Museum of Paleontology. 4 de outubro de 1995. Consultado o 11 de febreiro de 2012.
- ↑ Lamarck, Jean-Baptiste (1809). Philosophie Zoologique (en francés). París: Dentu et L'Auteur. OCLC 2210044.
- ↑ 28,0 28,1 Nardon, Paul; Grenier, Anne-Marie (1991). "Serial Endosymbiosis Theory and Weevil Evolution: The Role of Symbiosis". En Margulis, Lynn; Fester, René. Symbiosis as a Source of Evolutionary Innovation: Speciation and Morphogenesis. MIT Press. p. 162. ISBN 0-262-13269-9. LCCN 90020439. OCLC 22597587.
- ↑ 29,0 29,1 29,2 Gould 2002
- ↑ Ghiselin, Michael T. (1994). "The Imaginary Lamarck: A Look at Bogus 'History' in Schoolbooks". The Textbook Letter (The Textbook League). OCLC 23228649.
- ↑ Magner, Lois N. (2002). A History of the Life Sciences (3ª ed.). Nova York: Marcel Dekker. ISBN 0-8247-0824-5. LCCN 2002031313. OCLC 50410202.
- ↑ Jablonka, Eva; Lamb, Marion J. (2007). "Précis of Evolution in Four Dimensions". Behavioural and Brain Sciences (Cambridge University Press) 30 (4): 353–365. ISSN 0140-525X. doi:10.1017/S0140525X07002221.
- ↑ Burkhardt, Frederick; Smith, Sydney, eds. (1991). The Correspondence of Charles Darwin. The Correspondence of Charles Darwin. 7: 1858–1859. Cambridge University Press. ISBN 0-521-38564-4. LCCN 84045347. OCLC 185662993.; "Darwin, C. R. to Lubbock, John". Darwin Correspondence Project. Carta 2532 do 22 de novembro de 1859. University of Cambridge. Consultado o 1 de decembro de 2014.
- ↑ Sulloway, Frank J. (2009). "Why Darwin rejected intelligent design". Journal of Biosciences (Bangalore: Indian Academy of Sciences) 34 (2): 173–183. ISSN 0250-5991. PMID 19550032. doi:10.1007/s12038-009-0020-8.
- ↑ Dawkins, Richard (1990). The Blind Watchmaker. Penguin Science. Londres: Penguin Books. ISBN 0-14-014481-1. OCLC 60143870.
- ↑ Sober, Elliott (16 de xuño de 2009). "Did Darwin write the Origin backwards?". Proc. Natl. Acad. Sci. U.S.A. (Washington, D.C.: National Academy of Sciences) 106 (Supl. 1): 10048–10055. Bibcode:2009PNAS..10610048S. ISSN 0027-8424. doi:10.1073/pnas.0901109106.
- ↑ Mayr, Ernst (2002). What Evolution Is. Science Masters. Londres: Weidenfeld & Nicolson. p. 165. ISBN 0-297-60741-3. LCCN 2001036562. OCLC 248107061.
- ↑ Bowler 2003, pp. 145–146
- ↑ Sokal, Robert R.; Crovello, Theodore J. (1970). "The Biological Species Concept: A Critical Evaluation". The American Naturalist (University of Chicago Press) 104 (936): 127–153. ISSN 0003-0147. JSTOR 2459191. doi:10.1086/282646.
- ↑ Darwin, Charles; Wallace, Alfred (20 de agosto de 1858). "On the Tendency of Species to form Varieties; and on the Perpetuation of Varieties and Species by Natural Means of Selection". Journal of the Proceedings of the Linnean Society of London. Zoology 3 (9): 45–62. ISSN 1096-3642. doi:10.1111/j.1096-3642.1858.tb02500.x.
- ↑ Desmond, Adrian J. (17 de xullo de 2014). "Thomas Henry Huxley". Encyclopædia Britannica Online. Encyclopædia Britannica, Inc. Consultado o 2 de decembro de 2014.
- ↑ Liu, Y. S.; Zhou, X. M.; Zhi, M. X.; Li, X. J.; Wang, Q. L. (2009). "Darwin's contributions to genetics". Journal of Applied Genetics (Poznań: Institute of Plant Genetics) 50 (3): 177–184. ISSN 1234-1983. PMID 19638672. doi:10.1007/BF03195671.
- ↑ Weiling, Franz (1991). "Historical study: Johann Gregor Mendel 1822–1884". American Journal of Medical Genetics 40 (1): 1–25. PMID 1887835. doi:10.1002/ajmg.1320400103.
- ↑ Wright, Sewall (1984). Genetic and Biometric Foundations. Evolution and the Genetics of Populations 1. University of Chicago Press. p. 480. ISBN 0-226-91038-5. LCCN 67025533. OCLC 246124737.
- ↑ Provine, William B. (1971). The Origins of Theoretical Population Genetics. Chicago History of Science and Medicine (2ª ed.). University of Chicago Press. ISBN 0-226-68464-4. LCCN 2001027561. OCLC 46660910.
- ↑ Stamhuis, Ida H.; Meijer, Onno G.; Zevenhuizen, Erik J. A. (1999). "Hugo de Vries on Heredity, 1889-1903: Statistics, Mendelian Laws, Pangenes, Mutations". Isis (University of Chicago Press) 90 (2): 238–267. ISSN 0021-1753. JSTOR 237050. PMID 10439561. doi:10.1086/384323.
- ↑ Quammen, David (2006). The Reluctant Mr. Darwin: An Intimate Portrait of Charles Darwin and the Making of His Theory of Evolution. Great Discoveries (1ª ed.). Nova York: Atlas Books/W. W. Norton & Company. ISBN 978-0-393-05981-6. LCCN 2006009864. OCLC 65400177.
- ↑ * Bowler, Peter J. (1989). The Mendelian Revolution: The Emergence of Hereditarian Concepts in Modern Science and Society. Baltimore: Johns Hopkins University Press. ISBN 0-8018-3888-6. LCCN 89030914. OCLC 19322402.
- ↑ Watson, J. D.; Crick, F. H. C. (25 de abril de 1953). "Molecular Structure of Nucleic Acids: A Structure for Deoxyribose Nucleic Acid" (PDF). Nature (Londres) 171 (4356): 737–738. Bibcode:1953Natur.171..737W. ISSN 0028-0836. PMID 13054692. doi:10.1038/171737a0.
- ↑ Hennig, Willi (1999). Phylogenetic Systematics. Tradución de D. Dwight Davis e Rainer Zangerl. University of Illinois Press. p. 280. ISBN 0-252-06814-9. LCCN 78031969. OCLC 722701473.
- ↑ Wiley, E. O.; Lieberman, Bruce S. (2011). Phylogenetics: Theory and Practice of Phylogenetic Systematics (2ª ed.). Wiley-Blackwell. ISBN 978-0-470-90596-8. LCCN 2010044283. OCLC 741259265. doi:10.1002/9781118017883.
- ↑ Dobzhansky, Theodosius (1973). "Nothing in Biology Makes Sense Except in the Light of Evolution". The American Biology Teacher (National Association of Biology Teachers) 35 (3): 125–129. doi:10.2307/4444260.
- ↑ 53,0 53,1 53,2 Kutschera, Ulrich; Niklas, Karl J. (2004). "The modern theory of biological evolution: an expanded synthesis". Naturwissenschaften (Heidelberg: Springer-Verlag Heidelberg) 91 (6): 255–276. Bibcode:2004NW.....91..255K. ISSN 1432-1904. PMID 15241603. doi:10.1007/s00114-004-0515-y.
- ↑ Cracraft, Joel; Bybee, Rodger W., eds. (2005). Evolutionary Science and Society: Educating a New Generation (PDF). Biological Sciences Curriculum Study. ISBN 1-929614-23-3. OCLC 64228003. Arquivado dende o orixinal (PDF) o 18 de xullo de 2015. Consultado o 07 de xuño de 2016.
- ↑ Avise, John C.; Ayala, Francisco J. (11 de maio de 2010). "In the light of evolution IV: The human condition" (PDF). Proc. Natl. Acad. Sci. U.S.A. (Washington, D.C.: National Academy of Sciences) 107 (Supl. 2): 8897–8901. ISSN 0027-8424. doi:10.1073/pnas.100321410.
- ↑ Sturm, Richard A.; Frudakis, Tony N. (2004). "Eye colour: portals into pigmentation genes and ancestry". Trends in Genetics (Cambridge: Cell Press) 20 (8): 327–332. ISSN 0168-9525. PMID 15262401. doi:10.1016/j.tig.2004.06.010.
- ↑ 57,0 57,1 Pearson, Helen (25 de maio de 2006). "Genetics: What is a gene?". Nature (Londres) 441 (7092): 398–401. Bibcode:2006Natur.441..398P. ISSN 0028-0836. PMID 16724031. doi:10.1038/441398a.
- ↑ Visscher, Peter M.; Hill, William G.; Wray, Naomi R. (2008). "Heritability in the genomics era — concepts and misconceptions". Nature Reviews Genetics (Londres) 9 (4): 255–266. ISSN 1471-0056. PMID 18319743. doi:10.1038/nrg2322.
- ↑ Oetting, William S.; Brilliant, Murray H.; King, Richard A. (1996). "The clinical spectrum of albinism in humans". Molecular Medicine Today (Cambridge: Cell Press) 2 (8): 330–335. ISSN 1357-4310. PMID 8796918. doi:10.1016/1357-4310(96)81798-9.
- ↑ 60,0 60,1 Futuyma, Douglas J. (2005). Evolution. Sunderland: Sinauer Associates. ISBN 0-87893-187-2. LCCN 2004029808. OCLC 57311264.
- ↑ Phillips, Patrick C. (2008). "Epistasis—the essential role of gene interactions in the structure and evolution of genetic systems". Nature Reviews Genetics (Londres) 9 (11): 855–867. ISSN 1471-0056. PMC 2689140. PMID 18852697. doi:10.1038/nrg2452.
- ↑ 62,0 62,1 Rongling Wu; Min Lin (2006). "Functional mapping — how to map and study the genetic architecture of dynamic complex traits". Nature Reviews Genetics (Londres) 7 (3): 229–237. ISSN 1471-0056. PMID 16485021. doi:10.1038/nrg1804.
- ↑ Jablonka, Eva; Raz, Gal (2009). "Transgenerational Epigenetic Inheritance: Prevalence, Mechanisms, and Implications for the Study of Heredity and Evolution". The Quarterly Review of Biology (University of Chicago Press) 84 (2): 131–176. ISSN 0033-5770. PMID 19606595. doi:10.1086/598822.
- ↑ Bossdorf, Oliver; Arcuri, Davide; Richards, Christina L.; Pigliucci, Massimo (2010). "Experimental alteration of DNA methylation affects the phenotypic plasticity of ecologically relevant traits in Arabidopsis thaliana". Evolutionary Ecology (Dordrecht: Springer Netherlands) 24 (3): 541–553. ISSN 0269-7653. doi:10.1007/s10682-010-9372-7.
- ↑ Jablonka, Eva; Lamb, Marion J. (2005). Evolution in Four Dimensions: Genetic, Epigenetic, Behavioral, and Symbolic Variation in the History of Life. Ilustrado por Anna Zeligowski. MIT Press. ISBN 0-262-10107-6. LCCN 2004058193. OCLC 61896061.
- ↑ Jablonka, Eva; Lamb, Marion J. (2002). "The Changing Concept of Epigenetics". Annals of the New York Academy of Sciences (Wiley-Blackwell) 981 (1): 82–96. Bibcode:2002NYASA.981...82J. ISSN 0077-8923. PMID 12547675. doi:10.1111/j.1749-6632.2002.tb04913.x.
- ↑ Laland, Kevin N.; Sterelny, Kim (2006). "Perspective: Seven Reasons (Not) to Neglect Niche Construction". Evolution (John Wiley & Sons) 60 (9): 1751–1762. ISSN 0014-3820. doi:10.1111/j.0014-3820.2006.tb00520.x.
- ↑ Chapman, Michael J.; Margulis, Lynn (1998). "Morphogenesis by symbiogenesis" (PDF). International Microbiology (Barcelona: Socidedad Española para la Microbiología) 1 (4): 319–326. ISSN 1139-6709. PMID 10943381. Arquivado dende o orixinal (PDF) o 23 de agosto de 2014. Consultado o 16 de xullo de 2013.
- ↑ Wilson, David Sloan; Wilson, Edward O. (2007). "Rethinking the Theoretical Foundation of Sociobiology" (PDF). The Quarterly Review of Biology (University of Chicago Press) 82 (4): 327–348. ISSN 0033-5770. PMID 18217526. doi:10.1086/522809. Arquivado dende o orixinal (PDF) o 11 de maio de 2011. Consultado o 16 de xullo de 2013.
- ↑ Amos, William; Harwood, John (28 de febreiro de 1998). "Factors affecting levels of genetic diversity in natural populations". Philosophical Transactions of the Royal Society B: Biological Sciences (Londres: Royal Society) 353 (1366): 177–186. ISSN 0962-8436. PMC 1692205. PMID 9533122. doi:10.1098/rstb.1998.0200.
- ↑ 71,0 71,1 Ewens, Warren J. (2004). Mathematical Population Genetics. Interdisciplinary Applied Mathematics. I. Theoretical Introduction (2ª ed.). Nova York: Springer-Verlag New York. ISBN 0-387-20191-2. LCCN 2003065728. OCLC 53231891.
- ↑ Butlin, Roger K.; Tregenza, Tom (28 de febreiro de 1998). "Levels of genetic polymorphism: marker loci versus quantitative traits". Philosophical Transactions of the Royal Society B: Biological Sciences (Londres: Royal Society) 353 (1366): 187–198. ISSN 0962-8436. PMC 1692210. PMID 9533123. doi:10.1098/rstb.1998.0201.
- ↑ *Butlin, Roger K.; Tregenza, Tom (29 de decembro de 2000). "Correction for Butlin and Tregenza, Levels of genetic polymorphism: marker loci versus quantitative traits". Philosophical Transactions of the Royal Society B: Biological Sciences (Londres: Royal Society) 355 (1404): 1865. ISSN 0962-8436. doi:10.1098/rstb.2000.2000.
- ↑ Wetterbom, Anna; Sevov, Marie; Cavelier, Lucia; Bergström, Tomas F. (2006). "Comparative Genomic Analysis of Human and Chimpanzee Indicates a Key Role for Indels in Primate Evolution". Journal of Molecular Evolution (Nova York: Springer-Verlag New York) 63 (5): 682–690. ISSN 0022-2844. PMID 17075697. doi:10.1007/s00239-006-0045-7.
- ↑ Sawyer SA, Parsch J, Zhang Z, Hartl DL (2007). "Prevalence of positive selection among nearly neutral amino acid replacements in Drosophila". Proc. Natl. Acad. Sci. U.S.A. 104 (16): 6504–10. Bibcode:2007PNAS..104.6504S. PMC 1871816. PMID 17409186. doi:10.1073/pnas.0701572104.
- ↑ Hastings, P J; Lupski, JR; Rosenberg, SM; Ira, G (2009). "Mechanisms of change in gene copy number". Nature Reviews. Genetics 10 (8): 551–564. PMC 2864001. PMID 19597530. doi:10.1038/nrg2593.
- ↑ Sean B. Carroll; Jennifer K. Grenier; Scott D. Weatherbee. (2005). From DNA to Diversity: Molecular Genetics and the Evolution of Animal Design. Second Edition. Oxford: Blackwell Publishing. ISBN 1-4051-1950-0.
- ↑ Harrison P, Gerstein M (2002). "Studying genomes through the aeons: protein families, pseudogenes and proteome evolution". J Mol Biol 318 (5): 1155–74. PMID 12083509. doi:10.1016/S0022-2836(02)00109-2.
- ↑ Bowmaker JK (1998). "Evolution of colour vision in vertebrates". Eye (London, England) 12 (Pt 3b): 541–7. PMID 9775215. doi:10.1038/eye.1998.143.
- ↑ Gregory TR, Hebert PD (1999). "The modulation of DNA content: proximate causes and ultimate consequences". Genome Res. 9 (4): 317–24. PMID 10207154. doi:10.1101/gr.9.4.317.
- ↑ Hurles M (2004). "Gene duplication: the genomic trade in spare parts". PLoS Biol. 2 (7): E206. PMC 449868. PMID 15252449. doi:10.1371/journal.pbio.0020206.
- ↑ Liu N, Okamura K, Tyler DM (2008). "The evolution and functional diversification of animal microRNA genes". Cell Res. 18 (10): 985–96. PMC 2712117. PMID 18711447. doi:10.1038/cr.2008.278.
- ↑ Siepel A (2009). "Darwinian alchemy: Human genes from noncoding DNA". Genome Res. 19 (10): 1693–5. PMC 2765273. PMID 19797681. doi:10.1101/gr.098376.109.
- ↑ Orengo CA, Thornton JM (2005). "Protein families and their evolution-a structural perspective". Annu. Rev. Biochem. 74 (1): 867–900. PMID 15954844. doi:10.1146/annurev.biochem.74.082803.133029.
- ↑ Long M, Betrán E, Thornton K, Wang W (2003). "The origin of new genes: glimpses from the young and old". Nat. Rev. Genet. 4 (11): 865–75. PMID 14634634. doi:10.1038/nrg1204.
- ↑ Wang M, Caetano-Anollés G (2009). "The evolutionary mechanics of domain organization in proteomes and the rise of modularity in the protein world". Structure 17 (1): 66–78. PMID 19141283. doi:10.1016/j.str.2008.11.008.
- ↑ Weissman KJ, Müller R (2008). "Protein-protein interactions in multienzyme megasynthetases". Chembiochem 9 (6): 826–48. PMID 18357594. doi:10.1002/cbic.200700751.
- ↑ Radding C (1982). "Homologous pairing and strand exchange in genetic recombination". Annu. Rev. Genet. 16 (1): 405–37. PMID 6297377. doi:10.1146/annurev.ge.16.120182.002201.
- ↑ Agrawal AF (2006). "Evolution of sex: why do organisms shuffle their genotypes?". Curr. Biol. 16 (17): R696–704. PMID 16950096. doi:10.1016/j.cub.2006.07.063.
- ↑ Peters AD, Otto SP (2003). "Liberating genetic variance through sex". BioEssays 25 (6): 533–7. PMID 12766942. doi:10.1002/bies.10291.
- ↑ Goddard MR, Godfray HC, Burt A (2005). "Sex increases the efficacy of natural selection in experimental yeast populations". Nature 434 (7033): 636–40. Bibcode:2005Natur.434..636G. PMID 15800622. doi:10.1038/nature03405.
- ↑ 92,0 92,1 Morjan C, Rieseberg L (2004). "How species evolve collectively: implications of gene flow and selection for the spread of advantageous alleles". Mol. Ecol. 13 (6): 1341–56. PMC 2600545. PMID 15140081. doi:10.1111/j.1365-294X.2004.02164.x.
- ↑ Boucher Y, Douady CJ, Papke RT, Walsh DA, Boudreau ME, Nesbo CL, Case RJ, Doolittle WF (2003). "Lateral gene transfer and the origins of prokaryotic groups". Annu Rev Genet 37 (1): 283–328. PMID 14616063. doi:10.1146/annurev.genet.37.050503.084247.
- ↑ Walsh T (2006). "Combinatorial genetic evolution of multiresistance". Curr. Opin. Microbiol. 9 (5): 476–82. PMID 16942901. doi:10.1016/j.mib.2006.08.009.
- ↑ Kondo N, Nikoh N, Ijichi N, Shimada M, Fukatsu T (2002). "Genome fragment of Wolbachia endosymbiont transferred to X chromosome of host insect". Proc. Natl. Acad. Sci. U.S.A. 99 (22): 14280–5. Bibcode:2002PNAS...9914280K. PMC 137875. PMID 12386340. doi:10.1073/pnas.222228199.
- ↑ Sprague G (1991). "Genetic exchange between kingdoms". Curr. Opin. Genet. Dev. 1 (4): 530–3. PMID 1822285. doi:10.1016/S0959-437X(05)80203-5.
- ↑ Gladyshev EA, Meselson M, Arkhipova IR (2008). "Massive horizontal gene transfer in bdelloid rotifers". Science 320 (5880): 1210–3. Bibcode:2008Sci...320.1210G. PMID 18511688. doi:10.1126/science.1156407.
- ↑ Baldo A, McClure M (September 1, 1999). "Evolution and horizontal transfer of dUTPase-encoding genes in viruses and their hosts". J. Virol. 73 (9): 7710–21. PMC 104298. PMID 10438861.
- ↑ Rivera, M. C. and Lake, J. A. (2004). "The ring of life provides evidence for a genome fusion origin of eukaryotes". Nature 431 (9): 152–5. Bibcode:2004Natur.431..152R. PMID 15356622. doi:10.1038/nature02848.
- ↑ 100,0 100,1 100,2 Hurst LD (2009). "Fundamental concepts in genetics: genetics and the understanding of selection". Nat. Rev. Genet. 10 (2): 83–93. PMID 19119264. doi:10.1038/nrg2506.
- ↑ 101,0 101,1 101,2 Orr HA (2009). "Fitness and its role in evolutionary genetics". Nat. Rev. Genet. 10 (8): 531–9. PMC 2753274. PMID 19546856. doi:10.1038/nrg2603.
- ↑ Haldane J (1959). "The theory of natural selection today". Nature 183 (4663): 710–3. Bibcode:1959Natur.183..710H. PMID 13644170. doi:10.1038/183710a0.
- ↑ Lande R, Arnold SJ (1983). "The measurement of selection on correlated characters". Evolution 37 (6): 1210–26. JSTOR 2408842. doi:10.2307/2408842.
- ↑ Goldberg, Emma E; Igić, B (2008). "On phylogenetic tests of irreversible evolution". Evolution 62 (11): 2727–2741. PMID 18764918. doi:10.1111/j.1558-5646.2008.00505.x.
- ↑ Collin, Rachel; Miglietta, MP (2008). "Reversing opinions on Dollo's Law". Trends in Ecology & Evolution 23 (11): 602–609. PMID 18814933. doi:10.1016/j.tree.2008.06.013.
- ↑ Hoekstra H, Hoekstra J, Berrigan D, Vignieri S, Hoang A, Hill C, Beerli P, Kingsolver J (2001). "Strength and tempo of directional selection in the wild". Proc. Natl. Acad. Sci. U.S.A. 98 (16): 9157–60. Bibcode:2001PNAS...98.9157H. PMC 55389. PMID 11470913. doi:10.1073/pnas.161281098.
- ↑ Felsenstein (November 1, 1979). "Excursions along the Interface between Disruptive and Stabilizing Selection". Genetics 93 (3): 773–95. PMC 1214112. PMID 17248980.
- ↑ Andersson M, Simmons L (2006). "Sexual selection and mate choice". Trends Ecol. Evol. (Amst.) 21 (6): 296–302. PMID 16769428. doi:10.1016/j.tree.2006.03.015.
- ↑ Kokko H, Brooks R, McNamara J, Houston A (2002). "The sexual selection continuum". Proc. Biol. Sci. 269 (1498): 1331–40. PMC 1691039. PMID 12079655. doi:10.1098/rspb.2002.2020.
- ↑ Hunt J, Brooks R, Jennions M, Smith M, Bentsen C, Bussière L (2004). "High-quality male field crickets invest heavily in sexual display but die young". Nature 432 (7020): 1024–7. Bibcode:2004Natur.432.1024H. PMID 15616562. doi:10.1038/nature03084.
- ↑ Odum, Eugene P. (1971). Fundamentals of Ecology (3ª ed.). Saunders. ISBN 0-7216-6941-7. LCCN 76081826. OCLC 154846.
- ↑ Okasha, Samir (2006). Evolution and the Levels of Selection. Oxford University Press. ISBN 0-19-926797-9. LCCN 2006039679. OCLC 70985413.
- ↑ 113,0 113,1 Gould SJ (1998). "Gulliver's further travels: the necessity and difficulty of a hierarchical theory of selection". Philos. Trans. R. Soc. Lond., B, Biol. Sci. 353 (1366): 307–14. PMC 1692213. PMID 9533127. doi:10.1098/rstb.1998.0211.
- ↑ Mayr E (1997). "The objects of selection". Proc. Natl. Acad. Sci. U.S.A. 94 (6): 2091–4. Bibcode:1997PNAS...94.2091M. PMC 33654. PMID 9122151. doi:10.1073/pnas.94.6.2091.
- ↑ Maynard Smith J (1998). "The units of selection". Novartis Found. Symp. 213: 203–11; discussion 211–7. PMID 9653725.
- ↑ Hickey DA (1992). "Evolutionary dynamics of transposable elements in prokaryotes and eukaryotes". Genetica 86 (1–3): 269–74. PMID 1334911. doi:10.1007/BF00133725.
- ↑ Gould SJ, Lloyd EA (1999). "Individuality and adaptation across levels of selection: how shall we name and generalise the unit of Darwinism?". Proc. Natl. Acad. Sci. U.S.A. 96 (21): 11904–9. Bibcode:1999PNAS...9611904G. PMC 18385. PMID 10518549. doi:10.1073/pnas.96.21.11904.
- ↑ Lynch, M. (2007). "The frailty of adaptive hypotheses for the origins of organismal complexity". PNAS 104 (suppl. 1): 8597–8604. Bibcode:2007PNAS..104.8597L. PMC 1876435. PMID 17494740. doi:10.1073/pnas.0702207104.
- ↑ Smith N.G.C., Webster M.T., Ellegren, H. (2002). "Deterministic Mutation Rate Variation in the Human Genome". Genome Research 12 (9): 1350–1356. PMC 186654. PMID 12213772. doi:10.1101/gr.220502.
- ↑ Petrov DA, Sangster TA, Johnston JS, Hartl DL, Shaw KL (2000). "Evidence for DNA loss as a determinant of genome size". Science 287 (5455): 1060–1062. Bibcode:2000Sci...287.1060P. PMID 10669421. doi:10.1126/science.287.5455.1060.
- ↑ Petrov DA (2002). "DNA loss and evolution of genome size in Drosophila". Genetica 115 (1): 81–91. PMID 12188050. doi:10.1023/A:1016076215168.
- ↑ Kiontke K, Barriere A , Kolotuev I, Podbilewicz B , Sommer R, Fitch DHA , Felix MA (2007). "Trends, stasis, and drift in the evolution of nematode vulva development". Current Biology 17 (22): 1925–1937. PMID 18024125. doi:10.1016/j.cub.2007.10.061.
- ↑ Braendle C, Baer CF, Felix MA (2010). Barsh, Gregory S, ed. "Bias and Evolution of the Mutationally Accessible Phenotypic Space in a Developmental System". PLoS Genetics 6 (3): e1000877. PMC 2837400. PMID 20300655. doi:10.1371/journal.pgen.1000877. e1000877.
- ↑ Palmer, RA (2004). "Symmetry breaking and the evolution of development". Science 306 (5697): 828–833. Bibcode:2004Sci...306..828P. PMID 15514148. doi:10.1126/science.1103707.
- ↑ West-Eberhard, M-J. (2003). Developmental plasticity and evolution. New York: Oxford University Press. ISBN 978-0-19-512235-0.
- ↑ Stoltzfus, A and Yampolsky, L.Y. (2009). "Climbing Mount Probable: Mutation as a Cause of Nonrandomness in Evolution". J Hered 100 (5): 637–647. PMID 19625453. doi:10.1093/jhered/esp048.
- ↑ Yampolsky, L.Y. and Stoltzfus, A (2001). "Bias in the introduction of variation as an orienting factor in evolution". Evol Dev 3 (2): 73–83. PMID 11341676. doi:10.1046/j.1525-142x.2001.003002073.x.
- ↑ Haldane, JBS (1933). "The Part Played by Recurrent Mutation in Evolution". American Naturalist 67 (708): 5–19. JSTOR 2457127. doi:10.1086/280465.
- ↑ Protas, Meredith; Conrad, M; Gross, JB; Tabin, C; Borowsky, R (2007). "Regressive evolution in the Mexican cave tetra, Astyanax mexicanus". Current Biology 17 (5): 452–454. PMC 2570642. PMID 17306543. doi:10.1016/j.cub.2007.01.051.
- ↑ Maughan H, Masel J, Birky WC, Nicholson WL (2007). "The roles of mutation accumulation and selection in loss of sporulation in experimental populations of Bacillus subtilis". Genetics 177 (2): 937–948. PMC 2034656. PMID 17720926. doi:10.1534/genetics.107.075663.
- ↑ Masel J, King OD, Maughan H (2007). "The loss of adaptive plasticity during long periods of environmental stasis". American Naturalist 169 (1): 38–46. PMC 1766558. PMID 17206583. doi:10.1086/510212.
- ↑ 132,0 132,1 Masel J (2011). "Genetic drift". Current Biology 21 (20): R837–R838. PMID 22032182. doi:10.1016/j.cub.2011.08.007.
- ↑ Lande R (1989). "Fisherian and Wrightian theories of speciation". Genome 31 (1): 221–7. PMID 2687093. doi:10.1139/g89-037.
- ↑ Mitchell-Olds, Thomas; Willis, JH; Goldstein, DB (2007). "Which evolutionary processes influence natural genetic variation for phenotypic traits?". Nature Reviews Genetics 8 (11): 845–856. PMID 17943192. doi:10.1038/nrg2207.
- ↑ Nei M (2005). "Selectionism and neutralism in molecular evolution". Mol. Biol. Evol. 22 (12): 2318–42. PMC 1513187. PMID 16120807. doi:10.1093/molbev/msi242.
- ↑ Kimura M (1989). "The neutral theory of molecular evolution and the world view of the neutralists". Genome 31 (1): 24–31. PMID 2687096. doi:10.1139/g89-009.
- ↑ Kreitman M (1996). "The neutral theory is dead. Long live the neutral theory". BioEssays 18 (8): 678–83; discussion 683. PMID 8760341. doi:10.1002/bies.950180812.
- ↑ Leigh E.G. (Jr) (2007). "Neutral theory: a historical perspective". Journal of Evolutionary Biology 20 (6): 2075–91. PMID 17956380. doi:10.1111/j.1420-9101.2007.01410.x.
- ↑ 139,0 139,1 Gillespie, John H. (2001). "Is the population size of a species relevant to its evolution?". Evolution 55 (11): 2161–2169. PMID 11794777.
- ↑ R.A. Neher and B.I. Shraiman (2011). "Genetic Draft and Quasi-Neutrality in Large Facultatively Sexual Populations". Genetics 188 (4): 975–996. PMC 3176096. PMID 21625002. doi:10.1534/genetics.111.128876.
- ↑ Otto S, Whitlock M (June 1, 1997). "The probability of fixation in populations of changing size". Genetics 146 (2): 723–33. PMC 1208011. PMID 9178020.
- ↑ 142,0 142,1 Charlesworth B (2009). "Fundamental concepts in genetics: Effective population size and patterns of molecular evolution and variation". Nat. Rev. Genet. 10 (3): 195–205. PMID 19204717. doi:10.1038/nrg2526.
- ↑ Asher D. Cutter and Jae Young Choi (2010). "Natural selection shapes nucleotide polymorphism across the genome of the nematode Caenorhabditis briggsae". Genome Research 20 (8): 1103–1111. PMC 2909573. PMID 20508143. doi:10.1101/gr.104331.109.
- ↑ Lien S, Szyda J, Schechinger B, Rappold G, Arnheim N (2000). "Evidence for heterogeneity in recombination in the human pseudoautosomal region: high resolution analysis by sperm typing and radiation-hybrid mapping". Am. J. Hum. Genet. 66 (2): 557–66. PMC 1288109. PMID 10677316. doi:10.1086/302754.
- ↑ Barton, N H (2000). "Genetic hitchhiking". Philosophical Transactions of the Royal Society of London. Series B, Biological Sciences 355 (1403): 1553–1562. PMC 1692896. PMID 11127900. doi:10.1098/rstb.2000.0716.
- ↑ Wright, Sewall (1932). "The roles of mutation, inbreeding, crossbreeding and selection in evolution". Proc. 6th Int. Cong. Genet 1: 356–366.
- ↑ Coyne, Jerry A.; Barton, Turelli (1997). "Perspective: A Critique of Sewall Wright's Shifting Balance Theory of Evolution". Evolution. 3 51 (3): 643–671. doi:10.2307/2411143.
- ↑ 148,0 148,1 148,2 Scott EC, Matzke NJ (2007). "Biological design in science classrooms". Proc. Natl. Acad. Sci. U.S.A. 104 (suppl_1): 8669–76. Bibcode:2007PNAS..104.8669S. PMC 1876445. PMID 17494747. doi:10.1073/pnas.0701505104.
- ↑ Hendry AP, Kinnison MT (2001). "An introduction to microevolution: rate, pattern, process". Genetica. 112–113: 1–8. PMID 11838760. doi:10.1023/A:1013368628607.
- ↑ Leroi AM (2000). "The scale independence of evolution". Evol. Dev. 2 (2): 67–77. PMID 11258392. doi:10.1046/j.1525-142x.2000.00044.x.
- ↑ Gould 2002, pp. 657–658
- ↑ Gould SJ (1994). "Tempo and mode in the macroevolutionary reconstruction of Darwinism". Proc. Natl. Acad. Sci. U.S.A. 91 (15): 6764–71. Bibcode:1994PNAS...91.6764G. PMC 44281. PMID 8041695. doi:10.1073/pnas.91.15.6764.
- ↑ Jablonski, D. (2000). "Micro- and macroevolution: scale and hierarchy in evolutionary biology and paleobiology". Paleobiology 26 (sp4): 15–52. doi:10.1666/0094-8373(2000)26[15:MAMSAH]2.0.CO;2.
- ↑ Dougherty, Michael J. (20 de xullo de 1998). "Is the human race evolving or devolving?". Scientific American (Stuttgart: Georg von Holtzbrinck Publishing Group). ISSN 0036-8733.
- ↑ Carroll SB (2001). "Chance and necessity: the evolution of morphological complexity and diversity". Nature 409 (6823): 1102–9. PMID 11234024. doi:10.1038/35059227.
- ↑ Whitman W, Coleman D, Wiebe W (1998). "Prokaryotes: the unseen majority". Proc Natl Acad Sci U S A 95 (12): 6578–83. Bibcode:1998PNAS...95.6578W. PMC 33863. PMID 9618454. doi:10.1073/pnas.95.12.6578.
- ↑ 157,0 157,1 Schloss P, Handelsman J (2004). "Status of the microbial census". Microbiol Mol Biol Rev 68 (4): 686–91. PMC 539005. PMID 15590780. doi:10.1128/MMBR.68.4.686-691.2004.
- ↑ Nealson K (1999). "Post-Viking microbiology: new approaches, new data, new insights". Orig Life Evol Biosph 29 (1): 73–93. PMID 11536899. doi:10.1023/A:1006515817767.
- ↑ Buckling A, Craig Maclean R, Brockhurst MA, Colegrave N (2009). "The Beagle in a bottle". Nature 457 (7231): 824–9. Bibcode:2009Natur.457..824B. PMID 19212400. doi:10.1038/nature07892.
- ↑ Elena SF, Lenski RE (2003). "Evolution experiments with microorganisms: the dynamics and genetic bases of adaptation". Nat. Rev. Genet. 4 (6): 457–69. PMID 12776215. doi:10.1038/nrg1088.
- ↑ Mayr 1982, p. 483: "A adaptación... xa non pode ser considerada unha condición estática, un produto dun pasado creativo e en vez diso converteuse nun proceso dinámico continuado."
- ↑ A sexta edición do Oxford Dictionary of Science (2010) define a adaptación como calquera cambio na estrutura ou funcionamento dun organismo que o fai máis axeitado para o seu ambiente.
- ↑ Orr H (2005). "The genetic theory of adaptation: a brief history". Nat. Rev. Genet. 6 (2): 119–27. PMID 15716908. doi:10.1038/nrg1523.
- ↑ Dobzhansky, Theodosius (1968). "On Some Fundamental Concepts of Darwinian Biology". En Dobzhansky, Theodosius; Hecht, Max K.; Steere, William C. Evolutionary Biology. Volume 2 (1ª ed.). Nova York: Appleton-Century-Crofts. pp. 1–34. OCLC 24875357. doi:10.1007/978-1-4684-8094-8_1.
- ↑ * Dobzhansky, Theodosius (1970). Genetics of the Evolutionary Process. Nova York: Columbia University Press. pp. 4–6, 79–82, 84–87. ISBN 0-231-02837-7. LCCN 72127363. OCLC 97663.
- ↑ Dobzhansky, Theodosius (1956). "Genetics of Natural Populations. XXV. Genetic Changes in Populations of Drosophila pseudoobscura and Drosophila persimilis in Some Localities in California". Evolution (John Wiley & Sons) 10 (1): 82–92. ISSN 0014-3820. JSTOR 2406099. doi:10.2307/2406099.
- ↑ Nakajima A, Sugimoto Y, Yoneyama H, Nakae T (2002). "High-level fluoroquinolone resistance in Pseudomonas aeruginosa due to interplay of the MexAB-OprM efflux pump and the DNA gyrase mutation". Microbiol. Immunol. 46 (6): 391–5. PMID 12153116.
- ↑ Blount ZD, Borland CZ, Lenski RE (2008). "Inaugural Article: Historical contingency and the evolution of a key innovation in an experimental population of Escherichia coli". Proc. Natl. Acad. Sci. U.S.A. 105 (23): 7899–906. Bibcode:2008PNAS..105.7899B. PMC 2430337. PMID 18524956. doi:10.1073/pnas.0803151105.
- ↑ Okada H, Negoro S, Kimura H, Nakamura S (1983). "Evolutionary adaptation of plasmid-encoded enzymes for degrading nylon oligomers". Nature 306 (5939): 203–6. Bibcode:1983Natur.306..203O. PMID 6646204. doi:10.1038/306203a0.
- ↑ Ohno S (1984). "Birth of a unique enzyme from an alternative reading frame of the preexisted, internally repetitious coding sequence". Proc. Natl. Acad. Sci. U.S.A. 81 (8): 2421–5. Bibcode:1984PNAS...81.2421O. PMC 345072. PMID 6585807. doi:10.1073/pnas.81.8.2421.
- ↑ Copley SD (2000). "Evolution of a metabolic pathway for degradation of a toxic xenobiotic: the patchwork approach". Trends Biochem. Sci. 25 (6): 261–5. PMID 10838562. doi:10.1016/S0968-0004(00)01562-0.
- ↑ Crawford RL, Jung CM, Strap JL (2007). "The recent evolution of pentachlorophenol (PCP)-4-monooxygenase (PcpB) and associated pathways for bacterial degradation of PCP". Biodegradation 18 (5): 525–39. PMID 17123025. doi:10.1007/s10532-006-9090-6.
- ↑ Eshel I (1973). "Clone-selection and optimal rates of mutation". Journal of Applied Probability 10 (4): 728–738. JSTOR 3212376. doi:10.2307/3212376.
- ↑ Masel J, Bergman A, (2003). "The evolution of the evolvability properties of the yeast prion [PSI+]". Evolution 57 (7): 1498–1512. PMID 12940355.
- ↑ Lancaster AK, Bardill JP, True HL, Masel J (2010). "The Spontaneous Appearance Rate of the Yeast Prion [PSI+] and Its Implications for the Evolution of the Evolvability Properties of the [PSI+] System". Genetics 184 (2): 393–400. PMC 2828720. PMID 19917766. doi:10.1534/genetics.109.110213.
- ↑ Draghi J, Wagner G (2008). "Evolution of evolvability in a developmental model". Theoretical Population Biology 62: 301–315.
- ↑ 177,0 177,1 Bejder L, Hall BK (2002). "Limbs in whales and limblessness in other vertebrates: mechanisms of evolutionary and developmental transformation and loss". Evol. Dev. 4 (6): 445–58. PMID 12492145. doi:10.1046/j.1525-142X.2002.02033.x.
- ↑ Young, Nathan M.; Hallgrímsson, B (2005). "Serial homology and the evolution of mammalian limb covariation structure". Evolution 59 (12): 2691–704. PMID 16526515. doi:10.1554/05-233.1. Consultado o September 24, 2009.
- ↑ 179,0 179,1 Penny D, Poole A (1999). "The nature of the last universal common ancestor". Curr. Opin. Genet. Dev. 9 (6): 672–77. PMID 10607605. doi:10.1016/S0959-437X(99)00020-9.
- ↑ Hall, Brian K (2003). "Descent with modification: the unity underlying homology and homoplasy as seen through an analysis of development and evolution". Biological Reviews of the Cambridge Philosophical Society 78 (3): 409–433. PMID 14558591. doi:10.1017/S1464793102006097.
- ↑ Shubin, Neil; Tabin, C; Carroll, S (2009). "Deep homology and the origins of evolutionary novelty". Nature 457 (7231): 818–823. Bibcode:2009Natur.457..818S. PMID 19212399. doi:10.1038/nature07891.
- ↑ 182,0 182,1 Fong D, Kane T, Culver D (1995). "Vestigialization and Loss of Nonfunctional Characters". Ann. Rev. Ecol. Syst. 26 (4): 249–68. doi:10.1146/annurev.es.26.110195.001341.
- ↑ Zhang Z, Gerstein M (2004). "Large-scale analysis of pseudogenes in the human genome". Curr. Opin. Genet. Dev. 14 (4): 328–35. PMID 15261647. doi:10.1016/j.gde.2004.06.003.
- ↑ Jeffery WR (2005). "Adaptive evolution of eye degeneration in the Mexican blind cavefish". J. Hered. 96 (3): 185–96. PMID 15653557. doi:10.1093/jhered/esi028.
- ↑ Maxwell EE, Larsson HC (2007). "Osteology and myology of the wing of the Emu (Dromaius novaehollandiae) and its bearing on the evolution of vestigial structures". J. Morphol. 268 (5): 423–41. PMID 17390336. doi:10.1002/jmor.10527.
- ↑ Silvestri AR, Singh I (2003). "The unresolved problem of the third molar: would people be better off without it?". Journal of the American Dental Association (1939) 134 (4): 450–5. PMID 12733778. Arquivado dende o orixinal o 23 de agosto de 2014. Consultado o 16 de xullo de 2013.
- ↑ Coyne 2009, p. 62
- ↑ * Darwin, Charles (1872). The Expression of the Emotions in Man and Animals. Londres: John Murray. pp. 101, 103. LCCN 04002793. OCLC 1102785.
- ↑ Peter Gray (2007). Psychology (fifth ed.). Worth Publishers. p. 66. ISBN 0-7167-0617-2.
- ↑ Coyne 2009, pp. 85–86
- ↑ Anthony Stevens (1982). Archetype: A Natural History of the Self. Routledge & Kegan Paul. p. 87. ISBN 0-7100-0980-1.
- ↑ 192,0 192,1 Gould, S.J. (2002). The Structure of Evolutionary Theory. Cambridge: Belknap Press (Harvard University Press). ISBN 978-0-674-00613-3. Páxinas 1235-36.
- ↑ Pallen, Mark J.; Matzke, NJ (2006-10). "From The Origin of Species to the origin of bacterial flagella" (PDF). Nat Rev Micro 4 (10): 784–790. PMID 16953248. doi:10.1038/nrmicro1493. Consultado o September 18, 2009.
- ↑ Clements, Abigail; Bursac, D; Gatsos, X; Perry, AJ; Civciristov, S; Celik, N; Likic, VA; Poggio, S; Jacobs-Wagner, C (2009). "The reducible complexity of a mitochondrial molecular machine". Proceedings of the National Academy of Sciences 106 (37): 15791–15795. Bibcode:2009PNAS..10615791C. PMC 2747197. PMID 19717453. doi:10.1073/pnas.0908264106.
- ↑ Piatigorsky J, Kantorow M, Gopal-Srivastava R, Tomarev SI (1994). "Recruitment of enzymes and stress proteins as lens crystallins". EXS 71: 241–50. PMID 8032155.
- ↑ Wistow G (1993). "Lens crystallins: gene recruitment and evolutionary dynamism". Trends Biochem. Sci. 18 (8): 301–6. PMID 8236445. doi:10.1016/0968-0004(93)90041-K.
- ↑ Johnson NA, Porter AH (2001). "Toward a new synthesis: population genetics and evolutionary developmental biology". Genetica. 112–113: 45–58. PMID 11838782. doi:10.1023/A:1013371201773.
- ↑ Baguñà J, Garcia-Fernàndez J (2003). "Evo-Devo: the long and winding road". Int. J. Dev. Biol. 47 (7–8): 705–13. PMID 14756346.
*Love AC. (2003). "Evolutionary Morphology, Innovation and the Synthesis of Evolutionary and Developmental Biology". Biology and Philosophy 18 (2): 309–345. doi:10.1023/A:1023940220348. - ↑ Allin EF (1975). "Evolution of the mammalian middle ear". J. Morphol. 147 (4): 403–37. PMID 1202224. doi:10.1002/jmor.1051470404.
- ↑ Harris MP, Hasso SM, Ferguson MW, Fallon JF (2006). "The development of archosaurian first-generation teeth in a chicken mutant". Curr. Biol. 16 (4): 371–7. PMID 16488870. doi:10.1016/j.cub.2005.12.047.
- ↑ Carroll SB (2008). "Evo-devo and an expanding evolutionary synthesis: a genetic theory of morphological evolution". Cell 134 (1): 25–36. PMID 18614008. doi:10.1016/j.cell.2008.06.030.
- ↑ Wade MJ (2007). "The co-evolutionary genetics of ecological communities". Nat. Rev. Genet. 8 (3): 185–95. PMID 17279094. doi:10.1038/nrg2031.
- ↑ Geffeney S, Brodie ED, Ruben PC, Brodie ED (2002). "Mechanisms of adaptation in a predator-prey arms race: TTX-resistant sodium channels". Science 297 (5585): 1336–9. Bibcode:2002Sci...297.1336G. PMID 12193784. doi:10.1126/science.1074310.
*Brodie ED, Ridenhour BJ, Brodie ED (2002). "The evolutionary response of predators to dangerous prey: hotspots and coldspots in the geographic mosaic of coevolution between garter snakes and newts". Evolution 56 (10): 2067–82. PMID 12449493.
*Sean B. Carroll (December 21, 2009). "Remarkable Creatures – Clues to Toxins in Deadly Delicacies of the Animal Kingdom". New York Times. - ↑ Sachs J (2006). "Cooperation within and among species". J. Evol. Biol. 19 (5): 1415–8; discussion 1426–36. PMID 16910971. doi:10.1111/j.1420-9101.2006.01152.x.
*Nowak M (2006). "Five rules for the evolution of cooperation". Science 314 (5805): 1560–3. Bibcode:2006Sci...314.1560N. PMC 3279745. PMID 17158317. doi:10.1126/science.1133755. - ↑ Paszkowski U (2006). "Mutualism and parasitism: the yin and yang of plant symbioses". Curr. Opin. Plant Biol. 9 (4): 364–70. PMID 16713732. doi:10.1016/j.pbi.2006.05.008.
- ↑ Hause B, Fester T (2005). "Molecular and cell biology of arbuscular mycorrhizal symbiosis". Planta 221 (2): 184–96. PMID 15871030. doi:10.1007/s00425-004-1436-x.
- ↑ Bertram J (2000). "The molecular biology of cancer". Mol. Aspects Med. 21 (6): 167–223. PMID 11173079. doi:10.1016/S0098-2997(00)00007-8.
- ↑ Reeve HK, Hölldobler B (2007). "The emergence of a superorganism through intergroup competition". Proc Natl Acad Sci U S A. 104 (23): 9736–40. Bibcode:2007PNAS..104.9736R. PMC 1887545. PMID 17517608. doi:10.1073/pnas.0703466104.
- ↑ Axelrod R, Hamilton W (2005). "The evolution of cooperation". Science 211 (4489): 1390–6. Bibcode:1981Sci...211.1390A. PMID 7466396. doi:10.1126/science.7466396.
- ↑ Wilson EO, Hölldobler B (2005). "Eusociality: origin and consequences". Proc. Natl. Acad. Sci. U.S.A. 102 (38): 13367–71. Bibcode:2005PNAS..10213367W. PMC 1224642. PMID 16157878. doi:10.1073/pnas.0505858102.
- ↑ 211,0 211,1 Gavrilets S (2003). "Perspective: models of speciation: what have we learned in 40 years?". Evolution 57 (10): 2197–215. PMID 14628909. doi:10.1554/02-727.
- ↑ 212,0 212,1 212,2 de Queiroz K (2005). "Ernst Mayr and the modern concept of species". Proc. Natl. Acad. Sci. U.S.A. 102 (Suppl 1): 6600–7. Bibcode:2005PNAS..102.6600D. PMC 1131873. PMID 15851674. doi:10.1073/pnas.0502030102.
- ↑ 213,0 213,1 Ereshefsky, M. (1992). "Eliminative pluralism". Philosophy of Science 59 (4): 671–690. JSTOR 188136. doi:10.1086/289701.
- ↑ Mayr, E. (1942). Systematics and the Origin of Species. New York: Columbia Univ. Press. p. 120. ISBN 978-0-231-05449-2.
- ↑ Fraser C, Alm EJ, Polz MF, Spratt BG, Hanage WP (2009). "The bacterial species challenge: making sense of genetic and ecological diversity". Science 323 (5915): 741–6. Bibcode:2009Sci...323..741F. PMID 19197054. doi:10.1126/science.1159388.
- ↑ Short RV (1975). "The contribution of the mule to scientific thought". J. Reprod. Fertil. Suppl. (23): 359–64. PMID 1107543.
- ↑ Gross B, Rieseberg L (2005). "The ecological genetics of homoploid hybrid speciation". J. Hered. 96 (3): 241–52. PMC 2517139. PMID 15618301. doi:10.1093/jhered/esi026.
- ↑ Burke JM, Arnold ML (2001). "Genetics and the fitness of hybrids". Annu. Rev. Genet. 35 (1): 31–52. PMID 11700276. doi:10.1146/annurev.genet.35.102401.085719.
- ↑ Vrijenhoek RC (2006). "Polyploid hybrids: multiple origins of a treefrog species". Curr. Biol. 16 (7): R245–7. PMID 16581499. doi:10.1016/j.cub.2006.03.005.
- ↑ Rice, W.R.; Hostert (1993). "Laboratory experiments on speciation: what have we learned in 40 years". Evolution 47 (6): 1637–1653. doi:10.2307/2410209.
- Jiggins CD, Bridle JR (2004). "Speciation in the apple maggot fly: a blend of vintages?". Trends Ecol. Evol. (Amst.) 19 (3): 111–4. PMID 16701238. doi:10.1016/j.tree.2003.12.008.
- Boxhorn, J (1995). "Observed Instances of Speciation". TalkOrigins Archive. Consultado o 26 de decembro de 2008.
- Weinberg JR, Starczak VR, Jorg, D (1992). "Evidence for Rapid Speciation Following a Founder Event in the Laboratory". Evolution 46 (4): 1214–20. JSTOR 2409766. doi:10.2307/2409766.
- ↑ Herrel, A.; Huyghe, K.; Vanhooydonck, B.; Backeljau, T.; Breugelmans, K.; Grbac, I.; Van Damme, R.; Irschick, D.J. (2008). "Rapid large-scale evolutionary divergence in morphology and performance associated with exploitation of a different dietary resource". Proceedings of the National Academy of Sciences 105 (12): 4792–5. Bibcode:2008PNAS..105.4792H. PMC 2290806. PMID 18344323. doi:10.1073/pnas.0711998105.
- ↑ Losos, J.B. Warhelt, K.I. Schoener, T.W. (1997). "Adaptive differentiation following experimental island colonization in Anolis lizards". Nature 387 (6628): 70–3. Bibcode:1997Natur.387...70L. doi:10.1038/387070a0.
- ↑ Hoskin CJ, Higgle M, McDonald KR, Moritz C (2005). "Reinforcement drives rapid allopatric speciation". Nature 437 (7063): 1353–356. Bibcode:2005Natur.437.1353H. PMID 16251964. doi:10.1038/nature04004.
- ↑ Templeton AR (April 1, 1980). "The theory of speciation via the founder principle". Genetics 94 (4): 1011–38. PMC 1214177. PMID 6777243.
- ↑ Antonovics J (2006). "Evolution in closely adjacent plant populations X: long-term persistence of prereproductive isolation at a mine boundary". Heredity 97 (1): 33–7. PMID 16639420. doi:10.1038/sj.hdy.6800835.
- ↑ Nosil P, Crespi B, Gries R, Gries G (2007). "Natural selection and divergence in mate preference during speciation". Genetica 129 (3): 309–27. PMID 16900317. doi:10.1007/s10709-006-0013-6.
- ↑ Savolainen V, Anstett M-C, Lexer C, Hutton I, Clarkson JJ, Norup MV, Powell MP, Springate D, Salamin N, Baker WJr (2006). "Sympatric speciation in palms on an oceanic island". Nature 441 (7090): 210–3. Bibcode:2006Natur.441..210S. PMID 16467788. doi:10.1038/nature04566.
*Barluenga M, Stölting KN, Salzburger W, Muschick M, Meyer A (2006). "Sympatric speciation in Nicaraguan crater lake cichlid fish". Nature 439 (7077): 719–23. Bibcode:2006Natur.439..719B. PMID 16467837. doi:10.1038/nature04325. - ↑ Gavrilets S (2006). "The Maynard Smith model of sympatric speciation". J. Theor. Biol. 239 (2): 172–82. PMID 16242727. doi:10.1016/j.jtbi.2005.08.041.
- ↑ Wood TE, Takebayashi N, Barker MS, Mayrose I, Greenspoon PB, Rieseberg LH (2009). "The frequency of polyploid speciation in vascular plants". Proc. Natl. Acad. Sci. U.S.A. 106 (33): 13875–9. Bibcode:2009PNAS..10613875W. PMC 2728988. PMID 19667210. doi:10.1073/pnas.0811575106.
- ↑ Hegarty Mf, Hiscock SJ (2008). "Genomic clues to the evolutionary success of polyploid plants". Current Biology 18 (10): 435–44. PMID 18492478. doi:10.1016/j.cub.2008.03.043.
- ↑ Jakobsson M, Hagenblad J, Tavaré S (2006). "A unique recent origin of the allotetraploid species Arabidopsis suecica: Evidence from nuclear DNA markers". Mol. Biol. Evol. 23 (6): 1217–31. PMID 16549398. doi:10.1093/molbev/msk006.
- ↑ Säll T, Jakobsson M, Lind-Halldén C, Halldén C (2003). "Chloroplast DNA indicates a single origin of the allotetraploid Arabidopsis suecica". J. Evol. Biol. 16 (5): 1019–29. PMID 14635917. doi:10.1046/j.1420-9101.2003.00554.x.
- ↑ Bomblies K, Weigel D (2007). "Arabidopsis-a model genus for speciation". Curr Opin Genet Dev 17 (6): 500–4. PMID 18006296. doi:10.1016/j.gde.2007.09.006.
- ↑ Sémon M, Wolfe KH (2007). "Consequences of genome duplication". Curr Opin Genet Dev 17 (6): 505–12. PMID 18006297. doi:10.1016/j.gde.2007.09.007.
- ↑ Niles Eldredge and Stephen Jay Gould, 1972. "Punctuated equilibria: an alternative to phyletic gradualism" In T.J.M. Schopf, ed., Models in Paleobiology. San Francisco: Freeman Cooper. pp. 82–115. Reprinted in N. Eldredge Time frames. Princeton: Princeton Univ. Press. 1985
- ↑ Gould SJ (1994). "Tempo and mode in the macroevolutionary reconstruction of Darwinism". Proc. Natl. Acad. Sci. U.S.A. 91 (15): 6764–71. Bibcode:1994PNAS...91.6764G. PMC 44281. PMID 8041695. doi:10.1073/pnas.91.15.6764.
- ↑ Benton MJ (1995). "Diversification and extinction in the history of life". Science 268 (5207): 52–8. Bibcode:1995Sci...268...52B. PMID 7701342. doi:10.1126/science.7701342.
- ↑ Raup DM (1986). "Biological extinction in Earth history". Science 231 (4745): 1528–33. Bibcode:1986Sci...231.1528R. PMID 11542058. doi:10.1126/science.11542058.
- ↑ Avise JC, Hubbell SP, Ayala FJ. (2008). "In the light of evolution II: Biodiversity and extinction". Proc. Natl. Acad. Sci. U.S.A. 105 (Suppl 1): 11453–7. Bibcode:2008PNAS..10511453A. PMC 2556414. PMID 18695213. doi:10.1073/pnas.0802504105. Arquivado dende o orixinal o 02 de maio de 2019. Consultado o 01 de maio de 2019.
- ↑ 240,0 240,1 240,2 Raup DM (1994). "The role of extinction in evolution". Proc. Natl. Acad. Sci. U.S.A. 91 (15): 6758–63. Bibcode:1994PNAS...91.6758R. PMC 44280. PMID 8041694. doi:10.1073/pnas.91.15.6758.
- ↑ Novacek MJ, Cleland EE (2001). "The current biodiversity extinction event: scenarios for mitigation and recovery". Proc. Natl. Acad. Sci. U.S.A. 98 (10): 5466–70. Bibcode:2001PNAS...98.5466N. PMC 33235. PMID 11344295. doi:10.1073/pnas.091093698.
- ↑ Pimm S, Raven P, Peterson A, Sekercioglu CH, Ehrlich PR (2006). "Human impacts on the rates of recent, present and future bird extinctions". Proc. Natl. Acad. Sci. U.S.A. 103 (29): 10941–6. Bibcode:2006PNAS..10310941P. PMC 1544153. PMID 16829570. doi:10.1073/pnas.0604181103.
*Barnosky AD, Koch PL, Feranec RS, Wing SL, Shabel AB (2004). "Assessing the causes of late Pleistocene extinctions on the continents". Science 306 (5693): 70–5. Bibcode:2004Sci...306...70B. PMID 15459379. doi:10.1126/science.1101476. - ↑ Lewis OT (2006). "Climate change, species-area curves and the extinction crisis". Philos. Trans. R. Soc. Lond., B, Biol. Sci. 361 (1465): 163–71. PMC 1831839. PMID 16553315. doi:10.1098/rstb.2005.1712.
- ↑ Jablonski D (2001). "Lessons from the past: evolutionary impacts of mass extinctions". Proc. Natl. Acad. Sci. U.S.A. 98 (10): 5393–8. Bibcode:2001PNAS...98.5393J. PMC 33224. PMID 11344284. doi:10.1073/pnas.101092598.
- ↑ Quental, Tiago B.; Charles R. Marshall (June 20, 2013). "How the Red Queen Drives Terrestrial Mammals to Extinction". Science Express. doi:10.1126/science.1239431. Consultado o June 26, 2013.
- ↑ Robert Sanders, Media Relations (June 20, 2013). "The Red Queen was right: Life must continually evolve to avoid extinction" (News release). University of California Berkeley. Consultado o June 26, 2013.
- ↑ United States Geological Survey, ed. (9 de xullo de 2007). "Age of the Earth". Consultado o 31 de maio de 2015.
- ↑ Dalrymple, G. Brent (2001). "The age of the Earth in the twentieth century: a problem (mostly) solved". En Lewis, C. L. E.; Knell, S. J. The Age of the Earth: from 4004 BC to AD 2002. Geological Society Special Publication 190. Londres: Geological Society of London. pp. 205–221. ISBN 1-86239-093-2. ISSN 0305-8719. doi:10.1144/gsl.sp.2001.190.01.14.
- ↑ Manhesa, Gérard; Allègre, Claude J.; Dupréa, Bernard; Hamelin, Bruno (maio de 1980). "Lead isotope study of basic-ultrabasic layered complexes: Speculations about the age of the earth and primitive mantle characteristics". Earth and Planetary Science Letters (Amsterdam: Elsevier) 47 (3): 370–382. ISSN 0012-821X. doi:10.1016/0012-821X(80)90024-2.
- ↑ Kirk, Geoffrey; Raven, John; Schofield, Malcolm (1983). The Presocratic Philosophers: A Critical History with a Selection of Texts (2ª ed.). Cambridge University Press. p. 68. ISBN 0-521-27455-9.
- ↑ Borenstein, Seth (13 de novembro de 2013). "Oldest fossil found: Meet your microbial mom". Excite (Yonkers, NY: Mindspark Interactive Network). Associated Press. Consultado o 31 de maio de 2015.
- ↑ Pearlman, Jonathan (13 de novembro de 2013). "'Oldest signs of life on Earth found'". The Daily Telegraph (Londres: Telegraph Media Group). Consultado o 15 de decembro de 2014.
- ↑ Noffke, Nora; Christian, Daniel; Wacey, David; Hazen, Robert M. (16 de novembro de 2013). "Microbially Induced Sedimentary Structures Recording an Ancient Ecosystem in the ca. 3.48 Billion-Year-Old Dresser Formation, Pilbara, Western Australia". Astrobiology (New Rochelle, NY: Mary Ann Liebert, Inc.) 13 (12): 1103–1124. ISSN 1531-1074. PMC 3870916. PMID 24205812. doi:10.1089/ast.2013.1030.
- ↑ Ohtomo, Yoko; Kakegawa, Takeshi; Ishida, Akizumi; Nagase, Toshiro; Rosing, Minik T. (xaneiro de 2014). "Evidence for biogenic graphite in early Archaean Isua metasedimentary rocks". Nature Geoscience (Londres: Nature Publishing Group) 7 (1): 25–28. ISSN 1752-0894. doi:10.1038/ngeo2025.
- ↑ Borenstein, Seth (19 de outubro de 2015). "Hints of life on what was thought to be desolate early Earth". Excite (Yonkers, NY: Mindspark Interactive Network). Associated Press. Consultado o 20-10-2015.
- ↑ Bell, Elizabeth A.; Boehnike, Patrick; Harrison, T. Mark; Mao, Wendy L. (24 de novembro de 2015). "Potentially biogenic carbon preserved in a 4.1 billion-year-old zircon" (PDF). Proc. Natl. Acad. Sci. U.S.A. (Washington, D.C.: National Academy of Sciences) 112 (47): 14518–14521. ISSN 0027-8424. PMC 4664351. PMID 26483481. doi:10.1073/pnas.1517557112. Arquivado dende o orixinal (PDF) o 06 de novembro de 2015. Consultado o 30-12-2015.
- ↑ Doolittle, W. Ford (2000). "Uprooting the tree of life". Scientific American 282 (6): 90–95. PMID 10710791. doi:10.1038/scientificamerican0200-90.
- ↑ Peretó J (2005). "Controversies on the origin of life" (PDF). Int. Microbiol. 8 (1): 23–31. PMID 15906258. Arquivado dende o orixinal (PDF) o 24 de agosto de 2015. Consultado o 16 de xullo de 2013.
- ↑ Joyce GF (2002). "The antiquity of RNA-based evolution". Nature 418 (6894): 214–21. PMID 12110897. doi:10.1038/418214a.
- ↑ Trevors JT, Psenner R (2001). "From self-assembly of life to present-day bacteria: a possible role for nanocells". FEMS Microbiol. Rev. 25 (5): 573–82. PMID 11742692. doi:10.1111/j.1574-6976.2001.tb00592.x.
- ↑ Theobald, DL. (2010). "A formal test of the theory of universal common ancestry". Nature 465 (7295): 219–22. Bibcode:2010Natur.465..219T. PMID 20463738. doi:10.1038/nature09014.
- ↑ Bapteste E, Walsh DA (2005). "Does the 'Ring of Life' ring true?". Trends Microbiol. 13 (6): 256–61. PMID 15936656. doi:10.1016/j.tim.2005.03.012.
- ↑ Darwin, Charles (1859). On the Origin of Species (1st ed.). London: John Murray. p. 1. ISBN 0-8014-1319-2.
- ↑ Doolittle WF, Bapteste E (2007). "Pattern pluralism and the Tree of Life hypothesis". Proc. Natl. Acad. Sci. U.S.A. 104 (7): 2043–9. Bibcode:2007PNAS..104.2043D. PMC 1892968. PMID 17261804. doi:10.1073/pnas.0610699104.
- ↑ Kunin V, Goldovsky L, Darzentas N, Ouzounis CA (2005). "The net of life: reconstructing the microbial phylogenetic network". Genome Res. 15 (7): 954–9. PMC 1172039. PMID 15965028. doi:10.1101/gr.3666505.
- ↑ Jablonski D (1999). "The future of the fossil record". Science 284 (5423): 2114–16. PMID 10381868. doi:10.1126/science.284.5423.2114.
- ↑ Mason SF (1984). "Origins of biomolecular handedness". Nature 311 (5981): 19–23. Bibcode:1984Natur.311...19M. PMID 6472461. doi:10.1038/311019a0.
- ↑ Wolf YI, Rogozin IB, Grishin NV, Koonin EV (2002). "Genome trees and the tree of life". Trends Genet. 18 (9): 472–79. PMID 12175808. doi:10.1016/S0168-9525(02)02744-0.
- ↑ Varki A, Altheide TK (2005). "Comparing the human and chimpanzee genomes: searching for needles in a haystack". Genome Res. 15 (12): 1746–58. PMID 16339373. doi:10.1101/gr.3737405.
- ↑ 270,0 270,1 Cavalier-Smith T (2006). "Cell evolution and Earth history: stasis and revolution". Philos Trans R Soc Lond B Biol Sci 361 (1470): 969–1006. PMC 1578732. PMID 16754610. doi:10.1098/rstb.2006.1842.
- ↑ Schopf J (2006). "Fossil evidence of Archaean life". Philos Trans R Soc Lond B Biol Sci 361 (1470): 869–85. PMC 1578735. PMID 16754604. doi:10.1098/rstb.2006.1834.
*Altermann W, Kazmierczak J (2003). "Archean microfossils: a reappraisal of early life on Earth". Res Microbiol 154 (9): 611–17. PMID 14596897. doi:10.1016/j.resmic.2003.08.006. - ↑ Schopf J (1994). "Disparate rates, differing fates: tempo and mode of evolution changed from the Precambrian to the Phanerozoic". Proc Natl Acad Sci U S A 91 (15): 6735–42. Bibcode:1994PNAS...91.6735S. PMC 44277. PMID 8041691. doi:10.1073/pnas.91.15.6735.
- ↑ Poole A, Penny D (2007). "Evaluating hypotheses for the origin of eukaryotes". BioEssays 29 (1): 74–84. PMID 17187354. doi:10.1002/bies.20516.
- ↑ Dyall S, Brown M, Johnson P (2004). "Ancient invasions: from endosymbionts to organelles". Science 304 (5668): 253–57. Bibcode:2004Sci...304..253D. PMID 15073369. doi:10.1126/science.1094884.
- ↑ Martin W (2005). "The missing link between hydrogenosomes and mitochondria". Trends Microbiol. 13 (10): 457–59. PMID 16109488. doi:10.1016/j.tim.2005.08.005.
- ↑ Lang B, Gray M, Burger G (1999). "Mitochondrial genome evolution and the origin of eukaryotes". Annu Rev Genet 33 (1): 351–97. PMID 10690412. doi:10.1146/annurev.genet.33.1.351.
*McFadden G (1999). "Endosymbiosis and evolution of the plant cell". Curr Opin Plant Biol 2 (6): 513–19. PMID 10607659. doi:10.1016/S1369-5266(99)00025-4. - ↑ DeLong E, Pace N (2001). "Environmental diversity of bacteria and archaea". Syst Biol 50 (4): 470–8. PMID 12116647. doi:10.1080/106351501750435040.
- ↑ Kaiser D (2001). "Building a multicellular organism". Annu. Rev. Genet. 35 (1): 103–23. PMID 11700279. doi:10.1146/annurev.genet.35.102401.090145.
- ↑ Valentine JW, Jablonski D, Erwin DH (March 1, 1999). "Fossils, molecules and embryos: new perspectives on the Cambrian explosion". Development 126 (5): 851–9. PMID 9927587.
- ↑ Ohno S (1997). "The reason for as well as the consequence of the Cambrian explosion in animal evolution". J. Mol. Evol. 44 1 (S1): S23–7. PMID 9071008. doi:10.1007/PL00000055.
- Valentine J, Jablonski D (2003). "Morphological and developmental macroevolution: a paleontological perspective". Int. J. Dev. Biol. 47 (7–8): 517–22. PMID 14756327.
- ↑ Waters ER (2003). "Molecular adaptation and the origin of land plants". Mol. Phylogenet. Evol. 29 (3): 456–63. PMID 14615186. doi:10.1016/j.ympev.2003.07.018.
- ↑ Mayhew PJ (2007). "Why are there so many insect species? Perspectives from fossils and phylogenies". Biol Rev Camb Philos Soc 82 (3): 425–54. PMID 17624962. doi:10.1111/j.1469-185X.2007.00018.x.
- ↑ Carroll, Robert L. (2007). "The Palaeozoic Ancestry of Salamanders, Frogs and Caecilians". Zool J Linn Soc 150 (s1): 1–140. PMID 12752770. doi:10.1111/j.1096-3642.2007.00246.x.
- ↑ Wible JR, Rougier GW, Novacek MJ, Asher RJ (2007). "Cretaceous eutherians and Laurasian origin for placental mammals near the K/T boundary". Nature 447 (7147): 1003–1006. Bibcode:2007Natur.447.1003W. PMID 17581585. doi:10.1038/nature05854.
- ↑ Witmer LM (2011). "Palaeontology: An icon knocked from its perch". Nature 475 (7357): 458–459. PMID 21796198. doi:10.1038/475458a.
- ↑ Bull JJ, Wichman HA (2001). "Applied evolution". Annu Rev Ecol Syst 32 (1): 183–217. doi:10.1146/annurev.ecolsys.32.081501.114020.
- ↑ Doebley JF, Gaut BS, Smith BD (2006). "The molecular genetics of crop domestication". Cell 127 (7): 1309–21. PMID 17190597. doi:10.1016/j.cell.2006.12.006.
- ↑ Jäckel C, Kast P, Hilvert D (2008). "Protein design by directed evolution". Annu Rev Biophys 37 (1): 153–73. PMID 18573077. doi:10.1146/annurev.biophys.37.032807.125832.
- ↑ Maher B. (2009). "Evolution: Biology's next top model?". Nature 458 (7239): 695–8. PMID 19360058. doi:10.1038/458695a.
- ↑ Borowsky R (2008). "Restoring sight in blind cavefish". Curr. Biol. 18 (1): R23–4. PMID 18177707. doi:10.1016/j.cub.2007.11.023.
- ↑ Gross JB, Borowsky R, Tabin CJ (2009). Barsh, Gregory S., ed. "A novel role for Mc1r in the parallel evolution of depigmentation in independent populations of the cavefish Astyanax mexicanus". PLoS Genet. 5 (1): e1000326. PMC 2603666. PMID 19119422. doi:10.1371/journal.pgen.1000326.
- ↑ Merlo, Lauren M.F.; Pepper, John W.; Reid, Brian J.; Maley, Carlo C. (decembro de 2006). "Cancer as an evolutionary and ecological process.". Nature Reviews Cancer (Londres: Nature Publishing Group) 6 (12): 924–935. ISSN 1474-175X. PMID 17109012. doi:10.1038/nrc2013.
- ↑ Pan, Dabo; Weiwei Xue; Wenqi Zhang; et al. (outubro de 2012). "Understanding the drug resistance mechanism of hepatitis C virus NS3/4A to ITMN-191 due to R155K, A156V, D168A/E mutations: a computational study.". Biochimica et Biophysica Acta (BBA) - General Subjects (Amsterdam: Elsevier) 1820 (10): 1526–1534. ISSN 0304-4165. PMID 22698669. doi:10.1016/j.bbagen.2012.06.001.
- ↑ Woodford, Neil; Ellington, Matthew J. (xaneiro de 2007). Elsevier for the European Society of Clinical Microbiology and Infectious Diseases, ed. "The emergence of antibiotic resistance by mutation.". Clinical Microbiology and Infection (Amsterdam) 13 (1): 5–18. ISSN 1198-743X. PMID 17184282. doi:10.1111/j.1469-0691.2006.01492.x.
- ↑ Labbé, Pierrick; Berticat, Claire; Berthomieu, Arnaud; et al. (16 de novembro de 2007). "Forty Years of Erratic Insecticide Resistance Evolution in the Mosquito Culex pipiens". PLOS Genetics (San Francisco: Public Library of Science) 3 (11): e205. ISSN 1553-7390. PMID 18020711. doi:10.1371/journal.pgen.0030205.
- ↑ Neve, Paul (outubro de 2007). "Challenges for herbicide resistance evolution and management: 50 years after Harper". Weed Research (Hoboken: Wiley-Blackwell - European Weed Research Society) 47 (5): 365–369. ISSN 0043-1737. doi:10.1111/j.1365-3180.2007.00581.x.
- ↑ Rodríguez-Rojas, Alexandro; Rodríguez-Beltrán, Jerónimo; Couce, Alejandro; Blázquez, Jesús (agosto de 2013). "Antibiotics and antibiotic resistance: A bitter fight against evolution". International Journal of Medical Microbiology (Amsterdam: Elsevier) 303 (6–7): 293–297. ISSN 1438-4221. PMID 23517688. doi:10.1016/j.ijmm.2013.02.004.
- ↑ Schenk, Martijn F.; Szendro, Ivan G.; Krug, Joachim; de Visser, J. Arjan G. M. (28 de xuño de 2012). Public Library of Science, ed. "Quantifying the Adaptive Potential of an Antibiotic Resistance Enzyme". PLOS Genetics (San Francisco) 8 (6): e1002783. ISSN 1553-7390. PMID 22761587. doi:10.1371/journal.pgen.1002783.
- ↑ Read, Andrew F.; Lynch, Penelope A.; Thomas, Matthew B. (7 de abril de 2009). Public Library of Science, ed. "How to Make Evolution-Proof Insecticides for Malaria Control". PLOS Biology (San Francisco) 7 (4): e1000058. ISSN 1545-7885. PMID 19355786. doi:10.1371/journal.pbio.1000058.
- ↑ Fraser AS (1958). "Monte Carlo analyses of genetic models". Nature 181 (4603): 208–9. Bibcode:1958Natur.181..208F. PMID 13504138. doi:10.1038/181208a0.
- ↑ Rechenberg, Ingo (1973). Evolutionsstrategie – Optimierung technischer Systeme nach Prinzipien der biologischen Evolution (PhD thesis) (en German). Fromman-Holzboog.
- ↑ Holland, John H. (1975). Adaptation in Natural and Artificial Systems. University of Michigan Press. ISBN 0-262-58111-6.
- ↑ Koza, John R. (1992). Genetic Programming: On the Programming of Computers by Means of Natural Selection. MIT Press. ISBN 0-262-11170-5.
- ↑ Jamshidi M (2003). "Tools for intelligent control: fuzzy controllers, neural networks and genetic algorithms". Philosophical transactions. Series A, Mathematical, physical and engineering sciences 361 (1809): 1781–808. Bibcode:2003RSPTA.361.1781J. PMID 12952685. doi:10.1098/rsta.2003.1225.
- ↑ Browne, Janet (2003). Charles Darwin: The Power of Place. London: Pimlico. pp. 376–379. ISBN 0-7126-6837-3.
- ↑ Para unha visión xeral das controversias filosóficas, relixiosas e cosmolóxicas, ver:
- Dennett, D (1995). Darwin's Dangerous Idea: Evolution and the Meanings of Life. Simon & Schuster. ISBN 978-0-684-82471-0.
Para a recepción científica e social da evolución no século XIX e principios do XX, ver: - Johnston, Ian C. "History of Science: Origins of Evolutionary Theory". And Still We Evolve. Liberal Studies Department, Malaspina University College. Arquivado dende o orixinal o 07 de xaneiro de 2017. Consultado o May 24, 2007.
- Bowler 2003
- Zuckerkandl E (2006). "Intelligent design and biological complexity". Gene 385: 2–18. PMID 17011142. doi:10.1016/j.gene.2006.03.025.
- Dennett, D (1995). Darwin's Dangerous Idea: Evolution and the Meanings of Life. Simon & Schuster. ISBN 978-0-684-82471-0.
- ↑ Ross, M.R. (2005). "Who Believes What? Clearing up Confusion over Intelligent Design and Young-Earth Creationism" (PDF). Journal of Geoscience Education 53 (3): 319. Consultado o April 28, 2008.
- ↑ Hameed, Salman (December 12, 2008). "Science and Religion: Bracing for Islamic Creationism" (PDF). Science 322 (5908): 1637–1638. PMID 19074331. doi:10.1126/science.1163672. Arquivado dende o orixinal (PDF) o 10 de novembro de 2014. Consultado o 2009.
- ↑ Bowler 2003
- ↑ "Circular del Ministro de Fomento de 26 de febrero de 1875 (Orovio)". Legislación y documentos sobreeducación superior – Alma mater hispalense.
- ↑ Xosé Antón Fraga Vázquez. "Aportación ao estudo da polémica darwinista na Galiza do século XIX." (PDF).
- ↑ Francisco Díaz Fierros (coordinador). (2009). O darwinismo e Galicia. Universidade de Santiago de Compostela. Servizo de Publicacións e Intercambio Cientifico. ISBN 9788498872651.
- ↑ Spergel D. N.; Scott, EC; Okamoto, S (2006). "Science communication. Public acceptance of evolution". Science 313 (5788): 765–66. PMID 16902112. doi:10.1126/science.1126746.
- ↑ Spergel, D. N.; Verde, L.; Peiris, H. V.; Komatsu, E.; Nolta, M. R.; Bennett, C. L.; Halpern, M.; Hinshaw, G.; Jarosik, N. (2003). "First-Year Wilkinson Microwave Anisotropy Probe (WMAP) Observations: Determination of Cosmological Parameters". The Astrophysical Journal Supplement Series 148 (1): 175–94. Bibcode:2003ApJS..148..175S. arXiv:astro-ph/0302209. doi:10.1086/377226.
- ↑ Wilde SA, Valley JW, Peck WH, Graham CM (2001). "Evidence from detrital zircons for the existence of continental crust and oceans on the Earth 4.4 Gyr ago". Nature 409 (6817): 175–78. PMID 11196637. doi:10.1038/35051550.
- ↑ Branch, Glenn (March 2007). "Understanding Creationism after Kitzmiller". BioScience (American Institute of Biological Sciences) 57 (3): 278–284. doi:10.1641/B570313.
Véxase tamén[editar | editar a fonte]
| Wikimedia Commons ten máis contidos multimedia na categoría: Evolución |

Bibliografía[editar | editar a fonte]
- Bowler, Peter J. (2003). Evolution: The History of an Idea (en inglés) (3ª ed.). University of California Press. ISBN 0-520-23693-9. LCCN 2002007569. OCLC 49824702.
- Carroll, Sean B.; Grenier, Jennifer K.; Weatherbee, Scott D. (2005). From DNA to Diversity: Molecular Genetics and the Evolution of Animal Design (en inglés) (2nd ed.). Malden, MA: Blackwell Publishing. ISBN 1-4051-1950-0. LCCN 2003027991. OCLC 53972564.
- Coyne, Jerry A. (2009). Why Evolution is True (en inglés). Nova York: Viking. ISBN 978-0-670-02053-9. LCCN 2008033973. OCLC 233549529.
- Darwin, Charles (1859). On the Origin of Species by Means of Natural Selection, or the Preservation of Favoured Races in the Struggle for Life [A orixe das especies] (en inglés e galego) (1ª ed.). Londres: John Murray. LCCN 06017473. OCLC 741260650.
- Dawkins, R. (2006). The Selfish Gene: 30th Anniversary Edition. Oxford University Press. ISBN 0-19-929115-2.
- Futuyma, Douglas J. (2004). "The Fruit of the Tree of Life: Insights into Evolution and Ecology". En Cracraft, Joel; Donoghue, Michael J. Assembling the Tree of Life. Oxford University Press. ISBN 0-19-517234-5. LCCN 2003058012. OCLC 61342697. "Proceedings of a symposium held at the American Museum of Natural History in New York, 2002."
- Futuyma, Douglas J. (2005). Evolution (en inglés). Sunderland: Sinauer Associates. ISBN 0-87893-187-2. LCCN 2004029808. OCLC 57311264.
- Gould, S.J. (1989). Wonderful Life: The Burgess Shale and the Nature of History (en inglés). Nova York: W.W. Norton. ISBN 0-393-30700-X.
- Gould, S.J. (2002). The Structure of Evolutionary Theory (en inglés). Belknap Press. ISBN 0-674-00613-5. LCCN 2001043556. OCLC 47869352.
- Hall, Brian K.; Hallgrímsson, Benedikt (2008). Strickberger's Evolution (en inglés) (4ª ed.). Sudbury: Jones and Bartlett Publishers. ISBN 978-0-7637-0066-9. LCCN 2007008981. OCLC 85814089.
- Mayr, Ernst (1982). The Growth of Biological Thought: Diversity, Evolution, and Inheritance (en inglés). Tradución de John Ray. Belknap Press. ISBN 0-674-36445-7. LCCN 81013204. OCLC 7875904.
- Mayr, Ernst (2001). What Evolution Is (en inglés). Nova York: Basic Books. ISBN 0-465-04426-3.
- National Academy of Sciences; Institute of Medicine (2008). Science, Evolution, and Creationism (en inglés). Washington, D.C.: National Academy Press. ISBN 978-0-309-10586-6. LCCN 2007015904. OCLC 123539346.
- Ridley, Matt (1993). The Red Queen: Sex and the Evolution of Human Nature (en inglés). Nova York: Viking. ISBN 0-670-84357-1. OCLC 636657988.
- Zimmer, C. (2001). Evolution: The Triumph of an Idea (en inglés). Londres: HarperCollins. ISBN 0-06-019906-7.
Ligazóns externas[editar | editar a fonte]
- "How Evolution Works". Howstuffworks (en inglés).
- "Evolution Resources from the National Academies" (en inglés). U.S. National Academy of Sciences.
- "Understanding Evolution: your one-stop resource for information on Evolution" (en inglés). University of California, Berkeley.
- "Evolution of Evolution – 150 Years of Darwin's "On the Origin of Species"" (en inglés). National Science Foundation. Arquivado dende o orixinal o 27 de maio de 2013. Consultado o 16 de xullo de 2013.
- Price RG. "Understanding Evolution: History, Theory, Evidence, and Implications". RationalRevolution (en inglés).





![En 1842 Charles Darwin escribiu o seu primeiro esbozo do que sería o seu libro A orixe das especies.[16]](http://upload.wikimedia.org/wikipedia/commons/thumb/4/42/Charles_Darwin_aged_51.jpg/150px-Charles_Darwin_aged_51.jpg)
