Árbore filoxenética

Unha árbore filoxenética (xeralmente sinónimo de árbore evolutiva) é un diagrama ramificado ou "árbore" que mostra as relacións evolutivas inferidas entre varias especies biolóxicas ou outros grupos, é dicir a súa filoxenia, baseándose nas semellanzas e diferenzas nas súas características físicas ou xenéticas. Os taxons que quedan unidos na árbore considérase que descenden dun antepasado común.
Nunha árbore filoxenética enraizada, cada nodo con descendentes representa o antepasado común máis recente inferido dos descendentes, e nalgunhas árbores a lonxitude das liñas pode interpretarse como unha estimación do tempo. Cada nodo denomínase unidade taxonómica. Os nodos internos denomínanse xeralmente unidades taxonómicas hipotéticas, xa que non poden ser observadas directamente. As árbores son útiles en campos da bioloxía como a bioinformática, a sistemática, e a filoxenética comparativa.
Historia[editar | editar a fonte]

A idea dunha "árbore da vida" procede das antigas nocións dun progreso na evolución similar a subir por unha escada desde as formas "inferiores" ás "superiores" da vida. As representacións iniciais de árbores filoxenéticas "ramificadas" incluían un "gráfico paleontolóxico" que mostraba as relacións xeolóxicas entre as plantas e os animais como as do libro Elementary Geology (Xeoloxía Elemental) de Edward Hitchcock (primeira edición de 1840).
Charles Darwin (1859) tamén creou unha das primeiras ilustracións e popularizou a noción de "árbore" evolutiva no seu influente libro The Origin of Species (A orixe das Especies). Un século máis tarde, os biólogos evolutivos aínda utilizan diagramas en árbore para ilustrar a evolución porque ditos diagramas transmiten con efectividade o concepto de que a especiación ocorre por medio dunha separación adaptativa e semialeatoria das liñaxes de seres vivos. Co tempo, a clasificación das especies foi facéncose menos estática e máis dinámica.
Tipos[editar | editar a fonte]
Árbore enraizada[editar | editar a fonte]

Unha árbore filoxenética enraizada ou con raíz é unha árbore dirixida cun único nodo correspondente ao antepasado común máis recente (xeralmente imputado) de todas as entidades situadas nas follas da árbore. O método máis común para elaborar árbores enraizadas é o uso dun grupo externo (outgroup) o suficientemente próximo e non controvertido para permitir facer a inferencia a partir da secuencia de datos de trazos, pero o suficientemente afastado para ser claramente un grupo externo.
Árbore sen raíz[editar | editar a fonte]
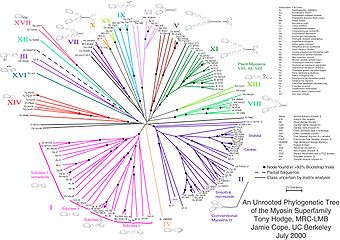
As árbores sen raíz ou non enraizadas ilustran o grao de relación entre os nodos folla sen facer asuncións sobre cal foi o seu antepasado. Para construílos ou inferilos non requiren unha raíz ancestral.[2] As árbores sen raíz sempre poden xerarse a partir das árbores enraizadas simplemente omitindo a raíz. Ao contrario, inferir a raíz a partir dunha árbore sen raíz require que haxa algunha maneira para poder identificar o antepasado. Isto faise normalmente incluíndo un grupo externo nos datos utilizados para que a raíz estea necesariamente entre o grupo externo e o resto dos taxons da árbore, ou introducindo asuncións adicionais sobre as velocidades relativas de evolución en cada póla, como pode ser aplicar unha hipótese de reloxo molecular. A figura 2 mostra unha árbore filoxenética sen raíz para as miosinas, unha superfamilia de proteínas.[3]
Árbore bifurcada[editar | editar a fonte]
Tanto as árbores filoxenéticas enraizadas coma as non enraizadas poden ser bifurcadas ou multifurcadas, e tamén etiquetadas ou non etiquetadas. Unha árbore bifurcada enraizada ten exactamente dous descendentes que se orixinan en cada nodo interior (é dicir, forma unha árbore binaria), e unha árbore bifurcada non enraizada ten a forma dunha árbore binaria sen raíz, unha árbore libre con exactamente tres veciños en cada nodo interior. A diferenza dos anteriores, unha árbore multifurcada enraizada pode ter máis de dous descendentes nalgúns nodos, e unha árbore multifurcada non enraizada pode ter máis de tres veciños nalgúns nodos. Unha árbore etiquetada ten valores específicos asignados ás súas follas, mentres que unha árbore non etiquetada, ás veces chamada forma arbórea, define soamente a topoloxía. O número de posibles árbores para un número dado de nodos folla depende do tipo específico de árbore, pero sempre hai máis árbores multifurcadas que bifurcadas, e máis árbores etiquetadas que non etiquetadas, e máis árbores enraizadas que non enraizadas. A última distinción é de grande relevencia biolóxica; prodúcese porque hai moitos lugares nunha árbore non enraizada onde se pode poñer a raíz. Para unha árbore bifurcada etiquetada habería:
árbores enraizadas totais e
árbores non enraizados totais, onde representa o número de nodos folla. Entre as árbores bifurcadas etiquetadas, o número de árbores non enraizadas con follas é igual ao número de árbores enraizadas con follas.[4]
Tipos de árbores especiais[editar | editar a fonte]

- Dendrograma é un termo amplo para designar as representacións diagramáticas dunha árbore filoxenética.
- Un cladograma é unha árbore filoxenética formada utilizando métodos cladísticos. Este tipo de ábore só representa un patrón de ramificación, é dicir, o tamaño das súas pólas non representa o tempo ou a cantidade relativa de cambio de caracteres.
- Un filograma é unha árbore filoxenética que ten tamaños das pólas proporcionais á cantidade de cambio nos caracteres.
- Un cronograma é unha árbore filoxenética que representa explicitamente o tempo evolutivo polo tamaño das súas pólas.
- Un diagrama de fuso (a miúdo chamado Romerograma polo paleontólogo norteamericano Alfred Romer) é a representación da evolución e abundancia de varios taxons a través do tempo, indicada polo grosor das liñas con forma de fuso ao longo do tempo.
Construción[editar | editar a fonte]
As árbores filoxenéticas entre un número non trivial de secuencias input constrúense usando métodos de filoxenética computacional. Métodos de matriz de distancia como neighbor-joining ou UPGMA, que calculan a distancia xenética a partir de aliñamentos de secuencia múltiple, son os máis simples para aplicar, pero non implican un modelo evolutivo. Moitos métodos de aliñamento de secuencias como ClustalW tamén crean árbores usando algoritmos máis simples (como os baseados na distancia) para a construción de árbores. A máxima parsimonia[7] é outro método simple de facer estimación de árbores filoxenéticas, pero leva implícito un modelo de evolución (é dicir parsimonia). Outros métodos máis avanzados usan o criterio de optimalidade[8] de máxima verosimilitude, a miúdo cunha rede bayesiana, e aplican un modelo explícito de evolución para a estimación dunha árbore filoxenética.[4] A identificación da árbore óptima usando moitas destas técnicas é o que na teoría de complexidade computacional se chama NP-hard (NP-complexo),[4] así que a investigación heurística e os métodos de optimización se usan en combinación con outras funcións para identificar unha árbore razoablemente boa que se corresponda cos datos.
Os métodos de construción de árbores poden ser avaliados baseándose en varios criterios:[9]
- eficiencia (canto se tarda en computar a resposta ou canta memoria se necesita)
- potencia (se fai bo uso dos datos ou desperdíciase a información)
- consistencia (se converxerá na mesma resposta repetidamente se se lle dan diferentes datos para o mesmo problema modelo)
- robustez (se se apaña ben coas violacións das asuncións do modelo subxacente)
- falsifiabilidade (se alerta cando non paga a pena usalo, é dicir cando as asuncións son violadas)
As técnicas de construción de árbores atraeron tamén a atención dos matemáticos. As árbores poden tamén construírse usando a teoría T.[10]
Limitacións[editar | editar a fonte]

Aínda que as árbores filoxenéticas elaboradas baseándose en xenes secuenciados ou datos xenómicos de diferentes especies poden reflectir a evolución desas especies, teñen tamén importantes limitacións. Pode que non representen con exactitude a historia evolutiva dos taxons incluídos no estudo. Os datos nos que están baseados inclúen "ruído"; a análise pode confundirse pola recombinación xenética,[11] a transferencia horizontal de xenes,[12] a hibridación entre especies que non eran os veciños máis próximos na árbore antes de que dita hibridación tivese lugar, evolución converxente, e secuencias conservadas.
Tamén hai problemas cando a análise se basea nun só tipo de carácter, como un só xene ou proteína ou só en análises morfolóxicas, porque outras árbores construídas a partir doutros datos de fontes non relacionadas a miúdo difiren da primeira. Isto é especialmente certo con material xenético que está suxeito a transferencias laterais de xenes e recombinación, no que diferentes bloques de haplotipos poden ter diferentes historias. En xeral, a árbore obtida nunha análise filoxenética é unha estimación da filoxenia dun carácter ou trazo (é dicir unha árbore dun xene) e non a filoxenia dun taxon (unha árbore de especies), aínda que, idealmente, ambos os dous deberían ser moi parecidos. Por esta razón, para minimizar estes problemas, os estudos filoxenéticos máis completos xeralmente usan unha combinación de xenes que proceden de diferentes fontes xenómicas (por exemplo, de mitocondrias ou plastidios fronte a xenomas nucleares), ou xenes que se esperaría que evolucionasen baixo diferentes réximes selectivos, para que esa homoplasia (falsa homoloxía) sexa improbable que se orixine por selección natural.
Cando se inclúen nas árbores especies extintas, estas son nodos terminais (nodos folla), xa que é improbable que sexan os antepasados directos dalgunha especie existente. Cando se utilizan datos de ADN nas árbores, hai que ter en conta que pouco "ADN antigo" útil (de especies extintas) queda preservado durante máis de 100.000 anos.
A gama de materiais de ADN útiles aumentou cos avances nas tecnoloxías de extracción e secuenciación. O desenvolvemento de tecnoloxías capaces de inferir secuencias de pequenos fragmentos, ou de patróns espaciais de produtos da degradación do ADN, poderían ampliar máis a gama de ADN considerado útil.
Nalgúns organismos, os endosimbiontes teñen unha historia xenética independente do seu hóspede.
Utilízanse as redes filoxenéticas cando as árbores bifurcadas non son as axeitadas, debido a estas complicacións que suxiren unha historia evolutiva máis reticulada dos organismos estudados.
Notas[editar | editar a fonte]
- ↑ Hodge T, Cope M (1 October 2000). "A myosin family tree". J Cell Sci 113 (19): 3353–4. PMID 10984423.
- ↑ http://www.ncbi.nlm.nih.gov/Class/NAWBIS/Modules/Phylogenetics/phylo9.html
- ↑ Maher BA (2002). "Uprooting the Tree of Life". The Scientist 16: 18. Arquivado dende o orixinal o 02 de outubro de 2003. Consultado o 09 de xullo de 2014. Arquivado 02 de outubro de 2003 en Wayback Machine.
- ↑ 4,0 4,1 4,2 Felsenstein J. (2004). Inferring Phylogenies Sinauer Associates: Sunderland, MA.
- ↑ Letunic, I; Bork, P (2007). "Interactive Tree Of Life (iTOL): an online tool for phylogenetic tree display and annotation.". Bioinformatics 23 (1): 127–8. PMID 17050570. doi:10.1093/bioinformatics/btl529.
- ↑ Ciccarelli, FD; Doerks, T; Von Mering, C; Creevey, CJ; Snel, B; Bork, P (2006). "Toward automatic reconstruction of a highly resolved tree of life". Science 311 (5765): 1283–7. Bibcode:2006Sci...311.1283C. PMID 16513982. doi:10.1126/science.1123061.
- ↑ A árbore filoxenética preferida é a que supón o menor cambio evolutivo para explicar os datos observados.
- ↑ Optimality criterion. Mide a adecuación dos datos a unha hipótese data.
- ↑ Penny, D.; Hendy, M. D.; Steel, M. A. (1992). "Progress with methods for constructing evolutionary trees". Trends in Ecology and Evolution 7: 73–79. doi:10.1016/0169-5347(92)90244-6.
- ↑ A. Dress, K. T. Huber, and V. Moulton. 2001. Metric Spaces in Pure and Applied Mathematics. Documenta Mathematica LSU 2001: 121-139
- ↑ Arenas M, Posada D (2010). "The effect of recombination on the reconstruction of ancestral sequences". Genetics 184 (4): 1133–1139. doi:10.1534/genetics.109.113423.
- ↑ Woese C (2002). "On the evolution of cells". Proc Natl Acad Sci USA 99 (13): 8742–7. Bibcode:2002PNAS...99.8742W. PMC 124369. PMID 12077305. doi:10.1073/pnas.132266999.
Véxase tamén[editar | editar a fonte]
Outros artigos[editar | editar a fonte]
- Campos de estudo
- Cladística
- Filoxenética comparada
- Filoxenética computacional
- Taxonomía evolutiva
- Bioloxía evolutiva
- Aliñamento de árbore xeneralizado
- Filoxenética
- Software
Bibliografía[editar | editar a fonte]
- Schuh, R. T. and A. V. Z. Brower. 2009. Biological Systematics: principles and applications (2nd edn.) ISBN 978-0-8014-4799-0
- MEGA, un software libre para debuxar árbore filoxenética.
Ligazóns externas[editar | editar a fonte]
| Commons ten máis contidos multimedia sobre: Phylogenetic tree |
- Imaxes
- Phylogenetic Trees Based on 16s rDNA
- Poster-sized tree of life illustration Arquivado 10 de febreiro de 2015 en Wayback Machine.
- Human Y-Chromosome 2002 Phylogenetic Tree
- En 2003, a revista Science dedicou un número especial á árbore da vida, incluíndo unha versión online dunha árbore da vida.
- iTOL: Interactive Tree Of Life
- Phylogenetic Tree of Artificial Organisms Evolved on Computers
- Miyamoto and Goodman's Phylogram of Eutherian Mammals
- Xeral
- Resumo de diferentes métodos de visualización de árbores dispoñible en doi 10.1016/j.tree.2011.12.002
- Discover Life Árbore interactiva baseada no Tree of Life Project
- PhyloCode
- A Multiple Alignment of 139 Myosin Sequences and a Phylogenetic Tree
- Tree of Life Web Project
- Phylogenetic inferring on the T-REX server Arquivado 18 de setembro de 2020 en Wayback Machine.
- NCBI's Taxonomy Database[1]
- ETE: A Python Environment for Tree Exploration Libraría de programación para analizar, manipular e visualizar árbore filoxenéticas. Ref.
- A daily-updated tree of (sequenced) life Arquivado 09 de xuño de 2014 en Wayback Machine. cite doi|10.1038/srep02015




