Secuenciación do ADN
A secuenciación do ADN é o proceso de determinar a orde precisa de nucleótidos dunha molécula de ADN. Para facer a secuenciación aplícanse diversos métodos e tecnoloxías que permiten determinar a orde das catro bases (adenina, guanina, citosina, e timina) que forman as cadeas do ADN. A aparición de métodos rápidos de secuenciación acelerou moito as investigacións e descubrimentos médicos e biolóxicos.
O coñecemento das secuencias de ADN fíxose indispensable para unha investigación biolóxica básica, e en numerosos campos aplicados como o diagnóstico, biotecnoloxía, bioloxía forense, e sistemática biolóxica. As rápidas velocidades de secuenciación acadadas coas modernas tecnoloxías de secuenciación do ADN foron fundamentais para a secuenciación de secuencias de ADN completas, ou mesmo xenomas completos de numerosas especies vivas, incluíndo o xenoma humano e outros xenomas de animais, plantas e microorganismos.
As primeiras secuencias de ADN obtivéronse a inicios da década de 1970 utilizando laboriosos métodos baseados na cromatografía bidimensional, e co desenvolvemento de métodos de secuenciación baseados na fluorescencia con análise automatizada,[1] a secuenciación do ADN fíxose máis fácil e moitísimo máis rápida.[2]
Usos da secuenciación[editar | editar a fonte]
A secuenciación do ADN pode utilizarse para determinar a secuencia dun determinado xene, de rexións xenéticas grandes (por exemplo, clusters de xenes ou operóns), cromosomas completos ou xenomas enteiros. Dependendo dos métodos utilizados, a secuenciación pode determinar a orde dos nucleótidos dun ADN ou ARN illado dunha célula de animal, planta, bacteria, arquea, ou virtualmente de calquera outra fonte de información xenética. As secuencias resultantes poden utilizarse en bioloxía molecular ou xenética para facer progresos científicos ou pode utilizalos o persoal médico para tomar decisións de tratamento ou para dar consello xenético.
Historia[editar | editar a fonte]
Aínda que en 1953 se estableceu que a estrutura do ADN era unha dobre hélice,[3] pasarían varias décadas antes de que fose posible analizar fragmentos de ADN para determinar a súa secuencia. A secuenciación do ARN foi unha das primeiras formas de secuenciación de nucleótidos. O punto culminante da secuenciación do ARN foi a obtención da secuencia do primeiro xene completo e o xenoma completo do bacteriófago MS2, identificado e publicado por Walter Fiers e colaboradores na Universidade de Gante (Bélxica), en 1972[4] e 1976.[5]
Fixéronse varios avances notables na secuenciación do ADN durante a década de 1970. Frederick Sanger desenvolveu métodos de secuenciación do ADN rápidos no Consello de Investigacións Médicas, de Cambridge, Reino Unido, e publicou un método para a "secuenciación do ADN con inhibidores da terminación da cadea" en 1977.[6] Walter Gilbert ed Allan Maxam na Universidade Harvard tamén desenvolveron métodos de secuenciación, como a "secuenciación de ADN por degradación química".[7][8] En 1973, Gilbert e Maxam obtiveron unha secuencia de 24 pares de bases usando un método coñecido como análise de punto errante.[9] Sumáronse novos avances na secuenciación co desenvolvemento simultáneo da tecnoloxía do ADN recombinante, que permitiu que fosen illadas mostras de ADN doutras fontes distintas de virus.
O primeiro xenoma de ADN completo en ser secuenciado foi o do bacteriófago φX174 en 1977.[10] Os científicos do Consello de Investigacións Médicas británico descifraron a secuencia completa do ADN do virus de Epstein-Barr en 1984, e atoparon que tiña 170 mil pares de bases.
O laboratorio de Leroy E. Hood no Instituto Tecnolóxico de California anunciou a primeira máquina de secuenciación de ADN semiautomática en 1986.[11] Seguidamente Applied Biosystems comercializou a primeira máqueina de secuenciación totalmente automatizada, a ABI 370, en 1987. En 1990, os Institutos Nacionais da Saúde (NIH) estadounidenses empezaron unha serie de ensaios de secuenciación a grande escala de Mycoplasma capricolum, Escherichia coli, Caenorhabditis elegans, e Saccharomyces cerevisiae cun custo de 0,75 dólares por base. Mentres, empezou a secuenciación de secuencias de ADNc humano chamadas etiquetas de secuencia expresadas no laboratorio de Craig Venter, nun intento de capturar a fracción codificante do xenoma humano.[12] En 1995, Venter, Hamilton Smith, e colegas en The Institute for Genomic Research (TIGR) publicaron o primeiro xenoma completo dun organismo de vida libre, a bacteria Haemophilus influenzae. O seu cromosoma circular contiña 1.830.137 bases e a súa publicación na revista Science[13] supuxo o primeiro uso publicado da escopeta de secuenciación dun xenoma completo, eliminando a necesidade de facer un traballo inicial de mapado. En 2001, usáronse os métodos da escopeta de secuenciación para producir unha secuencia borrador do xenoma humano.[14][15]
Desenvolvéronse outros varios métodos de secuenciación do ADN a mediados e finais da década de 1990. Estas técnicas comprenden as primeiras dos "métodos de secuenciación de seguinte xeración". En 1996, Pål Nyrén e o seu axudante Mostafa Ronaghi no Instituto de Tecnoloxía Real de Estocolmo publicaron o seu método de pirosecuenciación.[16] Un ano despois, Pascal Mayer e Laurent Farinelli rexistraron unha patente describindo a secuenciación de colonia de ADN.[17] Lynx Therapeutics publicou e comercializou o seu "MPSS" en 2000. Este método incorporaba unha tecnoloxía de secuenciación baseada en esferas de polímero mediadas por adaptador/ligador en paralelo, que foi o primeiro método de secuenciación de "seguinte xeración" dispoñible, aínda que non se venderon secuenciadores de ADN a outros laboratorios.[18] En 2004, 454 Life Sciences comercializou unha versión paralelizada de pirosecuenciación.[19][20] A primeira versión da súa máquina reduciu o custo da secuenciación á sesta parte comparado cos métodos automatizados de Sanger, e foi o segundo da nova xeración de tecnoloxías de secuenciación, despois da MPSS.[21]
As grandes cantidades de datos producidos pola secuenciación do ADN precisaron tamén o desenvolvemento de novos métodos e programas para a análise de secuencias. Phil Green e Brent Ewing da Universidade de Washington describiron a súa puntuación de calidade para o programa Phred para análises de datos de secuenciador en 1998.[22]
Métodos básicos[editar | editar a fonte]
Secuenciación de Maxam e Gilbert[editar | editar a fonte]
- Artigo principal: Secuenciación de Maxam e Gilbert.
Allan Maxam e Walter Gilbert publicaron un método de secuenciación do ADN en 1977 baseado na modificación química do ADN e a subseguinte clivaxe en bases específicas.[7] Tamén coñecido como secuenciación química, este método permitiu purificar mostras de ADN de dobre cadea para ser usadas sen unha posterior clonación. O uso neste método do etiquetado radioactivo e a súa complexidade técnica desanimou o seu uso amplo unha vez que se fixeron refinamentos nos métodos de Sanger.
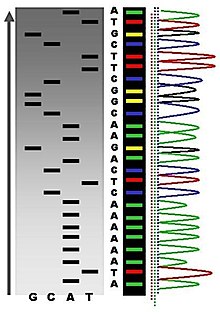
A secuenciación de Maxam e Gilbert require o etiquetado radioactivo nun extremo 5' do ADN e a purificación do fragmento de ADN que vai ser secuenciado. O tratamento químico xera despois roturas nunha pequena proporción dunha ou dúas das catro bases nucleotídicas en cada unha das catro reaccións (G, A+G, C, C+T). A concentración dos compostos modificadores é controlada para introducir como media unha modificación por molécula de ADN. Desrte modo, xérase unha serie de fragmentos etiquetados, desde o extremo radioetiquetado ao primeiro sitio de "corte" en cada molécula. Os fragmentos nas catro reaccións son sometidos a electroforese xuntos en xeles de acrilamida desnaturalizantes para a súa separación por tamaños. Para visualizar os fragmentos, o xel é exposto a película de raios X para autorradiografía, dando lugar a unha serie de bandas escuras cada unha correspondente a un fragmento de ADN radioetiquetado, do cal se pode deducir a secuencia.[7]
Métodos de terminación de cadea[editar | editar a fonte]
- Artigo principal: Secuenciación de Sanger.
O método de terminación de cadea desenvolvido por Frederick Sanger e colaboradores en 1977 axiña se converteu no método preferido de secuenciación debido á súa relativa simplicidade e fiabilidade.[6][23] O método de terminación de cadea usaba menos compostos tóxicos e menor cantidade de radioactividade que o método de Maxam e Gilbert. Debido á súa comparativa sinxeleza, o método de Sanger foi axiña automatizado e foi o método utilizado pola primeira xeración de secuenciadores de ADN.
A secuenciación de Sanger é o método que prevaleceu desde a década de 1980 ata mediados da década do 2000. Nese período, fixéronse grandes avances na técnica, como o etiquetado fluorescente, a electroforese capilar, e a automatización xeral. Estas melloras permitían unha secuenciación moito máis efeiciente, o que reduciu os seus custos. O método de Sanger, aplicado masivamente, é a tecnoloxía coa que se obtivo o primeiro xenoma humano en 2001, marcando o comezo da idade da xenómica. Porén, avanzada a década, chegaron ao mercado técnicas con estratexias totalmente diferentes, que rebaixaron o custo por xenoma desde uns 100 millóns de dólares en 2001 a só 10.000 en 2011.[24]
Métodos avanzados e secuenciación de novo[editar | editar a fonte]
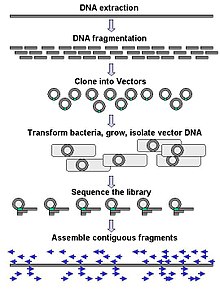
A secuenciación a grande escala con frecuencia pretende secuenciar fragmentos de ADN moi longos, como cromosomas enteiros, aínda que a secuenciación a grande escala pode tamén usarse para xerar cantidades moi grandes de secuencias curtas, como as que se encontran na técnica do phage display. Para obxectivos máis longos como os cromosomas, a estratexia máis común consiste en cortalos en anacos máis pequenos con encimas de restrición ou rompelos aplicando forzas mecánicas. O ADN fragmentado pode despois ser clonado nun vector de ADN e amplificado nun hóspede bacterianao como Escherichia coli. Os fragmentos curtos de ADN purificados dunha colonia bacteriana son secuenciados por separado e ensamblados electónicamente nunha longa secuencia continua.
O termo "secuenciación de novo" (en latín, "desde o principio") refírese especificamente aos métodos usados para determinar a secuencia dun ADN cuxa secuencia non se coñece previamente. As lagoas que queden na secuencia ensamblada poden encherse utilizando a técnica primer walking. As distintas estratexias teñen diferentes vantaxes en velocidade e precisión; os métodos de escopeta son moi utilizados para secuenciar xenomas grandes, pero a súa ensamblaxe é complexa e difícil, especialmente con repeticións de secuencia, que con frecuencia orixinan lagoas durante a ensamblaxe do xenoma.
A maioría das estratexias de secuenciación usan un paso de clonación in vitro para amplificar cada molécula de ADN, porque os seus métodos de detección molecular non son sensibles dabondo como para secuenciar unha soa molécula. Unha PCR de emulsión[25] illa moléculas de ADN por separado con esferas cubertas cun cebador en gotas acuosas dentro dunha fase de aceite. Despois aplícase a reacción en cadea da polimerase (PCR) para cubrir cada esfera con copias clonais de moléculas de ADN que despois se inmobilizan para unha posterior secuenciación. A PCR de emulsión utilízase nos métodos desenvolvidos por Marguilis et al. (comercializados por 454 Life Sciences), Shendure e Porreca et al. (tamén coñecidos como "secuenciación Polony", contracción de polymerase colony) e secuenciación SOLiD, (desenvolvida pola compañía Agencourt, despois chamada Applied Biosystems, e agora Life Technologies).[26][27][28]
Secuenciación de escopeta[editar | editar a fonte]
- Artigo principal: Secuenciación de escopeta.
A secuenciación de escopeta (shotgun) é un método de secuenciación deseñado para a análise de secuencias de ADN maiores de 1000 pares de bases, e ata de cromosomas enteiros. Este método require romper o ADN diana en fragmentos aleatoriamente. Despois de secuenciar cada un dos fragmentos, as secuencias poden ser reensambladas utilizando as súas rexións de solapamento.[29]
PCR ponte[editar | editar a fonte]
Outro método de amplificación clonal in vitro é a PCR ponte, na cal se amplifican os fragmentos sobre cebadores adheridos a unha superficie sólida [17][30][31] e forman "colonias de ADN" ou "clusters de ADN". Este método utilízase nos secuenciadores analizadores de xenoma da compañía Illumina. Métodos dunha soa molécula como o desenvolvido polo laboratorio de Stephen Quake (posteriormente comercializado por Helicos) son unha excepción: utilizan fluoróforos brillantes e excitación láser para detectar os eventos de adición de bases en cada molécula de ADN fixada a unha superficie, o que evita a necesidade de facer unha amplificación molecular.[32]
Métodos de seguinte xeración[editar | editar a fonte]

A grande demanda de métodos de secuenciación de baixo custo fixo que se desenvolvesen tecnoloxías de scuenciación de alto rendemento (ou secuenciación de seguinte xeración) que paralelizan o proceso de secuenciación, producindo miles ou millóns de secuencias ao mesmo tempo.[33][34] As tecnoloxías de secuenciación de alto rendemento están pensadas para rebaixar o custo da secuenciación do ADN máis do que é posible cos métodos estándar de colorante-terminador.[21] Na secuenciación de ultra-alto rendemento poden facerse en paralelo ata 500.000 operacións de secuenciación por síntese.[35][36][37]
| Método | Secuenciación en tempo real dunha soa molécula (Pacific Bio) | Ión semicondutor (secuenciación de Ion Torrent Systems) | Pirosecuenciación (454) | Secuenciación por síntese (Illumina) | Secuenciación por ligazón (secuenciación SOLiD) | Terminación de cadea (secuenciación de Sanger) |
|---|---|---|---|---|---|---|
| Lonxitude de lectura | 2900 bp de media[40] | 200 bp | 700 bp | de 50 a 250 bp | 50+35 ou 50+50 bp | de 400 a 900 bp |
| Precisión | 87% (en modo de lonxitude lida), 99% (en modo exactitude) | 98% | 99.9% | 98% | 99.9% | 99.9% |
| Lectura por execución | 35–75 mil [41] | ata 5 millóns | 1 millón | ata 3.000 millóns | de 1,2 a 1,4 miles de millóns | non dispoñible |
| Tempo por execución | de 30 minutos a 2 horas [42] | 2 horas | 24 horas | de 1 a 10 días, dependendo do secuenciador e da lonxitude de lectura especificada[43] | de 1 a 2 semanas | de 20 minutos a 3 horas |
| Custo por 1 millón de bases (en dólares $) | 2 $ | 1 $ | 10 $ | 0,05 a 0,15 $ | 0,13 $ | 2400 $ |
| Vantaxes | A maior lonxitude de lectura. Rápido. Detecta 4mC, 5mC, 6mA.[44] | Equipamento máis barato. Rápido. | Tamaño de lectura longo. Rápido. | Potencial para un rendemento de secuencia alto, dependendo do modelo do secuenciador e a aplicación desexada. | Baixo custo por base. | Lecturas individuais longas. Útil para moitas aplicacións. |
| Desvantaxes | Baixo rendemento a precisión alta. O equipamento pode ser moi caro. | Erros de homopolímeros. | As execucións son caras. Erros de homopolímeros. | O equipamento pode ser moi caro. | Máis lento que outros métodos. | Máis caro e pouco práctico para proxectos de secuenciación grandes. |
Secuencianción de sinaturas masivamente paralela (MPSS)[editar | editar a fonte]
A primeira das tecnoloxías de seguinte xeración, a secuenciación de sinaturas masivamente paralela (ou MPSS), foi desenvolvida na década de 1990 por Lynx Therapeutics, unha compañía fundada en 1992 por Sydney Brenner e Sam Eletr. A MPSS era un método baseado en esferas de polímero (cada unha contiña un tipo de secuencia de ADN) que usaba unha estratexia complexa de ligazón de adaptador seguida de decodificación de adaptador, e lectura da secuencia en incrementos de catro nucleótidos. Este método fixo que fose susceptible a un nesgo específico de secuencia ou perda de secuencias específicas. Como a tecnoloxía era tan complexa, a MPSS só foi utilizada pola propia Lynx Therapeutics e non se venderon máquinas de secuenciación a laboratorios independentes. Lynx Therapeutics fusionouse con Solexa (posteriormente adquirida por Illumina) en 2004, o que levou ao desenvolvemento da secuenciación por síntese, unha aproximación máis simple mercada a Manteia Predictive Medicine, que fixo que a MPSS quedase obsoleta. Porén, as propiedades esenciais da saída de datos da MPSS eran os típicos dos posteriores tipos de datos de métodos de "seguinte xeración", que incluían centos ou miles de curtas secuencias de ADN. No caso da MPSS, estas usábanse xeralmente para secuenciar ADNc para medir os niveis de expresión xénica.[45]
Secuenciación Polony[editar | editar a fonte]
O método de secuenciación Polony (contracción de polymerase colony) desenvolvido no laboratorio de George M. Church en Harvard, foi un dos primeiros sistemas de secuenciación de seguinte xeración e foi usado para secuenciar un xenoma completo en 2005. Combinaba unha libraría de etiquetas de extremos emparellados in vitro con PCR de emulsión, un microscopio automatizado, e química de secuenciación baseada en ligadores para secuenciar un xenoma de E. coli cunha precisión de >99.9999% e un custo de aproximadamente 1/9 do custo da secuenciación de Sanger.[46] A tecnoloxía pertencía a Agencourt Biosciences, despois de Agencourt Personal Genomics, e finalmente foi incorporada á plataforma de Applied Biosystems SOLiD, que agora pertence a Life Technologies.
Pirosecuenciación 454[editar | editar a fonte]
A compañía 454 Life Sciencies, despois adquirida por Roche Diagnostics, desenvolveu unha versión paralelizada da pirosecuenciación. O método amplifica o ADN dentro de pingas de auga en solución de aceite (PCR de emulsión), e cada pinga contén un só molde de ADN unido a esferas de polímero cubertas por un só cebador que despois forman unha colonia clonal. A máquina de secuenciación contén moitos pozos con volumes de picolitros, cada un dos cales contén unha soa esfera de polímero e encimas de secuenciación. A pirosecuenciación usa o encima luciferase para xerar luz ao detectar cada nucleótido engadido ao ADN nacente, e os datos combinados utilízanse para xear lecturas das secuencias.[26] Esta tecnoloxía proporciona lecturas dunha lonxitude intermedia e prezos por base entre os da secuenciación de Sanger nun extremo e Solexa e SOLiD no outro.[21]
Secuenciación de Illumina (Solexa)[editar | editar a fonte]
Solexa, que agora forma parte da compañía Illumina, desenvolveu un método de secuenciación baseado nunha tecnoloxía de colorantes terminadores reversible, e polimerases modificadas por enxeñaría, desenvolvidas na compañía.[47] A química da tecnoloxía foi desenvolvida por Solexa e o concepto do sistema Solexa foi inventado por Balasubramanian e Klennerman da Universidade de Cambridge. En 2004, Solexa absorbeu a compañía Manteia Predictive Medicine para obter unha tecnoloxía de secuenciación masivamente paralelizada baseada en "clusters de ADN", que implica a amplificación clonal do ADN sobre unha superficie. A tecnoloxía de clusters foi coadquirida xunto con Lynx Therapeutics de California. Despois, Solexa Ltd. fusionouse con Lynx para formar Solexa Inc.

Neste método as moléculas de ADN e os cebadores únense primeiro sobre unha placa e son amplificados con polimerase para que se formen colonias de ADN clonais locais, que despois foron denominadas "clusters de ADN". Para determinar a secuencia, engádense catro tipos de bases terminadoras reversibles (bases RT) e son eliminados por lavado os nucleótidos non incorporados. Unha cámara rexistra imaxes dos nucleótidos marcados fluorescentemente, despois elimínase quimicamente do ADN o colorante, xunto co bloqueador terminal 3', o que permite que empece o seguinte ciclo. A diferenza da pirosecuenciación, as cadeas de ADN son alongadas nun só nucleótido en cada vez e a captura das imaxes pode realizarse con certo atraso, o que permite que se capturen por medio de imaxes secuenciais conxuntos moi grandes de colonias de ADN tomadas por unha soa cámara.
Desacoplando a reacción encimática e a captura de imaxes o rendemento é óptimo e teoricamente a capacidade de secuenciación é ilimitada. Cunha configuración óptima, o rendemento ao que finalmente chega o instrumento está así ditado só pola taxa de conversión de analóxico a dixital da cámara, multiplicada polo número de cámaras e dividida polo número de píxeles por colonia de ADN que cómpren para visualizalas optimamente (aproximadamente 10 píxeles/colonia). En 2012, con cámaras que operaban a taxas de conversión de máis de 10 MHz A/D e a óptica, fluídica e encimática dispoñibles, o rendemento pode ser de múltiplos de 1 millón de nucleótidos/segundo, correspondentes aproximadamente ao equivalente a un xenoma humano a 1x de cobertura (número de veces que un nucleótido se le durante o proceso de secuenciación) por hora por instrumento, e 1 xenoma humano resecuenciado (a aproximadamente 30x) por día por instrumento (equipado cunha soa cámara).[48]
Secuenciación SOLiD[editar | editar a fonte]
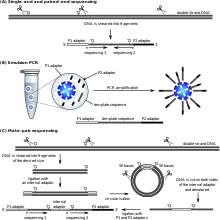
A tecnoloxía SOLiD de Applied Biosystems (agora unha marca de Life Technologies) emprega a secuenciación por ligazón, que utiliza o encima ADN ligase para identificar o nucleótido presente nunha posición determinada nunha secuencia de ADN. Nesta secuenciación, etiquétase (con fluorescencia) un conxunto (pool) de todos os posibles oligonucleótidos dunha lonxitude fixada segundo a posición secuenciada. Os oligonucleótidos son anelados (hibridados) e ligados; utilízase a ADN ligase para ligar as secuencias que coinciden, o que dá lugar a un sinal (fluorescente) que informa do nucleótido situado nesa posición. Antes de secuenciar, o ADN é amplificado por PCR de emulsión. As esferas que se forman, cada unha das cales contén copias dunha soa molécula de ADN, deposítanse nunha placa de cristal.[49] O resultado son secuencias de cantidades e lonxitudes comparables ás do método de secuenciación de Illumina.[21]
Secuenciación de ión semicondutor[editar | editar a fonte]
Ion Torrent Systems Inc. (que agora pertence a Life Technologies) desenvolveu un sistema chamado secuenciación de ión semicondutor baseado no uso de química de secuenciación estándar, pero cunha novidade, un sistema de detección baseado en semicondutores. Este método de secuenciación está baseado na detección dos ións hidróxeno (H+) que se liberan durante a polimerización do ADN, en contraposición aos métodos ópticos utilizados noutros sistemas de secuenciación. Un micropozo que contén unha fibra molde de ADN que vai ser secuenciada énchese cunha solución cun só tipo de nucleótido. Se o nucleótido introducido é complementario ao nucleótido inicial do molde, é incorporado na cadea complementaria en crecemento. Isto causa a liberación dun ión hidróxeno que é detectado por un sensor de ións hipersensitivo, o cal indica que tivo lugar a reacción. Se están presentes repeticións de homopolímero na secuencia molde, serán incorporados múltiples nucleótidos nun só ciclo. Isto orixina un número correspondente de ións hidróxeno liberados e un sinal electrónico proporcionalmente maior.[50]

Secuenciación de nanobolas de ADN[editar | editar a fonte]
A secuenciación de nanobolas de ADN é un tipo de tecnoloxía de secuenciación de alto rendemento usada para determinar a secuencia xenómica enteira dun organismo. A compañía Complete Genomics utiliza esta tecnoloxía para secuenciar mostra enviadas por investigadores independentes. O método utiliza a replicación de círculos rodantes para amplificar pequenos fragmentos de ADN xenómico que foron circularizados, e as copias quedan compactadas en nanobolas de ADN. Despois utilízase secuenciación non encadeada por ligazón para determinar a secuencia de nucleótidos.[51] Este método de secuenciación de ADN permite secuenciar gran cantidade de nanobolas de ADN en cada execución e cun baixo custo dos reactivos en comparación con outras plataformas de secuenciacioón de seguinte xeración.[52] Porén, só se determinan secuencias curtas de ADN en cada nanobola de ADN, o cal fai que o mapado das curtas lecturas nun xenoma de referencia sexa difícil.[53] Esta tecnoloxía tense utilizado para proxectos de secuenciación de múltiples xenomas e está programada para ser usada para máis.[54]
Secuenciación dunha soa molécula Heliscope[editar | editar a fonte]
A secuenciación Heliscope é un método de secuenciación dunha soa molécula desenvolvido por Helicos Biosciences. Utiliza fragmentos de ADN aos que se lle engadiron colas poli A adaptadoras, que están unidas á superficie da célula de fluxo. Os seguintes pasos implican a secuenciación baseada na extensión con lavados cíclicos da célula de fluxo con nucleótidos marcados fluorescentemente (un tipo de nucleótido de cada vez, como no método de Sanger). As lecturas realízanse polo secuenciador Heliscope. As lecturas son curtas, de ata 55 bases por execución, pero melloras recenten permiten lecturas máis precisas de tramos dun tipo de nucleótido.[55][56]
Este método de secuenciación e equipamento utilizáronse para secuenciar o xenoma do bacteriófago M13.[57]
Secuenciación dunha soa molécula en tempo real (SMRT)[editar | editar a fonte]
A secuenciación SMRT baséase na estratexia de secuenciación por síntese. O ADN sintetízase en guías de ondas en modo cero (ZMWs), que son pequenos contedores similares a pozos que teñen as ferramentas de captura situadas no fondo do pozo. As guías de ondas en modo cero son guías de ondas ópticas que guían a enerxía da luz a un volume que é pequeno en todas as súas dimensións comparado coa lonxitude de onda da luz. A secuenciación realízase usando polimerases non modificadas (unidas ao fondo das ZMW) e nucleótidos marcados fluorescentemente que flúen libres na solución. Os pozos están construídos de modo que só se detecte a fluorescencia do fondo do pozo. A marcaxe fluorescente sepárase do nucleótido cando este se incorpora na cadea de ADN, polo que a cadea de ADN queda inmodificada. Segundo Pacific Biosciences, que desenvolveu a tecnoloxía SMRT, esta metodoloxía permite a detección de modificacións de nucleótidos (como a metilación da citosina). Isto ocorre por observación da cinética da polimerase. Esta estratexia permite lecturas de ata 15.000 nucleótidos, con lecturas medias de lonxitudes entre 2,5 e 2,9 kb.[40]
Métodos en desenvolvemento[editar | editar a fonte]
Actualmente hai varios métodos de secuenciación do ADN que están en desenvolvemento, como o da ADN polimerase etiquetada,[58] lectura de secuencias como tránsitos de cadeas de ADN a través de nanoporos,[59][60] e técnicas baseadas en microscopía, como as que usan o microscopio de forza atómica ou o microscopio electrónico de transmisión, que se usan para identificar as posicións de cada nucleótido en fragmentos de ADN longos (>5.000 bp) por medio dun etiquetado dos nucleótidos con elementos máis pesados (por exemplo, halóxenos) para a detección visual e gravación.[61][62] As tecnoloxías de terceira xeración pretenden incrementar o rendemento e diminuír o tempo para obter os resultados e o custo ao eliminaren a necesidade de usar excesivos reactivos e aproveitar a procesividade da ADN polimerase.[63]
Secuenciación de ADN por nanoporos[editar | editar a fonte]
O método de secuenciación de ADN por nanoporos está baseado na lectura de sinais eléctricos que se producen ao paseren os nucleótidos por poros formados pola proteína bacteriana alfa-hemolisina unida covalentemente con ciclodextrina. Os nanoporos están inmersos nun fluído condutor e aplícase unha voltaxe a través del para que se cre unha corrente eléctrica debida ao paso de ións a través do nanoporo. O paso do ADN a través do nanoporo cambia neste a corrente de ións. Este cambio é dependente da forma, tamaño e lonxitude da secuencia de ADN. Cada tipo de nucleótido bloquea o fluxo de ións a través do poro durante un período de tempo diferente. O método ten un grande potencial de desenvolvemento, xa que non precisa nucleótidos modificados, pero aínda non se pode obter unha resolución dun só nucleótido.[64]
Sequenciación por hibridación[editar | editar a fonte]
A secuenciación por hibridación é un método non encimático que usa unha micromatriz de ADN. Etiquétase fluorescentemente un só conxunto de ADNs cuxa secuencia se pretende determinar e hibrídase cunha matriz que contén secuencias coñecidas. Os fortes sinais que indican hibridación procedentes dun determinado punto da matriz serven para identificar a súa secuencia no ADN que se está a secuenciar.[65]
Sequenciación con espectrometría de masas[editar | editar a fonte]
A espectrometría de masas pode utilizarse para determinar as secuencias de ADN. A espectrometría de masas de ionización/desorción de láser asistido por matriz ou MALDI-TOF MS, foi investigada como método alternativo á electroforese en xel para visualizar fragmentos de ADN. Con este método, os fragmentos dee ADN xerados polas reaccións de secuenciación de terminación de cadea compáranse pola súa masa en vez de polo seu tamaño. A masa de cada nucleótido é diferente e esta difeenza é detectable por espectroscopía de masas. As mutacións dun só nucleótido nun fragmento poden ser detectadas máis doadamente con espectroscopía de masas que só por electroforese en xel. A MALDI-TOF MS pode detectar máis facilmente as diferenza entre fragmentos de ARN, polo que os investigdores poden indirectamente secuenciar o ADN por estes métodos baseados na espectroscopía de masas convertendo primeiro o ADN en ARN.[66]
A maior resolución dos fragmentos de ADN que permiten os métodos baseados na espectroscopía de masas ten especial interese para os investigadores en ciencia forense, xa que poden ter que detectar polimorfismos dun só nucleótido en mostras de ADN humano para identificar a individuos. Estas mostras poden estar moi degradadas, polo que os investigadores forenses a miúdo prefiren examinar o ADN mitocondrial pola súa maior estabilidade e aplicacións para estudos de parentesco. Nos Estados Unidos, os métodos de secuenciación baseados en espectroscopía de masas foron utilizados para comparar as secuencias do ADN mitocondrial humano de mostras da base de datos do FBI [67] e de ósos atopados en fosas comúns de soldados da primeira guerra mundial.[68]
Os métodos de terminación de cadea temperá e TOF MS demostraron poder ler lonxitudes de ADN de ata 100 pares de bases.[69] Os investigadores non foron quen de superar este tamaño medio de lectura; igual que a secuenciación de terminación de cadea por si soa, a ecuenciación de ADN baseada na espectroscopía de masas pode non ser axeitada para proxectos de secuenciadción de novo grandes. Aínda así, un estudo recente utilizou as lecturas de secuencias curtas e a espectroscopía de masas para comparar polimorfismos dun só nucleótido en cepas patóxenas de Streptococcus.[70]
Secuenciación de Sanger microfluídica[editar | editar a fonte]
Na secuenciación de Sanger microfluídica a amplificación termocíclica completa de fragmentos de ADN e a súa separación por electroforese faise sobre unha soa oblea de cristal de aproximadamente de 10 cm de diámetro reducindo así o uso de reactivos e o seu custo.[71] En certos casos os investigadores mostraron que poden incrementar o rendemento da secuenciación convencional utilizando microchips.[72] Aínda haberá que facer moita máis investigación sobre esta tecnoloxía para facer que o seu uso exa efectivo.
Técnicas baseadas en microscopía[editar | editar a fonte]
Esta estratexia permite visualizar directamente a secuencia das moléculas de ADN utilizando microscopía electrónica. Demostrouse a primeira identificación de pares de bases de ADN en moléculas intactas de ADN por medio da incorporación encimática de bases modificadas, as cales conteñen átomos de número atómico elevado, e a visualización directa e identificación de bases marcadas individualizadamente nunha molécula de ADN sintética de 3.272 pares de bases e nun xenoma viral de 7.249 pares de bases.[73]
Secuecnciación con RNAP[editar | editar a fonte]
Este método está baseado no uso da ARN polimerase (RNAP), que está unida a esferas de poliestireno. Un dos extremos do ADN a secuenciar únese a outra desas esferas, e ambas as esferas sitúanse en trampas ópticas. O movemento da RNAP durante a transcrición fai que as esferas se acheguen e a súa distancia relativa cambia, o cal pode ser rexistrado á resolución dun só nucleótido. A secuencia dedúcese baseándose nas catro lecturas con concentracións diminuídas de cada un dos catro tipos de nucleótidos, de xeito similar ao método de Sanger.[74]
Secuenciación de alta resolución de virus in vitro[editar | editar a fonte]
Desenvolveuse un método para analizar conxuntos completos de interaccións proteicas usando unha combinación de pirosecuenciación 454 e un método de ARNm display de virus in vitro. Especificamente, este método liga covalentemente as proteínas de interese aos ARNm que as codifican, despois detecta os fragmentos de ARNm usando PCRs de reversotranscrición. O ARNm pode despois ser amplificado e secuenciado. O método combinado foi denominado IVV-HiTSeq e pode ser realizado en condicións libres de células, aínda que os seus resultados poden non reflectir as condicións in vivo.[75]
Iniciativas de desenvolvemento[editar | editar a fonte]
En outubro de 2006, a X Prize Foundation presentou unha iniciativa para promover o desenvolvemento de tecnoloxías de secuenciación de xenomas completos, chamada Archon X Prize, asignando como premio 10 millóns de dólares para o "primeiro equipo que poida construír un aparello e utilizalo para secuenciar 100 xenomas humanos en 10 días ou menos, cunha exactitude de non máis dun erro por cada 100.000 bases secuenciadas, con secuencias que cubran con precisión polo menos o 98% do xenoma, e a un custo rocorrente de non máis de 10.000 dólares de EEUU por xenoma."[76]
Todos os anos o National Human Genome Research Institute ou NHGRI promove bolsas para novas investigacións e desenvolvementos en xenómica. 2010 bolsas e 2011 candidatos incluían traballos en metodoloxías de secuenciación microfluídica, polony e de bases pesadas.[77]
Notas[editar | editar a fonte]
- ↑ Olsvik, Ørjan; Wahlberg, Johan; Petterson B; et al. (1993). "Use of automated sequencing of polymerase chain reaction-generated amplicons to identify three types of cholera toxin subunit B in Vibrio cholerae O1 strains". J. Clin. Microbiol. 31 (1): 22–25. PMC 262614. PMID 7678018. Arquivado dende o orixinal o 04 de xuño de 2020. Consultado o 09 de xullo de 2013.
- ↑ Pettersson E, Lundeberg J, Ahmadian A (2009). "Generations of sequencing technologies". Genomics 93 (2): 105–11. PMID 18992322. doi:10.1016/j.ygeno.2008.10.003.
- ↑ Watson JD, Crick FH (1953). "The structure of DNA". Cold Spring Harb. Symp. Quant. Biol. 18: 123–31. PMID 13168976. doi:10.1101/SQB.1953.018.01.020.
- ↑ Min Jou W, Haegeman G, Ysebaert M, Fiers W (1972). "Nucleotide sequence of the gene coding for the bacteriophage MS2 coat protein". Nature 237 (5350): 82–8. Bibcode:1972Natur.237...82J. PMID 4555447. doi:10.1038/237082a0.
- ↑ Fiers W; Contreras R; Duerinck F; et al. (1976). "Complete nucleotide sequence of bacteriophage MS2 RNA: primary and secondary structure of the replicase gene". Nature 260 (5551): 500–7. Bibcode:1976Natur.260..500F. PMID 1264203. doi:10.1038/260500a0.
- ↑ 6,0 6,1 Sanger F, Nicklen S, Coulson AR (1977). "DNA sequencing with chain-terminating inhibitors". Proc. Natl. Acad. Sci. U.S.A. 74 (12): 5463–7. Bibcode:1977PNAS...74.5463S. PMC 431765. PMID 271968. doi:10.1073/pnas.74.12.5463.
- ↑ 7,0 7,1 7,2 Maxam AM, Gilbert W (1977). "A new method for sequencing DNA". Proc. Natl. Acad. Sci. U.S.A. 74 (2): 560–4. Bibcode:1977PNAS...74..560M. PMC 392330. PMID 265521. doi:10.1073/pnas.74.2.560.
- ↑ Gilbert, W. DNA sequencing and gene structure. Nobel lecture, 8 December 1980.
- ↑ Gilbert W, Maxam A (1973). "The Nucleotide Sequence of the lac Operator". Proc. Natl. Acad. Sci. U.S.A. 70 (12): 3581–4. Bibcode:1973PNAS...70.3581G. PMC 427284. PMID 4587255. doi:10.1073/pnas.70.12.3581.
- ↑ Sanger F; Air GM; Barrell BG; et al. (1977). "Nucleotide sequence of bacteriophage phi X174 DNA". Nature 265 (5596): 687–95. Bibcode:1977Natur.265..687S. PMID 870828. doi:10.1038/265687a0.
- ↑ "Smithsonian Institue Archives". Arquivado dende o orixinal o 26 de setembro de 2017. Consultado o 10 de xullo de 2013.
- ↑ Adams MD; Kelley JM; Gocayne JD; et al. (1991). "Complementary DNA sequencing: expressed sequence tags and human genome project". Science 252 (5013): 1651–6. Bibcode:1991Sci...252.1651A. PMID 2047873. doi:10.1126/science.2047873.
- ↑ Fleischmann RD; Adams MD; White O; et al. (1995). "Whole-genome random sequencing and assembly of Haemophilus influenzae Rd". Science 269 (5223): 496–512. Bibcode:1995Sci...269..496F. PMID 7542800. doi:10.1126/science.7542800.
- ↑ Lander ES; Linton LM; Birren B; et al. (2001). "Initial sequencing and analysis of the human genome". Nature 409 (6822): 860–921. PMID 11237011. doi:10.1038/35057062.
- ↑ Venter JC; Adams MD; Myers EW; et al. (2001). "The sequence of the human genome". Science 291 (5507): 1304–51. Bibcode:2001Sci...291.1304V. PMID 11181995. doi:10.1126/science.1058040.
- ↑ M. Ronaghi, S. Karamohamed, B. Pettersson, M. Uhlen, and P. Nyren (1996). "Real-time DNA sequencing using detection of pyrophosphate release". Analytical Biochemistry 242 (1): 84–9. PMID 8923969. doi:10.1006/abio.1996.0432.
- ↑ 17,0 17,1 Eric H. Kawashima, Laurent Farinelli, Pascal Mayer. Patent: Method of nucleic acid amplification. Acceso 2012-12-22. Data 2005-05-12. [1] Arquivado 22 de febreiro de 2013 en Archive.is
- ↑ Brenner S; et al. (2000). "Gene expression analysis by massively parallel signature sequencing (MPSS) on microbead arrays". Nature Biotechnology (Nature Biotechnology) 18 (6): 630–634. PMID 10835600. doi:10.1038/76469.
- ↑ Stein RA (1 September 2008). "Next-Generation Sequencing Update". Genetic Engineering & Biotechnology News 28 (15).
- ↑ Margulies M; Egholm M; Altman WE; et al. (2005). "Genome Sequencing in Open Microfabricated High Density Picoliter Reactors". Nature 437 (7057): 376–80. Bibcode:2005Natur.437..376M. PMC 1464427. PMID 16056220. doi:10.1038/nature03959.
- ↑ 21,0 21,1 21,2 21,3 Schuster Stephan C. (2008). "Next-generation sequencing transforms today's biology". Nat. Methods 5 (1): 16–8. PMID 18165802. doi:10.1038/nmeth1156.
- ↑ Ewing, Brent; Green, Phil (1 de marzo de 1998). "Base-calling of automated sequencer traces using phred. II. Error probabilities". Genome Research 8 (3): 186–94. PMID 9521922. doi:10.1101/gr.8.3.186.
- ↑ Sanger F, Coulson AR (1975). "A rapid method for determining sequences in DNA by primed synthesis with DNA polymerase". J. Mol. Biol. 94 (3): 441–8. PMID 1100841. doi:10.1016/0022-2836(75)90213-2.
- ↑ Wetterstrand, Kris. "DNA Sequencing Costs: Data from the NHGRI Genome Sequencing Program (GSP)". National Human Genome Research Institute. Consultado o 30 May 2013.
- ↑ Richard Williams, Sergio G Peisajovich, Oliver J Miller, Shlomo Magdassi, Dan S Tawfik, Andrew D Griffiths (2006). "Amplification of complex gene libraries by emulsion PCR". Nature methods 3 (7): 545–550. PMID 16791213. doi:10.1038/nmeth896.
- ↑ 26,0 26,1 Margulies M; Egholm M; Altman WE; et al. (2005). "Genome Sequencing in Open Microfabricated High Density Picoliter Reactors". Nature 437 (7057): 376–80. Bibcode:2005Natur.437..376M. PMC 1464427. PMID 16056220. doi:10.1038/nature03959.
- ↑ Shendure, J.; Porreca, GJ; Reppas, NB; Lin, X; McCutcheon, JP; Rosenbaum, AM; Wang, MD; Zhang, K; Mitra, RD (2005). "Accurate Multiplex Polony Sequencing of an Evolved Bacterial Genome". Science 309 (5741): 1728–32. Bibcode:2005Sci...309.1728S. PMID 16081699. doi:10.1126/science.1117389.
- ↑ "Applied Biosystems' SOLiD technology". Arquivado dende o orixinal o 16 de maio de 2008. Consultado o 09 de xullo de 2013.
- ↑ Staden, R (1979 Jun 11). "A strategy of DNA sequencing employing computer programs.". Nucleic Acids Research 6 (7): 2601–10. PMID 461197. doi:10.1093/nar/6.7.2601.
- ↑ P. Mayer,L. Farinelli, G. Matton, C. Adessi, G. Turcatti, J. J. Mermod, E. Kawashima.DNA colony massively parallel sequencing ams98 presentation
- ↑ Method for performing amplification of nucleic acid with two primers bound to a single solid support. US patent - 5641658 [2]
- ↑ Braslavsky I, Hebert B, Kartalov E, Quake SR (2003). "Sequence information can be obtained from single DNA molecules". Proc. Natl. Acad. Sci. U.S.A. 100 (7): 3960–4. Bibcode:2003PNAS..100.3960B. PMC 153030. PMID 12651960. doi:10.1073/pnas.0230489100.
- ↑ Hall, Nell (2007). "Advanced sequencing technologies and their wider impact in microbiology". J. Exp. Biol. 209 (Pt 9): 1518–1525. PMID 17449817. doi:10.1242/jeb.001370.
- ↑ Church, George M. (2006). "Genomes for all". Sci. Am. 294 (1): 46–54. PMID 16468433. doi:10.1038/scientificamerican0106-46.
- ↑ Kalb, Gilbert; Moxley, Robert (1992). Massively Parallel, Optical, and Neural Computing in the United States. IOS Press. ISBN 90-5199-097-9.
- ↑ Ten Bosch, J. R.; Grody, W. W. (2008). "Keeping Up with the Next Generation". The Journal of Molecular Diagnostics 10 (6): 484–492. doi:10.2353/jmoldx.2008.080027. PMC 2570630. PMID 18832462.
- ↑ Tucker, T.; Marra, M.; Friedman, J. M. (2009). "Massively Parallel Sequencing: The Next Big Thing in Genetic Medicine". The American Journal of Human Genetics 85 (2): 142–154. doi:10.1016/j.ajhg.2009.06.022. PMC 2725244. PMID 19679224.
- ↑ Quail, Michael; Smith, Miriam E; Coupland, Paul; et al. (1 January 2012). "A tale of three next generation sequencing platforms: comparison of Ion torrent, pacific biosciences and illumina MiSeq sequencers". BMC Genomics 13 (1): 341. PMC 3431227. PMID 22827831. doi:10.1186/1471-2164-13-341.
- ↑ Liu, Lin; Li, Yinhu; Li, Siliang; et al. (1 January 2012). "Comparison of Next-Generation Sequencing Systems". Journal of Biomedicine and Biotechnology (Hindawi Publishing Corporation) 2012: 1–11. doi:10.1155/2012/251364.
- ↑ 40,0 40,1 "After a Year of Testing, Two Early PacBio Customers Expect More Routine Use of RS Sequencer in 2012". GenomeWeb. 10 January 2012.
- ↑ Rasko, David A.; Webster, Dale R.; Sahl, Jason W.; et al. (25 August 2011). "Origins of the Strain Causing an Outbreak of Hemolytic–Uremic Syndrome in Germany". N Engl J Med 365 (8): 709–717. doi:10.1056/NEJMoa1106920.
- ↑ Tran, Ben; Brown, Andrew M.K.; Bedard, Philippe L.; Winquist, Eric; Goss, Glenwood D.; Hotte, Sebastien J.; Welch, Stephen A.; Hirte, Hal W.; Zhang, Tong; Stein, Lincoln D.; Ferretti, Vincent; Watt, Stuart; Jiao, Wei; Ng, Karen; Ghai, Sangeet; Shaw, Patricia; Petrocelli, Teresa; Hudson, Thomas J.; Neel, Benjamin G.; et al. (1 January 2012). "Feasibility of real time next generation sequencing of cancer genes linked to drug response: Results from a clinical trial". Int. J. Cancer: 1547–1555. doi:10.1002/ijc.27817.
- ↑ van Vliet, Arnoud H.M. (1 January 2010). "Next generation sequencing of microbial transcriptomes: challenges and opportunities". FEMS Microbiology Letters 302 (1): 1–7. doi:10.1111/j.1574-6968.2009.01767.x.
- ↑ Murray, I. A.; Clark, T. A.; Morgan, R. D.; Boitano, M.; Anton, B. P.; Luong, K.; Fomenkov, A.; Turner, S. W.; Korlach, J.; Roberts, R. J. (2 October 2012). "The methylomes of six bacteria". Nucleic Acids Research. doi:10.1093/nar/gks891.
- ↑ Brenner, Sidney; Johnson, M; Bridgham, J; Golda, G; Lloyd, DH; Johnson, D; Luo, S; McCurdy, S; Foy, M (2000). "Gene expression analysis by massively parallel signature sequencing (MPSS) on microbead arrays". Nature Biotechnology (Nature Biotechnology) 18 (6): 630–634. PMID 10835600. doi:10.1038/76469.
- ↑ Shendure, J; Porreca, GJ; Reppas, NB; Lin, X; McCutcheon, JP; Rosenbaum, AM; Wang, MD; Zhang, K; Mitra, RD; Church, GM (2005 Sep 9). "Accurate multiplex polony sequencing of an evolved bacterial genome.". Science 309 (5741): 1728–32. PMID 16081699. doi:10.1126/science.1117389.
- ↑ Bentley, D. R.; Balasubramanian, S.; Swerdlow, H. P.; Smith, G. P.; Milton, J.; Brown, C. G.; Hall, K. P.; Evers, D. J. et al. (2008). "Accurate whole human genome sequencing using reversible terminator chemistry". Nature 456 (7218): 53–59. doi:10.1038/nature07517. PMC 2581791. PMID 18987734.
- ↑ Mardis ER (2008). "Next-generation DNA sequencing methods". Annu Rev Genomics Hum Genet 9: 387–402. PMID 18576944. doi:10.1146/annurev.genom.9.081307.164359.
- ↑ Valouev A; Ichikawa J; Tonthat T; et al. (2008). "A high-resolution, nucleosome position map of C. elegans reveals a lack of universal sequence-dictated positioning". Genome Res. 18 (7): 1051–63. PMC 2493394. PMID 18477713. doi:10.1101/gr.076463.108.
- ↑ Rusk N (2011). "Torrents of sequence". Nat Meth 8 (1): 44–44.
- ↑ Drmanac R.; et al. (2010). "Human Genome Sequencing Using Unchained Base Reads in Self-Assembling DNA Nanoarrays". Science 327 (5961): 78–81.
- ↑ Porreca JG (2010). "Genome Sequencing on Nanoballs". Nature Biotechnology 28 (1): 43–44. PMID 20062041. doi:10.1038/nbt0110-43.
- ↑ Drmanac R.; et al. (2010). "Human Genome Sequencing Using Unchained Base Reaads in Self-Assembling DNA Nanoarrays, Supplementary Material". Science 327 (5961): 78–81.
- ↑ Complete Genomics Arquivado 25 de agosto de 2010 en Wayback Machine. Press release, 2010
- ↑ "HeliScope Gene Sequencing / Genetic Analyzer System : Helicos BioSciences". Arquivado dende o orixinal o 02 de novembro de 2009. Consultado o 09 de xullo de 2013.
- ↑ Thompson, JF; Steinmann, KE (2010 Oct). "Single molecule sequencing with a HeliScope genetic analysis system.". Current protocols in molecular biology / edited by Frederick M. Ausubel ... [et al.] Chapter 7: Unit7.10. PMC 2954431. PMID 20890904. doi:10.1002/0471142727.mb0710s92.
- ↑ Harris, TD; Buzby, PR; Babcock, H; Beer, E; Bowers, J; Braslavsky, I; Causey, M; Colonell, J; Dimeo, J; Efcavitch, JW; Giladi, E; Gill, J; Healy, J; Jarosz, M; Lapen, D; Moulton, K; Quake, SR; Steinmann, K; Thayer, E; Tyurina, A; Ward, R; Weiss, H; Xie, Z (2008 Apr 4). "Single-molecule DNA sequencing of a viral genome.". Science 320 (5872): 106–9. PMID 18388294. doi:10.1126/science.1150427.
- ↑ "VisiGen Biotechnologies Inc. – Technology Overview" (en inglés). Visigenbio.com. Arquivado dende o orixinal o 07 de setembro de 2008. Consultado o 2009-11-15.
- ↑ "The Harvard Nanopore Group". Mcb.harvard.edu. Arquivado dende o orixinal o 21 de febreiro de 2002. Consultado o 2009-11-15.
- ↑ "Nanopore Sequencing Could Slash DNA Analysis Costs".
- ↑ US patent 20060029957, ZS Genetics, "Systems and methods of analyzing nucleic acid polymers and related components", issued 2005-07-14
- ↑ Xu M, Fujita D, Hanagata N (2009). "Perspectives and challenges of emerging single-molecule DNA sequencing technologies". Small 5 (23): 2638–49. PMID 19904762. doi:10.1002/smll.200900976.
- ↑ Schadt, E.E.; S. Turner, A. Kasarskis (2010). "A window into third-generation sequencing". Human Molecular Genetics 19 (R2): R227–40. PMID 20858600. doi:10.1093/hmg/ddq416.
- ↑ Stoddart, D; Heron, AJ; Mikhailova, E; Maglia, G; Bayley, H (2009 May 12). "Single-nucleotide discrimination in immobilized DNA oligonucleotides with a biological nanopore.". Proceedings of the National Academy of Sciences of the United States of America 106 (19): 7702–7. PMC 2683137. PMID 19380741. doi:10.1073/pnas.0901054106.
- ↑ Hanna GJ; Johnson VA; Kuritzkes DR; et al. (1 July 2000). "Comparison of Sequencing by Hybridization and Cycle Sequencing for Genotyping of Human Immunodeficiency Virus Type 1 Reverse Transcriptase". J. Clin. Microbiol. 38 (7): 2715–21. PMC 87006. PMID 10878069.
- ↑ J.R. Edwards, H.Ruparel, and J. Ju (2005). "Mass-spectrometry DNA sequencing". Mutation Research 573 (1–2): 3–12. PMID 15829234. doi:10.1016/j.mrfmmm.2004.07.021.
- ↑ Hall, Thomas A.; Budowle, Bruce; Jiang, Yun; Blyn, Lawrence; Eshoo, Mark; Sannes-Lowery, Kristin A.; Sampath, Rangarajan; Drader, Jared J.; Hannis, James C.; Harrell, Patina; Samant, Vivek; White, Neill; Ecker, David J.; Hofstadler, Steven A. (2005). "Base composition analysis of human mitochondrial DNA using electrospray ionization mass spectrometry: A novel tool for the identification and differentiation of humans". Analytical Biochemistry 344 (1): 53–69. doi:10.1016/j.ab.2005.05.028.
- ↑ Howard, R; Encheva, V; Thomson, J; Bache, K; Chan, YT; Cowen, S; Debenham, P; Dixon, A; Krause, JU; Krishan, E; Moore, D; Moore, V; Ojo, M; Rodrigues, S; Stokes, P; Walker, J; Zimmermann, W; Barallon, R (2011 Jun 15). "Comparative analysis of human mitochondrial DNA from World War I bone samples by DNA sequencing and ESI-TOF mass spectrometry.". Forensic science international. Genetics 7 (1): 1–9. PMID 21683667. doi:10.1016/j.fsigen.2011.05.009.
- ↑ Monforte, Joseph A.; Becker, Christopher H. (1 March 1997). "High-throughput DNA analysis by time-of-flight mass spectrometry". Nature Medicine 3 (3): 360–362. doi:10.1038/nm0397-360.
- ↑ Beres, S. B.; Carroll, R. K.; Shea, P. R.; Sitkiewicz, I.; Martinez-Gutierrez, J. C.; Low, D. E.; McGeer, A.; Willey, B. M.; Green, K.; Tyrrell, G. J.; Goldman, T. D.; Feldgarden, M.; Birren, B. W.; Fofanov, Y.; Boos, J.; Wheaton, W. D.; Honisch, C.; Musser, J. M. (8 February 2010). "Molecular complexity of successive bacterial epidemics deconvoluted by comparative pathogenomics". Proceedings of the National Academy of Sciences 107 (9): 4371–4376. doi:10.1073/pnas.0911295107.
- ↑ Kan, Cheuk-Wai; Fredlake, Christopher P.; Doherty, Erin A. S.; Barron, Annelise E. (1 November 2004). "DNA sequencing and genotyping in miniaturized electrophoresis systems". ELECTROPHORESIS 25 (21–22): 3564–3588. doi:10.1002/elps.200406161.
- ↑ Ying-Ja Chen, Eric E. Roller and Xiaohua Huang (2010). "DNA sequencing by denaturation: experimental proof of concept with an integrated fluidic device". Lab on Chip 10 (10): 1153–1159. doi:10.1039/b921417h.
- ↑ Bell, DC; Thomas, WK; Murtagh, KM; Dionne, CA; Graham, AC; Anderson, JE; Glover, WR (2012 Oct 9). "DNA Base Identification by Electron Microscopy.". Microscopy and microanalysis : the official journal of Microscopy Society of America, Microbeam Analysis Society, Microscopical Society of Canada 18 (5): 1–5. PMID 23046798. doi:10.1017/S1431927612012615.
- ↑ Pareek, CS; Smoczynski, R; Tretyn, A (2011 Nov). "Sequencing technologies and genome sequencing.". Journal of applied genetics 52 (4): 413–35. PMC 3189340. PMID 21698376. doi:10.1007/s13353-011-0057-x.
- ↑ Fujimori, S; Hirai, N; Ohashi, H; Masuoka, K; Nishikimi, A; Fukui, Y; Washio, T; Oshikubo, T; Yamashita, T; Miyamoto-Sato, E (2012). "Next-generation sequencing coupled with a cell-free display technology for high-throughput production of reliable interactome data.". Scientific reports 2: 691. PMC 3466446. PMID 23056904. doi:10.1038/srep00691.
- ↑ ""PRIZE Overview: Archon X PRIZE for Genomics"". Arquivado dende o orixinal o 17 de xuño de 2013. Consultado o 09 de xullo de 2013.
- ↑ "The Future of DNA Sequencing". Arquivado dende o orixinal o 17 de maio de 2013. Consultado o 09 de xullo de 2013.
Véxase tamén[editar | editar a fonte]
Outros artigos[editar | editar a fonte]
- Teoría da secuenciación do ADN
- Proxecto Xenoma
- Proxecto xenoma humano
- Minado de secuencias
- Didesoxinucleótidos
