Inactivación do cromosoma X


1. Células embrionarias en estadio inicial dunha muller
2. Cromosoma X materno
3. Cromosoma X paterno
4. Mitose e evento de inactivación do cromosoma X aleatoria
5. O cromosoma paterno é inactivado ao chou nunha célula filla; o cromosoma materno é inactivado na outra
6. O cromosoma paterno é inactivado ao chou en ambas as células fillas
7. O cromosoma materno é inactivado ao chou en ambas as células fillas
8. Tres posibles combinacións de resultados aleatorias.

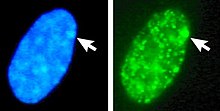
Esquerda: núcleo co ADN tinguido con DAPI. As frechas indican a localización do corpo de Barr (Xi). Dereita: proteínas histonas asociadas ao ADN deectadas.

A inactivación do cromosoma X ou inactivación X, tamén chamada lyonización (por Mary F. Lyon), é un proceso por medio do cal unha das copias do cromosoma X é inactivada nalgunhas femias de mamíferos. O cromosoma X inactivo é silenciado ao ser empaquetado de modo que adopta a estrutura transcricionalmente inactiva de heterocromatina. Como practicamente todas as femias de mamífero teñen dous cromosomas X, a inactivación do X impide que teñan o dobre de produtos xénicos do cromosoma X que os machos, os cales só posúen unha copia de dito cromosoma (compensación de dose). A escolla de cal dos cromosomas X será inactivado é aleatoria en mamíferos placentarios como os humanos, pero unha vez que un cromosoma X é inactivado, este permanece inactivo durante toda a vida da célula e nas células descendentes desta que haxa no organismo. A diferenza da inactivación do X aleatoria observada en mamíferos placentarios, esta inactivación en marsupiais afecta exclusivamente ao cromosoma X procedente do pai.
Historia[editar | editar a fonte]
En 1959 Susumu Ohno demostrou que os dous cromosomas X de mamíferos eran diferentes: un deles parecía similar aos autosomas; o outro estaba condensado e en estado heterocromático.[3] Este descubrimento suxeriu, independentemente a dous grupos de investigadores, que un dos cromosomas X sufría unha inactivación. En 1961, Mary F. Lyon propuxo a inactivación ao azar dun dos cromosomas X das femias para explicar o fenotipo a pintas de femias de rato heterocigotas para xenes da cor da pelame.[4] A hipótese de Lyon tamén explicaba por que unha das copias do cromosoma X das células das femias estaba moi condensada e por que os ratos cunha soa copia do cromosoma X se desenvolvían como femias infértiles. Isto suxeriulle[5] a Ernest Beutler, que estudaba femias heterocigotas para a deficiencia en glicosa-6-fosfato deshidroxenase (G6PD), que en tales heterocigotos había dúas poboacións de eritrocitos: as células deficientes e as normais,[6] dependendo de se o cromosoma X inactivado (no núcleo das células precursoras dos eritrocitos) contén o alelo G6PD normal ou defectivo.
Mecanismo[editar | editar a fonte]
Ciclo da activación do cromosoma X[editar | editar a fonte]
A inactivación do X forma parte do ciclo de activación do cromosoma X que ten lugar ao longo da vida da femia. O ovo e o cigoto fertilizado de ratos usan inicialmente transcritos maternos e todo o xenoma do embrión está silenciado ata a activación do xenoma cigótico. Por tanto, todas as células de rato sofren unha temperá inactivación impresa do cromosoma X derivado do pai durante o estadio embrionario de 4-8 células.[7][8][9][10] Os tecidos extraembrionarios (que dan lugar á placenta e outros tecidos de soporte do embrión) reteñen esta inactivación impresa temperanmente e así só o cromosoma X materno está activo neses tecidos.
Nos blastocistos temperáns, esta inactivación do X impresa inicial é revertida nas células da masa interna (que dan lugar ao embrión), e nestas células ambos os cromosomas X volven a estar activos de novo. Despois, cada unha destas células de forma independente e aleatoria inactivan unha copia do cromosoma X.[9] Este evento de inactivación é irreversible durante toda a vida do individuo, coa excepción da liña xerminal. Na liña xerminal feminina antes da entrada na meiose, a inactivación do X é revertida, polo que despois da meiose todos os ovocitos haploides conteñen un só cromosoma X activo.
Resumo[editar | editar a fonte]
Con Xi indícase o cromosoma X inactivo e con Xa o activo. XP denota o cromosoma X paterno e XM o materno. Cando o ovo (que leva un XM) é fecundado por un espermatozoide (que leva un XP), fórmase un cigoto diploide. A partir do cigoto, a través da etapa adulta e ata a seguinte xeración de ovos, o cromosoma sofre os seguintes cambios:
- Cigoto XiP XiM → sofre a activación cigótica xenómica, que conduce a:
- XaP XaM → sofre unha inactivación X impresa (paterna), que orixina:
- XiP XaM → sofre activación X no estadio de blastocisto temperán, o que produce:
- XaP XaM → sofre inactivación X aleatoria na liñaxe embrional (células da masa interna) no estadio de blastocisto, o que orixina:
- XiP XaM OU XaP XiM → sofre unha reactivación X nas células xerminais primordiais antes da meiose, o que conduce a:
- Células xerminais diploides XaM XaP en detención meiótica. Dado que a meiose I só se completa coa ovulación, as células xerminais humanas existen neste estadio desde as primeiras semanas do desenvolvemento ata a puberdade. Cando a meiose se completa isto forma:
- Células xerminais haploides XaM E XaP (ovos).
O ciclo de activación X foi mellor estudado en ratos, pero fixéronse tamén múltiples estudos en humanos. Como a maioría das probas proceden dos ratos, o esquema anterior representa os eventos neses roedores. A terminación da meiose foi simplificada aquí para maior claridade. Os pasos 1-4 poden estudarse en embrións orixinados por fertilización in vitro, e en células nai en diferenciación; a reactivación X ocorre no embrión en desenvolvemento e as seguintes etapas (6-7) dentro do corpo da femia, o que é moito máis difícil de estudar.
Sncronización do momento[editar | editar a fonte]
O momento en que ten lugar cada proceso depende da especie, e en moitos casos o momento preciso é obxecto de grandes debates.
| Proceso | Rato | Humano | |
| 1 | Activación xenómica cigótica | Estadio de 2-4 células[11] | Estadio de 2-8 células[11] |
| 2 | Inactivación X impresa (paterna) | Estadio de 4-8 células[10][12] | Non está claro se ten lugar en humanos[13] |
| 3 | Activación X | Estadio de blastocisto temperán | Estadio de blastocisto temperán |
| 4 | Inactivación X aleatoria na liñaxe embrional (células da masa interna) | Estadio de blastocisto tardío | Estadio de blastocisto tardío, despois da implantación[13] |
| 5 | Reactivación X en células xerminais primordiais antes da meiose | Desde antes da semana 4 do desenvolvemento ata a semana 14[14][15] |
Herdanza do status de inactivación a través das xeracións[editar | editar a fonte]
Os descendentes de cada célula que inactivou un determinado cromosoma X tamén terán desactivado ese mesmo cromoxoma X. Este fenómeno, que pode observarse na coloración de coiraza de tartaruga da pelame dos gatos cando as femias son heterocigotas para o xene ligado ao sexo implicado, non debería confundirse co mosaicismo, que é un termo que se refire especificamente ao xenotipo de varias poboacións celulares presentes no mesmo individuo; ao contrario, a inactivación X, que é un cambio epixenético que ten como resultado un fenotipo diferente, non é un cambio a nivel xenotípico. Para unha liñaxe ou célula individual a inactivación é, por tanto, nesgada ou non aleatoria, e isto pode dar lugar a síntomas suaves nas 'portadoras' femininas de trastornos xenéticos ligados ao X.[16]
Selección dun cromosoma X activo[editar | editar a fonte]
As femias normais posúen dous cromosomas X e nunha célula determinada un deles estará activo (designado como Xa) e o outro activo (Xi). Porén, os estudos de individuos con copias extra do cromosoma X indican que nas células con máis de dous cromosomas X hai un só Xa, e todos os demais cromosomas X están inactivados. Isto indica que o estado por defecto do cromosoma X en femias é a inactivación, pero sempre un dos cromosomas X se selecciona para estar activo.
Sábese que a inactivación do cromosoma X é un proceso aleatorio que se produce aproximadamente no momento da gastrulación no epiblasto (as células que darán lugar ao embrión). Os cromosomas X materno e paterno teñen igual probabilidade de inactivación. Isto suxeriría que se esperaría que as mulleres sufrisen trastornos ligados ao X nunha proporción do 50% con respecto aos homes (porque as mulleres teñen dous cromosomas X, mentres que os homes teñen só un); porén, na realidade, a frecuencia destes trastornos en femias é moito menor que esa cifra. Unha explicación desta disparidade é que entre o 12 e o 20% [17] dos xenes do cromosoma X inactivado seguen expresándose, o que proporciona ás mulleres unha protección adicional contra xenes defectuosos codificados no cromosoma X. Suxeriuse que esta disparidade tiña que ser unha proba dunha inactivación preferencial (non aleatoria). A inactivación preferencial do cromosoma X paterno dáse tanto en marsupiais coma en liñaxes celulares que forman as membranas que rodean o embrión,[18] mentres que nos mamíferos placentarios poden ser inactivados tanto o cromosoma X derivado do pai coma da nai en diferentes liñas celulares.[19]
O período de tempo en que se produce a inactivación do cromosoma X explica esta disparidade. A inactivación ocorre no epiblasto durante a gastrulación, o que dá lugar ao embrión.[20] A inactivación ocorre a nivel celular, resultando nunha expresión en mosaico, na cal grupos de células teñen un cromosoma X inactivo materno, mentres que noutros o cromosoma X inactivo é o paterno. Por exemplo, unha femia heterocigota para a hemofilia (unha enfermidade ligada ao X) tería aproximadamente a metade das súas células hepáticas funcionando perfectamente, o que normalmente é dabondo para asegurar unha coagulación do sangue normal.[21][22] Por azar poderían orixinarse significativamente máis células disfuncionais; porén, tales extremos estatísticos son improbables. As diferenzas xenéticas no cromosoma poden tamén facer que sexa máis probable que un determinado cromosoma X sufra inactivación. Ademais, se un cromosoma X ten unha mutación que dificulta o seu crecemento ou a fai non viable, as células que aleatoriamente inactivaron ese cromosoma X terán unha vantaxe selectiva sobre as células que aleatoriamente inactivaron o alelo normal. Así, aínda que a inactivación é inicialmente ao azar, as células que inactivan o alelo normal (deixando activo o alelo mutado) finalmente proliferarán menos e serán substituídas por células normais, as cales case todas teñen o mesmo cromosoma X activado.[21]
Hipotetízase que hai un 'factor de bloqueo' codificado nun autosoma, que se une ao cromosoma X e impide a súa inactivación. O modelo postula en concreto que hai un factor bloqueante limitante, polo que unha vez que a molécula de factor limitante dispoñible se une a un cromosoma X, o(s) restante(s) cromosoma(s) X non está(n) protexido(s) da inactivación. Este modelo está apoiado pola existencia dun só Xa nas células con moitos cromosomas X e pola existencia de dous cromosomas X activos en liñas celulares cun número de autosomas dúas veces o normal.[23]
As secuencias no centro de inactivación X (XIC), presentes no cromosoma X, controlan o silenciamento do cromosoma X. Suponse que o factor bloqueante hipotético se une a secuencias situadas dentro do centro de inactivación X. O XIC contén varios xenes que non son traducidos e que son responsables da transcrición de ARN implicados na inactivación. Estes xenes codifican varios ARN non codificantes longos, os cales son transcritos de máis de 200 nucleótidos con carapucha 5' e cola poliA 3' pero a diferenza do ARNm non codifican proteínas. Os principais ARN non codificantes longos do XIC son Xist, Tsix, Jpx e FTX. Ademais destes xenes contén tamén secuencias ás que se unen proteínas reguladoras.

Expresión de trastornos ligados ao X en femias heterocigotas[editar | editar a fonte]
O efecto da heterocigosidade do X en femias manifestase nalgúns trazos localizados, como o padrón da pelame dos gatos calico. Porén, pode ser máis difícil comprender completamente a expresión de trazos non localizados nestas femias, como a expresión de enfermidades.
Como os machos só teñen unha copia do cromosoma X, todos os xenes do cromosoma X expresados (ou alelos, no caso de formas con múltiples variantes dun mesmo xene na poboación) están localizadas nesa copia do cromosoma. As femias, porén, expresarán principalmente os xenes ou alelos localizados na copia do cromosoma X que permanece activo. Considerando a situación dun xene ou múltiples xenes que causan diferenzas individuais nun determinado fenotipo (é dicir, causan variacións observadas na poboación para ese fenotipo), en femias homocigotas non importa cal das copias do cromosoma está inactivada, xa que os alelos de ambas as copias son o mesmo. Porén, en femias que son heterocigotas nos xenes causais, a inactivación dunha copia do cromosoma en vez doutra pode ter un impacto directo sobre o valor fenotípico. Debido a este fenómeno, observouse un incremento en variación fenotípica en femias que son heterocigotas no xene ou xenes implicados con respecto ás que son homocigotas.[24] Hai moitos xeitos diferentes polos cales se pode desenvolver unha variación fenotípica. En moitos casos, as femias heterocigotas poden ses asintomáticas ou presentar só síntomas menores dunha determinada desorde, como a adrenoleucodistrofia ligada ao X.[25]
A diferenciación do fenotipo en femias heterocigotas é impulsada pola presenza de inactivación X nesgada. Tipicamente, cada cromosoma X é silenciado na metade das células, pero este proceso está nesgado cando ocorre a inactivación preferencial dun cromosoma. Pénsase que o nesgo acontece por azar ou por unha característica física dun cromosoma que pode causar que sexa silenciado con maior ou menor frecuencia, como unha mutación desfavorable.[26][27]
Como media, cada cromosoma X é inactivado na metade das células, porén do 5 ao 20% de mulleres "aparentemente normais" mostran inactivación do X nesgada.[26] En casos nos que o nesgo está presente, pode darse unha ampla variedade de expresión de síntomas, o que ten como resultado que a expresión varíe de menor a grave dependendo da proporción de nesgo. Un caso extremo disto pode verse cando femias xemelgas monocigotas teñen unha variación extrema na expresión da enfermidade de Menkes (un trastorno ligado ao X), con resultado de morte dunha das xemelgas mentres que a outra permanece asintomática.[28]
Crese que o nesgo na inactivación X podería ser causada por efectos no mecanismo que causa a inactivación ou efectos sobre o propio cromosoma.[26][27] Porén, a ligazón entre fenotipo e nesgo aínda é moi cuestionada e debería ser examinada caso por caso. Un estudo que examinou femias sintomáticas e asintomáticas que eran heterocigotas para as distrofias musculares de Duchenne e Becker non encontrou unha ligazón aparente entre a expresión de transcritos e a inactivación X nesgada. O estudo suxire que ambos os mecanismos están regulados independentemente e hai outros factores descoñecidos en xogo.[29]
Compoñente cromosómico[editar | editar a fonte]
O 'centro de inactivación X' (XIC) no cromosoma X é necesario e suficiente para causar a inactivación X. As translocacións cromosómicas que sitúan o centro de inactivación X nun autosoma causan a inactivación do autosoma e os cromosomas X carentes de centro de inactivación X non son inactivados.[30][31]
O XIC contén catro xenes de ARN que non se traducen: Xist, Tsix, Jpx e Ftx, que están implicados na inactivación X. O XIC tamén contén sitios de unión para proteínas regulatorias coñecidas e descoñecidas.[32]
ARNs Xist e Tsix[editar | editar a fonte]


O xene do transcrito específico do X inactivo (Xist, do inglés X-inactive specific transcript) codifica un grande ARN non codificante que actúa como mediador do silenciamento específico do cromosoma X, do cal se transcribe.[33] O cromosoma X inactivo está cuberto polo ARN Xist,[34] mentres que o Xa non (ver figura da dereita). Os cromosomas X que carecen do xene Xist non poden ser inactivados.[35] Situando o xene Xist artificialmente e facendo que se exprese noutro cromosoma causa o silenciamento dese cromosoma.[30][36]
Antes da inactivación, ambos os cromosomas X expresan debilmente o ARN Xist a partir do xene Xist. Durante o proceso de inactivación, o futuro Xa deixa de expresar Xist, mentres que o futuro Xi incrementa drasticamente a produción o ARN Xist. No futuro Xi, o ARN Xist cobre progresivamente o cromosoma, espallándose desde o XIC;[36] o ARN Xist non se localiza sobre o Xa. O silenciamento de xenes ao longo do Xi ocorre pouco despois do recubrimento polo ARN Xist.
Igual que Xist, o xene Tsix codifica un ARN grande que se cre que non codifica unha proteína. O ARN Tsix é transcrito como antisentido con respecto ao Xist, significando que o xene Tsix se solapa ao xene Xist e é transcrito da febra oposta do ADN do xene Xist.[31] O Tsix é un regulador negativo de Xist; os cromosomas X que carecen de expresión de Tsix (polo que teñen altos niveis da transcrición de Xist) son inactivados moito máis frecuentemente que os cromosomas normais.
Como o Xist, antes da inactivación, ambos os cromosomas X expresan debilmente o ARN Tsix a partir do xene Tsix. Despois do comezo da inactivación X, o futuro Xi deixa de expresar o ARN Tsix (e incrementa a expresión de Xist), mentres que o Xa continúa expresando Tsix durante varios días.
Rep A é un ARN non codificante longo que funciona con outro ARN non codificante longo, o Xist, para a inactivación X. Rep A inhibe a función de Tsix, o antisentido de Xist, en conxunción coa eliminación da expresión de Xist. Promove a metilación da rexión Tsix ao atraer PRC2 e así inactivar un dos cromosomas X.[32]
Silenciamento[editar | editar a fonte]
O cromosoma X inactivo non expresa a maioría dos seus xenes, a diferenza do cromosoma X activo. Isto débese ao silenciamento do Xi por heterocromatina represiva, que compacta o ADN do Xi e impide a expresión da maioría dos xenes.
Comparado co Xa, o Xi ten un alto nivel de metilación do ADN, baixos niveis de acetilación de histonas, baixos niveis de metilación da lisina-4 da histona H3 e altos niveis de metilación da lisina-9 da histona H3 e unha marca de metilación da lisina-27 da histona H3, a cal é situada polo complexo PRC2 recrutado por Xist, todo o cal están asociados co silenciamento de xenes.[37] O PRC2 regula a compactación da cromatina e a súa remodelación en varios procesos, como a resposta aos danos no ADN.[38] Adicionalmente, unha variante de histona chamada macroH2A (H2AFY) encóntrase exclusivamente nos nucleosomas xunto co Xi.[39][40]
Corpo de Barr[editar | editar a fonte]
- Artigo principal: Corpo de Barr.
O empaquetamento do ADN en heterocromatina, como no Xi, é un estado máis condensado que o da eucromatina, como no Xa. O X inactivo forma un corpo discreto dentro do núcleo chamado corpo de Barr.[41] O corpo de Barr está xeralmente localizado na periferia do núcleo, e é replicado posteriormente no ciclo celular e, como contén o Xi, contén modificacións da heterocromatina e o ARN Xist.
Xenes expresados no cromosoma X inactivo[editar | editar a fonte]
Unha fracción dos xenes do cromosoma X escapan á inactivación do Xi. O xene Xist é expresado a altos niveis no Xi e non se expresa no Xa.[42] Moitos outros xenes escapan á inactivación; algúns son expresados por igual no Xa e no Xi, e outros, aínda que tamén se expresan en ambos os cromosomas, son expresados predominantemente polo Xa.[43][44][45] Ata unha cuarta pate dos xenes do Xi humano poden escapar á inactivación.[43] Estudos feitos en ratos suxiren que en calquera tipo de célula, dun 3% a un 15% dos xenes escapan á inactivación, e que a identidade dos xenes que escapan varía entre tecidos.[44][45]
Moitos dos xenes que escapan á inactivación están presentes en rexións do cromosoma X que, a diferenza da maioría do cromosoma X, conteñen xenes que tamén están representados no cromosoma Y (os cromosomas X e Y son homólogos nesas porcións). Estas rexións denomínanse rexión pseudoautosómicas, xa que individuos dos dous sexos reciben dúas copias de cada xene destas rexións (como nun autosoma), a diferenza da maioría dos xenes dos cromosomas sexuais. Como os individuos de ambos os sexos reciben dúas copias de cada xene dunha rexión pseudoautosómica, non se necesita unha compensación de dose para as femias, polo que non se postula que nestas rexións do ADN evolucionasen mecanismos para escapar á inactivación X. Os xenes das rexións pseudoautosómicas do Xi non teñen as modificacións típicas do Xi e teñen poruco ARN Xist unido.
A existencia de xenes no X inactivo que non son silenciados explica os defectos observados en humanos con cantidades anormais de cromosomas X, como os que presentan síndrome de Turner (X0) ou síndrome de Klinefelter (XXY). Teoricamente, a inactivación X debería eliminar as diferenzas na dose de xenes entre individuos afectados e individuos co complemento cromosómico normal. Porén, en individuos afectados, a inactivación X é incompleta e a dose destes xenes non silenciados diferirá, xa que escapan da inactivación do X, o que é similar a unha aneuploidía autosómica.
Os mecanismos precisos que controlan o escape da inactivación X non se coñecen, mais as rexións sienciadas e que escapan teñen distintas marcas na cromatina.[44][46] Suxeriuse que o escape da inactivación do X podería estar mediada pola expresión dun ARN non codificante longo dentro dos dominios cromosómicos de escape.[2]
Usos en bioloxía experimental[editar | editar a fonte]
Stanley Michael Gartler utilizou a inactivación do cromosoma X para demostrar a orixe clonal dos cancros. O exame de tecidos normais e tumores de femias heterocigotas para isoenzimas do xene ligado ao sexo da G6PD demostrou que as células tumorais deses individuos expresan só unha forma de G6PD, mentres que os tecidos normais están compostos dunha mestura case igual de células que expresan os dous fenotipos diferentes. Este padrón suxire que unha soa célula, e non unha poboación, crece orixinando un cancro.[47] Porén, este padrón demostrouse que estaba errado na maioría dos tipos de cancros, o que indica que algúns cancros poden ser de orixe policlonal.[48]
Ademais, medir o status de metilación (inactivación) dun receptor de andróxenos polimórfico humano (HUMARA) localizado no cromosoma X é considerado o método máis exacto de estimar a clonalidade en biopsias de cancros femininos.[49] Comprobouse unha gran variedade de tumores con este método, algúns, como o carcinoma celular renal,[50] eran monoclonais, mentres que outros (por exemplo, o mesotelioma[51]) eran policlonais.
Tamén se fixeron investigacións usando a inactivación do cromosoma X para silenciar a actividade de cromosomas autosómicos. Por exemplo, Jiang et al. inseriu unha copia do xene Xist nunha copia do cromosoma 21 en células nai derivadas dun individuo con trisomía 21 (síndrome de Down).[52] O xene Xist inserido induce a formación do corpo de Barr, desencadea modificacións estables da heterocromatina e silencia a maioría dos xenes na copia extra do cromosoma 21. Nestas células nai modificadas, o silenciamento de xenes mediado por Xist parece reverter algúns dos defectos asociados coa síndrome de Down.
Notas[editar | editar a fonte]
- ↑ Gartler SM, Varadarajan KR, Luo P, Canfield TK, Traynor J, Francke U, Hansen RS (September 2004). "Normal histone modifications on the inactive X chromosome in ICF and Rett syndrome cells: implications for methyl-CpG binding proteins". BMC Biology 2: 21. PMC 521681. PMID 15377381. doi:10.1186/1741-7007-2-21.
- ↑ 2,0 2,1 Reinius B, Shi C, Hengshuo L, Sandhu KS, Radomska KJ, Rosen GD, Lu L, Kullander K, Williams RW, Jazin E (November 2010). "Female-biased expression of long non-coding RNAs in domains that escape X-inactivation in mouse". BMC Genomics 11: 614. PMC 3091755. PMID 21047393. doi:10.1186/1471-2164-11-614.
- ↑ Ohno S, Kaplan WD, Kinosita R (October 1959). "Formation of the sex chromatin by a single X-chromosome in liver cells of Rattus norvegicus". Experimental Cell Research 18 (2): 415–8. PMID 14428474. doi:10.1016/0014-4827(59)90031-X.
- ↑ Lyon MF (April 1961). "Gene action in the X-chromosome of the mouse (Mus musculus L.)". Nature 190 (4773): 372–3. Bibcode:1961Natur.190..372L. PMID 13764598. doi:10.1038/190372a0.
- ↑ Beutler E (January 2008). "Glucose-6-phosphate dehydrogenase deficiency: a historical perspective". Blood 111 (1): 16–24. PMID 18156501. doi:10.1182/blood-2007-04-077412.
- ↑ Beutler E, Yeh M, Fairbanks VF (January 1962). "The normal human female as a mosaic of X-chromosome activity: studies using the gene for C-6-PD-deficiency as a marker". Proceedings of the National Academy of Sciences of the United States of America 48 (1): 9–16. Bibcode:1962PNAS...48....9B. PMC 285481. PMID 13868717. doi:10.1073/pnas.48.1.9.
- ↑ Takagi N, Sasaki M (August 1975). "Preferential inactivation of the paternally derived X chromosome in the extraembryonic membranes of the mouse". Nature 256 (5519): 640–2. Bibcode:1975Natur.256..640T. PMID 1152998. doi:10.1038/256640a0.
- ↑ Cheng MK, Disteche CM (August 2004). "Silence of the fathers: early X inactivation". BioEssays 26 (8): 821–4. PMID 15273983. doi:10.1002/bies.20082. (require subscrición (?)).
- ↑ 9,0 9,1 Okamoto I, Otte AP, Allis CD, Reinberg D, Heard E (January 2004). "Epigenetic dynamics of imprinted X inactivation during early mouse development". Science 303 (5658): 644–9. Bibcode:2004Sci...303..644O. PMID 14671313. doi:10.1126/science.1092727.
- ↑ 10,0 10,1 Deng Q, Ramsköld D, Reinius B, Sandberg R (January 2014). "Single-cell RNA-seq reveals dynamic, random monoallelic gene expression in mammalian cells". Science 343 (6167): 193–6. Bibcode:2014Sci...343..193D. PMID 24408435. doi:10.1126/science.1245316.
- ↑ 11,0 11,1 Xue Z, Huang K, Cai C, Cai L, Jiang CY, Feng Y, Liu Z, Zeng Q, Cheng L, Sun YE, Liu JY, Horvath S, Fan G (August 2013). "Genetic programs in human and mouse early embryos revealed by single-cell RNA sequencing". Nature (en inglés) 500 (7464): 593–7. Bibcode:2013Natur.500..593X. PMC 4950944. PMID 23892778. doi:10.1038/nature12364.
- ↑ Borensztein M, Syx L, Ancelin K, Diabangouaya P, Picard C, Liu T, Liang JB, Vassilev I, Galupa R, Servant N, Barillot E, Surani A, Chen CJ, Heard E (March 2017). "Xist-dependent imprinted X inactivation and the early developmental consequences of its failure". Nature Structural & Molecular Biology (en inglés) 24 (3): 226–233. PMC 5337400. PMID 28134930. doi:10.1038/nsmb.3365.
- ↑ 13,0 13,1 Deng X, Berletch JB, Nguyen DK, Disteche CM (June 2014). "X chromosome regulation: diverse patterns in development, tissues and disease". Nature Reviews. Genetics (en inglés) 15 (6): 367–78. PMC 4117651. PMID 24733023. doi:10.1038/nrg3687.
- ↑ Vértesy Á, Arindrarto W, Roost MS, Reinius B, Torrens-Juaneda V, Bialecka M, et al. (May 2018). "Parental haplotype-specific single-cell transcriptomics reveal incomplete epigenetic reprogramming in human female germ cells". Nature Communications (en inglés) 9 (1): 1873. Bibcode:2018NatCo...9.1873V. PMC 5951918. PMID 29760424. doi:10.1038/s41467-018-04215-7.
- ↑ Guo F, Yan L, Guo H, Li L, Hu B, Zhao Y, et al. (June 2015). "The Transcriptome and DNA Methylome Landscapes of Human Primordial Germ Cells". Cell 161 (6): 1437–52. PMID 26046443. doi:10.1016/j.cell.2015.05.015.
- ↑ Puck JM, Willard HF (January 1998). "X inactivation in females with X-linked disease". The New England Journal of Medicine 338 (5): 325–8. PMID 9445416. doi:10.1056/NEJM199801293380611.
- ↑ Balaton BP, Cotton AM, Brown CJ (30 December 2015). "Derivation of consensus inactivation status for X-linked genes from genome-wide studies". Biology of Sex Differences 6 (35): 35. PMC 4696107. PMID 26719789. doi:10.1186/s13293-015-0053-7.
- ↑ Graves JA (1996). "Mammals that break the rules: genetics of marsupials and monotremes". Annual Review of Genetics 30: 233–60. PMID 8982455. doi:10.1146/annurev.genet.30.1.233.
- ↑ Lyon MF (January 1972). "X-chromosome inactivation and developmental patterns in mammals". Biological Reviews of the Cambridge Philosophical Society 47 (1): 1–35. PMID 4554151. doi:10.1111/j.1469-185X.1972.tb00969.x.
- ↑ Migeon, B (2010). "X chromosome inactivation in human cells". The Biomedical & Life Sciences Collection. Henry Stewart Talks, Ltd. pp. 1–54. Consultado o 15 December 2013.
- ↑ 21,0 21,1 Gartler SM, Goldman MA (2001). "X-Chromosome Inactivation" (PDF). Encyclopedia of Life Sciences (Nature Publishing Group): 1–2. Arquivado dende o orixinal (PDF) o 19 de abril de 2022. Consultado o 15 de marzo de 2019.
- ↑ Connallon T, Clark AG (April 2013). "Sex-differential selection and the evolution of X inactivation strategies". PLoS Genetics 9 (4): e1003440. PMC 3630082. PMID 23637618. doi:10.1371/journal.pgen.1003440.
- ↑ Barakat TS, Gribnau J (2010). "X Chromosome Inactivation and Embryonic Stem Cells". En Meshorer E, Plath K. The Cell Biology of Stem Cells. Landes Bioscience and Springer Science+Business Media.
- ↑ Ma L, Hoffman G, Keinan A (March 2015). "X-inactivation informs variance-based testing for X-linked association of a quantitative trait". BMC Genomics 16: 241. PMC 4381508. PMID 25880738. doi:10.1186/s12864-015-1463-y.
- ↑ Habekost CT, Pereira FS, Vargas CR, Coelho DM, Torrez V, Oses JP, Portela LV, Schestatsky P, Felix VT, Matte U, Torman VL, Jardim LB (October 2015). "Progression rate of myelopathy in X-linked adrenoleukodystrophy heterozygotes". Metabolic Brain Disease 30 (5): 1279–84. PMID 25920484. doi:10.1007/s11011-015-9672-2.
- ↑ 26,0 26,1 26,2 Belmont JW (June 1996). "Genetic control of X inactivation and processes leading to X-inactivation skewing". American Journal of Human Genetics 58 (6): 1101–8. PMC 1915050. PMID 8651285.
- ↑ 27,0 27,1 Holle JR, Marsh RA, Holdcroft AM, Davies SM, Wang L, Zhang K, Jordan MB (July 2015). "Hemophagocytic lymphohistiocytosis in a female patient due to a heterozygous XIAP mutation and skewed X chromosome inactivation". Pediatric Blood & Cancer 62 (7): 1288–90. PMID 25801017. doi:10.1002/pbc.25483.
- ↑ Burgemeister AL, Zirn B, Oeffner F, Kaler SG, Lemm G, Rossier E, Büttel HM (November 2015). "Menkes disease with discordant phenotype in female monozygotic twins". American Journal of Medical Genetics. Part A 167A (11): 2826–9. PMID 26239182. doi:10.1002/ajmg.a.37276.
- ↑ Brioschi S, Gualandi F, Scotton C, Armaroli A, Bovolenta M, Falzarano MS, Sabatelli P, Selvatici R, D'Amico A, Pane M, Ricci G, Siciliano G, Tedeschi S, Pini A, Vercelli L, De Grandis D, Mercuri E, Bertini E, Merlini L, Mongini T, Ferlini A (August 2012). "Genetic characterization in symptomatic female DMD carriers: lack of relationship between X-inactivation, transcriptional DMD allele balancing and phenotype". BMC Medical Genetics 13: 73. PMC 3459813. PMID 22894145. doi:10.1186/1471-2350-13-73.
- ↑ 30,0 30,1 Lee JT, Jaenisch R (March 1997). "Long-range cis effects of ectopic X-inactivation centres on a mouse autosome". Nature 386 (6622): 275–9. Bibcode:1997Natur.386..275L. PMID 9069285. doi:10.1038/386275a0.
- ↑ 31,0 31,1 Lee JT, Davidow LS, Warshawsky D (April 1999). "Tsix, a gene antisense to Xist at the X-inactivation centre". Nature Genetics 21 (4): 400–4. PMID 10192391. doi:10.1038/7734.
- ↑ 32,0 32,1 Mercer, T.R., Dinger, M.E., Mattick, J.S., (2009). Long non-coding RNAs: insight into functions. Nature Reviews Genetics. (10) 155-159.
- ↑ Hoki Y, Kimura N, Kanbayashi M, Amakawa Y, Ohhata T, Sasaki H, Sado T (January 2009). "A proximal conserved repeat in the Xist gene is essential as a genomic element for X-inactivation in mouse". Development 136 (1): 139–46. PMID 19036803. doi:10.1242/dev.026427.
- ↑ Ng K, Pullirsch D, Leeb M, Wutz A (January 2007). "Xist and the order of silencing" (Review Article). EMBO Reports 8 (1): 34–9. PMC 1796754. PMID 17203100. doi:10.1038/sj.embor.7400871.
Figura 1 ARN Xist rodea o X do cal se transcribe.
- ↑ Penny GD, Kay GF, Sheardown SA, Rastan S, Brockdorff N (1996). "Requirement for Xist in X chromosome inactivation". Nature 379 (6561): 131–7. Bibcode:1996Natur.379..131P. PMID 8538762. doi:10.1038/379131a0. Erro no estilo Vancouver: wikilink (Axuda)
- ↑ 36,0 36,1 Herzing LB, Romer JT, Horn JM, Ashworth A (March 1997). "Xist has properties of the X-chromosome inactivation centre". Nature 386 (6622): 272–5. Bibcode:1997Natur.386..272H. PMID 9069284. doi:10.1038/386272a0.
- ↑ Ng K, Pullirsch D, Leeb M, Wutz A (January 2007). "Xist and the order of silencing" (Review Article). EMBO Reports 8 (1): 34–9. PMC 1796754. PMID 17203100. doi:10.1038/sj.embor.7400871.
Table 1 Features of the inactive X territory
– Orixinado de;
Chow JC, Yen Z, Ziesche SM, Brown CJ (2005). "Silencing of the mammalian X chromosome". Annual Review of Genomics and Human Genetics 6: 69–92. PMID 16124854. doi:10.1146/annurev.genom.6.080604.162350.
Lucchesi JC, Kelly WG, Panning B (2005). "Chromatin remodeling in dosage compensation". Annual Review of Genetics 39: 615–51. PMID 16285873. doi:10.1146/annurev.genet.39.073003.094210. - ↑ Veneti Z, Gkouskou KK, Eliopoulos AG (July 2017). "Polycomb Repressor Complex 2 in Genomic Instability and Cancer". Int J Mol Sci 18 (8). PMC 5578047. PMID 28758948. doi:10.3390/ijms18081657.
- ↑ Costanzi C, Pehrson JR (June 1998). "Histone macroH2A1 is concentrated in the inactive X chromosome of female mammals". Nature 393 (6685): 599–601. Bibcode:1998Natur.393..599C. PMID 9634239. doi:10.1038/31275.
- ↑ Costanzi C, Stein P, Worrad DM, Schultz RM, Pehrson JR (June 2000). "Histone macroH2A1 is concentrated in the inactive X chromosome of female preimplantation mouse embryos" (PDF). Development 127 (11): 2283–9. PMID 10804171.
- ↑ Barr ML, Bertram EG (April 1949). "A morphological distinction between neurones of the male and female, and the behaviour of the nucleolar satellite during accelerated nucleoprotein synthesis". Nature 163 (4148): 676–677. Bibcode:1949Natur.163..676B. PMID 18120749. doi:10.1038/163676a0.
- ↑ Plath K, Mlynarczyk-Evans S, Nusinow DA, Panning B (2002). "Xist RNA and the mechanism of X chromosome inactivation". Annual Review of Genetics 36: 233–78. PMID 12429693. doi:10.1146/annurev.genet.36.042902.092433.
- ↑ 43,0 43,1 Carrel L, Willard HF (March 2005). "X-inactivation profile reveals extensive variability in X-linked gene expression in females". Nature 434 (7031): 400–4. Bibcode:2005Natur.434..400C. PMID 15772666. doi:10.1038/nature03479.
- ↑ 44,0 44,1 44,2 Calabrese JM, Sun W, Song L, Mugford JW, Williams L, Yee D, Starmer J, Mieczkowski P, Crawford GE, Magnuson T (November 2012). "Site-specific silencing of regulatory elements as a mechanism of X inactivation". Cell 151 (5): 951–63. PMC 3511858. PMID 23178118. doi:10.1016/j.cell.2012.10.037.
- ↑ 45,0 45,1 Yang F, Babak T, Shendure J, Disteche CM (May 2010). "Global survey of escape from X inactivation by RNA-sequencing in mouse". Genome Research 20 (5): 614–22. PMC 2860163. PMID 20363980. doi:10.1101/gr.103200.109.
- ↑ Berletch JB, Yang F, Disteche CM (June 2010). "Escape from X inactivation in mice and humans". Genome Biology 11 (6): 213. PMC 2911101. PMID 20573260. doi:10.1186/gb-2010-11-6-213.
- ↑ Linder D, Gartler SM (October 1965). "Glucose-6-phosphate dehydrogenase mosaicism: utilization as a cell marker in the study of leiomyomas". Science 150 (3692): 67–9. Bibcode:1965Sci...150...67L. PMID 5833538. doi:10.1126/science.150.3692.67.
- ↑ Parsons BL (2008). "Many different tumor types have polyclonal tumor origin: evidence and implications". Mutation Research 659 (3): 232–47. PMID 18614394. doi:10.1016/j.mrrev.2008.05.004.
- ↑ Chen GL, Prchal JT (September 2007). "X-linked clonality testing: interpretation and limitations". Blood 110 (5): 1411–9. PMC 1975831. PMID 17435115. doi:10.1182/blood-2006-09-018655.
- ↑ Petersson F, Branzovsky J, Martinek P, Korabecna M, Kruslin B, Hora M, et al. (July 2014). "The leiomyomatous stroma in renal cell carcinomas is polyclonal and not part of the neoplastic process". Virchows Archiv 465 (1): 89–96. PMID 24838683. doi:10.1007/s00428-014-1591-9.
- ↑ Comertpay S, Pastorino S, Tanji M, Mezzapelle R, Strianese O, Napolitano A, Baumann F, Weigel T, Friedberg J, Sugarbaker P, Krausz T, Wang E, Powers A, Gaudino G, Kanodia S, Pass HI, Parsons BL, Yang H, Carbone M (December 2014). "Evaluation of clonal origin of malignant mesothelioma". Journal of Translational Medicine 12: 301. PMC 4255423. PMID 25471750. doi:10.1186/s12967-014-0301-3.
- ↑ Jiang J, Jing Y, Cost GJ, Chiang JC, Kolpa HJ, Cotton AM, et al. (August 2013). "Translating dosage compensation to trisomy 21". Nature 500 (7462): 296–300. Bibcode:2013Natur.500..296J. PMC 3848249. PMID 23863942. doi:10.1038/nature12394.
Véxase tamén[editar | editar a fonte]
| Wikimedia Commons ten máis contidos multimedia na categoría: Inactivación do cromosoma X |
Bibliografía[editar | editar a fonte]
- Huynh KD, Lee JT (May 2005). "X-chromosome inactivation: a hypothesis linking ontogeny and phylogeny". Nature Reviews. Genetics 6 (5): 410–8. PMID 15818384. doi:10.1038/nrg1604.
- Goto T, Monk M (June 1998). "Regulation of X-chromosome inactivation in development in mice and humans" (Review Article). Microbiology and Molecular Biology Reviews 62 (2): 362–78. PMC 98919. PMID 9618446.
- Lyon MF (December 2003). "The Lyon and the LINE hypothesis". Seminars in Cell & Developmental Biology (Review Article) 14 (6): 313–8. PMID 15015738. doi:10.1016/j.semcdb.2003.09.015.
- Ng K, Pullirsch D, Leeb M, Wutz A (January 2007). "Xist and the order of silencing" (Review Article). EMBO Reports 8 (1): 34–9. PMC 1796754. PMID 17203100. doi:10.1038/sj.embor.7400871.
- Cerase A, Pintacuda G, Tattermusch A, Avner P (August 2015). "Xist localization and function: new insights from multiple levels". Genome Biology 16: 166. PMC 4539689. PMID 26282267. doi:10.1186/s13059-015-0733-y.
Outros artigos[editar | editar a fonte]
- Sistema de determinación do sexo
- Compensación de dose
- Corpo de Barr
- Heterocromatina
- Epixenética
- Inactivación X nesgada
Ligazóns externas[editar | editar a fonte]
- Kruszelnicki K (2004-02-11). "Hybrid Auto-Immune Women 3". ABC Science.
