Hibridación in situ fluorescente

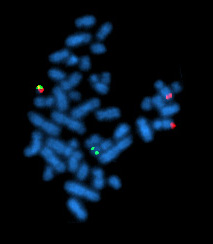


A hibridación in situ fluorescente (FISH, do inglés Fluorescence in situ hybridization)[1] é unha técnica citoxenética desenvolvida por investigadores médicos a comezos da década de 1980[2] que se utiliza para detectar e localizar a presenza ou ausencia de secuencias de ADN específicas nos cromosomas. A FISH usa sondas fluorescentes que se unen só a aquelas partes do cromosoma coas cales teñen un alto grao de complementariedade de secuencia. Pode utilizarse a microscopia de fluorescencia para atopar a sonda fluorescente unida aos cromosomas. A FISH úsase con frecuencia para atopar características específicas nun ADN para usala en consellos xenéticos, medicina e identificación de especies.[3] A FISH pode tamén utilizarse para detectar e localizar dianas de ARN específicas (ARNm, ARN non codificante longo e microARN) en células, células tumorais circulantes e mostras de tecidos. Neste contexto, pode axudar a definir os patróns espazo-temporais de expresión xénica nas células e tecidos.
Protocolo básico
[editar | editar a fonte]O primeiro paso da técnica consiste na desnaturalización do ADN para separar a dobre hélice. Á mostra desnaturalizada se lle engade entón a sonda de interese (fragmento de ADN marcado fluorescentemente). Primeiro, as sondas hibridan nas rexións específicas para as que foron deseñadas. Despois, tínguense os núcleos cunha cor de contraste inespecífica (xeralmente DAPI). As sondas de ADN poden marcarse con moléculas fluorescentes denominadas fluoróforos (método directo) ou non fluorescentes que se detectan con anticorpos fluorescentes (método indirecto). Por último, visualízase a mostra preparada baixo un microscopio de fluorescencia.
Sondas de ARN e ADN
[editar | editar a fonte]
Poden deseñarse sondas de ARN para calquera xene ou calquera secuencia dentro dun xene para visualizar o ARNm,[4][5][6] o ARN non codificante longo (ARNncl)[7][8][9] ou o microARN en células e tecidos. A FISH utilízase para examinar o ciclo de reprodución celular, especificamente os núcleos en interfase para detectar calquera anormalidade cromosómica.[10] Con esta técnica pódese analizar moito máis facilmente unha gran serie de casos arquivados para así identificar o cromosoma que se localiza porque ten puntos fluorescentes, creando unha sonda baseándose nun cromosoma artificial que sirva para atraer a cromosomas similares.[10] A hibridación sinaliza para cada sonda cando se detecta unha anormalidade nuclear.[10] Cada sonda para a detección de ARNms e ARNs non codificantes longos está composta por 20 pares de oligonucleótidos, e cada un deses pares cobre un espazo de 40-50 bp. Para a detección de microARN, as sondas usan química propietaria (de marca comercial) para a detección, e cobren a secuencia completa do microARN.

As sondas a miúdo derivan de fragmentos de ADN que foron illados, purificados e amplificados para o seu uso no Proxecto Xenoma Humano. O tamaño do xenoma humano é tan grande, comparado coa lonxitude que se podería secuenciar directamente, que foi necesario dividir o xenoma en fragmentos. Na análise final estes fragmentos ordénanse dixerindo unha copia de cada fragmento en fragmentos aínda máis pequenos usando endonucleases específicas de secuencia, medindo o tamaño de cada pequeno fragmento utilizando cromatografía de exclusión por tamaños, e empregando esa información para determinar onde se solapan os fragmentos grandes. Para preservar os fragmentos coas súas secuencias de ADN individuais, os fragmentos engádense a un sistema con poboacións bacterianas en continua replicación, e quedan almacenados no interior das bacterias. As poboacións clonais de bacterias, cada unha das cales mantén un só cromosoma artificial, almacénanse en varios laboratorios de todo o mundo. Os cromosomas artificiais (BAC) poden ser extraídos e etiquetados nun laboratorio. Estes fragmentos teñen da orde de 100 mil pares de bases, e son a base da maioría das sondas de FISH.
Preparación e hibridación de ARN
[editar | editar a fonte]Para permitir o acceso á diana as células, células tumorais circulantes (CTCs), ou incluídas en parafina e fixadas con formaldehido ou preparacións de tecidos conxelados deben ser primeiro fixadas, e despois permeabilizadas. A FISH tamén se utilizou con éxito con células non fixadas.[11] Unha sonda específica para unha diana, composta de 20 pares de oligonucleótidos, hibrida co(s) ARN(s) diana. Sistemas de amplificación compatibles pero separados permiten facer ensaios múltiples (ata dúas dianas por ensaio). A amplificación do sinal conséguese por medio dunha serie de pasos de hibridación secuenciais. Ao final do ensaio as mostras de tecidos visualízanse baixo o microscopio de fluorescencia.
Preparación e hibridación do ADN
[editar | editar a fonte]
Primeiro, constrúese unha sonda. A sonda debe ser grande dabondo como para poder hibridarse especificamente coa súa diana pero non tan grande que impida o proceso de hibridación. A sonda é marcada directamente con fluoróforos, con dianas para anticorpos ou con biotina. Esta marcaxe pode facerse de varias maneiras, como por nick translation, ou por PCR usando nucleótidos marcados.
Despois faise unha preparación de cromosomas en metafase ou núcleos en interfase. Os cromosomas están firmemente unidos a un substrato, xeralmente vidro. Deben bloquearse as secuencias de ADN repetitivas engadindo curtos fragmentos de ADN á mostra. A sonda é despois aplicada ao ADN do cromosoma e incubada durante aproximadamente 12 horas mentres se hibrida. Fanse varios lavados que eliminan todas as sondas non hibridadas ou parcialmente hibridadas. Os resultados visualízanse despois e cuantifícanse usando un microscopio que poida excitar a marcaxe fluorescente e gravar as imaxes.
Se o sinal fluorescente é feble, pode ser necesaria a amplificación do sinal para que se supere o limiar de detección do microscopio. A forza do sinal fluorescente depende de moitos factores, como a eficiencia do etiquetado das sondas, o tipo de sonda e o tipo de tinguidura. Á molécula de tinguidura únense anticorpos marcados fluorescentemente ou estreptavidina. Estes compoñentes secundarios son seleccionados para que teñan un sinal forte.
Variacións nas sondas e análises
[editar | editar a fonte]
A FISH é unha técnica moi xeral. As diferenzas entre as varias técnicas de FISH débense xeralmente a variacións na secuencia e etiquetado das sondas; e a como se usan estas en combinación. As sondas son divididas en dúas categorías xenéticas: celular e acelular. O termo "In situ" na FISH refírese á situación da sonda, que se sitúa nas propias células.[12]
O tamaño das sondas é importante porque as sondas máis grandes hibridan menos especificamente que as máis curtas; "unha curta febra de ADN ou ARN (xeralmente de 10 a 25 nucleótidos) que é complementaria dunha secuencia diana dada, pode usarse para identificar ou localizar a diana.". O solapamento define a resolución das características detectables. Por exemplo, se o obxectivo dun experimento é detectar o punto de rotura dunha translocación, entón o solapamento das sondas (o grao no que a secuencia de ADN está contida nas sondas adxacentes) define a fiestra mínima na cal se pode detectar o punto de rotura.
A mestura de secuencias das sondas determina o tipo de características que as sondas poden detectar. As sondas que se hibridan ao longo de todo un cromosoma utilízanse para contar o número de copias dun determinado cromosoma, observar translocacións, ou identificar fragmentos extracromosómicos de cromatina. Isto adoita denominarse "pintura de cromosoma completo" ("whole-chromosome painting"). Se se utilizan todas as posibles sondas, cada cromosoma, (o xenoma completo) quedaría marcado fluorescentemente, o cal non sería útil para determinar as características de secuencias determinadas. Porén, é posible crear unha mestura de sondas máis pequenas que son específicas dunha rexión particular (locus) do ADN; estas mesturas utilízanse para detectar mutacións por deleción. Cando se combinan cunha cor específica, utilízase unha mestura de sondas específicas de locus para detectar translocacións moi específicas. Con frecuencia utilízanse mesturas de sondas específicas de locus especiais para contar cromosomas, ao unirse ás rexións centroméricas dos cromosomas, que son o suficientemente distintivas para identificar cada cromosoma (coa excepción dos cromosomas 13, 14, 21 e 22.)
Outras varias técnicas utilizan mesturas de sondas de diferentes cores. Como pode detectarse un rango de cores nas mesturas das tinguiduras fluorescentes, cada cromosoma humano pode ser identificado por unha cor característica usando mesturas de sondas de cromosoma completo e diversas proporcións de cores. Aínda que hai máis cromosomas que cores de tinguiduras fluorescentes que se poidan distinguir doadamente, poden utilizarse as proporcións de mesturas de sondas para crear cores secundarias. De xeito similar á hibridación xenómica comparativa, a mestura de sondas para as cores secundarias créase mesturando a correcta proporción de dous conxuntos de sondas de diferentes cores para o mesmo cromosoma. Esta técnica denomínase ás veces M-FISH.
A mesma física que fai posible ter unha variedade de cores na M-FISH pode usarse para a detección de translocacións. É dicir, as cores que son adxacentes parecen solaparse e obsérvase unha cor secundaria. Algúns ensaios deséñanse para observar se a cor secundaria está presente ou ausente nos casos que interesa. Un exemplo é a detección de translocacións BCR/ABL, nas que a cor secundaria indica que hai enfermidade. Esta variación adoita chamarse FISH de dobre fusión ou D-FISH. A situación oposta, na que a ausencia da cor secundaria é o que indica patoloxía, pode poñerse en evidencia por medio dun ensaio para investigar translocacións nas que se coñece ou é constante só un dos puntos de rotura. As sondas específicas de locus están feitas para un lado do punto de rotura e o outro cromosoma intacto. En células normais obsérvase a cor secundaria, mais cando hai translocación só se observan as cores primarias. Esta técnica adoita chamarse break-apart FISH.
Sondas ISH QuantiGene ViewRNA
[editar | editar a fonte]O uso de sondas ISH QuantiGene ViewRNA é un método para detectar e cuantificar moléculas de ARNm, ARN non codificante longo e microARN en mostras de tecidos que están fixados con formaldehido e incluídos en parafina, frescos ou conxelados, e en mostras de células e de células tumorais circulantes (CTC). As sondas ISH ViewRNA permiten detectar unha molécula individual de ARNm con practicamente nigún ruído de fondo. Cada sonda (para a detección de ARNm e ARNncl) está composta por 20 pares de oligonucleótidos. Cada par oligo forma unha plataforma necesaria para a ensamblaxe da estrutura de amplificación do sinal (árbore) por medio dunha serie de pasos de hibridación secuenciais usando a tecnoloxía de amplificación de sinal do ADN ramificado (bDNA, de branched DNA). Cada estrutura completamente ensamblada, cobre un espeazo de 40-50 bit/s da diana ARNm/ARNncl, e ten capacidade para amplificar o sinal unhas 400 veces. Por tanto, unha sonda específica de diana típica (que contén 20 pares de oligos) ten a capacidade de xerar unha amplificación de sinal multiplicada por 8.000. Sistemas de amplificación de sinal independentes pero compatibles permiten a detección simultánea de ata catro dianas ARNm/ARNncl en células ou CTCs e ata dous ARNm/ARNncl longo en tecidos.
Sondas FISH de ARN Stellaris(R)
[editar | editar a fonte]O FISH de ARN Stellaris, antes coñecida como FISH de ARN dunha soa molécula, é un método de detección e cuantificación de ARNm e outras moléculas de ARN longas nunha capa delgada de mostra de tecido. As dianas poden visualizarse fiablemente aplicando moitas sondas de oligonucleótidos cunha soa etiquetaxe curtas.[13] A unión de ata 48 oligos etiquetados fluorescentemente a unha soa molécula de ARNm proporciona fluorescencia suficiente como para detectar e localizar con exactitude cada ARNm diana nunha imaxe de microsocpia de fluorescencia de campo amplo. As sondas que non se unen á secuencia pretendida non chegan a ter fluorescencia localizada dabondo como para poder ser distinguidas do ruído de fondo.[14]
Os ensaios de FISH de ARN dunha soa molécula poden realizarse en ensaios simples ou múltiples, e poden utilizarse como un experimento posterior a unha PCR cuantitativa, ou visualizados simultaneamente cun ensaio con anticorpo fluorescente. A tecnoloxía ten aplicacións potenciais no diagnóstico do cancro,[15] neurociencia, análise da expresión xénica,[16] e diagnósticos de xenómica personalizada (companion diagnostics).
Fiber FISH
[editar | editar a fonte]Na técnica fiber FISH (FISH de fibra) alternativa para preparacións en interfase ou metafase, as fibras de ADN interfásico desproteinizado (sen histonas) son adheridas a unha lámina ou porta de modo que queden estendidas en liña recta, en lugar de estaren enroladas apertadamente, como na FISH convencional, ou adoptaren unha conformación de territorio cromosómico, como na FISH de interfase. Isto realízase aplicando cizalladura mecánica ao longo da lonxitude do porta, ou ben ás células que foron fixadas ao porta e despois lisadas, ou a unha solución de ADN purificado. Con este propósito está usándose cada vez máis unha técnica chamada peiteado cromosómico (chromosome combing). A conformación estendida do cromosoma permite unha resolución moito máis alta, mesmo por debaixo dunhas poucas quilobases. Aínda que a preparación das mostras é conceptualmente simple, require unha certa habilidade, e só se usa rutineiramente en laboratorios especializados.
Q-FISH
[editar | editar a fonte]A Q-FISH combina a FISH con PNAs e un software computacional para cuantificar a intensidade da fluorescencia. Esta técnica utilízase de rutina para investigar a lonxitude dos telómeros.
Flow-FISH
[editar | editar a fonte]A Flow-FISH (FISH de fluxo) utiliza citometría de fluxo para realizar a FISH automaticamente usando medidas de fluorescencia por célula.
Aplicacións médicas
[editar | editar a fonte]Cando os pais que tiveron un fillo con discapacidade de desenvolvemento queren saber os riscos de ter outro fillo coa mesma condición, pode dárselle esa información analizando o ADN dos pais. Nos casos nos que a discapacidade do neno non está ben comprendida, a causa pode potencialmente determinarse mediante FISH e técnicas citoxenéticas. Exemplos de doenzas que se diagnostican por medio de FISH son a síndrome de Prader-Willi, a síndrome de Angelman, a síndrome da deleción 22q13, a leucemia mielóxena crónica, a leucemia linfoblástica aguda, o Cri-du-chat, a síndrome velocardiofacial, e a síndrome de Down. A FISH feita a espermatozoides está indicada para homes cun cariotipo meiótico ou somático anormal e para os que teñen oligozoospermia, xa que aproximadamente o 50% dos homes oligozoospérmicos teñen un incremento na taxa de anormalidades cromosómicas nos espermatozoides.[17] A análise dos cromosomas 21, X e Y é suficiente para identificar os individuos oligozoospérmicos en risco.[17]
En medicina, a FISH pode utilizarse para diagnosticar, para avaliar o prognóstico, ou para avaliar a remisión dunha doenza, como por exemplo o cancro. O tratamento pode despois ser especificamente adaptado ao caso. Un exame tradicional no que se fai unha análise de cromosomas metafásicos xeralmente non serve para identificar as características que distinguen unha doenza doutra, debido ás sutís características dos cromosomas, pero a FISH pode dilucidar estas diferenzas. A FISH pode tamén usarse para detectar células enfermas máis facilmente que polos métodos citoxenéticos estándar, que necesitan utilizar células en división e supoñen moito traballo e unha preparación manual que leva moito tempo e a análise de preparacións por un especialista. A FISH non require usar células vivas e pode ser cuantificada automaticamente, xa que un computador conta os puntos fluorescentes presentes. Porén, cómpre un tecnólogo adestrado para distinguir as sutís diferenzas nos patróns de bandeado en cromosomas metafásicos dobrados e curvados.
A FISH pode incorporarse a un dispositivo microfluídico Lab-on-a-chip. Esta tecnoloxía aínda está nunha fase de desenvolvemento mais, como outros métodos de lab-on-a-chip, pode levar ao desenvolvemento de técnicas de diagnóstico máis portátiles.[18][19] Na FISH on chip emprégase un chip microfluídico con estreitas canles polas que se fai pasar a suspensión celular purificada por capilaridade, lavada previamente con PBS. Unha vez adheridas ou fixadas as células ás canles por calor, dixerimos as células mediante a adición de proteinase K e desnaturalizamos o seu material xenético, novamente por un incremento de temperatura. Tras estes pasos, xa poden ser engadidas as sondas e reactivos necesarios, que difundirán ao longo de toda a canle, e poden observarse os núcleos baixo o microscopio no mesmo chip e de maneira ordenada. A FISH on chip é unha técnica moi útil para detectar anomalías cromosómicas (aneuploidías), entre outros defectos. No caso do alzhéimer, é habitual utilizar mostras de linfocitos procedentes de sangue periférico, fibroblastos ou mostras de urina.
Identificación de especies
[editar | editar a fonte]A FISH úsase con frecuencia en estudos clínicos. Se un paciente é infectado cun patóxeno sospeitoso, cultívanse en ágar bacterias procedentes dos tecidos e fluídos do paciente para determinar a identidade do patóxeno. Porén, moitas bacterias, mesmo as de especies ben coñecidas, non crecen ben en condicións de laboratorio. A FISH pode utilizarse para detectar directamente a presenza do microbio sospeitoso en mostras de tecidos do paciente.
A FISH pode tamén utilizarse para comparar os xenomas de dúas especies biolóxicas, para deducir as súas relacións evolutivas. Unha técnica de hibridación similar denomínase zoo blot. As sondas de FISH bacterianas son a miúdo cebadores para a rexión do ARNr 16S.
A FISH utilízase moito no campo da ecoloxía microbiana, para identificar microorganismos. As biopelículas, por exemplo, están compostas de complexas organizacións xeralmente de moitas especies de bacterias. Preparando sondas de ADN para unha especie e realizando a FISH con dita sonda pode visualizarse a distribución de especies concretas na biopelícula. Se se preparan sondas (de dúas cores distintas) para dúas especies pode visualizarse e estudar a co-localización destas dúas especies na biopelícula, e isto pode ser útil para determinar a arquitectura fina da biopelícula.
Hibridación xenómica comparativa
[editar | editar a fonte]A hibridación xenómica comparativa pode describirse como un método que usa a FISH de maneira paralela á comparación da forza de hibridación para detectar calquera alteración de importancia no proceso de duplicación de secuencias de ADN no xenoma do núcleo.[20]
Cariotipo virtual
[editar | editar a fonte]Realizar un cariotipado virtual é outra alternativa á FISH dispoñible clinicamente relativamente barata, que usa miles ou millóns de sondas nunha soa matriz para detectar os cambios no número de copias, en todo o xenoma, a unha resolución sen precedentes. Actualmente, este tipo de análises só detecta as ganancias ou perdas de material cromosómico e non detecta rearranxos equilibrados, como translocacións e inversións que son a marca distintiva de aberracións que se observan en moitos tipos de leucemias e linfomas.
Cariotipo espectral
[editar | editar a fonte]O cariotipado espectral (SKY, M-FISH) é unha imaxe de cromosomas coloreados. Implica realizar a FISH utilizando moitas sondas para ver cada cromosoma etiquetado no seu estado metafásico. Este FISH multicolor permite observar os 23 pares de cromosomas á vez, tinguidos con diferentes sondas fluorescentes. Un programa informático encárgase de analizar as imaxes e formar o cariograma: organiza os cromosomas de acordo coa emisión das sondas que ten integradas e combínaas ata dar as 23 combinacións necesarias. Utilízase con frecuencia no estudo de células tumorais. O poder de dito método débese á súa habilidade para:
- Determinar rapidamente se hai algún cromosoma adicional no cariotipo e de que cromosoma se trata, porque se poderá identificar pola súa cor.
- Determinar se está presente algún cromosoma translocado e que cromosomas están implicados na translocación pola combinación de dúas cores asociadas a cromosomas diferentes nun mesmo cromosoma.
- Rápida identificación de material cromosómico dun cromosoma que foi inserido noutro cromosoma pola variación da cor do fragmento inserido respecto á cor de todo o cromosoma.
- Identificación de cromosomas pequenos ou fragmentados que frecuentemente implican o problema de determinar a súa orixe, como é o caso dos cromosomas marcadores.
As desvantaxes do método é que é caro e non detecta translocacións pequenas nin se poden ver as bandas, polo que ten menos resolución que a FISH convencional.
Galería
[editar | editar a fonte]-
Outro esquema do proceso FISH.
-
Chip microfluídico que rebaixa o custo por test da FISH nun 90%.
-
Imaxe de FISH con etiquetado dual; Bifidobacterias Cy3, bacterias totais FITC.
Notas
[editar | editar a fonte]- ↑ Tamén se pode ver traducida en textos científicos como "hibridación fluorescente in situ" ou "hibridación in situ con fluorescencia", entre outras posibilidades (ver Google Académico).
- ↑ Langer-Safer, P. R.; Levine, M.; Ward, D. C. (1982). "Immunological method for mapping genes on Drosophila polytene chromosomes". Proceedings of the National Academy of Sciences 79 (14): 4381. Bibcode:1982PNAS...79.4381L. doi:10.1073/pnas.79.14.4381. PMC 346675. PMID 6812046.
- ↑ Amann, Rudolf; Fuchs, Bernhard M. (2008). "Single-cell identification in microbial communities by improved fluorescence in situ hybridization techniques". Nature Reviews Microbiology 6 (5): 339–348. doi:10.1038/nrmicro1888.
- ↑ Anthony, S. J.; St. Leger, J. A.; Pugliares, K.; Ip, H. S.; Chan, J. M.; Carpenter, Z. W.; Navarrete-Macias, I.; Sanchez-Leon, M.; Saliki, J. T.; Pedersen, J.; Karesh, W.; Daszak, P.; Rabadan, R.; Rowles, T.; Lipkin, W. I. (2012). "Emergence of Fatal Avian Influenza in New England Harbor Seals". MBio 3 (4): e00166–e00112. doi:10.1128/mBio.00166-12. PMC 3419516. PMID 22851656.
- ↑ Everitt, A. R.; Clare, S.; Pertel, T.; John, S. P.; Wash, R. S.; Smith, S. E.; Chin, C. R.; Feeley, E. M.; Sims, J. S.; Adams, D. J.; Wise, H. M.; Kane, L.; Goulding, D.; Digard, P.; Anttila, V.; Baillie, J. K.; Walsh, T. S.; Hume, D. A.; Palotie, A.; Xue, Y.; Colonna, V.; Tyler-Smith, C.; Dunning, J.; Gordon, S. B.; Everingham, K.; Dawson, H.; Hope, D.; Ramsay, P.; Walsh (Local Lead Investigator), T. S. et al. (2012). "IFITM3 restricts the morbidity and mortality associated with influenza". Nature 484 (7395): 519. Bibcode:2012Natur.484..519. doi:10.1038/nature10921. PMID 22446628.
- ↑ Louzada, S.; Adega, F.; Chaves, R. (2012). "Defining the sister rat mammary tumor cell lines HH-16 cl.2/1 and HH-16.cl.4 as an in vitro cell model for Erbb2". PLoS ONE 7 (1): e29923. Bibcode:2012PLoSO...729923L. doi:10.1371/journal.pone.0029923. PMC 3254647. PMID 22253826.
- ↑ Ting, D. T.; Lipson, D.; Paul, S.; Brannigan, B. W.; Akhavanfard, S.; Coffman, E. J.; Contino, G.; Deshpande, V.; Iafrate, A. J.; Letovsky, S.; Rivera, M. N.; Bardeesy, N.; Maheswaran, S.; Haber, D. A. (2011). "Aberrant Overexpression of Satellite Repeats in Pancreatic and Other Epithelial Cancers". Science 331 (6017): 593. Bibcode:2011Sci...331..593T. doi:10.1126/science.1200801. PMID 21233348.
- ↑ Zhang, B.; Arun, G.; Mao, Y. S.; Lazar, Z.; Hung, G.; Bhattacharjee, G.; Xiao, X.; Booth, C. J.; Wu, J.; Zhang, C.; Spector, D. L. (2012). "The lncRNA Malat1 is Dispensable for Mouse Development but Its Transcription Plays a cis-Regulatory Role in the Adult". Cell Reports 2 (1): 111–23. doi:10.1016/j.celrep.2012.06.003. PMC 3408587. PMID 22840402.
- ↑ Lee, K.; Kunkeaw, N.; Jeon, S. H.; Lee, I.; Johnson, B. H.; Kang, G. -Y.; Bang, J. Y.; Park, H. S.; Leelayuwat, C.; Lee, Y. S. (2011). "Precursor miR-886, a novel noncoding RNA repressed in cancer, associates with PKR and modulates its activity". RNA 17 (6): 1076. doi:10.1261/rna.2701111. PMID 21518807.
- ↑ 10,0 10,1 10,2 Bernasconi, B.; Karamitopolou-Diamantiis, E.; Tornillo, L.; Lugli, A.; Di Vizio, D.; Dirnhofer, S.; Wengmann, S.; Glatz-Krieger, K.; Fend, F.; Capella, C.; Insabato, L.; Terracciano, L. M. (2008). "Chromosomal instability in gastric mucosa-associated lymphoid tissue lymphomas: A fluorescent in situ hybridization study using a tissue microarray approach". Human Pathology 39 (4): 536–42. doi:10.1016/j.humpath.2007.08.009. PMID 18234275.
- ↑ Haroon, Mohamed F., Skennerton, Connor T., Steen, Jason A., Lachner, Nancy, Hugenholtz, Philip, & Tyson, Gene W. (2013). "Chapter One – In-Solution Fluorescence In Situ Hybridization and Fluorescence-Activated Cell Sorting for Single Cell and Population Genome Recovery". En F. DeLong Edward. Methods in Enzymology 531. Academic Press. pp. 3–19.
- ↑ Camesano, Terri A. and Mello, Charlene M. (2008). ACS Symposium Series. American Chemical Society. ISBN 9780841274303.
- ↑ Raj, A.; Van Den Bogaard, P.; Rifkin, S. A.; Van Oudenaarden, A.; Tyagi, S. (2008). "Imaging individual mRNA molecules using multiple singly labeled probes". Nature Methods 5 (10): 877. doi:10.1038/nmeth.1253. PMID 18806792.
- ↑ Biosearch Technologies Signs Exclusive License for Single Molecule FISH Technologies from UMDNJ. biosearchtech.com
- ↑ "A New Test for Recurrent Colon Cancer". Annals of Internal Medicine (en inglés) 131 (11): 805. 1999. doi:10.7326/0003-4819-131-11-199912070-00024.
- ↑ Kosman, D.; Mizutani, C. M.; Lemons, D; Cox, W. G.; McGinnis, W; Bier, E (2004). "Multiplex Detection of RNA Expression in Drosophila Embryos". Science 305 (5685): 846. doi:10.1126/science.1099247. PMID 15297669.
- ↑ 17,0 17,1 Sarrate, Z.; Vidal, F.; Blanco, J. (2010). "Role of sperm fluorescent in situ hybridization studies in infertile patients: Indications, study approach, and clinical relevance". Fertility and Sterility 93 (6): 1892. doi:10.1016/j.fertnstert.2008.12.139. PMID 19254793.
- ↑ Kurz, C. M.; v.d. Moosdijk, S.; Thielecke, H.; Velten, T. (2011). "Towards a cellular multi-parameter analysis platform: Fluorescence in situ hybridization (FISH) on microhole-array chips". 2011 Annual International Conference of the IEEE Engineering in Medicine and Biology Society. p. 8408. doi:10.1109/IEMBS.2011.6092074. ISBN 978-1-4577-1589-1.
- ↑ Dill, K., Hui Liu, R., Grodzinski, P. (2008). Microarrays: Preparation, Microfluidics, Detection Methods, and Biological Applications. Springer. p. 323. ISBN 0387727167.
- ↑ "Comparative Genomic Hybridization". McGraw-Hill Dictionary of Scientific and Technical Terms. Consultado o September 19, 2013.
Véxase tamén
[editar | editar a fonte]Outros artigos
[editar | editar a fonte]| Commons ten máis contidos multimedia sobre: Hibridación in situ fluorescente |
- Hibridación in situ, a técnica usada para o etiquetado
- Hibridación in situ cromoxénica (CISH)
- Citoxenética molecular
Bibliografía
[editar | editar a fonte]- Pernthaler A, Pernthaler J, Amann R (2002). "Fluorescence In Situ Hybridization and Catalyzed Reporter Deposition for the Identification of Marine Bacteria". Applied and Environmental Microbiology 68 (6): 3094–3101. PMC 123953. PMID 12039771. doi:10.1128/AEM.68.6.3094-3101.2002.
- Wagner M, Horn M, Daims H (2003). "Fluorescence in situ hybridisation for the identification and characterisation of prokaryotes". Current Opinion in Microbiology 2003 (6): 302–309. doi:10.1016/S1369-5274(03)00054-7.
- Carthy, J.D. (1965). Viewpoints In Biology. England: Butterworth & Co. p. 66.
Ligazóns externas
[editar | editar a fonte]Fluorescence in Situ Hybridization Medical Subject Headings (MeSH) na Biblioteca Nacional de Medicina dos EUA.
- Información sobre fiber FISH de Olympus Corporation
- Guide to fiber FISH de Octavian Henegariu
- Fibre FISH protocol Arquivado 23 de outubro de 2006 en Wayback Machine. do Human Genome Project no Sanger Centre
- CARD-FISH, BioMineWiki Arquivado 28 de xullo de 2020 en Wayback Machine.
- Preparation of Complex DNA Probe Sets for 3D FISH with up to Six Different Fluorochromes
- FISH technical notes and protocols from GeneDetect.com
- Fotos de bacterias con FISHArquivado 05 de febreiro de 2015 en Wayback Machine.



