PCR en tempo real
A reacción en cadea da polimerase en tempo real (ou PCR en tempo real, do inglés real-time PCR), tamén chamada PCR cuantitativa (en inglés, quantitative PCR; qPCR ou Q-PCR) ou PCR en tempo real cuantitativa é unha variante da reacción en cadea da polimerase (PCR) utilizada para amplificar e simultaneamente cuantificar de forma absoluta o produto da amplificación de ácidos desoxirribonucleicos (ADN). Nela emprégase basicamente o mesmo procedemento que na PCR convencional (de punto final), un molde de ADN, polo menos un par de cebadores específicos, dNTPs, un tampón químico de reacción adecuado, e un encima ADN polimerase termoestable; a dita mestura adiciónase unha substancia marcada cun fluoróforo que, nun termociclador que conteña sensores para medir a fluorescencia producida tras excitar o fluoróforo á lonxitude de onda axeitada, permita medir a taxa de xeración dun ou máis produtos específicos.[1] Dita medición, realízase logo de cada ciclo de amplificación e esa é a razón de que se chame PCR en tempo real (é dicir, PCR inmediata, simultánea).
A PCR cuantitativa xunto aos chips de ADN son modernas metodoloxías para o estudo da expresión xénica, aínda que outros métodos tradicionais como o northern blot, que non teñen tanta precisión, tamén se utilizan moito.[2] A variabilidade que se introduce na cuantificación usando este tipo de PCR, e que sempre supón un erro na estimación, deriva da integridade do ADN, eficiencia encimática e outros moitos factores, polo que se desenvolveron numerosos sistemas de estandarización. Hainos para cuantificar de forma absoluta a expresión xénica, pero, de forma máis común, oriéntanse á cuantificación relativa do xene de estudo respecto doutro, denominado «normalizador», que se selecciona debido á súa expresión case constante; estes genes adoitan denominarse, en inglés, house-keeping genes (~xenes de mantemento) debido a que adoitan estar implicados en funcións básicas para a supervivencia celular, e xeralmente teñen unha expresión constitutiva (continua).[3][4] Desta maneira, efectuando en cada experimento a medición dos xenes de interese e dividíndoos pola expresión do xene normalizador seleccionado é posible comparar os xene de interese aínda sen coñecer en termos absolutos o seu nivel de expresión. Os xenes normalizadores máis empregados son aqueles que codifican as seguintes proteínas: tubulina, gliceraldehido-3-fosfato deshidroxenase, albumina, ciclofilina, e tamén os dos ARNs ribosómicos etc.[2]
Terminoloxía e siglas
[editar | editar a fonte]En moitos casos o molde que se emprega para a PCR cuantitativa non é desde o principio ADN, senón que pode ser ADN complementario (ADNc) monocatenario, obtido por retrotranscrición a partir dun ácido ribonucleico (ARN); neste caso, a técnica é unha "PCR cuantitativa (en tempo real) tras reversotranscriptase" (ou RT-Q-PCR ou RT-qPCR ou qRT-PCR). Nesta técnica combínase a qPCR coa RT-PCR. Debe evitarse a confusión coa técnica denominada "PCR tras reversotranscriptase" (RT-PCR, do inglés reverse transcriptase PCR), na cal existe un paso de retrotranscrición de ARN a ADN pero que non cuantifica o produto en tempo real (a non ser que se combine coa qPCR como se indicou).
As directrices MIQE[5] propoñen que a abreviatura qPCR se use para a PCR en tempo real cuantitativa e que RT-qPCR se use para a técnica combinada de PCR en tempo real e PCR tras reversotranscriptase [2]. Aínda que o acrónimo "RT-PCR" normalmente significa só PCR tras reversotranscriptase pero non PCR en tempo real, o feito é que non todos os autores se adhiren a esta convención (e moitas veces aparece usada RT-PCR como PCR en tempo real),[6] polo que o risco de confusión coas siglas é evidente, e hai que atender sempre ao contexto en que se usan.
Fundamento
[editar | editar a fonte]- Artigo principal: Reacción en cadea da polimerase.
A PCR cuantitativa realízase nun termociclador con capacidade de facer incidir sobre cada mostra un feixe de luz dunha lonxitude de onda determinada e de detectar a fluorescencia emitida polo fluorocromo excitado. Este termociclador é un aparato con capacidade para quentar e arrefriar rapidamente as mostras, de modo que se aproveiten as cualidades fisicoquímicas dos ácidos nucleicos e as encimáticas da ADN polimerase.
O proceso da PCR xeralmente consiste nunha serie de cambios de temperatura que se repiten de 25 a 40 veces, chamados ciclos, onde cada un posúe un mínimo de tres etapas: a primeira, realizada a unha temperatura de arredor dos 95 °C, permite a separación dos ácidos nucleicos bicatenarios en febras separadas; o segundo, a unha temperatura duns 50-60 °C, permite o aliñamento (annealing) dos cebadores ao ADN molde (hibridación cebador-ADN molde);[7] o terceiro, a 68-72 °C, facilita a polimerización por parte da ADN polimerase. Debido ao pequeno tamaño dos fragmentos amplificados usualmente neste tipo de PCR pode omitirse o último paso, porque o encima pode amplificar durante a rampla (na gráfica) entre a temperatura de aliñamento e a de desnaturalización. Ademais, algúns termocicladores engaden a cada ciclo uns segundos máis a outra temperatura, por exemplo a 80 °C, a fin de reducir o ruído pola presenza de dímeros de cebadores cando se utiliza un colorante inespecífico. As temperaturas usadas e o tempo aplicado en cada ciclo dependen de gran variedade de parámetros, como: o encima usado para a síntese de ADN, a concentración de ións divalentes e desoxirribonucleótidos (dNTPs) na reacción e a temperatura de unión dos cebadores.[8]
Clasificación
[editar | editar a fonte]Podemos clasificar as técnicas de PCR cuantitativa segundo o emprego de fluorocromos non específicos ou ben de sondas moleculares dependentes da secuencia.
- Nas técnicas baseadas en fluorocromos inespecíficos detéctase a xeración exponencial de ADN de dobre cadea empregando un fluorocromo que se une inespecificamente a aquel. Un exemplo de colorante que permite esta detección é o SYBR Green (Verde SYBR), que, unha vez excitado mediante luz azul (λmax = 488 nm) emite luz verde (λmax = 522 nm).[9] Posúe a vantaxe de requirir só un par de cebadores para efectuar a amplificación, o que abarata o seu custo; porén, só é posible amplificar un produto en cada reacción.
- As técnicas baseadas en sondas específicas utilizan polo menos un oligonucleótido marcado fluorescentemente. Tipicamente esta sonda está unida a dous fluorocromos e hibrida na zona intermedia entre os dous cebadores (o amplicón), é dicir, entre o cebador directo ou cara a adiante (forward) e o inverso (reverse). Deste modo, cando a sonda está intacta, presentan unha transferencia de enerxía de resonancia de fluorescencia (FRET). Dita FRET non se produce cando os dous fluorocromos están a certa distancia debido á degradación da sonda mediante a actividade de exonuclease 5'-3' da ADN polimerase, ou ben debido á separación física dos fluorocromos por un cambio na conformación da sonda. Isto permite monitorizar o cambio do patrón de fluorescencia e deducir o nivel de amplificación do xene.
Análise de temperatura de fusión
[editar | editar a fonte]
A Q-PCR permite, empregando un fluorocromo que se une inespecificamente á dobre hélice do ADN, xeralmente SYBR Green, identificar fragmentos amplificados de DNA concretos a partir da temperatura de fusión (tamén denominada valor Tm, do inglés melting temperature), que é específica para o fragmento amplificado que se está a buscar; e cuxos resultados se obteñen a partir da observación da curva de disociación das mostras de ADN analizadas.[11]
Isto permite, a diferenza da PCR convencional, prescindir do emprego posterior de técnicas de electroforese para a visualización dos resultados de todas as mostras. Porque, malia que a PCR cuantitativa é unha técnica cinética, adoita ser avaliada a punto final. Así, con esta técnica poden obterse resultados máis rápidos, e cun menor gasto de reactivos ao aforrar os que se terían empregado na electroforese; se, segundo o criterio do investigador, posteriormente é necesario correr en xeles só aquelas mostras cuxos resultados previos na PCR en tempo real se poden considerar dubidosos ou para ratificar resultados en mostras positivas.
Cuantificación da expresión xénica
[editar | editar a fonte]A cuantificación pode realizarse en termos absolutos ou relativos. No primeiro caso, a estratexia é relacionar o sinal de amplificación obtido co contido en ADN empregando unha curva de calibrado; para este enfoque é vital que a PCR da mostra e dos elementos da recta de calibrado posúan unha mesma eficiencia de amplificación. No segundo caso, exprésase o cambio nos niveis de expresión do ARN mensaxeiro (ARNm) interpretado en forma de ADN complementario (ADNc), xerado por retrotranscrición a partir do ARNm; esta cuantificación relativa é máis doada de realizar, xa que non require curva de calibrado, e consiste na comparación entre o nivel de expresión do xene a estudar e a dun xene control (tamén chamado de referencia, interno ou normalizador ou, en inglés, housekeeping gene ou xene de mantemento).
Por tanto, na cuantificación relativa é irrelevante en que unidades se expresa, e os seus resultados son comparables entre múltiples experimentos de RT-Q-PCR. De feito, o propósito de empregar un ou máis xenes de normalización é corrixir a variación non específica, como as diferenzas na cantidade e calidade do ARN utilizado, que poden afectar ás eficiencias de retrotranscrición e de PCR. Con todo, o aspecto fundamental é que a estabilidade do xene de referencia sexa unha realidade.[12]
A selección dos xenes internos realizouse clasicamente en bioloxía molecular analizando a estabilidade da expresión en estudos cualitativos ou de baixa sensibilidade, como o exame visual de xeles de ARN, densitometría de northern blots ou PCR semicuantitativa (PCR mimic). En plena era da xenómica, é posible realizar unha aproximación rápida a grande escala empregando chips de ADN para moitos organismos.[13] Porén, describiuse que a maioría dos xenes usados como normalizadores na cuantificación da expresión de ARN mensaxeiro varían segundo as condicións experimentais.[14][15][16] Por todo isto, cómpre realizar un estudo metodolóxico previo sobre cal empregar coa finalidade de seleccionar, con axuda de ferramentas estatísticas, os máis axeitados.
Desenvolvéronse varios algoritmos estatísticos que detectan que xene ou xenes son os máis apropiados para a normalización dun conxunto de tecidos nunhas condicións dadas: algúns, como geNORM ou BestKeeper, actúan sobre unha matriz de expresión de xenes de referencia para diversos tecidos, realizando comparacións por pares e medias xeométricas.[17][18]
Modelización
[editar | editar a fonte]A diferenza da PCR de punto final (ou PCR convencional), a PCR en tempo real permite cuantificar o nivel de produto obtido en calquera momento da amplificación mediante o sinal de fluorescencia (en realidade, mediante o seu nivel sobre un limiar). Os valores de fluorescencia, expresados como logaritmos para estudar doadamente a fase exponencial de amplificación, que aparece como unha liña recta ao representar graficamente o logaritmo da fluorescencia fronte ao número de ciclos; este segmento, denominado segmento cuantificable, permite valorar a cantidade de ADN inicial.
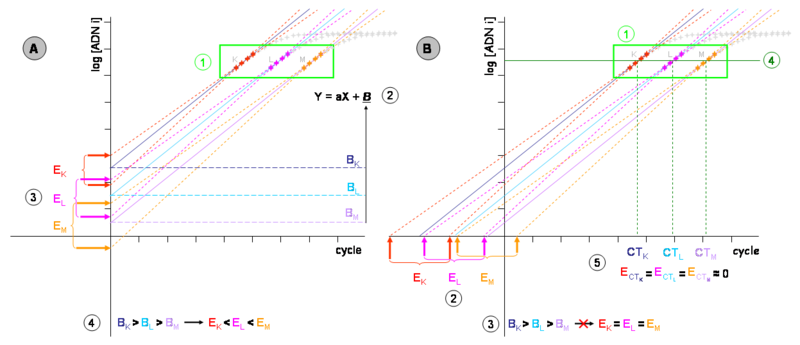
Gráfica da esquerda (A)
[editar | editar a fonte]As cinéticas de tres PCR de tres mostras distintas (K, L e M) de concentracións de ADN inicial decrecentes (concretamente, redúcense á décima parte cada vez) represéntanse nun gráfico do logaritmo da fluorescencia (en ordenadas) fronte ao ciclo de PCR (en abscisas). Non se representan as fases previas á exponencial.
- Zona de segmentos cuantificables de cada mostra. En gris a zona de saturación, fóra xa da zona linear.
- Cada un dos segmentos cuantificables permite definir unha ecuación da recta de tipo U=ax+b, que permite modelizar a eficiencia da amplificación (a pendente a) e, mediante a ordenada na orixe b, a cantidade de ADN no ciclo 0, polo menos teoricamente.
- Como as medidas experimentais levan sempre un erro, dita cuantificación arrastra un erro estocástico. Se as mostras de concentracións K, L e M foran amplificadas durante máis ciclos, obteríanse cinéticas diferentes, aínda que bastante próximas (represéntanse os seus segmentos cuantificables en vermello, rosa e laranxa). Cada unha destas medidas permite establecer unha nova ecuación, representada en puntos da mesma cor. As ordenadas na orixe (b) diferentes tamén se miden. Así, podemos avaliar o erro ou incerteza da técnica avaliando as diferenzas entre as pendentes b (EK, EL, EM).
- Non obstante, dita imprecisión na medida varía para cada mostra (EK é inferior a EL, que é, á súa vez, máis pequena que EM). Unha proxección da ecuación da dereita sobre o eixe de ordenadas ou unha das súas paralelas dará lugar a un «erro dependente da concentración de ADN inicial».
Gráfica da dereita (B)
[editar | editar a fonte]- As ecuacións obtidas segundo os segmentos cuantificables poden extrapolarse cara ao eixe de abscisas, aínda que se trate dun valor que carece de significado bioquímico e teno só matemático.
- Os ángulos que modelizan o erro experimental (liñas de puntos vermellos, laranxas ou rosas) permiten definir as novas incerteza EK, EL e EM. Estas incertezas son maiores que na gráfica da esquerda (gráfica A), pero manteñen a súa proporcionalidade. Por tanto, sobre a medida agora xeramos un «erro independente da concentración de ADN inicial».
- É posible proxectar rectas paralelas entre si, sobre a recta definida sobre unha paralela ao eixe de abscisas de modo que se corten os segmentos cuantificables pola metade. Este segmento é denominado «limiar de detección».
- Os valores en X (número de ciclos) destas interseccións denomínanse "CT" (ou «Ct», do inglés cycle threshold ou limiar de ciclo), aínda que tamén poden chamarse "CP" (do inglés crossing point, punto de cruzamento). Trátase pois, dos valores matemáticos definidos sobre o espazo de números reais positivos e non dos enteiros positivos (aínda que unha fracción do ciclo non posúa realidade experimental). Estes valores, inversamente proporcionais á cantidade de ADN inicial, adoitan posuír unha incerteza sobre a medida mínima, en xeral inferior ao 5%.
Rectas de calibrado
[editar | editar a fonte]Como se indicou no apartado de cuantificación, empregar o CT, como valor matemático, permite obter resultados fiables, mais este feito pode non ser explotado directamente. A fin de coñecer a cantidade de ADN inicial, é preciso realizar novas transformaciones matemáticas que requiren coñecer a eficiencia de PCR, que adoita determinarse grazas a unha recta de calibrado.

- Gráfica da esquerda (A)
As novas mostras F, G, H, I, J, K, L, M e N, de concentración de ADN inicial decrecente (unha orde de magnitude cada vez) amplifícanse mediante PCR nun mesmo experimento. Cada cinética permite determinar un CT para cada un (é dicir, un número en referencia a un ciclo en concreto). Represéntanse as concentracións de ADN como número de moléculas por tubo (neste caso, F posúe 70 millóns e N, 0,7).
Os rendementos representados corresponden a «n» reaccións, cuxa fiabilidade se debe á existencia de réplicas independentes na reacción, persoal e reactivos. A fluorescencia móstrase en unidades arbitrarias e o ruído de fondo foi limpado. Hai que salientar que a mostra Nn non se amplificou en absoluto.
Os valores CT medios en función da cantidade de ADN inicial de todas as réplicas poden representarse nun gráfico semilogarítmico. Deste xeito, a recta de calibrado para estes valores medios pode definirse grazas a unha regresión linear cun determinado coeficiente de correlación (r2) que, para ser considerado de calidade, debe ter un valor de 0,9999. Porén, han de representarse os erros, xeralmente definidos segundo o rango de valores obtidos para un punto.
Con estes datos, é posible estudar:
- A fase «cuantitativa e detectable da PCR». Na cal todas as mostras son detectables e están aliñadas en todos os seus puntos coa súa recta particular. Xeralmente, esta fase comprende as concentracións de ADN iniciais arredor de 102 ou 108 copias do ácido nucleico. Por debaixo destas cifras os fenómenos estocásticos alteran perceptiblemente os resultados, aínda que é posible compensalos cun alto número de réplicas nas medidas. Por riba destes valores, o «ruído de fondo» é baixo dabondo como para que non se poida determinar; neste caso, é posible compensar esta deficiencia mediante un protocolo de PCR cunha eficiencia moi alta ou, de forma máis simple, diluíndo a mostra inicial.
- A fase «ás veces detectable pero non cuantitativa da PCR». Comprende as concentracións de ADN inicial entre unha copia e a decena de copias. A porcentaxe de mostras medidas, no exemplo da gráfica, indícase por medio das concentracións M e N, é dicir, 83% para unha concentración media de sete copias e 28% cando tres dos catro tubos conteñen unha copia (0,7 de concentración, ou -0,15 en logaritmo). A dispersión das medidas, e, por tanto, a marxe de erro, increméntanse perceptiblemente. Nótese que un bo número de medidas M e N non se aliñan coa súa recta particular, aínda que non o fagan por motivos aleatorios. Por tanto, esta fase só se pode replicar con precisión replicando máis veces as medidas.
- A recta de calibrado, por tanto, representada nun gráfico semilogarítmico dá lugar a unha recta definida pola fórmula Y = aX + B onde:
- Y é o CT medido polo termociclador.
- A pendente a deriva da eficiencia da PCR, e pode calcularse ploa ecuación
- Nótese que no esquema se representa o caso máis frecuente no que a concentración está expresada en logaritmos decimais. Esta pendente está a miúdo considerada como unha constante de amplificación para cada xene, par de cebadores e condición de PCR particular. Por iso esta pendente ou eficiencia de amplificación utilízase para cuantificar na PCR cuantitativa.
- X é a concentración de ADN inicial expresada en logaritmo de copias/tubo, ng/µL, unidades arbitrarias etc.
- B é un punto matemático sen realidade experimental (log 0 = 1/∞) que, non obstante, pode usarse para calibrar cada experimento de PCR (os «runs», en inglés) cos seus semellantes. Deste modo, se as rectas de calibrado o foron pola súa intersección á orixe B, a dispersión será menor, agás para os puntos M e N.
- A recta de regresión non pasa polo punto central da dispersión en cada medida para as concentracións M e N, pero si segundo a pendente e un factor de «amortecemento». É dicir: se consideramos CT medios para L e N serán modelizados de mellor maneira mediante un polinomio de segundo grao. O software dalgúns termocicladores permite ter en conta este «amortecemento», pero hai que ter tamén en conta que:
- Dito amortecemento é extremadamente variable dunha recta de calibrado a outra, e a corrección que se modeliza non corresponde probablemente a aquela que pasa pola mostra cuantificada. O software comercial modelízao para unha soa mostra.
- A imprecisión na cuantificación a estas concentracións é tan importante que pode ser necesaria a modelización do «amortecemento».
- Este «amortecemento» corresponde, cando se debuxan as rectas, a unha redución da pendente logo dun aumento da eficacia de PCR, así que pode reducirse o incremento dos efectos estocásticos. Nótese ademais que este «amortecemento» se define principalmente pola concentración máis baixa (N, 0,7 copias no exemplo). Noutras palabras, non poderá realizarse ningunha amplificación se non se ten polo menos unha molécula completa do ADN a amplificar. O nesgo producido na distribución gaussiana do erro pode provocar esta aparición de datos estraños ou «amortecementos medios».
A recta de calibrado permite unha cuantificación para un protocolo experimental dado pero hai que ter en conta que existen multitude de fontes de erro potenciais, como diferenzas de composición química do tampón de reacción, das mostras (presenza de proteínas, ARN etc) e mesmo do diluente (xeralmente auga).
Enfoques
[editar | editar a fonte]Como se indicou anteriormente, é posible cuantificar a expresión xénica tanto en termos absolutos coma en relativos (é dicir, por comparación coa expresión doutro xene). No segundo caso, é de vital importancia seleccionar como xene estándar un cuxa expresión realmente non varíe cando se somete ao individuo ao tratamento experimental cuxo efecto na transcrición se desexa estudar (por exemplo, un estrés ambiental,[19] biótico[20] ou tipo de tecido[21]).
- Cuantificación absoluta
Baséase nas características da fase exponencial da curva sigmoide de emisión de fluorescencia.[22] Responde á ecuación:
- onde Q é a cantidade de ADN, n corresponde ao número de ciclo, o é o ciclo de partida e E a eficiencia da reacción.
Entón, no ciclo no que se supera o nivel limiar (é dicir, o CT), dise que:
(1)
- Cuantificación relativa
Establece unha relación R entre a cantidade de ADN inicial dunha mostra respecto da dunha testemuña, que se asume se expresa de forma invariable e independente do tratamento. Na súa detección temos que:[4]
- substituíndo de (1) temos que
- e, por tanto,
o:
Desde 2002 existe unha tendencia a empregar varios xenes normalizadores para realizar unha cuantificación relativa fiable; deste modo, xéranse factores de normalización que ponderan dalgún modo o impacto de cada xene interno; unha aproximación común baséase no emprego de medias xeométricas destes xenes normalizadores.[17]
Selección de xenes de normalización
[editar | editar a fonte]A análise estatística que permite a detección dos xenes expresados de forma máis estable na serie de tecidos estudada é crucial, porque del depende a elección dos xenes que se usarán como control interno durante os ensaios de cuantificación relativa. Co fin de avaliar esta estabilidade, nalgúns casos compáranse os seus valores CT; noutros, as súas cantidades relativas utilizando a mostra cuxo CT é menor como elemento normalizador.
Como primeira aproximación o algoritmo geNorm[17] permite o cálculo dun valor de estabilidade M inversamente proporcional á estabilidade do xene en cuestión, e dunha serie de valores "PV" que definen o número mínimo de xenes adecuado para efectuar unha normalización fiable. O cómputo do valor M baséase en definir a variación media, calculada comparando pares dous a dous, dun xene fronte a todos os demais xenes presentes no estudo. O algoritmo realízase en varios pasos, xa que en cada rolda de comparacións se suprime o xene que obtivo un peor valor; deste modo, pode adxudicarse un valor M a cada xene agás para os máis estables, que comparten o mesmo. En canto aos valores PV, o seu cómputo baséase no deseño dun factor de normalización óptimo; ao principio, este realízase cos dous xenes máis estables pero, secuencialmente, vánselle engadindo outros ata que dita adición non mellora significativamente a precisión daquel. Así, defínese un valor PV para as comparacións entre Vn/n+1, estimado como a desviación estándar dos ratios transformados logaritmicamente de .
Outro algoritmo, denominado NormFinder, aproveita os valores CT para axustar un modelo matemático da expresión xénica que pode avaliar as variacións presentes dentro e entre os grupos (tipo de órganos, tratamentos químicos...) definidos polo investigador. Deste modo, os xenes cunha variación inter e intragrupo mínima son os considerados máis estables, e posúen un valor de estabilidade S mínimo.[23]
Tamén é posible avaliar non xa a estabilidade mediante comparacións dous a dous, senón analizar o coeficiente de variación dos niveis de expresión relativos normalizados. Esta aproximación, propia de qBase ou qBasePlus,[24] require da transformación dos valores CT iniciais en cantidades relativas tendo en conta os valores de eficiencia da PCR e usando como calibrador o xene con menor CT; tras isto, calcúlase un factor de normalización para cada mostra empregando a media xeométrica dos valores relativos estimados para todos os xenes candidatos.
Controis
[editar | editar a fonte]Débense realizar varios tipos de controis:
- Control negativo: engadimos todos os reactivos necesarios menos a mostra, polo que non deberemos obter amplificación.
- Control de inhibidores (control positivo):
- Externos: realizaremos un tubo en paralelo para cada mostra no que se amplifica un fragmento a partir dunha cantidade coñecida de copias (mesmos cebadores, con deleción ou inserción ou outro fragmento non relacionado).
- Internos: Engádese unha cantidade mínima coñecida e detectable dunha secuencia modificada da secuencia diana que se amplifica, cos mesmos cebadores pero que se detecta cun fluorocromo distinto.
- Control de cuantificación (estándares):
- Externos: utilízase a mesma secuencia que se quere cuantificar pero modificando no sitio da sonda ou noutro lugar. Isto evita problemas de contaminación.
- Control sen transcrición inversa: Este utilízase cando o temperado é un ADNc preparado a partir dun paso de transcrición inversa desde un ARN. Este control é especialmente útil para avaliar o paso de purificación dos ARN e evitar contaminantes.
Emprego de sondas específicas
[editar | editar a fonte]A PCR en tempo real pode realizarse marcando de maneira fluorescente oligonucleótidos que detectan especificamente a aparición do produto desexado. O fundamento desta técnica baséase no uso do FRET ou transferencia de enerxía de resonancia de Förster, que é un mecanismo de transferencia de enerxía entre cromóforos. O FRET fundaméntase en que a excitación dun cromóforo pode transferirse a outro próximo, xeralmente cando ambos os dous se sitúan na mesma molécula, mediante un mecanismo acoplador dipolo-dipolo.[25] No caso de que os cromóforos sexan fluorescentes (isto é, fluorocromos), o mecanismo subxacente continúa sendo o mesmo: a enerxía transfírese, o que desemboca na aparición de fluorescencia (hai que salientar que non é a fluorescencia a transferida)[26][27] As sondas empregadas en PCR en tempo real existentes son:

- As sondas TaqMan permiten medir a produción de produtos de PCR mediante un sistema de sondas marcadas mediante dous fluorocromos. A súa utilidade débese a que posúen un fluoróforo no seu extremo 3' e unha molécula no 5' que bloquea a súa emisión de fluorescencia (denominada en inglés «quencher», inhibidor da fluorescencia); esta sonda marcada híbrida especificamente na parte central do produto de PCR a obter. Deste modo, cando se efectúa a PCR (coa sonda máis o par de cebadores específicos), a sonda híbrida no amplicón, pero, debido á proximidade do fluoróforo ao quencher, non se emite fluorescencia; cando a polimerase se atopa coa sonda hidrolízaa mediante a súa actividade exonuclease 5'-3', o cal provoca a separación do quencher do fluorocromo e, por tanto, a emisión de fluorescencia, a cal está relacionada coa cantidade de amplicón producido.[28] Hai que salientar dúas vantaxes primordiais fronte ás sondas inespecíficas, como o bromuro de etidio ou o SYBR GREEN, porque coas sondas taqman a fluorescencia que se produce é específica da amplificación que esteamos a estudar, ademais de permitir que se usen varios fluorocromos na mesma reacción e detectar varios ADN/ARN ao mesmo tempo. A desvantaxe coa que nos encontramos é que hai que deseñar sondas específicas en cada estudo, mentres que coas inespecíficas non se necesitaría deseñar unha nova para cada ensaio, o que, por outro lado, provoca que aumente o número de falsos positivos (diminúe a especificidade).

- As sondas tipo Molecular Beacons (~faros ou balizas moleculares) son tamén oligonucleótidos de cadea simple que, pola súa estrutura, posúen unha zona de apareamento de bases interna e, por tanto, forman unha forquita. En presenza do amplicón a sonda ábrese e únese preferentemente a el, o que produce a emisión de fluorescencia. Estruturalmente, posúen a zona complementaria ao amplicón na zona de curvatura da forquita, a de complementariedade interna na zona do pescozo da forquita e os fluoróforos nos seus extremos: o doador no 5' e o aceptor no 3'. Cando a sonda está pechada en forquita, o fluoróforo do 3' impide a emisión de fluorescencia por parte do propio do 5', cousa que non ocorre ao unirse ao amplicón.[29]
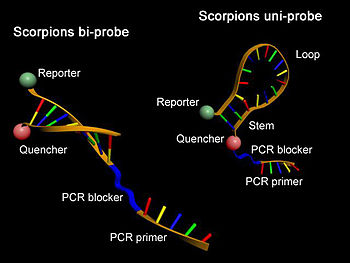
- Sondas Scorpion (escorpión). Trátase de moléculas mixtas que conteñen un cebador específico para o amplicón unido covalentemente a unha forquita similar ás sondas do tipo molecular beacon que, na súa zona de curvatura, posúen un elemento complementario ao amplicón. Os fluoróforos doador e aceptor atópanse na estrutura de forquita; deste modo, cando esta está pechada non se produce a emisión de fluorescencia, o que si ocorre cando ambos se separan debido á presenza do amplicón e á apertura da zona en forquita.[30]
Aplicacións tecnolóxicas
[editar | editar a fonte]Aínda que o uso máis amplamente difundido da Q-PCR consiste na avaliación da expresión xénica de xenes concretos de forma relativa (empregando ARNm da mostra e retrotranscribíndoo a ADNc, que é medido mediante a técnica), desenvolvéronse outras aplicacións fóra do ámbito puramente académico. As aplicacións de impacto na industria inclúen a cuantificación de carga microbiana en alimentos ou en material vexetal, a detección de OMX (organismos modificados xeneticamente) e a cuantificación e xenotipificación de patóxenos virais en humanos.
Diagnósticos
[editar | editar a fonte]A PCR cuantitativa diagnóstica aplícase para detectar rapidamente ácidos nucleicos que serven para diagnosticar doenzas infecciosas,, cancros e anormalidades xenéticas. A introdución de ensaios de PCR cuantitativa nos laboratorios de microbioloxía clínica supuxo unha mellora na diagnose das doenzas infecciosas,[31] e utilízase como ferramenta para detectar novas doenzas emerxentes, como novas cepas de virus da gripe.[32]
Usos microbiolóxicos
[editar | editar a fonte]A PCR cuantitativa utilízana tamén os microbiólogos que traballan no campo da seguridade alimentaria, deterioración dos alimentos e fermentación e para avaliar o risco microbiano na calidade da auga (para beber ou uso recreativo) e na protección da saúde pública.[33]
O ensaio antibacteriano de reconto de colonias virtual[34] utiliza unha técnica de cuantificación de datos chamada Cinética de crecemento cuantitativa (QGK, ou Quantitative Growth Kinetics) que é matematicamente idéntica á Q-PCR, excepto que que son as células bacterianas, en vez das copias de produtos de PCR, as que se incrementan exponencialmente. O equivalente na QGK do ciclo limiar denomínase "tempo limiar".
Usos en investigación
[editar | editar a fonte]Nas instalacións para investigación, a PCR cuantitativa úsase principalmente para facer medicións cuantitativas da transcrición xenética. A tecnoloxía pode utilizarse para determinar como a expresión xenética dun xene particular cambia co tempo, como ocorre na resposta dos cultivos celulares e tecidos á administración dun fármaco, na progresión da diferenciación celular, ou na resposta a cambios nas condicións ambientais. Tamén se utiliza para a determinación da cigosidade dos animais transxénicos usados en investigación.
Detección de fitopatóxenos
[editar | editar a fonte]A produción de propágulos vexetais ou plántulas libres de patóxenos é unha constante na industria agronómica por cuestións económicas e de sanidade. No caso de Phytophthora ramorum, un fungo que causa a morte súbita en carballos e outras especies, desenvolvéronse sistemas baseados en sondas Taqman que poden detectar unha cantidade de 10 a 100 fg de ADN mesturados no ADN da planta hospedadora. A discriminación entre o ADN do patóxeno e o da planta faise amplificando secuencias ITS, que son uns espazadores situados na zona codificante dos xenes de ARN ribosómico, que son característicos para cada taxon.[35] Existen variantes con sondas scorpion, molecular beacon e LAMP para o mesmo patóxeno que, ademais, poden aplicarse no campo.[36]
Detección de OMX
[editar | editar a fonte]A Q-PCR (precedida de retrotranscrición) emprégase na detección de OMXs debido á alta sensibilidade e rango dinámico de detección de ADN; as súas alternativas, como son a análise do ADN ou das proteínas adoitan posuír menos sensibilidade. Para iso empréganse cebadores específicos que amplifiquen non xa o propio transxene, senón o seu promotor, terminador e mesmo as súas secuencias intermedias, empregadas durante o proceso de enxeñaría do vector. Ademais, como o proceso de creación dunha planta transxénica adoita levar á inserción de máis dunha copia do transxene, cómpre avaliar a súa cantidade; para iso, efectúasse unha cuantificación relativa utilizando como xene control un xene, propio da especie tratada, que se encontre en copia única.[37][38]
Cuantificación e xenotipificación en clínica
[editar | editar a fonte]As viroses en humanos poden deberse a infeccións por parte de patóxenos concretos ou a coinfeccións, e este feito non só pode dificultar o diagnóstico mediante as técnicas clásicas, senón que pode causar un distinto prognóstico e a necesidade de usar unha determinada quimioterapia. O uso da Q-PCR posibilita tanto a cuantificación coma a xenotipificación (ou xenotipado, é dicir, a caracterización da cepa, que se fai mediante curvas de fusión) de virus como o HBV (virus da hepatite B).[39] O grao de infección, cuantificado como as copias de xenoma viral por unidade de tecido do paciente, é relevante en moitos casos; por exemplo, a probabilidade de que o virus do herpes simple de tipo 1 se reactive está relacionada co número de neuronas infectadas nos ganglios.[40] Esta cuantificación realízase mediante retrotranscrición ou sen ela, en caso de que os virus se integren no xenoma humano nalgún momento do seu ciclo, como no caso do HPV (virus do papiloma humano), algunha de cuxas variantes está asociada coa aparición de cancro de cérvix.[41]
Notas
[editar | editar a fonte]- ↑ Watson, J, D.; Baker, T. A.; Bell, S. P.; Gann, A.; Levine, M. et Losick, R (2004). Benjamin Cummings - San Francisco, ed. Molecular Biology of the Gene (5ª ed.). ISBN 0-321-22368-3.
- ↑ 2,0 2,1 Michael W. Pfaff, Ales Tichopad, Christian Prgomet and Tanja P. Neuvians (2005). Determination of stable housekeeping genes, differentially regulated target genes and sample integrity: BestKeeper – Excel-based tool using pair-wise correlations Arquivado 13 de setembro de 2019 en Wayback Machine. Biotechonology Letters 26:509-515
- ↑ Vandesompele J, De Preter K, Pattyn F, Poppe B, Van Roy N, De Paepe A, Speleman F (2002) Accurate normalisation of real-time quantitative RT-PCR data by geometric averaging of multiple internal control genes Arquivado 27 de maio de 2020 en Wayback Machine.. Gen. Biol. 3: 1–12.
- ↑ 4,0 4,1 Pfaffl, Michael W.; Horgan, Graham W.; Dempfle, Leo (2002-05-01). "Relative expression software tool (REST) for group-wise comparison and statistical analysis of relative expression results in real-time PCR". Nucleic Acids Research 30 (9): e36. ISSN 1362-4962. PMC 113859. PMID 11972351. doi:10.1093/nar/30.9.e36.
- ↑ The MIQE Guidelines - Minimum Information for Publication of Quantitative Real-Time PCR Experiments. [1]
- ↑ edited by Julie Logan, Kirstin Edwards, and Nick Saunders. (2009). Logan J, Edwards K, Saunders N, ed. Real-Time PCR: Current Technology and Applications. Caister Academic Press. ISBN 978-1-904455-39-4.
- ↑ Rychlik W, Spencer WJ, Rhoads RE (1990). "Optimization of the annealing temperature for DNA amplification in vitro". Nucl Acids Res 18: 6409–6412. PMID 2243783. doi:10.1093/nar/18.21.6409.
- ↑ Joseph Sambrook and David W. Russel (2001). Cold Spring Harbor Laboratory Press, ed. Molecular Cloning: A Laboratory Manual (3rd ed. ed.). Cold Spring Harbor, N.Y. ISBN 0-87969-576-5.
- ↑ Zipper, H. et al. (2004). Investigations on DNA intercalation and surface binding by SYBR Green I, its structure determination and methodological implications. Nucleic Acids Res. 32, e103. PMID 15249599
- ↑ Ponchel, F.; Toomes, C.; Bransfield, K.; Leong, F.T.; Douglas, S.H.; Field, S.L.; Bell, S.M.; Combaret, V.; Puisieux, A.; Mighell, A.J.; Outros (2003). "Real-time PCR based on SYBR-Green I fluorescence: An alternative to the TaqMan assay for a relative quantification of gene rearrangements, gene amplifications and micro gene deletions" (w). BMC Biotechnol 3 (1): 18. doi:10.1186/1472-6750-3-18.
- ↑ Ririe, K.M.; Rasmussen, R.P.; Wittwer, C.T. (1997). "Product Differentiation by Analysis of DNA Melting Curves during the Polymerase Chain Reaction" (PDF). Analytical Biochemistry 245 (2): 154–160. doi:10.1006/abio.1996.9916. Arquivado dende o orixinal (PDF) o 05 de agosto de 2004. Consultado o 11 de abril de 2015.
- ↑ Brunner, Amy M; Yakovlev, Igor A; Strauss, Steven H (2004). "Validating internal controls for quantitative plant gene expression studies". BMC Plant Biology 4 (1): 14. PMC 515301. PMID 15317655. doi:10.1186/1471-2229-4-14.
- ↑ Czechowski, Tomasz; Stitt, Mark; Altmann, Thomas; Udvardi, Michael K.; Scheible, Wolf-Rüdiger (2005-09). "Genome-Wide Identification and Testing of Superior Reference Genes for Transcript Normalization in Arabidopsis". Plant Physiology (en inglés) 139 (1): 5–17. ISSN 0032-0889. PMC 1203353. PMID 16166256. doi:10.1104/pp.105.063743.
- ↑ Thellin O, Zorzi W, Lakaye B, De Borman B, Coumans B, Henne G, Grisar T, Igout A, Heinen E (1999) Housekeeping genes as internal standards: use and limits. J Biotechnol 75: 197–200
- ↑ Radonić, Aleksandar; Thulke, Stefanie; Mackay, Ian M; Landt, Olfert; Siegert, Wolfgang; Nitsche, Andreas (2004-01). "Guideline to reference gene selection for quantitative real-time PCR". Biochemical and Biophysical Research Communications (en inglés) 313 (4): 856–862. doi:10.1016/j.bbrc.2003.11.177.
- ↑ Dheda, Keertan; Huggett, Jim F.; Bustin, Stephen A.; Johnson, Margaret A.; Rook, Graham; Zumla, Alimuddin (2004-07). "Validation of housekeeping genes for normalizing RNA expression in real-time PCR". BioTechniques (en inglés) 37 (1): 112–119. ISSN 0736-6205. doi:10.2144/04371RR03.
- ↑ 17,0 17,1 17,2 Vandesompele J, De Preter K, Pattyn F, Poppe B, Van Roy N, De Paepe A, Speleman F (2002) Accurate normalization of real-time quantitative RT-PCR data by geometric averaging of multiple internal control genes. Genome Biol 37: RESEARCH0034
- ↑ Pfaffl, Michael W.; Tichopad, Ales; Prgomet, Christian; Neuvians, Tanja P. (2004-03). "Determination of stable housekeeping genes, differentially regulated target genes and sample integrity: BestKeeper – Excel-based tool using pair-wise correlations". Biotechnology Letters (en inglés) 26 (6): 509–515. ISSN 0141-5492. doi:10.1023/B:BILE.0000019559.84305.47.
- ↑ Roger Brown, H.; Ni, Hong; Benavides, Gina; Yoon, Lawrence; Hyder, Karim; Giridhar, Jaisri; Gardner, Guy; Tyler, Ronald D.; Morgan, Kevin T. (2002). "Correlation of Simultaneous Differential Gene Expression in the Blood and Heart with Known Mechanisms of Adriamycin-Induced Cardiomyopathy in the Rat" (w). Toxicologic Pathology 30 (4): 435. PMID 12187937. doi:10.1080/01926230290105604.
- ↑ Nicot, Nathalie; Hausman, Jean-Francois; Hoffmann, Lucien; Evers, Daniele (2005). "Housekeeping gene selection for real-time RT-PCR normalization in potato during biotic and abiotic stress". Journal of Experimental Botany 56 (421): 2907–2914. PMID 16188960. doi:10.1093/jxb/eri285.
- ↑ Dheda, K.; Huggett, J.F.; Bustin, S.A.; Johnson, M.A.; Rook, G.; Zumla, A. (2004). "Validation of housekeeping genes for normalizing RNA expression in real-time PCR" (PDF). Biotechniques 37: 112–119.
- ↑ Bustin, S.A. (2000). "Absolute quantification of mRNA using real-time reverse transcription polymerase chain reaction assays" (PDF). Journal of Molecular Endocrinology 25 (2): 169–193. PMID 11013345. doi:10.1677/jme.0.0250169. Arquivado dende o orixinal (PDF) o 06 de xullo de 2010. Consultado o 11 de abril de 2015.
- ↑ Andersen, Claus Lindbjerg; Jensen, Jens Ledet; Orntoft, Torben Falck (2004). "Normalization of Real-Time Quantitative Reverse Transcription-PCR Data: A Model-Based Variance Estimation Approach to Identify Genes Suited for Normalization, Applied to Bladder and Colon Cancer Data Sets" (w). Cancer Research 64 (15): 5245–5250. PMID 15289330. doi:10.1158/0008-5472.CAN-04-0496.
- ↑ Hellemans, J.; Mortier, G.; De Paepe, A.; Speleman, F.; Vandesompele, J. (2007). "qBase relative quantification framework and software for management and automated analysis of real- …". Genome Biol 8 (2): R19. doi:10.1186/gb-2007-8-2-r19. Arquivado dende o orixinal o 19 de abril de 2015. Consultado o 11 de abril de 2015.
- ↑ Förster T. Zwischenmolekulare Energiewanderung und Fluoreszenz, Ann. Physik 1948, 437, 55. doi 10.1002/andp.19484370105
- ↑ Joseph R. Lakowicz, "Principles of Fluorescence Spectroscopy", Plenum Publishing Corporation, 2nd edition (July 1, 1999)
- ↑ "FRET microscopy tutorial from Olympus". Arquivado dende o orixinal o 29 de xuño de 2012. Consultado o 11 de abril de 2015.
- ↑ Heid, C.A.; Stevens, J.; Livak, K.J.; Williams, P.M. (1996). "Real time quantitative PCR" (PDF). Genome Research 6 (10): 986–994. doi:10.1101/gr.6.10.986.
- ↑ Tyagi, S.; Kramer, F.R.; Outros (1996). "Molecular Beacons: Probes that Fluoresce upon Hybridization" (PDF). Nature Biotechnology 14 (3): 303–308. doi:10.1038/nbt0396-303. Arquivado dende o orixinal (PDF) o 07 de setembro de 2006. Consultado o 11 de abril de 2015.
- ↑ Whitcombe, D.; Theaker, J., Guy, S.P., Brown, T., Little, S. (1999). "Detection of PCR products using self-probing amplicons and fluorescence" (PDF). Nature Biotechnology (en inglés) 17: 804–807. doi:10.1038/11751.
- ↑ Sails AD (2009). "Applications in Clinical Microbiology". Real-Time PCR: Current Technology and Applications. Caister Academic Press. ISBN 978-1-904455-39-4.
- ↑ "FDA Authorizes Emergency Use of Influenza Medicines, Diagnostic Test in Response to Swine Flu Outbreak in Humans. FDA News, April 27, 2009.". Arquivado dende o orixinal o 07 de maio de 2009. Consultado o 14 de abril de 2015.
- ↑ Filion, M (editor) (2012). Quantitative Real-time PCR in Applied Microbiology. Caister Academic Press. ISBN 978-1-908230-01-0.
- ↑ Ericksen B, Wu Z, Lu W, Lehrer RI. (2005). "Antibacterial Activity and Specificity of the Six Human α-Defensins". Antimicrob Agents Chemother. 49 (1): 269–75. PMC 538877. PMID 15616305. doi:10.1128/AAC.49.1.269-275.2005.
- ↑ Baldwin, B.G. (1992). "Phylogenetic utility of the internal transcribed spacers of nuclear ribosomal DNA in plants: An example from the Compositaogy". Molecular Phylogenetics and Evolution 1: 3–16. doi:10.1016/1055-7903(92)90030-K.
- ↑ Tomlinson, J. A.;; Barker, I.; Boonham, N. (2007). "Faster, Simpler, More-Specific Methods for Improved Molecular Detection of Phytophthora ramorum in the Field". Applied and Environmental Microbiology 73 (12): 4040–4047. PMID 17449689. doi:10.1128/AEM.00161-07. Arquivado dende o orixinal (w) o 13 de setembro de 2019. Consultado o 11 de abril de 2015.
- ↑ Holst-jensen, A.; Ronning, S.B.; Lovseth, A.; Berdal, K.G. (2003). "PCR technology for screening and quantification of genetically modified organisms (GMOs)" (w). Analytical and Bioanalytical Chemistry 375 (8): 985–993.
- ↑ Brodmann, P.D.; Ilg, E.C.; Berthoud, H.; Herrmann, A. (2002). "… -Time Quantitative Polymerase Chain Reaction Methods for Four Genetically Modified Maize Varieties …". Journal of AOAC International 85 (3): 646–653. doi:10.5555/jaoi.2002.85.3.646.
- ↑ Yeh, S.H.; Tsai, C.Y.; Kao, J.H. ; Liu, C.J.; Kuo, T.J.; Lin, M.W.; Huang, W.L.; Lu, S.F.; Jih, J.; Chen, D.S.; outros (2004). "Quantification and genotyping of hepatitis B virus in a single reaction by real-time PCR and melting …". Journal of Hepatology 41 (4): 659–666. doi:10.1016/j.jhep.2004.06.031.
- ↑ Sawtell, N.M. (1998). "The Probability of in Vivo Reactivation of Herpes Simplex Virus Type 1 Increases with the Number of Latently Infected Neurons in the Ganglia". Journal of Virology 72 (8): 6888–6892. Arquivado dende o orixinal o 12 de outubro de 2008. Consultado o 11 de abril de 2015.
- ↑ Peter, M.; Rosty, C., Couturier, J., Radvanyi, F., Teshima, H., Sastre-garau, X. (2006). "MYC activation associated with the integration of HPV DNA at the MYC locus in genital tumors" (w). Oncogene 25 (44): 5985–5993. doi:10.1038/sj.onc.1209625.
Véxase tamén
[editar | editar a fonte]Bibliografía
[editar | editar a fonte]- Elyse Poitras et Alain Houde (2002). La PCR en temps réel: principes et applications. Reviews in Biology and Biotechnology. 2(2):2-11.
- Bustin SA (2000). Absolute quantification of mRNA using real-time reverse transcription polymerase chain reaction assays. J Mol Endocrinol. 25(2):169-93.
- Higuchi, R., Dollinger, G., Walsh, P.S., Griffith, R. (1992). Simultaneous amplification and detection of specific DNA-sequences. Bio-Technology 10 (4), 413–417.
- Holland, P.M., Abramson, R.D., Watson, R., Gelfand, D.H. (1991). Detection of specific polymerase chain reaction product by utilizing the 50 !30 exonuclease activity of Thermus aquaticus DNA polymerase. Proc. Natl. Acad. Sci. USA 88 (16), 7276–7280.
- Kubista M, Andrade JM, Bengtsson M, Forootan A, Jonak J, Lind K, Sindelka R, Sjoback R, Sjogreen B, Strombom L, Stahlberg A, Zoric N (2006). The real-time polymerase chain reaction. Mol Aspects Med. 27(2-3):95-125.
Ligazóns externas
[editar | editar a fonte]- The Reference in Q-PCR Academic & Industrial Information Platform (en inglés)
- Q-PCR tutorial. University of South Carolina (en inglés)
- Artículos sobre PCR en tempo real (en inglés)

![{\displaystyle E=({\acute {i}}ndice\;do\;logaritmo)^{\frac {-1}{pendente}}={\sqrt[{-pendente}]{{\acute {i}}ndice\;do\;logaritmo}}}](https://wikimedia.org/api/rest_v1/media/math/render/svg/5a2c36dd96f41d48162a8da06f6edf8f9962a2d6)






