Enolase
| Fosfopiruvato hidratase | |||||||||
|---|---|---|---|---|---|---|---|---|---|

| |||||||||
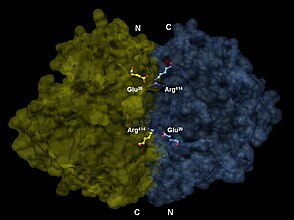
| Dímero de enolase de lévedo.[1] | |||||||||
| Identificadores | |||||||||
| Número EC | 4.2.1.11 | ||||||||
| Número CAS | 9014-08-8 | ||||||||
| Bases de datos | |||||||||
| IntEnz | vista de IntEnz | ||||||||
| BRENDA | entrada de BRENDA | ||||||||
| ExPASy | vista de NiceZyme | ||||||||
| KEGG | entrada de KEGG | ||||||||
| MetaCyc | vía metabólica | ||||||||
| PRIAM | perfil | ||||||||
| Estruturas PDB | RCSB PDB PDBe PDBj PDBsum | ||||||||
| Gene Ontology | AmiGO / EGO | ||||||||
| |||||||||
| Enolase | |||||||||
|---|---|---|---|---|---|---|---|---|---|
 Estrutura de raios X e mecanismo catalítico da enolase de lagosta mariña | |||||||||
| Identificadores | |||||||||
| Símbolo | Enolase_N | ||||||||
| Pfam | PF03952 | ||||||||
| Pfam clan | CL0227 | ||||||||
| InterPro | IPR020811 | ||||||||
| PROSITE | PDOC00148 | ||||||||
| SCOPe | 1els / SUPFAM | ||||||||
| |||||||||
| Enolase | |||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|
 | |||||||||||
| Identificadores | |||||||||||
| Símbolo | Enolase | ||||||||||
| Pfam | PF00113 | ||||||||||
| InterPro | IPR000941 | ||||||||||
| PROSITE | PDOC00148 | ||||||||||
| |||||||||||
A enolase, tamén chamada fosfopiruvato hidratase, é un metaloencima responsable de catalizar a conversión de 2-fosfoglicerato (2-PG) en fosfoenolpiruvato (PEP) e auga, no noveno e penúltimo paso da glicólise. A enolase é un encima da clase das liases, concretamente das hidroliases, que rompen enlaces carbono-oxíxeno. A enolase pode catalizar tamén a reacción inversa, dependendo de cales sexan as concentracións no ambiente dos substratos,[3] polo que intervén tamén na gliconeoxénese. O pH óptimo para este encima é 6,5.[4] A enolase está presente en todos os tecidos e organismos que poden facer a glicólise. O encima foi descuberto por Lohmann e Meyerhof en 1934.[5] Nos humanos a deficiencia de ENO1 está ligada a unha anemia hemolítica hereditaria, mentres que a de ENO3 está ligada a un trastorno de almacenamento de glicóxeno.
Isoencimas
[editar | editar a fonte]Hai tres subunidades que poden conformar os dímeros de enolase, chamadas α, β, e γ, cada unha codificada por un xene distinto, que poden combinarse para formar cinco isoencimas diferentes: αα, αβ, αγ, ββ, e γγ.[3][6] Deles, os tres seguintes (todos eles homodímeros) son os que máis comunmente se encontran nos tecidos humanos adultos:
- αα ou enolase non neuronal (NNE), que se encontra en diversos tecidos, como os do fígado, cerebro, riles, bazo, tecido adiposo. Tamén chamados enolase 1.
- ββ ou enolase específica do músculo (MSE). Tamén chamada enolase 3.
- γγ ou enolase específica de neuronas (NSE). Tamén chamada enolase 2.
Estrutura
[editar | editar a fonte]A enolase ten unha masa molecular de 82.000-100.000 dalton dependendo da isoforma de que se trate.[3][4] Na alfa enolase humana, as dúas subunidades son antiparalelas en canto á súa orientación de modo que o Glu20 dunha subunidade forma un enlace iónico coa Arg414 da outra subunidade.[3] Cada subunidade ten dous dominios distintos. O dominio N-terminal menor consta de tres hélices α e catro láminas β.[3][6] O dominio C-terminal maior empeza con dúas follas beta β seguidas de dúas hélices α e ramata nun barril composto de follas β e hélices α alternantes dispostas de modo que as follas β queden rodeadas de hélices α.[3][6] A estrutura globular compacta do encima orixínase polas significativas interaccións hidrofóbicas entre estes dous dominios.
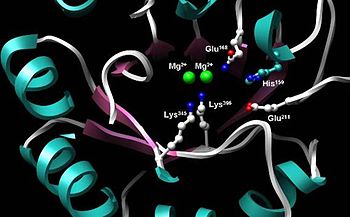
A enolase é un encima moi conservado que ten cinco residuos no sitio activo que son especialmente importantes para a súa actividade, que son: His159, Glu168, Glu211, Lys345, Lys396. Unha enolase mutante que difira nalgún dos residuos Glu168, Glu211, Lys345, ou Lys396 comparada coa enolase de tipo salvaxe, ten un nivel de actividade 105 veces menor.[3] Ademais, os cambios que afectan á His159 fan que o mutante teña só o 0,01% da súa actividade catalítica.[3] Forman parte integral da enolase dous cofactores Mg2+ situados no sitio activo, que serven para estabilizar as cargas negativas no substrato.[3][6]
-
Representación en 3-D dun dímero de enolase en orientación antiparalela. Un Glu20 N-terminal dunha das subunidades do dímero forma un enlace iónico coa Arg414 C-terminal da outra para estabilizar a estrutura cuaternaria do encima.
-
Sitio activo da enolase no medio do barril do dominio C-terminal. Están representados dous cofactores Mg2+ e cinco residuos moi conservados imprescindibles para a súa función catalítica: His159, Glu168, Glu211, Lys345, Lys396.
Mecanismo
[editar | editar a fonte]
Usando sondas isotópicas, o mecanismo global proposto para converter o 2-PG en PEP é unha reacción de eliminación E1cb na que está implicado un intermediato carbanión.[7] O seguinte mecanismo detallado está baseado en estudos da estrutura cristalina e cinética.[3][8][9][10][11][12][13] Cando o substrato 2-fosfoglicerato se une á α-enolase, o seu grupo carboxilo coordínase con dous cofactores ións magnesio no sitio activo. Isto estabiliza a carga negativa no oxíxeno desprotonado á vez que incrementa a acidez do hidróxeno alfa. A Lys345 da enolase desprotona o hidróxeno alfa, e a carga negativa resultante é estabilizada por resonancia co oxíxeno do carboxilato e polos cofactores Mg2+. Despois da creación do intermediato carbanión, o OH de C3 é eliminado como auga coa axuda do Glu211, e fórmase o PEP.
Adicionalmente, no encima teñen lugar cambios conformacionais que axudan á catálise. Na α-enolase humana, o substrato está rotado na súa posición ao unirse ao encima debido ás interaccións cos dous ións magnesio catalíticos, coa Gln167, e Lys396. Os movementos dos bucles Ser36 a His43, Ser158 a Gly162, e Asp255 a Asn256 permiten que a Ser39 se coordine co Mg2+ e bloquee o sitio activo. Ademais de coordinarse cos ións magnesio catalíticos, o pKa do hidróxeno alfa do substrato rebáixase tamén debido á protonación do grupo fosforilo pola acción da His159 e a súa proximidade á Arg374. A Arg374 tamén causa que a Lys345 do sitio activo sexa desprotonada, o cal prepara á lisina Lys345 para que exerza o seu papel no mecanismo.
Uso diagnóstico
[editar | editar a fonte]En experimentos médicos recentes, medíronse as concentracións de enolase para intentar diagnosticar certas condicións e a súa gravidade. Por exemplo, as concentracións máis altas de enolase no líquido cefalorraquídeo están máis fortemente correlacionadas co astrocitoma de grao baixo que as doutros encimas comprobados como a aldolase, piruvato quinase, creatina quinase, e lactato deshidroxenase).[14] O mesmo estudo mostrou que o crecemento tumoral máis rápido se daba en pacientes cos maiores niveis de enolase do líquido cefalorraquídeo. Identificáronse tamén niveis incrementados de enolase en pacientes que sufriron un infarto de miocardio recente ou un accidente cerebrovascular. Inferiuse que os niveis de enolase específica de neuronas do líquido cefalorraquídeo, a enolase específica de neuronas (NSE) do soro sanguíneo, e a creatina quinase (tipo BB) son indicativos para facer o prognóstico de vítimas de parada cardíaca.[15] Outros estudos enfocáronse cara ao valor prognóstico dos valores de NSE en vítimas de accidentes cerebrovasculares.[16]
Os autoanticorpos contra a alfa-enolase están asociados coa rara síndrome chamada encefalopatía de Hashimoto.[17]
Inhibidores da enolase
[editar | editar a fonte]Sintetizáronse pequenas moléculas inhibidoras da enolase para usalas como sondas químicas do mecanismo catalítico do encima. A máis potente delas é o fosfonoacetohidroxamato, que na súa forma non protonada ten afinidade polo encima. Ten unha semellanza estrutural co presunto intermediato catalítico que se forma entre o PEP e o 2-PG. Fixéronse intentos de usar este inhibidor como un fármaco anti-tripanosoma, e máis recentemente, como un axente anticancro, especificamente nos glioblastomas que son deficientes en enolase debido á deleción homocigótica do xene ENO1 como parte do locus 1p36.
O fluoruro é un competidor coñecido do substrato da enolase 2-PG. O fluoruro forma parte dun complexo co magnesio e o fosfato, que se une ao sitio activo en lugar do 2-PG.[4] Beber auga fluorada proporciona un nivel de fluoruro que inhibe a actividade da enolase das bacterias da boca sen causar dano aos humanos. A interrupción da vía glicolítica das bacterias é unha prevención da carie.[18][19]
Notas
[editar | editar a fonte]- ↑ PDB 2ONE; Zhang E, Brewer JM, Minor W, Carreira LA, Lebioda L (1997). "Mechanism of enolase: the crystal structure of asymmetric dimer enolase-2-phospho-D-glycerate/enolase-phosphoenolpyruvate at 2.0 A resolution". Biochemistry 36 (41): 12526–34. PMID 9376357. doi:10.1021/bi9712450.
- ↑ Vollmar M, Krysztofinska E, Chaikuad A, Krojer T, Cocking R, Vondelft F, Bountra C, Arrowsmith CH, Weigelt J, Edwards A, Yue WW, Oppermann U (2010). "Crystal Structure of Human Beta Enolase Enob". To be published. doi:10.2210/pdb2xsx/pdb.
- ↑ 3,00 3,01 3,02 3,03 3,04 3,05 3,06 3,07 3,08 3,09 Pancholi V (2001). "Multifunctional α-enolase: its role in diseases". Cell Mol Life Sci. 58 (7): 902–20. PMID 11497239. doi:10.1007/PL00000910.
- ↑ 4,0 4,1 4,2 Hoorn RK, Flickweert JP, Staal GE (1974). "Purification and properties of enolase of human erythroctyes". Int J Biochem 5 (11–12): 845–52. doi:10.1016/0020-711X(74)90119-0.
- ↑ Lohman K & Meyerhof O (1934) Über die enzymatische umwandlung von phosphoglyzerinsäure in brenztraubensäure und phosphorsäure (Enzymatic transformation of phosphoglyceric acid into pyruvic and phosphoric acid). Biochem Z 273, 60–72.
- ↑ 6,0 6,1 6,2 6,3 Peshavaria M, Day IN (1991). "Molecular structure of the human muscle-specific enolase gene (ENO3)". Biochem J. 275 (Pt 2): 427–33. PMC 1150071. PMID 1840492.
- ↑ Dinovo EC, Boyer PD (1971). "Isotopic probes of the enolase reaction mechanism". J Biol Chem 240: 4586–93.
- ↑ Poyner RR, Laughlin LT, Sowa GA, Reed GH (1996). "Toward identification of acid/base catalysts in the active site of enolase: comparison of the properties of K345A, E168Q, and E211Q variants". Biochemistry 35 (5): 1692–9. PMID 8634301. doi:10.1021/bi952186y.
- ↑ Reed GH, Poyner RR, Larsen TM, Wedekind JE, Rayment I (1996). "Structural and mechanistic studies of enolase". Current Opinion in Structural Biology 6 (6): 736–43. PMID 8994873. doi:10.1016/S0959-440X(96)80002-9.
- ↑ Wedekind JE, Reed GH, Rayment I (1995). "Octahedral coordination at the high-affinity metal site in enolase: crystallographic analysis of the MgII—enzyme complex from yeast at 1.9 Å resolution". Biochemistry 34 (13): 4325–30. PMID 7703246. doi:10.1021/bi00013a022.
- ↑ Wedekind JE, Poyner RR, Reed GH, Rayment I (1994). "Chelation of serine 39 to Mg2+ latches a gate at the active site of enolase: structure of the bis(Mg2+) complex of yeast enolase and the intermediate analog phosphonoacetohydroxamate at 2.1-Å resolution". Biochemistry 33 (31): 9333–42. PMID 8049235. doi:10.1021/bi00197a038.
- ↑ Larsen TM, Wedekind JE, Rayment I, Reed GH (1996). "A carboxylate oxygen of the substrate bridges the magnesium ions at the active site of enolase: structure of the yeast enzyme complexed with the equilibrium mixture of 2-phosphoglycerate and phosphoenolpyruvate at 1.8 Å resolution". Biochemistry 35 (14): 4349–58. PMID 8605183. doi:10.1021/bi952859c.
- ↑ Duquerroy S, Camus C, Janin J (1995). "X-ray structure and catalytic mechanism of lobster enolase". Biochemistry 34 (39): 12513–23. PMID 7547999. doi:10.1021/bi00039a005.
- ↑ Royds JA, Timperley WR, Taylor CB (1981). "Levels of enolase and other enzymes in the cerebrospinal fluid as indices of pathological change". J Neurol Neurosurg Psychiatr. 44 (12): 1129–35. PMC 491233. PMID 7334408. doi:10.1136/jnnp.44.12.1129.
- ↑ Roine RO, Somer H, Kaste M, Viinikka L, Karonen SL (1989). "Neurological outcome after out-of-hospital cardiac arrest. Prediction by cerebrospinal fluid enzyme analysis". Arch Neurol. 46 (7): 753–6. PMID 2742544.
- ↑ Hay E, Royds JA, Davies-Jones GA, Lewtas NA, Timperley WR, Taylor CB (1984). "Cerebrospinal fluid enolase in stroke". J Neurol Neurosurg Psychiatr. 47 (7): 724–9. PMC 1027902. PMID 6747647. doi:10.1136/jnnp.47.7.724.
- ↑ Fujii A, Yoneda M, Ito T, Yamamura O, Satomi S, Higa H, Kimura A, Suzuki M, Yamashita M, Yuasa T, Suzuki H, Kuriyama M (2005). "Autoantibodies against the amino terminal of alpha-enolase are a useful diagnostic marker of Hashimoto's encephalopathy". J. Neuroimmunol. 162 (1–2): 130–6. PMID 15833368. doi:10.1016/j.jneuroim.2005.02.004.
- ↑ Centers for Disease Control and Prevention (CDC) (2002). "Populations receiving optimally fluoridated public drinking water—United States, 2000". MMWR Morb Mortal Wkly Rep. 51 (7): 144–7. PMID 11905481.
- ↑ Hüther FJ, Psarros N, Duschner H (1 April 1990). "Isolation, characterization, and inhibition kinetics of enolase from Streptococcus rattus FA-1". Infect Immun. 58 (4): 1043–7. PMC 258580. PMID 2318530. Arquivado dende o orixinal o 28 de maio de 2020. Consultado o 16 de decembro de 2013.
Véxase tamén
[editar | editar a fonte]Ligazóns externas
[editar | editar a fonte]- MeshName Enolase