Nucleosoma
Os nucleosomas son as unidades básicas por medio das que se realiza a compactación do ADN nos eucariotas. Constan dun segmento de ADN enrolado arredor dun núcleo de proteínas histonas.[1] Esta estrutura é a miúdo comparada a un fío enrolado nun carrete.[2]
Os nucleosomas forman as unidades repetidas básicas da cromatina eucariótica,[3] que se usan para empaquetar os grandes xenomas eucarióticos no núcleo permitindo ao mesmo tempo un adecuado acceso a el (en células de mamíferos debe empaquetarse aproximadamente unha lonxitude de 2 m de ADN dentro dun núcleo duns 10 µm de diámetro). A cadea de nucleosomas pode pregarse formando unha serie de estruturas de orde progresivamente superior, ata orixinar finalmente os cromosomas; isto compacta o ADN e á vez crea un novo nivel de control regulatorio que asegura a correcta expresión dos xenes. Pénsase que os nucleosomas levan información epixenética herdada en forma de modificacións covalentes no seu núcleo de histonas. Don e Ada Olins [4] e Roger D. Kornberg.[5][6] propuxeron en 1974 a hipótese do nucleosoma para explicar isto.
O núcleo do nucleosoma consta de aproximadamente 147[7] pares de bases de ADN enrolado á esquerda dando 1,67 voltas superhelicoidais arredor do octámero de histonas formado por dúas copias de cada unha das catro histonas: H2A, H2B, H3, e H4.[8] As partículas do núcleo (core) do nucleosoma están conectadas por tramos de "ADN espazador", que pode ter uns 80 pares de bases de longo. Tecnicamente, o nucleosoma defínese como dito núcleo máis unha desas rexións espazadoras de ADN; aínda que a palabra se usa con frecuencia como sinónimo do núcleo ou core.[9]
As histonas de unión (linker) como a H1 e as súas isoformas están implicadas na compactación da cromatina e sitúanse na base do nucleosoma preto dos puntos de entrada e saída do ADN e unidas ás rexións espazadoras do ADN.[10] Os nucleosomas non condensados sen as histonas de unión (H1) semellan vistos ao microscopio electrónico as "doas dun colar de ADN".[11]
A diferenza da maioría das células eucarióticas, as células espermáticas maduras usan en gran medida protaminas para compactar o seu ADN xenómico, moi probablemente para acadar un grao de compactación aínda maior.[12] Nas arqueas atopáronse tamén equivalentes das histonas e unha estrutura da cromatina simplificada,[13] o que proba que os eucariotas non son os únicos organismos que posúen nucleosomas.
Estrutura[editar | editar a fonte]
Estrutura do núcleo (core) do nucleosoma[editar | editar a fonte]

Visión de conxunto[editar | editar a fonte]
Os primeiros estudos estruturais xa forneceron probas de que o ADN rodeaba un octámero de histonas dando case dúas voltas nunha superhélice levoxira. En 1997 O grupo de Richmond resolveu a primeira estrutura cristalina do nucleosoma con resolución case atómica, na que se mostraban algúns dos principais detalles desta partícula. Hai que sinalar, porén, que o o ADN palindrómico alfa-satélite humano, fundamental para conseguir a estrutura cristalina do nucleosoma de 1997, obtívose en realidade polo grupo de Bunick no Laboratorio nacional de Oak Ridge, en Oak Ridge, Tennessee.[14][15] O grupo de investigación de Bunick foi pioneiro no desenvolvemento do ADN palindrómico alfa-satélite humano e isto foi un avance esencial para poder determinar a estrutura do núcleo do nucleosoma con alta resolución.[16][17][18]
Ata agora foron resoltas as estruturas duns 20 núcleos de nucleosomas distintos,[19] incluíndo aqueles que contiñan variantes das histonas normais e histonas de diferentes especies. A estrutura do núcleo ou core do nucleosoma está extraordinariamente conservada na evolución, e medidas comparativas de nucleosomas de especies tan diferentes como o sapo Xenopus e o lévedo Saccharomyces mostran unha desviación estatística mínima.[20]
O núcleo ou core do nucleosoma[editar | editar a fonte]
A partícula nuclear do nucleosoma (mostrada na figura) consta dunhas 146[7] pares de bases de ADN enrolado dando 1,67 voltas de superhélice levoxira arredor do octámero de histonas, e consta de dúas copias de cada unha das catro histonas core H2A, H2B, H3, e H4. Os nucleosomas contiguos están unidos por un tramo de ADN libre chamado ADN espazador ou linker DNA (que varía en lonxitude de 10 - 80 pares de bases dependendo da especie e tipo de tecido[13]).
Interaccións proteicas no nucleosoma[editar | editar a fonte]
As proteínas histonas do octámero conteñen un motivo estrutural característico denominado "pregamento de histona" que consiste en tres alfa-hélices (α1-3) separadas por dous bucles (L1-2). En disolución as histonas forman heterodímeros H2A-H2B e heterotetrámeros H3-H4. As histonas dimerízanse polas súas longas hélices α2 con orientación antiparalela, e no caso das H3 e H4, dous destes dímeros forman un grupo de 4 hélices estabilizado por unha intensa interacción H3-H3. O dímero H2A/H2B únese ao tetrámero H3/H4 debido a interaccións entre H4 e H2B, as cales inclúen a formación dun agrupamento hidrofóbico.[8] O octámero de histonas está formado por un tetrámero central H3/H4 que queda en medio de dous dímeros H2A/H2B. Debido á forte carga básica (positiva) dos catro tipos de histonas do octámero, o octámero é só estable en presenza do ADN ou en concentracións salinas moi altas.
Interaccións histona-ADN[editar | editar a fonte]
No nucleosoma establécense unhas 120 interaccións directas proteína-ADN e varios centos de interaccións indirectas mediadas pola auga.[21] As interaccións directas proteína-ADN non se producen regularmente por toda a superficie do octámero senón que máis ben están localizadas en sitios concretos. Isto débese á formación de dous tipos sitios de unión do ADN no octámero; o sitio α1α1 que usa a forma de hélice α1 de dúas histonas adxacentes e o sitio L1L2 formado polos bucles L1 e L2. As principais interaccións co ADN son enlaces salinos (electrostáticos) e enlaces de hidróxeno entre os grupos básicos e hidroxilo das cadeas laterais dos aminoácidos ou os grupos amida da cadea proteínica, e os fosfatos do ADN. Isto é importante dado que a ubicua distribución dos nucleosomas nos xenomas require que o factor de unión ao ADN non sexa específico da secuencia. Aínda que os nucleosomas tenden a preferir algunhas secuencias do ADN máis ca outras,[22] poden unirse a practicamente calquera secuencia, o que se pensa que se debe á flexibilidade na formación desas interaccións mediadas por moléculas de auga. Ademais, establécense interaccións non polares entre cadeas laterais das proteínas e os grupos desoxirribosa, e unha cadea lateral de arxinina intercálase no suco menor do ADN en todos os 14 puntos en que este queda fronte á superficie do octámero. A distribución e a forza dos sitios de unión do ADN sobre a superficie do octámero distorsiona o ADN situado sobre o núcleo do nucleosoma. O ADN non está uniformemente dobrado e contén defectos de torsión. A torsión da forma B do ADN libre en disolución é de 10,5 pares de bases por volta, pero a torsión total do ADN do nucleosoma é de só 10,2 pares de bases por volta, variando desde un valor de 9.4 a 10.9 pares de bases por volta.
Dominios da cola das histonas[editar | editar a fonte]
As extensión con forma de cola das histonas supoñen o 30% da masa das histonas, pero non son visibles nas estruturas cristalinas do nucleosoma debido á súa grande flexibilidade, e crese que están moi desestructuradas.[23] As colas N-terminais das histonas H3 e H2B pasan a través dunha canle formada polos sucos menores das dúas cadeas do ADN, sobresaíndo do ADN cada 20 pares de bases. Por outra parte, a cola N-terminal da histona H4 ten unha rexión de aminoácidos moi básicos (16-25), a cal, na estrutura cristalina, establece unha interacción coa rexión superficial fortemente acídica do dímero H2A-H2B doutro nucleosoma, o que é potencialmente relevante para establecer estruturas de orde superior nos nucleosomas. Esta interacción pénsase que acontece tamén en condicións fisiolóxicas e suxire que a acetilación da cola da H4 distorsiona as estruturas de orde superior da cromatina.
Estruturas de orde superior[editar | editar a fonte]

O grao de organización do ADN ao que se chega nos nucleosomas non explica totalmente a compactación do ADN observada no núcleo. Cómpre que exista unha compactación da cromatina de grao superior, pero non se comprende totalmente. Os coñecementos actuais[19] son que a sucesión de nucleosomas co seu ADN espazador forman a fibra de 10 nm da cromatina, coñecida descritivamente como o "colar de doas", que ten unha razón de compactación de aproximadamente 5 a 10.[13] A cadea de nucleosomas pode dispoñerse formando a fibra de 30 nm, unha estrutura máis compacta cunha razón de compactación de ~50[13], cuxa formación depende da presenza da histona H1.
Presentouse unha estrutura cristalina de tetranucleosoma que se usou para elaborar e propoñer unha estrutura en 2-start hélice da fibra de 30 nm.[24] Pero hai aínda bastantes reservas sobre este modelo, xa que é incompatible con datos recentes obtidos con microscopía electrónica.[25] Á parte disto, a estrutura da cromatina non se comprende ben, pero a suxestión clásica é que a fibra de 30 nm se dispón formando bucles ao longo dun armazón proteico central para formar a eucromatina transcricionalmemnte activa. Unha maior compactación orixinaría a heterocromatina transcricionalmente inactiva.
Dinámica dos nucleosomas[editar | editar a fonte]
Aínda que o nucleosoma é un complexo proteína-ADN moi estable, non é estático e demostrouse que sofre un certo número de cambios estruturais, incluíndo o reposicionamento do nucleosoma e cambios no sitio de exposición de ADN. Dependendo da situación, os nucleosomas poden inhibir ou facilitar a unión de factores de transcrición. As posicións dos nucleosomas están controladas por tres factores principais: Primeiro, a afinidade intrínseca de unión do octámero de histonas depende da secuencia de ADN. Segundo, o nucleosoma pode ser desprazado ou recrutado pola unión competitiva ou cooperativa doutros factores proteicos. Terceiro, o nucleosoma pode ser translocado activamente por complexos remodeladores dependentes do ATP.[26] [27] [28]
Modulación da estrutura do nucleosoma[editar | editar a fonte]
Os xenomas eucarióticos están sempre asociados á cromatina; non obstante, as células necesitan regular tanto espacial coma temporalmente loci específicos dentro da gran masa de cromatina. Para conseguir o alto grao de control requirido para coordinar procesos nucleares tales como a replicación do ADN, a súa reparación e a transcrición, as células desenvolveron varios xeitos de modular a estrutura e función da cromatina de forma local e específica. Isto pode implicar modificacións covalentes das histonas, incorporación de variantes das histonas normais, e a remodelación non covalente feita por encimas remodeladores dependentes do ATP.[13][29][30][31][32][33]
Ensamblaxe dos nucleosomas in vitro[editar | editar a fonte]
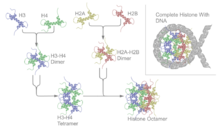
Os nucleosomas poden ensamblarse in vitro tanto usando histonas nativas purificadas coma histonas recombinantes.[34][35] Unha técnica estándar para enrolar o ADN arredor das histonas require o uso da diálise de sales. Nesta técnica incúbanse xuntos octámeros de histonas e un molde ADN espido a unha concentración salina 2 M. Reducindo a modo a concentración salina, o ADN equilíbrase nunha posición na que se enrola arredor dos octámeros de histonas, formando os nucleosomas. En condicións apropiadas, este proceso de reconstitución permite mapear experimentalmente a afinidade do nucleosoma por posicionarse nunha determinada secuencia.[36]
Notas[editar | editar a fonte]
- ↑ Reece, Jane; Campbell, Neil (2002). Biology. San Francisco: Benjamin Cummings. ISBN 0-8053-6624-5.
- ↑ Backstage with a command performer Arquivado 20 de xullo de 2011 en Wayback Machine. News Release, Rockefeller University, Feb. 18, 2003
- ↑ Alberts, Bruce (2002). Molecular biology of the cell (4th ed.). New York: Garland Science. p. 207. ISBN 0-8153-4072-9.
- ↑ Olins AL, Olins DE (1974). "Spheroid chromatin units (v bodies)". Science 183 (4122): 330–2. PMID 4128918. doi:10.1126/science.183.4122.330.
- ↑ McDonald D, "Milestone 9, (1973-1974) The nucleosome hypothesis: An alternative string theory", Nature Milestones: Gene Expression. (2005) Dec 1; http://www.nature.com/milestones/geneexpression/milestones/articles/milegene09.html
- ↑ Kornberg RD (1974). "Chromatin structure: a repeating unit of histones and DNA". Science 184 (139): 868–71. PMID 4825889. doi:10.1126/science.184.4139.868.
- ↑ 7,0 7,1 En diferentes cristais observáronse valores de 146 e 147 pares de bases.
- ↑ 8,0 8,1 Luger K, Mäder AW, Richmond RK, Sargent DF, Richmond TJ (1997). "Crystal structure of the nucleosome core particle at 2.8 A resolution". Nature 389 (6648): 251–60. PMID 9305837. doi:10.1038/38444.
- ↑ Alberts, Bruce (2007). Molecular biology of the cell (5th ed.). New York: Garland Science. p. 211. ISBN 978-0-8153-4106-2.
- ↑ Zhou YB, Gerchman SE, Ramakrishnan V, Travers A, Muyldermans S (1998). "Position and orientation of the globular domain of linker histone H5 on the nucleosome". Nature 395 (6700): 402–5. PMID 9759733. doi:10.1038/26521.
- ↑ Thoma F, Koller T, Klug A (1979). "Involvement of histone H1 in the organization of the nucleosome and of the salt-dependent superstructures of chromatin". J. Cell Biol. 83 (2 Pt 1): 403–27. PMC 2111545. PMID 387806. doi:10.1083/jcb.83.2.403.
- ↑ Clarke HJ (1992). "Nuclear and chromatin composition of mammalian gametes and early embryos". Biochem. Cell Biol. 70 (10-11): 856–66. PMID 1297351. doi:10.1139/o92-134.
- ↑ 13,0 13,1 13,2 13,3 13,4 Felsenfeld G, Groudine M (2003). "Controlling the double helix". Nature 421 (6921): 448–53. PMID 12540921. doi:10.1038/nature01411.
- ↑ Electrophoresis. 1995 Oct;16(10):1861-4. Preparative separation of nucleosome core particles containing defined-sequence DNA in multiple translational phases. Harp JM, Palmer EL, York MH, Gewiess A, Davis M, Bunick GJ.
- ↑ Large-scale production of palindrome DNA fragments. Palmer EL, Gewiess A, Harp JM, York MH, Bunick GJ. Anal Biochem. 1995 Oct 10;231(1):109-14.
- ↑ Acta Crystallogr D Biol Crystallogr. 1996 Mar 1;52(Pt 2):283-8. X-ray diffraction analysis of crystals containing twofold symmetric nucleosome core particles. Harp JM, Uberbacher EC, Roberson AE, Palmer EL, Gewiess A, Bunick GJ.
- ↑ Acta Crystallogr D Biol Crystallogr. 2000 Dec;56(Pt 12):1513-34. Asymmetries in the nucleosome core particle at 2.5 A resolution. Harp JM, Hanson BL, Timm DE, Bunick GJ.
- ↑ Methods Enzymol. 2004;375:44-62. Preparation and crystallization of nucleosome core particle. Hanson BL, Alexander C, Harp JM, Bunick GJ.
- ↑ 19,0 19,1 Chakravarthy S, Park YJ, Chodaparambil J, Edayathumangalam RS, Luger K (2005). "Structure and dynamic properties of nucleosome core particles". FEBS Lett. 579 (4): 895–8. PMID 15680970. doi:10.1016/j.febslet.2004.11.030.
- ↑ White CL, Suto RK, Luger K (2001). "Structure of the yeast nucleosome core particle reveals fundamental changes in internucleosome interactions". EMBO J. 20 (18): 5207–18. PMC 125637. PMID 11566884. doi:10.1093/emboj/20.18.5207.
- ↑ Davey CA, Sargent DF, Luger K, Maeder AW, Richmond TJ (2002). "Solvent mediated interactions in the structure of the nucleosome core particle at 1.9 a resolution". J. Mol. Biol. 319 (5): 1097–113. PMID 12079350. doi:10.1016/S0022-2836(02)00386-8.
- ↑ Segal E, Fondufe-Mittendorf Y, Chen L; et al. (2006). "A genomic code for nucleosome positioning". Nature 442 (7104): 772–8. PMC 2623244. PMID 16862119. doi:10.1038/nature04979.
- ↑ Zheng C, Hayes JJ (2003). "Structures and interactions of the core histone tail domains". Biopolymers 68 (4): 539–46. PMID 12666178. doi:10.1002/bip.10303.
- ↑ Schalch T, Duda S, Sargent DF, Richmond TJ (2005). "X-ray structure of a tetranucleosome and its implications for the chromatin fibre". Nature 436 (7047): 138–41. PMID 16001076. doi:10.1038/nature03686.
- ↑ Robinson PJ, Fairall L, Huynh VA, Rhodes D (2006). "EM measurements define the dimensions of the "30-nm" chromatin fiber: evidence for a compact, interdigitated structure". Proc. Natl. Acad. Sci. U.S.A. 103 (17): 6506–11. PMC 1436021. PMID 16617109. doi:10.1073/pnas.0601212103.
- ↑ Teif VB, Rippe K (2009). "Predicting nucleosome positions on the DNA: combining intrinsic sequence preferences and remodeler activities". Nucleic Acids Res 37 (17): 5641–5655. PMC 2761276. PMID 19625488. doi:10.1093/nar/gkp610.
- ↑ Pennings S, Muyldermans S, Meersseman G, Wyns L (1989). "Formation, stability and core histone positioning of nucleosomes reassembled on bent and other nucleosome-derived DNA". J. Mol. Biol. 207 (1): 183–92. PMID 2738923. doi:10.1016/0022-2836(89)90449-X.
- ↑ Li G, Levitus M, Bustamante C, Widom J (2005). "Rapid spontaneous accessibility of nucleosomal DNA". Nat. Struct. Mol. Biol. 12 (1): 46–53. PMID 15580276. doi:10.1038/nsmb869.
- ↑ Allfrey VG, Faulkner R, Mirsky AE (1964). "Acetylation and methylation of histones and their possible role in the regulation of RNA synthesis". Proc. Natl. Acad. Sci. U.S.A. 51: 786–94. PMC 300163. PMID 14172992. doi:10.1073/pnas.51.5.786.
- ↑ Strahl BD, Allis CD (2000). "The language of covalent histone modifications". Nature 403 (6765): 41–5. PMID 10638745. doi:10.1038/47412.
- ↑ Cosgrove MS, Boeke JD, Wolberger C (2004). "Regulated nucleosome mobility and the histone code". Nat. Struct. Mol. Biol. 11 (11): 1037–43. PMID 15523479. doi:10.1038/nsmb851.
- ↑ Ye J, Ai X, Eugeni EE; et al. (2005). "Histone H4 lysine 91 acetylation a core domain modification associated with chromatin assembly". Mol. Cell 18 (1): 123–30. PMC 2855496. PMID 15808514. doi:10.1016/j.molcel.2005.02.031.
- ↑ Whitehouse I, Flaus A, Cairns BR, White MF, Workman JL, Owen-Hughes T (1999). "Nucleosome mobilization catalysed by the yeast SWI/SNF complex". Nature 400 (6746): 784–7. PMID 10466730. doi:10.1038/23506.
- ↑ Hayes JJ, Lee KM (1997). "In vitro reconstitution and analysis of mononucleosomes containing defined DNAs and proteins". Methods 12 (1): 2–9. PMID 9169189. doi:10.1006/meth.1997.0441.
- ↑ Dyer PN, Edayathumangalam RS, White CL; et al. (2004). "Reconstitution of nucleosome core particles from recombinant histones and DNA". Meth. Enzymol. 375: 23–44. PMID 14870657.
- ↑ Yenidunya A, Davey C, Clark D, Felsenfeld G, Allan J (1994). "Nucleosome positioning on chicken and human globin gene promoters in vitro. Novel mapping techniques". J. Mol. Biol. 237 (4): 401–14. PMID 8151701. doi:10.1006/jmbi.1994.1243.
Véxase tamén[editar | editar a fonte]
Outros artigos[editar | editar a fonte]
Ligazóns externas[editar | editar a fonte]
- Nucleosomes on the group page of Timothy Richmond
- Nucleosome at the PDB
- Dynamic Remodeling of Individual Nucleosomes Across a Eukaryotic Genome in Response to Transcriptional Perturbation
- Nucleosome positioning data and tools online (annotated list, constantly updated) Arquivado 10 de febreiro de 2015 en Wayback Machine.
