Isocitrato deshidroxenase
| Isocitrato deshidroxenase | |||||||||
|---|---|---|---|---|---|---|---|---|---|

| |||||||||
| Estrutura cristalográfica da isocitrato deshidroxenase de Escherichia coli.[1] Hai tres sitios activos. Un isocitrato está no sitio de unión para o NADP+. | |||||||||
| Identificadores | |||||||||
| Número EC | 1.1.1.42 | ||||||||
| Número CAS | 9028-48-2 | ||||||||
| Bases de datos | |||||||||
| IntEnz | vista de IntEnz | ||||||||
| BRENDA | entrada de BRENDA | ||||||||
| ExPASy | vista de NiceZyme | ||||||||
| KEGG | entrada de KEGG | ||||||||
| MetaCyc | vía metabólica | ||||||||
| PRIAM | perfil | ||||||||
| Estruturas PDB | RCSB PDB PDBe PDBj PDBsum | ||||||||
| Gene Ontology | AmiGO / EGO | ||||||||
| |||||||||
| isocitrato deshidroxenase (NAD+) | |||||||||
|---|---|---|---|---|---|---|---|---|---|
| Identificadores | |||||||||
| Número EC | 1.1.1.41 | ||||||||
| Número CAS | 9001-58-5 | ||||||||
| Bases de datos | |||||||||
| IntEnz | vista de IntEnz | ||||||||
| BRENDA | entrada de BRENDA | ||||||||
| ExPASy | vista de NiceZyme | ||||||||
| KEGG | entrada de KEGG | ||||||||
| MetaCyc | vía metabólica | ||||||||
| PRIAM | perfil | ||||||||
| Estruturas PDB | RCSB PDB PDBe PDBj PDBsum | ||||||||
| Gene Ontology | AmiGO / EGO | ||||||||
| |||||||||
| Isocitrato deshidroxenase | |||||||||
|---|---|---|---|---|---|---|---|---|---|
 Estrutura cristalina da isocitrato deshidroxenase en complexo con isocitrato e Mn | |||||||||
| Identificadores | |||||||||
| Símbolo | IDH | ||||||||
| Pfam | PF03971 | ||||||||
| Pfam clan | CL0270 | ||||||||
| InterPro | IPR004436 | ||||||||
| SCOPe | 1ofg / SUPFAM | ||||||||
| |||||||||
A isocitrato deshidroxenase (IDH) (número EC: 1.1.1.42 e 1.1.1.41) é un encima que cataliza a descarboxilación oxidativa do isocitrato, producindo α-cetoglutarato e CO2, que é unha reacción do ciclo do ácido cítrico ou de Krebs. O proceso opera en dous pasos, nos que se produce a oxidación do isocitrato (cun grupo alcohol secundario) a oxalosuccinato (cun grupo cetona), seguida da descarboxilación do grupo carboxilo beta a cetona, formando alfa-cetoglutarato e CO2. Nos humanos, existen tres isoformas da IDH: IDH1, IDH2 e IDH3. A IDH3 cataliza o terceiro paso do ciclo do ácido cítrico á vez que converte o NAD+ en NADH e encóntrase só na mitocondria. As isoformas IDH1 e IDH2 catalizan a mesma reacción pero fóra do ciclo do ácido cítrico e utilizan o NADP+ como cofactor en lugar do NAD+, e están localizadas no citosol, mitocondrias e peroxisomas.[2]
Isoencimas[editar | editar a fonte]
Os isoencimas da isocitrato deshidroxenase humana son os seguintes:
IDH dependentes do NADP+[editar | editar a fonte]
Estes isoencimas dependentes do NADP+ funcionan como homodímeros:
|
| ||||||||||||||||||||||||||||||||||||||||||||
IDH dependentes do NAD+[editar | editar a fonte]
O isoencima IDH3 é un heterotetrámero que está composto por dúas subunidades alfa, unha beta, e unha gamma:
|
|
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
Estrutura[editar | editar a fonte]

A NAD-IDH está composta por 3 subuniddes, está regulada alostericamente, e require a integración dun ión Mg2+ ou Mn2+. O homólogo máis similar do que se coñece a estrutura é a IDH NADP-dependente de Escherichia coli, que ten só dúas subunidades e un 13% de identidade e un 29% de semellanza baseándose nas secuencias de aminoácidos, o que a fai bastante diferente á IDH humana. Todas as NADP-IDHs son homodímeros.
Aínda que a maioría das IDH son homodímeros (formados por dúas subunidades idénticas), nalgunhas especies son monómeros. Comparando as IDH de C. glutamicum e E. coli,[4] que son monómero e dímero, respectivamente, ambos os encimas catalizan eficazmente idénticas reaccións. Porén, a de C. glutamicum ten unha actividade dez veces maior que a de E. coli e sete veces máis afinidade/especificidade polo NADP. C. glutamicum favorece o uso de NADP+ sobre o de NAD+. En termos de estabilidade en resposta á temperatura, ambos os encimas mostraron ter unha similar Tm ou temperatura de fusión entre os 55 °C e os 60 °C. Porén, o monómero de C. glutamicum mostrou unha estabilidade máis consistente a temperaturas maiores. O dímero de E. coli mostrou estabilidade a temperaturas máis altas do normal debido ás interaccións entre as súas dúas subunidades.
Regulación[editar | editar a fonte]
A reacción do ciclo do ácido cítrico na que intervén a IDH, debido ao seu grande cambio de enerxía libre negativo, é unha das reaccións irreversibles do ciclo do ácido cítrico, e, por tanto, debe estar coidadosamente regulada para evitar un gasto innecesario de isocitrato (coa conseguinte acumulación de alfa-cetoglutarato). O ADP é estimulador da reacción. A IDH de E. coli está regulada por fosforilación e desfosforilación do encima realizado por un encima bifuncional quinase/fosfatase.[5]
Mecanismos catalíticos[editar | editar a fonte]
A isocitrato deshidroxenase cataliza as seguintes reaccións:
- Isocitrato + NAD+ 2-cetoglutarato + CO2 + NADH + H+
- Isocitrato + NADP+ 2-cetoglutarato + CO2 + NADPH + H+
- Isocitrato + NADP+ Mg2+(ión metálico) alfa-cetoglutarato + NADPH + H+ + CO2[6][7][8]

Pasos[editar | editar a fonte]
No ciclo do ácido cítrico, o isocitrato, producido a partir da isomerización do citrato, sofre unha oxidación e unha descarboxilación. No centro activo da IDH, o isocitrato está rodeado de residuos dos aminoácidos arxinina, tirosina, asparaxina, serina, treonina, e ácido aspártico. A imaxe mostra a reacción global catalizada pola IDH. Os reactivos necesarios para que funcione o mecanismo deste encima son isocitrato, NAD+/NADP+, e Mn2+ ou Mg2+. Os produtos da reacción son alfa-cetoglutarato, dióxido de carbono, e NADH + H+/NADPH + H+.[7] Utilízanse moléculas de auga para axudar a desprotonar o oxíxeno (O3) do isocitrato.
O Paso 1 é a oxidación do carbono alfa (C#2).[6][7] O primeiro que ocorre é a oxidación do isocitrato. Nese proceso,[6] o grupo alcohol do carbono alfa (C#2) é desprotonado e os electróns flúen ao carbono alfa formando un grupo cetona e retirando un hidruro do C#2 utilizando o NAD+/NADP+ como cofactor que acepta electróns. A oxidación do carbono alfa convérteo nun lugar a onde, no seguinte paso, chegarán electróns desde o grupo carboxilo e empuxarán os electróns de volta cara ao oxíxeno (creando o dobre enlace no oxíxeno) ou captarán un protón procedente dunha lisina próxima.
O paso 2 é a descarboxilación do oxalosuccinato. Neste paso,[6][7] o oxíxeno do grupo carboxilo é desprotonado por unha tirosina próxima e os electróns flúen ao carbono 2. Despréndese unha molécula de dióxido de carbono do carbono beta do isocitrato e os electróns flúen ao oxíxeno da cetona desde o carbono alfa, creando unha carga negativa no oxíxeno do carbono alfa e formando un dobre enlace alfa-beta entre os carbonos 2 e 3. O par solitario de electróns no oxíxeno do carbono alfa capta un protón dunha lisina adxacente.
O paso 3 é a saturación do dobre enlace alfa-beta entre os carbonos 2 e 3. Neste paso da reacción,[6][7] a lisina desprotona o oxíxeno do carbono alfa e o par solitario de electróns no oxíxeno do carbono alfa volve a formar o dobre enlace cetona e expulsa o par solitario (que formaba o dobre enlace entre os carbonos alfa e beta), captando un protón dunha tirosina próxima.[10] Esta reacción ten como resultado a formación do alfa-cetoglutarato, NADH + H+/NADPH + H+, e CO2.
-
Paso de oxidorredución no que se utiliza o NAD+ como aceptor dun hidruro.[10]
-
Descarboxilación do oxalosuccinato.[10]
-
Saturación do dobre enlace alfa-beta insaturado.[10]
-
Isocitrato deshidroxenase dependente do NADP+ mitocondrial porcina en complexo con Mn2+ e isocitrato. Vista da superficie do peto do centro activo onde o isocitrato está unido por aminoácidos polares.[3]
-
Isocitraro deshidroxenase dependente do NADP+ mitocondrial porcina en complexo co Mn2+ e o isocitrato.[3]
-
Complexo do encima porcino. Centro activo do isocitrato e aminoácidos adxacentes.[3]
Centro activo[editar | editar a fonte]
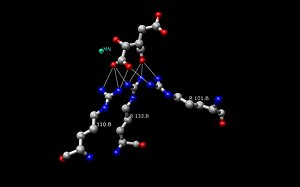
A estrutura da IDH en Escherichia coli foi a primeira deste encima que se construíu e comprendeu.[10] Desde entón, a maioría dos investigadores utilizaron o encima de Escherichia coli para facer comparacións con outras IDH, que se viu que a maioría eran similares en estrutura e función. Esta semellanza na estrutura e función indica que son estruturas conservadas e tamén o son as secuencias de aminoácidos.[8] Os centros activos na maioría das IDH procarióticas están conservados tamén. As IDH eucarióticas non se coñecen tan ben. Cada un dos dímeros da IDH ten dous centros activos.[10] En cada centro activo únese unha molécula de NAD+/NADP+ e un ión metálico (Mg2+,Mn2+). En xeral, cada centro activo ten unha secuencia conservada de aminoácidos para cada sitio de unión específico. En Desulfotalea psychrophila (DpIDH)[10] e porcinos (PcIDH)[3] hai tres substratos unidos no centro activo.
As características principais de unión ao centro activo son:
- O isocitrato únese no centro activo nunha secuencia conservada de aproximadamente oito aminoácidos por medio de enlaces de hidróxeno. Estes ácidos inclúen (poden variar en residuos pero con similares propiedades) tirosina, serina, asparaxina, tres arxininas, tirosina, e lisina. As súas posicións na cadea polipeptídica varían pero están todos próximos (Arg131 DpIDH e Arg133 PcIDH, Tyr138 DpIDH e Tyr140 PcIDH).[10]
- O ión metálico (Mg2+, Mn2+) únese a tres aminoácidos conservados por medio de enlaces de hidróxeno. Estes aminoácidos inclúen tres residuos aspartato.[10]
- O NAD+ e NADP+ únense ao centro activo en catro rexións con propiedades similares en distintos encimas IDH. Estas rexións varían pero están arredor das posicións [250–260], [280–290], [300–330], e [365–380]. A proximidade das rexións está conservada.[10]
Importancia clínica[editar | editar a fonte]

Atopáronse mutacións específicas no xene IDH1 da isocitrato deshidroxenase en varios tumores cerebrais como astrocitomas, oligodendrogliomas e glioblastoma multiforme, e atopáronse mutacións en case todos os casos de glioblastomas secundarios, os cales se desenvolven a partir de gliomas de grao inferior, pero raramente en glioblastoma multiforme primario de grao alto. Os pacientes cuxos tumores tiñan unha mutación IDH1 presentaban unha supervivencia máis prolongada.[12] Non se sabe como as mutacións IDH1 contribúen ao desenvolvemento do glioblastoma multiforme.[13] Ademais, atopáronse mutacións de IDH2 e IDH1 en ata o 20% dos casos de leucemia mieloide aguda (AML) citoxeneticamente normal.[14] Estas mutacións sábese que producen (D)-2-hidroxiglutarato a partir de alfa-cetoglutarato. Mutacións de mosaico somático deste xene están asociadas á enfermidade de Ollier e á síndrome de Maffucci.[15]
Notas[editar | editar a fonte]
- ↑ PDB 1CW7; Cherbavaz DB, Lee ME, Stroud RM, Koshland DE (2000). "Active site water molecules revealed in the 2.1 A resolution structure of a site-directed mutant of isocitrate dehydrogenase". J. Mol. Biol. 295 (3): 377–85. PMID 10623532. doi:10.1006/jmbi.1999.3195.
- ↑ Corpas FJ; et al. (1999). "Peroxisomal NADP-Dependent Isocitrate Dehydrogenase. Characterization and Activity Regulation during Natural Senescence". Plant Physiology 121 (3): 921–928. PMC 59455. PMID 10557241. doi:10.1104/pp.121.3.921.
- ↑ 3,0 3,1 3,2 3,3 3,4 3,5 PDB 1LWD; Ceccarelli C, Neil B (2002). "The Crystal Structure of Porcine Mitochondrial NADP+-dependent Isocitrate Dehydrogenase Complexed with Mn2+ and Isocitrate". Journal of Biological Chemistry 277 (45): 43454–43462. PMID 12207025. doi:10.1074/jbc.M207306200.
- ↑ Chen R, Yang H (November 2000). "A highly specific monomeric isocitrate dehydrogenase from Corynebacterium glutamicum". Arch. Biochem. Biophys. 383 (2): 238–45. doi:10.1006/abbi.2000.2082. PMID 11185559.
- ↑ La Porte, D.C. The isocitrate dehydrogenase phosphorylation cycle: regulation and enzymology. J Cell Biochem. 1993 Jan;51(1):14-8. PMID 8381789. [1]
- ↑ 6,0 6,1 6,2 6,3 6,4 Tadhg P. Begley; McMurry, John (2005). The Organic Chemistry of Biological Pathways. Roberts and Co. Publishers. pp. 189–190. ISBN 0-9747077-1-6.
- ↑ 7,0 7,1 7,2 7,3 7,4 Cox, Michael; Nelson, David R.; Lehninger, Albert L (2005). Lehninger Principles of Biochemistry. San Francisco: W.H. Freeman. pp. 609–611. ISBN 0-7167-4339-6.
- ↑ 8,0 8,1 Yasutake Y, Watanabe S, Yao M, Takada Y, Fukunaga N, Tanaka I (2003). "Crystal Structure of the Monomeric Isocitrate Dehydrogenase in the Presence of NADP+". Journal of Biological Chemistry 278 (38): 36897–36904. PMID 12855708. doi:10.1074/jbc.M304091200.
- ↑ Aoshima M, Igarashi Y (2008). "Nondecarboxylating and decarboxylating isocitrate dehydrogenases: oxalosuccinate reductase as an ancestral form of isocitrate dehydrogenase". Journal of bacteriology 190 (6): 2050–5. PMC 2258884. PMID 18203822. doi:10.1128/JB.01799-07.
- ↑ 10,00 10,01 10,02 10,03 10,04 10,05 10,06 10,07 10,08 10,09 Fedøy AE, Yang N, Martinez A, Leiros HK, Steen IH (2007). "Structural and functional properties of isocitrate dehydrogenase from the psychrophilic bacterium Desulfotalea psychrophila reveal a cold-active enzyme with an unusual high thermal stability". J. Mol. Biol. 372 (1): 130–49. PMID 17632124. doi:10.1016/j.jmb.2007.06.040.
- ↑ Capper D, Zentgraf H, Balss J, Hartmann C, von Deimling A (2009). "Monoclonal antibody specific for IDH1 R132H mutation". Acta Neuropathol. 118 (5): 599–601. PMID 19798509. doi:10.1007/s00401-009-0595-z.
- ↑ Hartmann C, Hentschel B, Wick W; et al. (2010). "Patients with IDH1 wild type anaplastic astrocytomas exhibit worse prognosis than IDH1-mutated glioblastomas, and IDH1 mutation status accounts for the unfavorable prognostic effect of higher age: implications for classification of gliomas". Acta Neuropathol. 120 (6): 707–18. PMID 21088844. doi:10.1007/s00401-010-0781-z.
- ↑ Parsons DW, Jones S, Zhang X, Lin JC, Leary RJ, Angenendt P, Mankoo P, Carter H, Siu IM, Gallia GL, Olivi A, McLendon R, Rasheed BA, Keir S, Nikolskaya T, Nikolsky Y, Busam DA, Tekleab H, Diaz LA, Hartigan J, Smith DR, Strausberg RL, Marie SK, Shinjo SM, Yan H, Riggins GJ, Bigner DD, Karchin R, Papadopoulos N, Parmigiani G, Vogelstein B, Velculescu VE, Kinzler KW (2008). "An integrated genomic analysis of human glioblastoma multiforme". Science 321 (5897): 1807–12. PMC 2820389. PMID 18772396. doi:10.1126/science.1164382.
- ↑ Ward PS, Patel J, Wise DR; et al. (2010). "The common feature of leukemia-associated IDH1 and IDH2 mutations is a neomorphic enzyme activity converting alpha-ketoglutarate to 2-hydroxyglutarate". Cancer Cell 17 (3): 225–34. PMC 2849316. PMID 20171147. doi:10.1016/j.ccr.2010.01.020.
- ↑ Amary, MF; Damato, S, Halai, D, Eskandarpour, M, Berisha, F, Bonar, F, McCarthy, S, Fantin, VR, Straley, KS, Lobo, S, Aston, W, Green, CL, Gale, RE, Tirabosco, R, Futreal, A, Campbell, P, Presneau, N, Flanagan, AM (2011-11-06). "Ollier disease and Maffucci syndrome are caused by somatic mosaic mutations of IDH1 and IDH2". Nature Genetics 43 (12): 1262–5. PMID 22057236. doi:10.1038/ng.994.
Véxase tamén[editar | editar a fonte]
Outros artigos[editar | editar a fonte]
Ligazóns externas[editar | editar a fonte]
- Isocitrate dehydrogenase: RCSB PDB Molécula do mesArquivado 24 de decembro de 2013 en Wayback Machine.


![Paso de oxidorredución no que se utiliza o NAD+ como aceptor dun hidruro.[10]](http://upload.wikimedia.org/wikipedia/commons/thumb/d/dc/IsocitratedehydrogenaseloseH.gif/236px-IsocitratedehydrogenaseloseH.gif)
![Descarboxilación do oxalosuccinato.[10]](http://upload.wikimedia.org/wikipedia/commons/thumb/8/8e/IsocitratedehydrogenaseloseCO2.gif/231px-IsocitratedehydrogenaseloseCO2.gif)
![Saturación do dobre enlace alfa-beta insaturado.[10]](http://upload.wikimedia.org/wikipedia/commons/thumb/b/b4/Isocitratedehydrogenaselosedb.gif/250px-Isocitratedehydrogenaselosedb.gif)
![Isocitrato deshidroxenase dependente do NADP+ mitocondrial porcina en complexo con Mn2+ e isocitrato. Vista da superficie do peto do centro activo onde o isocitrato está unido por aminoácidos polares.[3]](http://upload.wikimedia.org/wikipedia/commons/thumb/6/66/Porcine_Mitochondrial_IDH_surface_pocket_view.jpg/237px-Porcine_Mitochondrial_IDH_surface_pocket_view.jpg)
![Isocitraro deshidroxenase dependente do NADP+ mitocondrial porcina en complexo co Mn2+ e o isocitrato.[3]](http://upload.wikimedia.org/wikipedia/commons/thumb/1/13/Porcine_Mitochondrial_IDH_1lwd.jpg/237px-Porcine_Mitochondrial_IDH_1lwd.jpg)
![Complexo do encima porcino. Centro activo do isocitrato e aminoácidos adxacentes.[3]](http://upload.wikimedia.org/wikipedia/commons/thumb/d/da/Porcine_Mitochondrial_IDH_ball_view.jpg/237px-Porcine_Mitochondrial_IDH_ball_view.jpg)