Xenética inversa
A xenética inversa é un método de investigación que se usa para intentar descubrir a función dun xene analizando os efectos fenotípicos dunha secuencia específica dun xene preparado por enxeñaría.
A xenética inversa xeralmente procede na dirección oposta dos cribados da chamada (por oposición á xenética inversa) xenética cara a adiante ou directa (forward genetics) da xenética clásica. Mentres que a xenética cara a adiante trata de atopar as bases xenéticas dun fenotipo ou trazo, a xenética inversa trata de atopar que fenotipos se orixinan como resultado da presenza de determinadas secuencias xenéticas.
A xenética inversa trata de conectar unha determinada secuencia dada cos efectos específicos que ten no organismo.
Técnicas usadas[editar | editar a fonte]
Para coñecer a influencia que ten unha secuencia xénica no fenotipo ou descubrir a súa función biolóxica, os investigadores adoitan facer cambios por enxeñaría ou alterar o ADN dun xene. Despois de introducir este cambio, búscase o efecto desas alteracións en todo o organismo. Hai varios métodos que se poden aplicar na xenética inversa:
Delecións dirixidas e mutacións puntuais[editar | editar a fonte]
A mutaxénese dirixida a sitio é unha sofisticada técnica que pode cambiar rexións reguladoras no promotor dun xene ou facer cambios sutís nun codón no marco de lectura aberto do xene para identificar os residuos de aminoácidos importantes para o funcionamento da proteína.

Alternativamente, a técnica pode usarse para crear alelos nulos para que o xene non sexa funcional. Por exemplo, nalgúns organismos pode facerse a deleción dun xene por gene targeting (por exemplo por knockout de xenes), como en lévedos, ratos e musgos. Un caso único entre as plantas é o musgo Physcomitrella patens, no que pode facerse un knockout de xenes por recombinación homóloga para crear musgos knockout (ver figura) que é case tan eficaz coma en lévedos.[2] No caso do sistema modelo de lévedos créanse delecións dirixidas en cada xene non esencial do seu xenoma.[3] No caso do sistema modelo da planta creáronse enormes bibliotecas de mutantes baseándose en construtos de alteración de xenes.[4] No knock-in de xenes, un exón endóxeno substitúese por unha secuencia alterada de interese.[5]
Nalgúns casos poden usarse alelos condicionais para que o xene teña un funcionamento normal ata que se active o alelo condicional. Isto podería supoñer facer un 'knock-in' dun sitio de recombinase (como os sitios lox ou frt) que causan unha deleción no xene de interese cando se induce unha recombinase específica (como CRE ou FLP). As recombinases CRE ou FLP poden ser inducidas por tratamentos químicos, shock térmico ou ser restrinxidas a un conxunto determinado de tecidos.
Outra técnica que se pode usar é a TILLING. Este é un método que combina unha técnica eficiencte estándar de mutaxénese cun mutáxeno químico como o metanosulfonato de etilo (EMS) cunha técnica sensible de cribado de ADN que identifique as mutacións puntuais nun xene diana.
Silenciamento de xenes[editar | editar a fonte]
O descubrimento do silenciamento de xenes usando ARN bicatenario, tamén chamado interferencia de ARN (RNAi), e o desenvolvemento do knockdown de xenes e os oligos Morpholino, fixeron da expresión de xenes alterados unha técnica accessible para moitos investigadores. Este método denomínase a miúdo knockdown de xenes, xa que os seus efectos son xeralmente temporais, a diferenza do knockout de xenes, no que son permanentes.
A interferencia de ARN crea un efecto específico de knockout sen, en realidade, mutar o ADN de interese. En Caenorhabditis elegans, a interferencia de ARN foi utilizada sistematicamente para interferir na expresión da maioría dos xenes no xenoma. A interferencia de ARN actúa dirixindo sistemas celulares para degradar os ARNm dianas.
A interferencia de ARN, especificamente o silenciamento de xenes, converteuse nunha ferramenta útil para silenciar a expresión de xenes e identificar e analizar os seus fenotipos de perda de función. Cando as mutacións aparecen en alelos, a función que representan e cofifican tamén está mutada e perdida; isto denomínase xeralmente mutación de perda de función.[6] A capacidade de analizar o fenotipo de perda de función permite tamén a análise da función de xenes cando non hai acceso a alelos mutantes.[7]
Mentres que a interferencia de ARN depende de compoñentes celulares para ser eficaz (por exemplo, as proteínas Dicer, o complexo RISC) unha alternativa simple ao knockdown de xenes é o uso dos oligos Morpholino antisentido, os cales se unen e bloquean o acceso ao ARNm diana sen depender da actividade de proteínas celulares e sen necesariamente acelerar a degradación do ARNm. Os Morpholinos son efectivos en sistemas que en complexidade van desde unha tradución nun sistema libre de células nun tubo de ensaio a estudos in vivo en modelos de grandes animais.
Interferencia usando transxenes[editar | editar a fonte]
Outra aproximación de xenética molecular é a creación de organismos transxénicos que sobreexpresan un xene normal de interese. O frenotipo resultante pode reflectir a función normal do xene.
Alternativamente é posible sobreexpresar formas mutantes dun xene que interfiren coa función do xene de tipo silvestre normal. Por exemplo, a sobreexpresión dun xene mutante pode ter como resultado altos niveis dunha proteína non funcional o que dá lugar a unha interacción negativa dominante coa proteína de tipo silvestre. Neste caso a versión mutante supera a proteína silvestre e dá lugar a un fenotipo mutante.
Outras formas mutantes poden orixinar unha proteína que está regulada anormalmente e é activa constitutivamente (constantemente). Isto pode deberse a que se eliminou o dominio regulador ou se mutou un residuo de aminoácido específico que é modificado reversiblemente (por fosforilación, metilación ou ubiquitinación). Ambos os cambios son críticos para modular a función da proteína e a miúdo causan fenotipos característicos.
Síntese de vacinas[editar | editar a fonte]
A xenética inversa desempeña un importante papel na síntese de vacinas. As vacinas poden crearse obtendo por enxeñaría novos xenotipos de cepas de virus infectivas pero que diminúen a súa potencia patoxénica dabondo como para facilitar a resposta inmunitaria do hóspede. O enfoque da xenética inversa na síntese de vacinas utiliza secuencias xenéticas virais coñecidas para crear o fenotipo desexado: un virus que ten unha potencia patolóxica debilitada e á vez unha semellanza coa cepa de virus circulante. A xenética inversa proporciona unha estratexia conveniente ao método tradicional de crear vacinas inactivadas, virus que foron "matados" (neutralizados) por calor ou outros métodos químicos.
As vacinas xeradas por métodos de xenética inversa son vacinas atenuadas, xa que conteñen virus funcionais pero debilitados (atenuados). Estas vacinas atenuadas créanse combinando xenes dunha cepa de virus actual ou nova con virus previamente atenuados da mesma especie.[8] Os virus atenuados créanse propagando un virus vivo en condicións novas non habituais nel, como en ovos de polo. Isto produce unha cepa viral que aínda é funcional, pero non é patoxénica para os humanos,[9] xa que estes virus fanse defectivos e non poden replicar o seu xenoma o suficiente como para propagarse e xerar unha infección suficiente no hóspede. Porén, os xenes virais aínda se expresan na célula hóspede nun só ciclo de replicación, o que permite o desenvolvemento da inmunidade.[10]
Vacina da gripe[editar | editar a fonte]
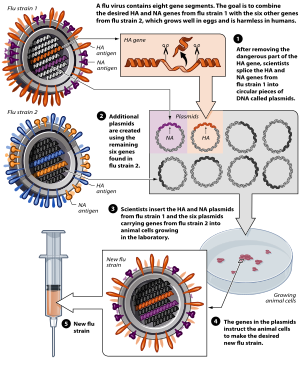
Unha maneira común de crear unha vacina usando técnicas de xenética inversa é utilizar plásmidos para sintetizar virus atenuados. Esta técnica úsase principalmente para a produción das vacinas da gripe anuais, na que un sistema de oito plásmidos pode producir rapidamente unha vacina efectiva. O xenoma completo do virus da gripe A consta de oito segmentos de ARN, polo que a combinación de seis plásmidos de ADN complementario (ADNc) viral atenuado con dous plásmidos de tipo silvestre permite construír a cepa da vacina atenuada. Para o desenvolvemento de vacinas da gripe, o cuarto e sesto segmentos de ARN, que codifican as proteínas hemaglutinina e neuraminidase, respectivamente, tómanse do virus circulante, mentres que os outros seis segmentos derivan da cepa mestra previamente atenuada. As proteínas hemaglutinina e neuraminidase mostran unha alta variedade antixénica, e, por tanto, tómanse da cepa real contra a cal se produce a vacina para crear unha vacina que se corresponda ben co virus epidémico.[8]
As secuencias de ADNc correspondentes ao ARN viral son sintetizadas a partir de cepas mestras atenuadas usando RT-PCR.[8] Este ADNc pode despois inserirse entre un promotor da ARN polimerase I (Pol I) e a secuencia terminadora. O ADNc e a secuencia pol I son despois, á súa vez, rodeados por un promotor de ARN polimerase II (Pol II) e un sitio de poliadenilación.[11] Esta secuencia completa é despois inserida nun plásmido. Seis plásmidos derivados do ADNc da cepa mestra atenuada son cotransfectados nunha célula diana, xeralmente nun ovo de polo, xunto con dous plásmidos da cepa do virus da gripe silvestre circulante nese momento. Dentro da célula diana, os dous encimas Pol I e Pol II transcriben o ADNc viral para sintetizar tanto o ARN viral de sentido negativo coma o ARNm viral de sentido positivo, creando así un virus atenuado.[8] O resultado é unha cepa vacina defectiva que é similar á cepa do virus real, o que permite que o hóspede desenvolva a inmunidade. Esta cepa vacina sintetizada pode despois usarse como un virus semente para crear futuras vacinas.
Vantaxes e desvantaxes[editar | editar a fonte]
As vacinas preparadas por enxeñaría por xenética inversa teñen varias vantaxes sobre os deseños de vacinas tradicionais. A principal é a velocidade de produción. Debido á alta variación antixénica nas glicoproteínas hemaglutinina e neuraminidase, no caso do virus da gripe, a estratexia da xenética inversa permite formular rapidamente o xenotipo necesario, é dicir, un que conteña as hemaglutininas e neuraminidases tomadas do virus real circulante nese momento.[8] Ademais, como o produto final da produción de vacinas atenuadas por xenética inversa é un virus "vivo", orixina unha maior inmunoxenicdade que nas vacinas inactivadas tradicionais,[12] as cales deben ser inutilizadas usando procedementos químicos antes de seren usadas como vacinas. Porén, debido á natureza funcional dos virus atenuados, poden orixinarse complicacións en pacientes inmunodeficientes.[13] Existe tamén a posibilidade de que unha mutación no virus podería causar que a vacina se convertese nun virus non atenuado normal virulento.[14]
Notas[editar | editar a fonte]
- ↑ Egener et al. BMC Plant Biology 2002 2:6 doi 10.1186/1471-2229-2-6
- ↑ Reski R (1998). "Physcomitrella and Arabidopsis: the David and Goliath of reverse genetics". Trends Plant Sci 3 (6): 209–210. doi:10.1016/S1360-1385(98)01257-6. Arquivado dende o orixinal o 10 de setembro de 2012. Consultado o 02 de novembro de 2018.
- ↑ Winzeler EA, Shoemaker DD, Astromoff A, Liang H, Anderson K, Andre B, et al. (August 1999). "Functional characterization of the S. cerevisiae genome by gene deletion and parallel analysis". Science 285 (5429): 901–6. PMID 10436161. doi:10.1126/science.285.5429.901.
- ↑ Schween G, Egener T, Fritzowsky D, Granado J, Guitton MC, Hartmann N, Hohe A, Holtorf H, Lang D, Lucht JM, Reinhard C, Rensing SA, Schlink K, Schulte J, Reski R (May 2005). "Large-scale analysis of 73 329 physcomitrella plants transformed with different gene disruption libraries: production parameters and mutant phenotypes". Plant Biology 7 (3): 228–37. PMID 15912442. doi:10.1055/s-2005-837692.
- ↑ Manis JP (December 2007). "Knock out, knock in, knock down--genetically manipulated mice and the Nobel Prize". The New England Journal of Medicine (PDF) (Massachusetts Medical Society) 357 (24): 2426–9. OCLC 34945333. PMID 18077807. doi:10.1056/NEJMp0707712.
- ↑ McClean, Phillip. "Types of Mutations". Genes and Mutations. North Dakota State University. Consultado o April 27, 2015.
- ↑ Lamour, Kurt; Tierney, Melinda. "An Introduction to Reverse Genetic Tools for Investigating Gene Function". APSnet. The American Phytopathological Society. Arquivado dende o orixinal o 23 de novembro de 2018. Consultado o 02 de novembro de 2018.
- ↑ 8,0 8,1 8,2 8,3 8,4 Hoffmann, Erich; Krauss, Scott; Perez, Daniel; Webby, Richard; Webster, Robert (2002). "Eight-plasmid system for rapid generation of influenza virus vaccines" (PDF). Vaccine 20: 3165–3170. doi:10.1016/s0264-410x(02)00268-2 – vía Elsevier.
- ↑ Badgett MR, Auer A, Carmichael LE, Parrish CR, Bull JJ (October 2002). "Evolutionary dynamics of viral attenuation". Journal of Virology 76 (20): 10524–9. PMC 136581. PMID 12239331. doi:10.1128/JVI.76.20.10524-10529.2002.
- ↑ Lauring AS, Jones JO, Andino R (June 2010). "Rationalizing the development of live attenuated virus vaccines". Nature Biotechnology 28 (6): 573–9. PMC 2883798. PMID 20531338. doi:10.1038/nbt.1635.
- ↑ Mostafa A, Kanrai P, Petersen H, Ibrahim S, Rautenschlein S, Pleschka S (2015-01-23). "Efficient generation of recombinant influenza A viruses employing a new approach to overcome the genetic instability of HA segments". PLoS One 10 (1): e0116917. PMC 4304806. PMID 25615576. doi:10.1371/journal.pone.0116917.
- ↑ Stobart CC, Moore ML (June 2014). "RNA virus reverse genetics and vaccine design". Viruses 6 (7): 2531–50. PMC 4113782. PMID 24967693. doi:10.3390/v6072531.
- ↑ "General Recommendations on Immunization". www.cdc.gov (en inglés). Consultado o 2017-04-01.
- ↑ Shimizu H, Thorley B, Paladin FJ, Brussen KA, Stambos V, Yuen L, Utama A, Tano Y, Arita M, Yoshida H, Yoneyama T, Benegas A, Roesel S, Pallansch M, Kew O, Miyamura T (December 2004). "Circulation of type 1 vaccine-derived poliovirus in the Philippines in 2001". Journal of Virology 78 (24): 13512–21. PMC 533948. PMID 15564462. doi:10.1128/JVI.78.24.13512-13521.2004.
Véxase tamén[editar | editar a fonte]
Outros artigos[editar | editar a fonte]
Ligazóns externas[editar | editar a fonte]
- Do sitio do National Institute of Allergy and Infectious Diseases (NIAID):
- Do sitio do National Center for Biotechnology Information (NCBI):
- Neumann G, Hatta M, Kawaoka Y (2003). "Reverse genetics for the control of avian influenza". Avian Diseases 47 (3 Suppl): 882–7. PMID 14575081. doi:10.1637/0005-2086-47.s3.882.
- Neumann G, Fujii K, Kino Y, Kawaoka Y (November 2005). "An improved reverse genetics system for influenza A virus generation and its implications for vaccine production". Proceedings of the National Academy of Sciences of the United States of America 102 (46): 16825–9. PMC 1283806. PMID 16267134. doi:10.1073/pnas.0505587102.
- Ozaki H, Govorkova EA, Li C, Xiong X, Webster RG, Webby RJ (February 2004). "Generation of high-yielding influenza A viruses in African green monkey kidney (Vero) cells by reverse genetics". Journal of Virology 78 (4): 1851–7. PMC 369478. PMID 14747549. doi:10.1128/JVI.78.4.1851-1857.2004.
