Electroforese en xel de proteínas

A electoforese en xel de proteínas é un método para analizar as proteínas que se encontran nun fluído ou un extracto. A electroforese pode realizarse cun pequeno volume de mostra de varias maneiras alternativas con ou sen medio de soporte: electroforese en xel de poliacrilamida con dodecil sulfato sódico (SDS-PAGE), electroforese de fluxo libre, electroenfoque, isotacoforese, electroforese de afinidade, inmunoelectroforese, contraelectroforese e electroforese de capilaridade. Cada método ten moitas variacións con determinadas vantaxes e limitacións. A electroforese en xel adoita facerse en combinación con electroblotting ou inmunoblotting para dar información adicional sobre proteínas específicas.
Métodos de xeles desnaturalizantes[editar | editar a fonte]
SDS-PAGE[editar | editar a fonte]
- Artigo principal: SDS-PAGE.
A SDS-PAGE é un conxunto de técnicas para separar proteínas segundo a súa mobilidade electroforética (que está en función do peso molecular da cadea polipeptídica) en estado desnaturalizado (non pregado). Na maioría das proteínas, a unión do SDS ao polipéptido crea unha distribución uniforme de cargas por unidade de masa, o que ten como resultado un fraccionamento aproximadamente polo tamaño da molécula durante a electroforese.
O SDS é un forte axente deterxente usado para desnaturalizar proteínas nativas orixinando polipéptidos non pregados. Cando unha mestura de proteínas se quenta a 100 °C en presenza de SDS, o deterxente envólvese arredor do esqueleto do polipéptido. Neste proceso, as cargas intrínsecas dos polipéptidos son desprezables comparadas coas cargas negativas ás que contribúe o tratamento con SDS. Así os polipéptidos despois do tratameto pasan a ser estruturas con forma de bastón que posúen unha densidade de carga uniforme, que é a mesma carga neta negativa por unidade de lonxitude. As mobilidades electroforéticas destas proteínas serán unha función linear dos logaritmos dos seus pesos moleculares.
Métodos de xeles nativos[editar | editar a fonte]
Os xeles nativos, tamén chamados non desnaturalizantes, analizan as proteínas que están aínda no seu estado pregado. Neste caso, a mobilidade electroforética depende non só da razón carga-masa, senón tamén na forma física e tamaño da proteína.
PAGE nativa azul[editar | editar a fonte]
A BN-PAGE (Blue native-PAGE ou PAGE nativa azul) é unha técnica de PAGE nativa na que a tinguidura azul brillante Coomassie (Coomassie Brilliant Blue) proporciona as cargas necesarias aos complexos proteicos para a súa separación electroforética.[1][2] A desvantaxe do Coomassie é que ao unirse ás proteínas pode actuar como un deterxente causando que os complexos se disocien. Outro inconveniente é a diminución (quenching) potencial da quimioluminescencia (por exemplo, na posterior detección por western blot ou ensaios de actividade) ou fluorescencia de proteínas con grupos prostéticos (por exemplo, hemo ou clorofila) ou marcados con tingiduras fluorescentes.
PAGE nativa clara[editar | editar a fonte]
A CN-PAGE (denominado comunmente PAGE nativa) separa proteínas hidrosolubles e de membrana nun xel de gradiente de poliacrilamida. Utiliza unha tinguidura non cargada polo que a mobilidade electroforética de proteínas en CN-PAGE (a diferenza da técnica de cambio de carga da BN-PAGE) está relacionada coa carga intrínseca das proteínas.[3] A distancia de migración depende da carga proteica, o seu tamaño e o tamaño de poro do xel. En moitos casos este método ten unha resolución máis baixa que a BN-PAGE, pero a CN-PAGE ofrece vantaxes dado que a tinguidura Coomassie interferiría coas posteriores técnicas analíticas, por exemplo foi descrita como unha técnica de separación a microscala eficiente para análises de FRET.[4] Ademais a CN-PAGE é máis suave que a BN-PAGE polo que pode manter ensamblaxes supramoleculares lábiles de complexos de proteínas de membrana que son disociados nas condicións dunha BN-PAGE.
PAGE nativa cuantitativa[editar | editar a fonte]
- Artigo principal: QPNC-PAGE.
Os complexos proteicos pregados de interese sepáranse limpamente e prediciblemente debido ás propiedades específicas do xel de poliacrilamida. As proteínas separadas son eluídas continuamente nun eluente fisiolóxico e transportadas a un colector de fracción. Nalgunhas fraccións do PAGE os cofactores metálicos poden ser identificados e cuantificados absolutamente por ICP-MS de alta resolución. As estruturas respectivas das metaloproteínas illadas poden determinarse por espectroscopia de RMN en solución.[5]
Sistemas tampón[editar | editar a fonte]

A maioría das separacións de proteínas realízanse usando un sistema tampón "descontinuo" (ou DISC) que aumenta significativamente a definición das bandas no xel. Durante a electroforese nun sistema de xel descontinuo, fórmase un gradiente de ións nos estadios iniciais da electroforese que causa que todas as proteínas se enfoquen nunha soa banda definida. A formación do gradiente de ións conséguese elixindo un valor de pH ao que os ións do tampón están moderadamenre cargados comparados coas proteínas cubertas de SDS. Estas condicións proporcionan un ambiente no cal as reaccións de Kohlrausch determinan a condutividade molar. Como resultado, as proteínas cubertas con SDS están moi concentradas nunha fina zona duns 19 μm en cuestión de poucos minutos. Neste estadio todas as proteínas migran á mesma velocidade de migración por isotacoforese. Isto ocorre nunha rexión do xel que ten grandes poros, polo que a matriz do xel non retarda a migración durante o proceso de enfocado ou "amontoamento".[6][7] A separación das proteínas polo seu tamaño conséguese na rexión de "resolución" máis baixa do xel. O xel de resolución normalmente ten un tamaño de poro moito máis pequeno, que causa un efecto de cribado que agora determina a mobilidade electroforética das proteínas. Ao mesmo tempo, a parte separadora do xel tamén ten un valor de pH no cal os ións do tampón como media transportan unha carga maior, causando que "deixen atrás" as proteínas cubertas de SDS e eliminen o gradiente de ións e, por tanto, o efecto de amontoamento (stacking).
Un sistema tampón descontinuo moi estendido é o sistema tris-glicina ou "Laemmli", que amontoa a un pH de 6,8 e resolve a un pH de ~8,3-9,0. Un inconveniente deste sistema é que estes valores de pH poden promover a formación de enlaces disulfuro entre residuos de cisteína nas proteínas porque o pKa da cisteína está entre 8 e 9 e porque o axente redutor presente no tampón de caga non comigra coas proteínas. Avances recentes na tecnoloxía de tamponamento diminúen este problema ao resolveren as proteínas a un pH bastante por debaixo do pKa da cisteína (por exemplo, bis-tris, pH 6,5) e inclúen axentes redutores (por exemplo bisulfito de sodio) que se move no xel por diante das proteínas para manter un ambiente redutor. Un beneficio adicional de usar tampóns con valores de pH máis baixos é que o xel de acrilamida é máis estable a valores de pH máis baixos, polo que os xeles poden ser almacenados durante longos períodos de tempo antes do seu uso.[8][9]
Electroforese en xel de proteínas en gradiente de SDS[editar | editar a fonte]
A medida que se aplica a voltaxe, os anións (e moléculas da mostra cargadas negativamente) migran cara ao eléctrodo positivo (ánodo) na cámara inferior, o ión en cabeza é o Cl− (alta mobilidade e alta concentración); o glicinato é o ión de cola (baixa mobilidade e baixa concentración). As partículas SDS-proteína non migran libremente no límite entre o Cl− do tampón do xel e a Gly− do tampón do cátodo. Friedrich Kohlrausch atopou que a lei de Ohm tamén se aplicaba a electrólitos disoltos. A causa da caída de voltaxe entre os tampóns Cl− e glicina, as proteínas son comprimidas (amontoadas) en capas delgadas dun micrómetro.[10] A fronteira móvese a través dun gradiente de poros e a proteína amontoada dispérsase gradualmente debido a un incremento da resistencia friccional da matriz do xel. O amontoamento e desamontoamento ocorre continuamente no xel de gradiente, para cada proteína nunha posición diferente. Para un completo desamontoamento das proteínas a concentración do xel de poliacrilamida debe exceder o 16% T. O sistema de dous xeles de "Laemmli" é un xel de gradiente simple. A descontinidade de pH dos tampóns non é significativa para a calidade da separación, e non é necesario un "xel de amontoamento" cun pH diferente.
Visualización[editar | editar a fonte]
A tinguidura para proteínas máis usada é o azul brillante Coomassie. É unha tinguidura aniónica, que se une non especificamente a proteínas. As proteínas do xel son fixadas con ácido acético e simultaneamete tinguidas. O exceso de tinguidura incorpórase ao xel e pode ser retirado facendo unha destinguidura lavando coa mesma solución pero sen a tinguidura. As proteínas detéctanse como bandas azuis sobre un fondo claro.
Cando cómpre utilizar un método de tinguidura máis sensible que o Coomassie utilízase normalmente unha tinguidura de prata. A tinguidura de prata é un procedemento sensible para detectar cantidades traza de proteína nos xeles, pero pode tamén servir para visualizar ácidos nucleicos ou polisacáridos.
No mercado existen métodos de visualización que non usan unha tinguidura como o Coomassie ou a prata. Por exemplo Bio-Rad Laboratories vende xeles ”sen tinguidura” para a SDS-PAGE.
Igual que na electroforese en xel de ácidos nucleicos, úsase normalmente unha tinguidura de rastreo. As tinguiduras aniónicas dunha mobilidade electroforética coñecida inclúense normalmente no tampón da mostra. Unha tinguidura de rastreo común é o azul de bromofenol. Esta tinguidura está coloreada a pH de álcali ou neutro e é unha molécula pequena cargada negativamente que se move cara ao ánodo. Como é unha molécula moi móbil, móvese por diante da maioría das proteínas.
Aplicacións médicas[editar | editar a fonte]

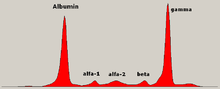
- Artigos principais: Electroforese de proteínas séricas e Proteínas sanguíneas.
En medicina, a electroforese de proteínas é un método utilizado para analizar proteínas principalmente do soro sanguíneo. Antes do uso xeneralizado da electroforese en xel, a electroforese de proteínas realizábase por medio de electroforese de fluxo libre (en papel) ou por inmunoelectroforese.
Tradicionalmente, considérase que hai dúas clases de proteínas sanguíneas: albuminas séricas e globulinas. Xeralmente aparecen en igual proporción, pero as albuminas son moléculas moito máis pequenas e lixeiras, cargadas negativamente, polo que se acumulan albuminas nos xeles electroforéticos. Unha pequena banda situada antes da albumina representa a transtiretina (tamén chamada prealbumina). Algúns medicamentos ou compostos químicos corporais poden orixinar as súas propias bandas, pero xeralmente son pequenas. Obsérvanse bandas anormais (picos) na gammopatía monoclonal de importancia indeterminada e no mieloma múltiple, e son útiles para a diagnose destas condicións.
As globulinas clasificadas polo seu padrón de bandas (cos seus principais representantes):
- A banda alfa (α) consta de dúas partes, 1 e 2:
- α1 - α1-antitripsina, α1-glicoproteína ácida.
- α2 - haptoglobina, α2-macroglobulina, α2-antiplasmina, ceruloplasmina.
- A banda beta (β) - transferrina, LDL, complemento
- A banda gamma (γ) - inmunoglobulinas (IgA, IgD, IgE, IgG e IgM). As paraproteínas (no mieloma múltiple) xeralmente aparecen nesta banda.
Os procedementos médicos actuais normais inclúen a determinación de numerosas proteínas do plasma sanguíneo como hormonas e encimas, algúns deles tamén determinados por electroforese. Porén, a electroforese en xel é principalmente unha ferramenta de investigación, incluso cando o obxectivo a estudar son as proteínas sanguíneas.
Notas[editar | editar a fonte]
- ↑ Schägger, H.; Jagow, G. (1991). "Blue native electrophoresis for isolation of membrane protein complexes in enzymatically active form". Anal. Biochem. 199 (2): 223–231. PMID 1812789. doi:10.1016/0003-2697(91)90094-A.
- ↑ Wittig, I.; Braun, H.P.; Schägger, H. (2006). "Blue native PAGE". Nat. Protoc. 1 (1): 418–428. PMID 17406264. doi:10.1038/nprot.2006.62.
- ↑ Wittig, I.; Schägger, H. (Nov 2005). "Advantages and limitations of clear-native PAGE". Proteomics 5 (17): 4338–46. PMID 16220535. doi:10.1002/pmic.200500081. Arquivado dende o orixinal o 05 de xaneiro de 2013. Consultado o 28 de maio de 2020.
- ↑ Gavin P.D.; Devenish R.J.; Prescott M. (2003). "FRET reveals changes in the F1–stator stalk interaction during activity of F1F0-ATP synthase". Biochim Biophys Acta 1607 (2–3): 167–79. PMID 14670607. doi:10.1016/j.bbabio.2003.09.013.
- ↑ Kastenholz, B. (2004). "Preparative native continuous polyacrylamide gel electrophoresis (PNC‐PAGE): an efficient method for isolating cadmium cofactors in biological systems". Protein Pept Lett 37 (4): 657–65. doi:10.1081/AL-120029742.
- ↑ Ornstein L (decembro de 1964). "Disc Electrophoresis. I. Background and Theory". Annals of the New York Academy of Sciences 121 (2): 321–349. Bibcode:1964NYASA.121..321O. PMID 14240533. doi:10.1111/j.1749-6632.1964.tb14207.x.
- ↑ Davis BJ (decembro de 1964). "Disc Electrophoresis. 2, Method and application to human serum proteins". Ann. N. Y. Acad. Sci. 121 (2): 404–427. Bibcode:1964NYASA.121..404D. PMID 14240539. doi:10.1111/j.1749-6632.1964.tb14213.x.
- ↑ Schägger H, von Jagow G (1987). "Tricine-sodium dodecyl sulfate-polyacrylamide gel electrophoresis for the separation of proteins in the range from 1 to 100 kDa". Anal. Biochem. 166 (2): 368–379. PMID 2449095. doi:10.1016/0003-2697(87)90587-2.
- ↑ Wiltfang J, Arold N, Neuhoff V (1991). "A new multiphasic buffer system for sodium dodecyl sulfate-polyacrylamide gel electrophoresis of proteins and peptides with molecular masses 100,000-1000, and their detection with picomolar sensitivity". Electrophoresis 12 (5): 352–366. PMID 1718736. doi:10.1002/elps.1150120507.
- ↑ Kohlrausch F (1897). "Ueber Concentrations-Verschiebungen durch Electrolyse im Inneren von Lösungen und Lösungsgemischen". Annalen der Physik und Chemie 62 (10): 209–239. Bibcode:1897AnP...298..209K. doi:10.1002/andp.18972981002.
Véxase tamén[editar | editar a fonte]
Outros artigos[editar | editar a fonte]
- Electroforese de afinidade
- Electroblotting
- Electroenfoque
- Electroforese en xel de poliacrilamida (PAGE)
- Inmunoelectroforese
- Inmunofixación
- Electroforese en xel nativa
- QPNC-PAGE
- Paraproteína
- Proteólise paralela rápida (FASTpp)[1]
- Electroforese en xel de ácidos nucleicos
Ligazóns externas[editar | editar a fonte]
- Recurso educativo sobre a electroforese de proteínas
- Electroforese en xel de proteínas Arquivado 26 de xaneiro de 2021 en Wayback Machine.
- ↑ Minde DP (2012). "Determining biophysical protein stability in lysates by a fast proteolysis assay, FASTpp". PLOS One 7 (10): e46147. Bibcode:2012PLoSO...746147M. PMC 3463568. PMID 23056252. doi:10.1371/journal.pone.0046147.
