Sentido (bioloxía molecular)
En bioloxía molecular e xenética sentido ou senso é un concepto utilizado para comparar a polaridade de moléculas de ácidos nucleicos, como o ADN e ARN, con outras moléculas de ácidos nucleicos. Este concepto é distinto da direccionalidade do ADN con respecto aos extremos 5' e 3'. Dependendo do contexto na bioloxía molecular, o sentido pode ter significados lixeiramente distintos.
ADN sentido
[editar | editar a fonte]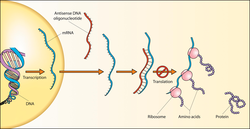
Para entender ben o concepto cómpre ter en conta que a transcrición do ARN se realiza por complementariedade de bases e que o ADN xeralmente é bicatenario. Só unha das cadeas do ADN se transcribe a ARN; esa cadea e o ARN formado a partir dela son complementarios en bases, polo que a súa secuencia non é igual. A outra cadea do ADN non se transcribe pero é de secuencia idéntica á do ARN, pero con T en vez de U (e é complementaria da outra cadea de ADN). Só se traduce a proteínas no ribosoma o ARNm, nunca o ADN.
Os biólogos moleculares chaman cadea "sentido" ou "con sentido" ou cadea "positiva" (+) á cadea que ten a secuencia igual á do ARNm que vai ser traducido a proteínas, pero o ARNm non se transcribiu dela senón da outra cadea de ADN. Por tanto, os seus codóns son os mesmos que determinan a secuencia da proteína nese xene, xa que son os mesmos que leva o ARNm.
A outra cadea do ADN chámase "antisentido" ou cadea "negativa" (-) porque a súa secuencia é distinta da do ARNm traducible, polo que a súa secuencia carece de sentido xenético se se intentasen traducir os seus codóns. Porén, é desta cadea da que se transcribiu o ARNm de forma complementaria en bases.
Algunhas veces utilízase o termo cadea codificante, que xeralmente se refire á cadea sentido; porén, hai que ter en conta tamén o concepto de "ambisentido". En virus os ARN codificantes e non codificantes poden ser transcritos de xeito similar de ambas as cadeas, e nalgúns casos son transcritos en ambas as direccións desde unha rexión promotora común, ou transcritos desde intróns, en ambas as cadeas (ver "ambisenstido" máis abaixo).[1][2][3]
Finalmente, téñase en conta que non todos os xenes están codificados na mesma cadea ou febra, senón que algúns xenes están codificados nunha das cadeas e outros xenes na outra, polo que as cadeas sentido e antisentido varían segundo o xene consierado.
ADN antisentido
[editar | editar a fonte]Como dixemos, o ADN antisentido é a cadea que non ten os codóns que servirían para codificar os aminoácidos da proteína, pero que se transcribe a un ARNm que si ten os codóns complementarios aos anteriores, que servirán para traducir a proteína no ribosoma (que son os mesmos codóns que ten a cadea sentido).
Por exemplo, un triplete de bases ou codón como 3'-TAC-5' no ADN antisentido pode utilizarse como molde para ser copiado complementariamente ao codón 5'-AUG-3' dun ARNm (AUG é o codón do aminoácido metionina), e estes dous codóns son moi diferentes. Polo contrario, o ADN sentido terá o triplete ATG que é idéntico ao AUG (e por iso se chama sentido) coa soa diferenza de que ten timina (T) en vez de uracilo (U) por tratarse dun ADN (o uracilo é típico do ARN e a timina do ADN).
En bioloxía e investigación utilízanse curtas moléculas antisentido, que poden interaccionar coas cadeas complementarias a elas de ácidos nucleicos, modificando a expresión xénica. Ver a sección "oligonucleótidos antisentido" máis abaixo.
Exemplo cun ADN de dobre cadea
[editar | editar a fonte]Cadea de ADN 1: cadea antisentido (transcrita a)→ cadea de ARN (sentido)
Cadea de ADN 2: cadea sentido
| 3'TACCGCTATAGCGTTT 5' | Cadea de ADN antisentido (molde/non codificante), cadea Watson | Utilizada como molde para a transcrición. |
| 5'ATGGCGATATCGCAAA 3' | Cadea de ADN sentido (non molde/codificante), cadea Crick | Complementaria da cadea molde. |
| 5'AUGGCGAUAUCGCAAA 3' | transcrito de ARNm sentido | Cadea de ARN que se transcribiu a partir da cadea de ADN non codificante (ADN molde/antisentido). Nota1: Excepto polo feito de que todas as timinas son agora uracilos (T → U), é complementaria da cadea de ADN non codificante (ADN molde/antisentido) e idéntica da cadea de ADN codificante (non molde/sentido). Nota2 Hai un codón de iniciación AUG no extremo 5' (aínda que os ARNm reais empezan por unha secuencia 5' UTR non traducible, que non se mostra no exemplo). |
| 3'UACCGCUAUAGCGUUU 5' | transcrito de ARNm antisentido | Cadea de ARN que é complementaria da cadea de ADN codificante (non molde/sentido). Utilízase na interferencia de ARN. |
Xeralmente a cadea antisentido (que é a que se transcribe) se coloca arriba nos esquemas e a sentido abaixo. Per isto é arbitrario e non sempre se escriben nesas posicións. O importante é ver onde están situados os extremos 5' e 3', xa que determinan a dirección de transcrición e tradución.
Unha secuencia 5' CGCTAT 3' é igual a unha secuencia 3' TATCGC 5' se os extremos 5' e 3' están indicados como no exemplo. Se os extremos non están indicados a convención é asumir que a secuencias se escribiu en dirección 5'-3'. Unha boa regra para descubrir a cadea "sentido" é buscar o codón de iniciación ATG do ADN (AUG no ARNm). No exemplo da táboa anterior, o ARNm con sentido ten o codón AUG no extremo 5'. A tradución procede en dirección 5'-3'.
Ambisentido
[editar | editar a fonte]Un xenoma monocatenario que conteña tanto sentido positivo coma negativo dise que é ambisentido. Isto pode ocorrer en virus nos que a transcrición ten lugar en varias roldas. Os Bunyavirus conteñen 3 fragmentos de ARN monocatenarios que teñen seccións de sentido positivo e outras de sentido negativo. Os arenavirus son tamén virus de ARN monocatenario con xenoma ambisentido, xa que presentan un xenoma de 2 fragmentos de ARN que son principalmente de sentido negativo agás nunha parte dos extremos 5' dos fragmentos de ARN longo e pequeno do seu xenoma (non hai ambisentido no de tamaño intermedio).
Sentido do ARN en virus
[editar | editar a fonte]En viroloxía, o xenoma dun virus de ARN pode ser de sentido positivo, tamén chamado "cadea +", ou de sentido negativo, tamén chamado "cadea -". Na maioría dos casos, os termos sentido e cadea (ou fibra) úsanse indistintamente, o que fai que cadea positiva sexa equivalente a sentido positivo, e cadea + equivalente a sentido +. Na clasificación dos virus utilízase o criterio de ver se son de xenoma de sentido positivo ou negativo.
Sentido positivo (+)
[editar | editar a fonte]O sentido positivo dun ARN viral significa que unha determinada secuencia de ARN viral pode ser traducida directamente nun ribosoma para formar as proteínas virais corespondentes. Por tanto, nos virus de ARN de sentido positivo, o xenoma de ARN viral pode ser considerado como o ARNm viral, e pode ser inmediatamente traducido pola célula hóspede, sen necesidade de ningún outro intermediario de ARN. Algúns virus, como por exemplo os Coronaviridae, teñen xenomas deste tipo e non necesitan ter unha ARN polimerase empaquetada dentro do virión.
Sentido negativo (-)
[editar | editar a fonte]O ARN viral de sentido negativo é complementario do ARNm viral, polo que non pode ser directamente traducido a proteínas e debe ser convertido primeiro por unha ARN polimerase nun ARN de sentido positivo (complementario) antes da tradución, xa que este é o que funciona como ARNm. Algúns virus, como o da gripe por exemplo, teñen este tipo de xenomas e deben levar dentro do virión unha ARN polimerase.
ARN antisentido
[editar | editar a fonte]O ARN antisentido utilízase na célula ou nos experimentos e terapia antisentido para a interferencia de ARN, que bloquea a expresión xénica. O ARN antisentido é un transcrito de ARN que é complementario a un ARNm endóxeno. Noutras palabras, é unha cadea non codificante complementaria da secuencia codificante dun ARN da célula; isto é similar ao ARN viral de sentido negativo. Unha técnica utilizada para bloquear a expresión dun xene que interese é a introdución dun transxene que codifica un ARN antisentido. O ARN antisentido marcado radioactivamente pode usarse para mostrar o nivel de transcrición de xenes en varios tipos de células. Algúns análogos de ácidos nucleicos estanse a aplicar experimentalmente como terapia antisentido.
Cando o ARNm forma un dúplex cunha secuencia complementaria de ARN antisentido, a tradución queda bloqueada. Este proceso denomínase interferencia de ARN.
Utilízanse experimentalmente moléculas de ácidos nucleicos antisentido para que se unan a un ARNm determinado e impedir así a expresión de xenes específicos. As Terapias antisentido están tamén en desenvolvemento e nalgúns países xa hai varias aprobadas para uso en humanos como os oligos fosforotioato antisentido fomivirsen e mipomersen[4].
As células poden producir de forma natural moléculas de ARN antisentido, que interaccionan con moléculas de ARNm complementarias da célula e inhiben a súa expresión.
Oligonucleótidos antisentido
[editar | editar a fonte]O silenciamento de xenes pode conseguirse introducindo nas células un curto "oligonucleótido antisentido" que é complementario a un ARN diana determinado. Este experimento realizárono por primeira vez Zamecnik e Stephenson en 1978[5] e segue sendo unha útil estratexia para experimentos de laboratorio e para aplicacións clínicas potenciais (terapia antisentido).[6]
Se o nucleótido antisentido contén un tramo de ADN ou un imitador do ADN (como ADN fosforotioato, 2'F-ANA, ou outros) pode recrutar a RNase H para degradar o ARN diana. Isto fai que o mecanismo de silenciamento de xenees sexa catalítico. O ARN bicatenario pode tamén actuar como axente antisentido dependente de encima catalítico por medio da vía RNAi/siRNA, que implica o recoñecemento do ARNm diana por medio de apareamento entre as fibras sentido-antisentido seguido da degradación do ARNm diana polo complexo de silenciamento inducido por ARN (RISC). O plásmido R1 sistema hok/sok é outro exemplo máis dun proceso de regulación antisentido dependente de encima, por medio da degradación encimática do ARN dúplex resultante.
Outros mecanismos antisentido non son dependentes de encima, pero implican o bloqueo estérico do seu ARN diana (por exemplo, para impedir a tradución ou inducir o splicing alternativo). Os mecanismos de bloqueo estérico antisentido a miúdo usan oligonucleótidos que están moi modificados. Como non hai necesidade de recoñecemento pola RNase H, este pode incluír tipos químicos como 2'-O-alquil, ácido nucleico peptídico (PNA), ácido nucleico bloqueado (LNA), e oligómeros morfolino.
Notas
[editar | editar a fonte]- ↑ Anne-Lise Haenni (2003). "Expression strategies of ambisense viruses". Virus Research 93 (2): 141–150. PMID 12782362. doi:10.1016/S0168-1702(03)00094-7.
- ↑ Kakutani T, Hayano Y, Hayashi T, Minobe Y. (1991). "Ambisense segment 3 of rice stripe virus: the first instance of a virus containing two ambisense segments". J Gen Virol. 72: 465–8. PMID 1993885.
- ↑ Zhu Y, Hayakawa T, Toriyama S, Takahashi M. (1991). "Complete nucleotide sequence of RNA 3 of rice stripe virus: an ambisense coding strategy". J Gen Virol. 72: 763–7. PMID 2016591.
- ↑ Staff (29 January 2013) FDA approves new orphan drug Kynamro to treat inherited cholesterol disorder U.S. Food and Drug Administration, Retrieved 31 January 2013
- ↑ Zamecnik, P.C.; Stephenson, M.L. (1978). "Inhibition of Rous sarcoma Virus Replication and Cell Transformation by a Specific Oligodeoxynucleotide". Proc. Natl. Acad. Sci. USA 75 (1): 280–284.
- ↑ Watts, J.K.; Corey, D.R. (2012). "Silencing Disease Genes in the Laboratory and in the Clinic". J. Pathol 226 (2): 365–379. doi:10.1002/path.2993.
Véxase tamén
[editar | editar a fonte]Outros artigos
[editar | editar a fonte]- ADN
- Direccionalidade (bioloxía molecular)
- Virus de ARN
- Terapia antisentido
- Transcrición xenética
- Tradución de proteínas
- Marco de lectura aberto (ORF)
Bibliografía
[editar | editar a fonte]- Prescott, L. (1993). Microbiology, Wm. C. Brown Publishers, ISBN 0-697-01372-3
- Annual Review of Biochemistry Vol. 60: 631-652 (Data de publicación do volume, xullo de 1991) doi [//dx.doi.org/10.1146/annurev.bi.60.070191.003215 10.1146/annurev.bi.60.070191.003215 Antisense RNA Y Eguchi, T Itoh, and J Tomizawa] Arquivado 16 de setembro de 2019 en Wayback Machine.
- Weiss, B. (ed.): Antisense Oligodeoxynucleotides and Antisense RNA : Novel Pharmacological and Therapeutic Agents, CRC Press, Boca Raton, FL, 1997.
